
| Sequence ID | X_DroMel_CAF1 |
|---|---|
| Location | 21,666,015 – 21,666,123 |
| Length | 108 |
| Max. P | 0.500000 |

| Location | 21,666,015 – 21,666,123 |
|---|---|
| Length | 108 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 80.26 |
| Mean single sequence MFE | -38.92 |
| Consensus MFE | -24.63 |
| Energy contribution | -26.30 |
| Covariance contribution | 1.67 |
| Combinations/Pair | 1.26 |
| Mean z-score | -1.39 |
| Structure conservation index | 0.63 |
| SVM decision value | -0.06 |
| SVM RNA-class probability | 0.500000 |
| Prediction | OTHER |
Download alignment: ClustalW | MAF
>X_DroMel_CAF1 21666015 108 - 22224390 AAUGCCCCGACCUGGAACGUGAC---AGUUCACAGUUGGGUUUAUAGUUGGCCGGACUGUACUUUUCAUAAAUGUCCAGUCCGGAGGUGG---------CCACCAAACGGGCCAGCGAUG .....((((((.((((((.....---.)))).))))))))......(((((((((((((.((...........)).))))))...(((..---------..))).....))))))).... ( -42.40) >DroVir_CAF1 8598 108 - 1 UGACCGCCGAUCUGGAACGUGAC---AGUUCACAGUUGGGUUUAUAGUUGGCCGGACUGUACUUUUCGUAUAUGUCCAGGGCAGAUGUGG---------CAACAAAAUGUGCUAGGGAUG ...((((((((...((((.((((---........)))).))))...)))))).(((((((((.....))))).))))..((((.((.((.---------...))..)).)))).)).... ( -33.90) >DroPse_CAF1 10672 111 - 1 UGAGCCCCGAUCUAGAACGUGACGAUGGUUCACUGUUGGGUUUAUAGUUGGCCGGACUGUACUUUUCGUACAUGUCCAGCCCCGAGGUGG---------CCACUAAACGUGCUAGGGAUG ..........(((((.((((..((((((....))))))......((((.(((((((((((((.....))))).)))).(((....)))))---------)))))).)))).))))).... ( -38.30) >DroWil_CAF1 7440 117 - 1 UGUGACCCGAUCUAGAACGUGAU---AGUUCACAGUUGGGUAUAUAGUUUGCCGGACAGUAUUUCUCGUAUGCAUCUAGACCGGAUGUGGCUACUGUGGCCAACAUACGGGCCAGGGAUG .((.(((((.((((((..((((.---...)))).(((.((((.......)))).))).((((.......)))).)))))).)))..)).))..((.(((((........))))).))... ( -40.00) >DroAna_CAF1 6600 108 - 1 CAAGAGCCGACCUGGAACGUGAC---AGGUCACAGUUGGGUUUAUAGUUGGCCGGACUGUACUUUUCGUAGAUGUCCAAUCCGGAGGUGG---------CCACCAGGCGGGCCAGCGACG ...(((((((((((........)---))))).(....))))))...((((((((((((.(((.....))).).))))............(---------((....))).))))))).... ( -40.60) >DroPer_CAF1 10311 111 - 1 UGAGCCCCGAUCUAGAACGUGACGAUGGUUCACUGUUGGGUUUAUAGUUGGCCGGACUGUACUUUUCGUACAUGUCCAGCCCCGAGGUGG---------CCACUAAACGUGCUAGGGAUG ..........(((((.((((..((((((....))))))......((((.(((((((((((((.....))))).)))).(((....)))))---------)))))).)))).))))).... ( -38.30) >consensus UGAGCCCCGAUCUAGAACGUGAC___AGUUCACAGUUGGGUUUAUAGUUGGCCGGACUGUACUUUUCGUACAUGUCCAGCCCGGAGGUGG_________CCACCAAACGGGCCAGGGAUG .....((((((...((((.........))))...)))))).......(((((.(((((((((.....))))).))))...(((..(((((((.....)))))))...))))))))..... (-24.63 = -26.30 + 1.67)

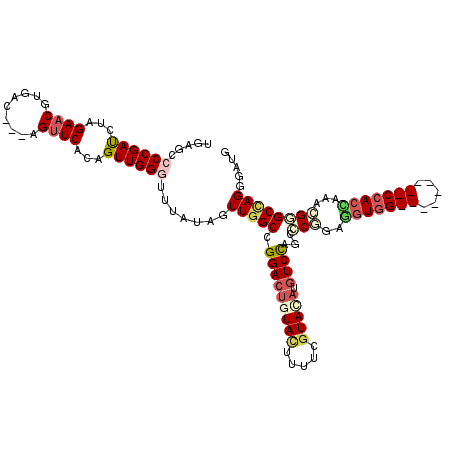
Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 13:08:46 2006