
| Sequence ID | X_DroMel_CAF1 |
|---|---|
| Location | 1,629,787 – 1,629,907 |
| Length | 120 |
| Max. P | 0.997903 |

| Location | 1,629,787 – 1,629,877 |
|---|---|
| Length | 90 |
| Sequences | 5 |
| Columns | 92 |
| Reading direction | forward |
| Mean pairwise identity | 91.88 |
| Mean single sequence MFE | -25.56 |
| Consensus MFE | -20.22 |
| Energy contribution | -20.46 |
| Covariance contribution | 0.24 |
| Combinations/Pair | 1.04 |
| Mean z-score | -3.82 |
| Structure conservation index | 0.79 |
| SVM decision value | 2.96 |
| SVM RNA-class probability | 0.997903 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>X_DroMel_CAF1 1629787 90 + 22224390 UUUGUUAACAGCUACUGUUGGCAGAUAUCCAAAAUAUCGAUAU-AAGCGGAC-UGAUUCGAGCAGUAACAUUACGAUGUAAGUAUCGAUAUU (((((((((((...))))))))))).......(((((((((((-......((-((.......)))).((((....))))..))))))))))) ( -24.00) >DroSec_CAF1 24905 90 + 1 UUUGUUAACAGCAACUGUUAGCAGAUAUCCA-AAUAUCGAUAUUAUGCAGAC-UGAUGCGAGCAGUAACAUUACGAUGUAAGUAUCGAUAUU (((((((((((...)))))))))))......-((((((((((((.((((...-(((((..........)))))...)))))))))))))))) ( -26.40) >DroSim_CAF1 41421 90 + 1 UUUGUUAACAGCAACUGUUAGCAGAUAUCCA-AAUAUCGAUAUUAUGCAGAC-UGAUGCGAGCAGUAACAUUACGAUGUAAGUAUCGAUAUU (((((((((((...)))))))))))......-((((((((((((.((((...-(((((..........)))))...)))))))))))))))) ( -26.40) >DroEre_CAF1 26251 89 + 1 UUUGUUAACAGCAACUGUUAGCAGAUAUCCAAAAUAUCGAUA---UGCAGACAUUCCGCAAGCAGUAACAUUACGAUGUAAGUAUCGAUAUU (((((((((((...))))))))))).......((((((((((---(....(((((.(....)..(((....))))))))..))))))))))) ( -25.50) >DroYak_CAF1 29188 89 + 1 UUUGUUAACAGCAACUGUUAGCAGAUAUCCAAAAUAUCGAUA---UGCAGACAUUCCGCAAGCAGUAACAUUACGAUGUAAGUAUCGAUAUU (((((((((((...))))))))))).......((((((((((---(....(((((.(....)..(((....))))))))..))))))))))) ( -25.50) >consensus UUUGUUAACAGCAACUGUUAGCAGAUAUCCAAAAUAUCGAUAU_AUGCAGAC_UGAUGCGAGCAGUAACAUUACGAUGUAAGUAUCGAUAUU (((((((((((...))))))))))).......(((((((((((...((.............))....((((....))))..))))))))))) (-20.22 = -20.46 + 0.24)

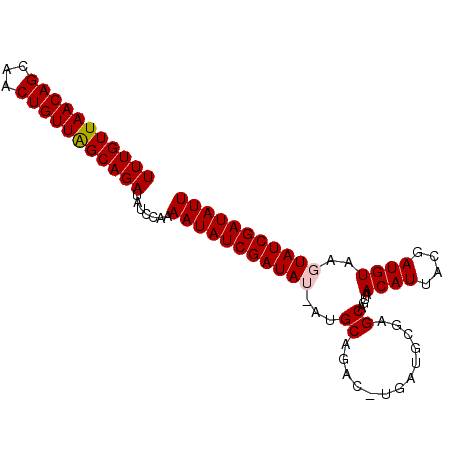
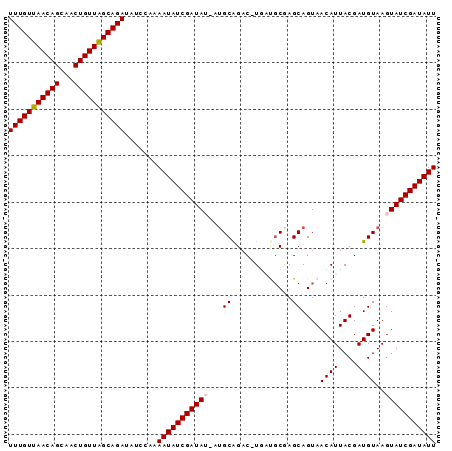
| Location | 1,629,800 – 1,629,907 |
|---|---|
| Length | 107 |
| Sequences | 5 |
| Columns | 110 |
| Reading direction | forward |
| Mean pairwise identity | 90.83 |
| Mean single sequence MFE | -30.94 |
| Consensus MFE | -22.44 |
| Energy contribution | -24.32 |
| Covariance contribution | 1.88 |
| Combinations/Pair | 1.06 |
| Mean z-score | -3.45 |
| Structure conservation index | 0.73 |
| SVM decision value | 1.60 |
| SVM RNA-class probability | 0.966998 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>X_DroMel_CAF1 1629800 107 + 22224390 ACUGUUGGCAGAUAUCCAAAAUAUCGAUAU-AAGCGGAC-UGAUUCGAGCAGUAACAUUACGAUGUAAGUAUCGAUAUUAGAUAUUGUGAUA-ACUGCUCACAUCGCUAG ..(((.(((((.((((((((((((((((((-......((-((.......)))).((((....))))..))))))))))).....))).))))-.))))).)))....... ( -28.20) >DroSec_CAF1 24918 108 + 1 ACUGUUAGCAGAUAUCCA-AAUAUCGAUAUUAUGCAGAC-UGAUGCGAGCAGUAACAUUACGAUGUAAGUAUCGAUAUUGGAUAUUGUGAUAAACUGCUCACAUCGCUAG ...(((.(((((((((..-......)))))).))).)))-.((((.(((((((...((((((((((.((((....))))..))))))))))..))))))).))))..... ( -34.60) >DroSim_CAF1 41434 108 + 1 ACUGUUAGCAGAUAUCCA-AAUAUCGAUAUUAUGCAGAC-UGAUGCGAGCAGUAACAUUACGAUGUAAGUAUCGAUAUUGGAUAUUGUGAUAAACUGCUCACAUCGCUAG ...(((.(((((((((..-......)))))).))).)))-.((((.(((((((...((((((((((.((((....))))..))))))))))..))))))).))))..... ( -34.60) >DroEre_CAF1 26264 107 + 1 ACUGUUAGCAGAUAUCCAAAAUAUCGAUA---UGCAGACAUUCCGCAAGCAGUAACAUUACGAUGUAAGUAUCGAUAUUGGAUAUUGUGAUAAACAGCUCACAUCCCUAG ..(((.(((.((((((((..(((((((((---(....(((((.(....)..(((....))))))))..))))))))))))))))))((.....)).))).)))....... ( -29.30) >DroYak_CAF1 29201 107 + 1 ACUGUUAGCAGAUAUCCAAAAUAUCGAUA---UGCAGACAUUCCGCAAGCAGUAACAUUACGAUGUAAGUAUCGAUAUUGGAUAUUGUGAUAAAUUGCGCGCAUCCCUAG .......((.((((((((..(((((((((---(....(((((.(....)..(((....))))))))..))))))))))))))))))(((........)))))........ ( -28.00) >consensus ACUGUUAGCAGAUAUCCAAAAUAUCGAUAU_AUGCAGAC_UGAUGCGAGCAGUAACAUUACGAUGUAAGUAUCGAUAUUGGAUAUUGUGAUAAACUGCUCACAUCGCUAG .((((.....(((((.....)))))........))))....((((.(((((((...((((((((((.((((....))))..))))))))))..))))))).))))..... (-22.44 = -24.32 + 1.88)


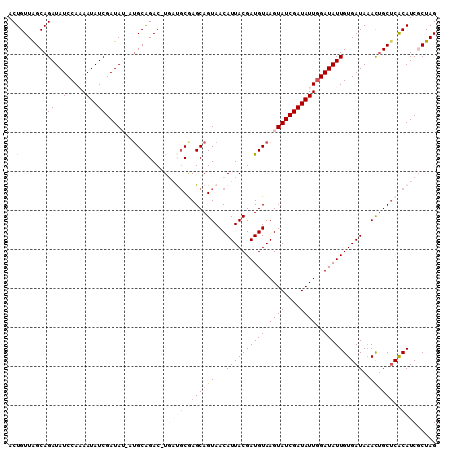
| Location | 1,629,800 – 1,629,907 |
|---|---|
| Length | 107 |
| Sequences | 5 |
| Columns | 110 |
| Reading direction | reverse |
| Mean pairwise identity | 90.83 |
| Mean single sequence MFE | -26.40 |
| Consensus MFE | -20.46 |
| Energy contribution | -21.50 |
| Covariance contribution | 1.04 |
| Combinations/Pair | 1.03 |
| Mean z-score | -2.24 |
| Structure conservation index | 0.77 |
| SVM decision value | 1.28 |
| SVM RNA-class probability | 0.939815 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>X_DroMel_CAF1 1629800 107 - 22224390 CUAGCGAUGUGAGCAGU-UAUCACAAUAUCUAAUAUCGAUACUUACAUCGUAAUGUUACUGCUCGAAUCA-GUCCGCUU-AUAUCGAUAUUUUGGAUAUCUGCCAACAGU .......(((..((((.-((((.(((.....((((((((((...((((....)))).((((.......))-))......-.))))))))))))))))).))))..))).. ( -23.20) >DroSec_CAF1 24918 108 - 1 CUAGCGAUGUGAGCAGUUUAUCACAAUAUCCAAUAUCGAUACUUACAUCGUAAUGUUACUGCUCGCAUCA-GUCUGCAUAAUAUCGAUAUU-UGGAUAUCUGCUAACAGU .(((((.(((((........)))))((((((((((((((((..(((...)))((((.((((.......))-))..))))..)))))))).)-))))))).)))))..... ( -29.10) >DroSim_CAF1 41434 108 - 1 CUAGCGAUGUGAGCAGUUUAUCACAAUAUCCAAUAUCGAUACUUACAUCGUAAUGUUACUGCUCGCAUCA-GUCUGCAUAAUAUCGAUAUU-UGGAUAUCUGCUAACAGU .(((((.(((((........)))))((((((((((((((((..(((...)))((((.((((.......))-))..))))..)))))))).)-))))))).)))))..... ( -29.10) >DroEre_CAF1 26264 107 - 1 CUAGGGAUGUGAGCUGUUUAUCACAAUAUCCAAUAUCGAUACUUACAUCGUAAUGUUACUGCUUGCGGAAUGUCUGCA---UAUCGAUAUUUUGGAUAUCUGCUAACAGU .(((((((((((........))))).(((((((((((((((...((((....)))).......(((((.....)))))---)))))))))..))))))))).)))..... ( -27.90) >DroYak_CAF1 29201 107 - 1 CUAGGGAUGCGCGCAAUUUAUCACAAUAUCCAAUAUCGAUACUUACAUCGUAAUGUUACUGCUUGCGGAAUGUCUGCA---UAUCGAUAUUUUGGAUAUCUGCUAACAGU .(((.((((.........)))).((((((((((((((((((...((((....)))).......(((((.....)))))---)))))))))..))))))).)))))..... ( -22.70) >consensus CUAGCGAUGUGAGCAGUUUAUCACAAUAUCCAAUAUCGAUACUUACAUCGUAAUGUUACUGCUCGCAUCA_GUCUGCAU_AUAUCGAUAUUUUGGAUAUCUGCUAACAGU .(((((.(((((........)))))((((((((((((((((...((((....))))....((..((.....))..))....)))))))))..))))))).)))))..... (-20.46 = -21.50 + 1.04)

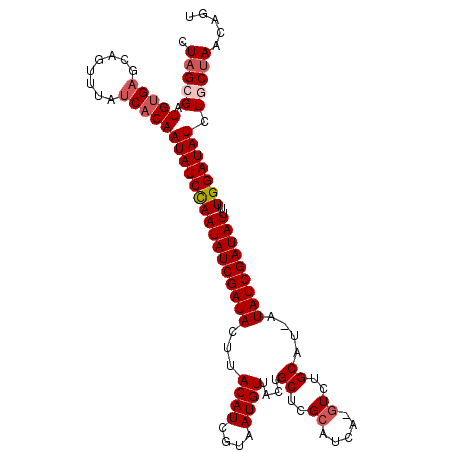
Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 09:48:00 2006