
| Sequence ID | X_DroMel_CAF1 |
|---|---|
| Location | 8,620,334 – 8,620,434 |
| Length | 100 |
| Max. P | 0.999925 |

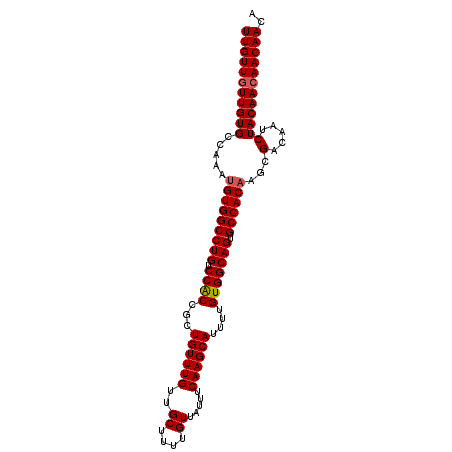
| Location | 8,620,334 – 8,620,434 |
|---|---|
| Length | 100 |
| Sequences | 5 |
| Columns | 101 |
| Reading direction | forward |
| Mean pairwise identity | 97.62 |
| Mean single sequence MFE | -34.54 |
| Consensus MFE | -33.54 |
| Energy contribution | -33.78 |
| Covariance contribution | 0.24 |
| Combinations/Pair | 1.03 |
| Mean z-score | -4.04 |
| Structure conservation index | 0.97 |
| SVM decision value | 4.59 |
| SVM RNA-class probability | 0.999925 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
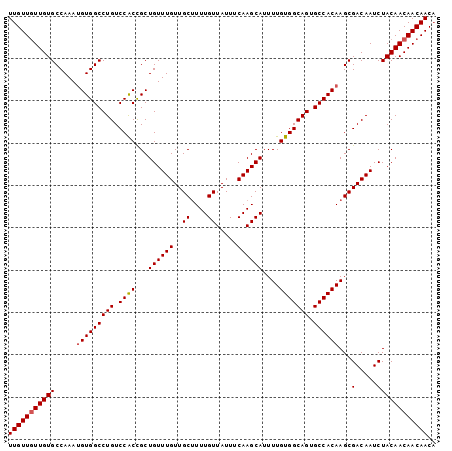
>X_DroMel_CAF1 8620334 100 + 22224390 UUGUUGUUGUGCCAAAUGUGGCCUGUCCACCGCUGUUUGUUGCUUUUGUUAUUUCAAGCAUUUUGUGGCAGUGCCACAAGCGACAAUCUACAACAACAAC- (((((((((((.....(((((((((.((((...((((((..((....)).....))))))....))))))).))))))...(.....)))))))))))).- ( -35.40) >DroSec_CAF1 58025 101 + 1 UUGUUGUUGUGCCAAAUGUGGCCUGUCCACCGCUGUUUGUUGCGUUUGUUAUUUCAAGCAUUUUGUGGCAGUGCCACAAGCGACAAUCUACAACAACAACA (((((((((((......((((........))))...((((((((((((......)))))...(((((((...))))))))))))))..))))))))))).. ( -37.90) >DroSim_CAF1 28212 100 + 1 UUGUU-UUGUGCCAAAAGUGGCCUGUCCACCGCUGUUUGUUGCUUUUGUUAUUUCAAGCAUUUUGUGGCAGUGCCACAAGCGACAAUCUACAACAACAACA ((((.-((((((.....((((((((.((((...((((((..((....)).....))))))....))))))).)))))..)).))))...))))........ ( -28.30) >DroEre_CAF1 70736 101 + 1 UUGUUGUUGUGCCAAAUGUGGCCUGUCCACCGCUGUUUGUUGCUUUUGUUAUUUCAAGCAUUUUGUGGCAGUGCCACAAGCGACAAUCUACAACAACAACA (((((((((((.....(((((((((.((((...((((((..((....)).....))))))....))))))).))))))...(.....)))))))))))).. ( -35.40) >DroYak_CAF1 59236 101 + 1 UUGUUGUUGUGCCAAAUGUGGCCUGUCCGCUGCUGUUUGUUGCUUUUGUUAUUUCAAGCAUUUUGUGGCAGUGCCACAAGCGACAAUCUACAACAACAACA (((((((((((.....(((((((((.((((...((((((..((....)).....))))))....))))))).))))))...(.....)))))))))))).. ( -35.70) >consensus UUGUUGUUGUGCCAAAUGUGGCCUGUCCACCGCUGUUUGUUGCUUUUGUUAUUUCAAGCAUUUUGUGGCAGUGCCACAAGCGACAAUCUACAACAACAACA (((((((((((.....(((((((((.((((...((((((..((....)).....))))))....))))))).))))))...(.....)))))))))))).. (-33.54 = -33.78 + 0.24)

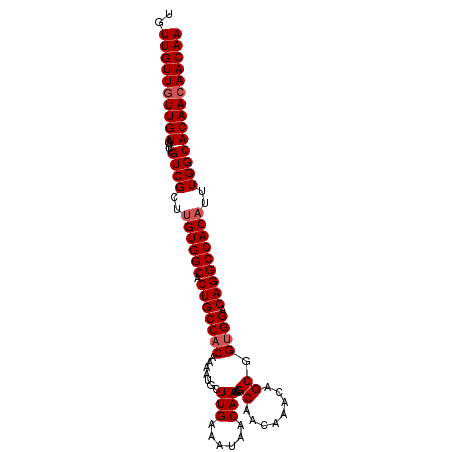
| Location | 8,620,334 – 8,620,434 |
|---|---|
| Length | 100 |
| Sequences | 5 |
| Columns | 101 |
| Reading direction | reverse |
| Mean pairwise identity | 97.62 |
| Mean single sequence MFE | -35.60 |
| Consensus MFE | -33.12 |
| Energy contribution | -33.72 |
| Covariance contribution | 0.60 |
| Combinations/Pair | 1.00 |
| Mean z-score | -4.50 |
| Structure conservation index | 0.93 |
| SVM decision value | 3.79 |
| SVM RNA-class probability | 0.999618 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
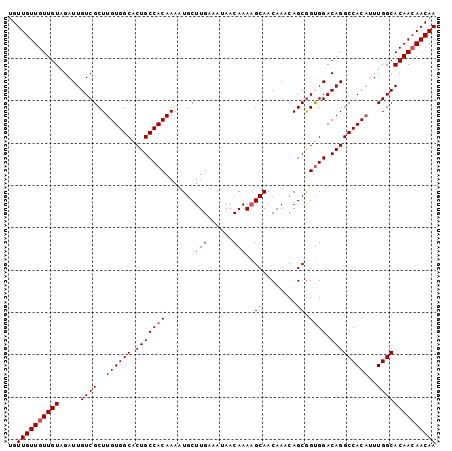
>X_DroMel_CAF1 8620334 100 - 22224390 -GUUGUUGUUGUAGAUUGUCGCUUGUGGCACUGCCACAAAAUGCUUGAAAUAACAAAAGCAACAAACAGCGGUGGACAGGCCACAUUUGGCACAACAACAA -.((((((((((.....((((..((((((.(((((((....(((((..........))))).(.......))))).)))))))))..)))))))))))))) ( -37.30) >DroSec_CAF1 58025 101 - 1 UGUUGUUGUUGUAGAUUGUCGCUUGUGGCACUGCCACAAAAUGCUUGAAAUAACAAACGCAACAAACAGCGGUGGACAGGCCACAUUUGGCACAACAACAA ..((((((((((.....((((..((((((.(((((((.......(((......))).(((........))))))).)))))))))..)))))))))))))) ( -38.50) >DroSim_CAF1 28212 100 - 1 UGUUGUUGUUGUAGAUUGUCGCUUGUGGCACUGCCACAAAAUGCUUGAAAUAACAAAAGCAACAAACAGCGGUGGACAGGCCACUUUUGGCACAA-AACAA ..(((((.((((.(.(..(((((((((((...)))))))..(((((..........))))).......))))..).)..((((....))))))))-))))) ( -29.20) >DroEre_CAF1 70736 101 - 1 UGUUGUUGUUGUAGAUUGUCGCUUGUGGCACUGCCACAAAAUGCUUGAAAUAACAAAAGCAACAAACAGCGGUGGACAGGCCACAUUUGGCACAACAACAA ..((((((((((.....((((..((((((.(((((((....(((((..........))))).(.......))))).)))))))))..)))))))))))))) ( -37.30) >DroYak_CAF1 59236 101 - 1 UGUUGUUGUUGUAGAUUGUCGCUUGUGGCACUGCCACAAAAUGCUUGAAAUAACAAAAGCAACAAACAGCAGCGGACAGGCCACAUUUGGCACAACAACAA ..((((((((((...((((((((((((((...)))))))..(((((..........)))))..........)).)))))((((....)))))))))))))) ( -35.70) >consensus UGUUGUUGUUGUAGAUUGUCGCUUGUGGCACUGCCACAAAAUGCUUGAAAUAACAAAAGCAACAAACAGCGGUGGACAGGCCACAUUUGGCACAACAACAA ..((((((((((.....((((..((((((.(((((((.......(((......)))..((........)).)))).)))))))))..)))))))))))))) (-33.12 = -33.72 + 0.60)

Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 10:54:58 2006