
| Sequence ID | dm3.chr3R |
|---|---|
| Location | 5,486,142 – 5,486,255 |
| Length | 113 |
| Max. P | 0.769422 |

| Location | 5,486,142 – 5,486,255 |
|---|---|
| Length | 113 |
| Sequences | 15 |
| Columns | 113 |
| Reading direction | forward |
| Mean pairwise identity | 81.31 |
| Shannon entropy | 0.45019 |
| G+C content | 0.49853 |
| Mean single sequence MFE | -37.41 |
| Consensus MFE | -21.37 |
| Energy contribution | -21.07 |
| Covariance contribution | -0.30 |
| Combinations/Pair | 1.83 |
| Mean z-score | -1.54 |
| Structure conservation index | 0.57 |
| Background model | dinucleotide |
| Decision model | sequence based alignment quality |
| SVM decision value | 0.63 |
| SVM RNA-class probability | 0.769422 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
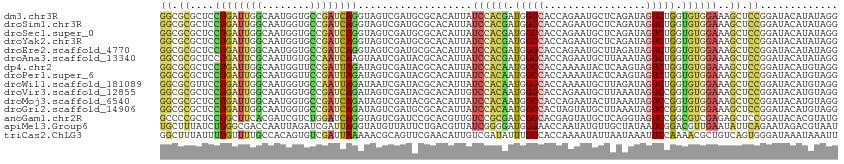
>dm3.chr3R 5486142 113 + 27905053 GGCGCGCUCCUGAUUGGCAAUGGUGCCGAUCAGGUAGUCGAUGCGCACAUUAUCCACGAUGGGCACCAGAAUGCUCAGAUAGUCUGGUGUGGAAAGCUCCGGAUACAUAUAGG .((((((((((((((((((....))))))))))).)))....))))....(((((.......((((((((.((......)).))))))))(((....))))))))........ ( -46.50, z-score = -2.94, R) >droSim1.chr3R 11668012 113 - 27517382 GGCGCGCUCCUGAUUGGCAAUGGUGCCGAUCAGGUAGUCGAUGCGCACAUUAUCCACGAUGGGCACCAGAAUGCUCAGAUAGUCUGGUGUGGAAAGCUCCGGAUACAUAUAGG .((((((((((((((((((....))))))))))).)))....))))....(((((.......((((((((.((......)).))))))))(((....))))))))........ ( -46.50, z-score = -2.94, R) >droSec1.super_0 4709609 113 - 21120651 GGCGCGCUCCUGAUUGGCAAUGGUGCCGAUCAGGUAGUCGAUGCGCACAUUAUCCACGAUGGGCACCAGAAUGCUCAGAUAGUCUGGUGUGGAAAGCUCCGGAUACAUAUAGG .((((((((((((((((((....))))))))))).)))....))))....(((((.......((((((((.((......)).))))))))(((....))))))))........ ( -46.50, z-score = -2.94, R) >droYak2.chr3R 9539614 113 + 28832112 GGCGCGCUCCUGAUUGGCAAUGGUGCCGAUCAGGUAGUCGAUGCGCACAUUAUCCACGAUGGGCACCAGAAUGCUCAGAUAGUCUGGUGUGGAAAGCUCCGGAUACAUAUAGG .((((((((((((((((((....))))))))))).)))....))))....(((((.......((((((((.((......)).))))))))(((....))))))))........ ( -46.50, z-score = -2.94, R) >droEre2.scaffold_4770 1634622 113 - 17746568 GGCGCGCUCCUGAUUGGCAAUGGUGCCGAUCAGGUAGUCGAUGCGCACAUUAUCCACGAUGGGCACCAGAAUGCUUAGAUAGUCUGGUGUGGAAAGCUCCGGAUACAUAUAGG .((((((((((((((((((....))))))))))).)))....))))....(((((.......((((((((.((......)).))))))))(((....))))))))........ ( -46.50, z-score = -3.16, R) >droAna3.scaffold_13340 9549948 113 - 23697760 GGCGCGCUCCUGAUUCGCAAUUGUGCCAAUCAAGUAAUCGAUACGCACAUUAUCCACGAUGGGCACCAGAAUGCUUAAAUAGUCUGGUGUGGAAAGCUCCGGAUACAUAUAGG .(((..(....)...)))...(((((..(((........)))..))))).(((((.......((((((((.((......)).))))))))(((....))))))))........ ( -28.70, z-score = 0.03, R) >dp4.chr2 25696013 113 + 30794189 GGCGCGCUCCUGAUUGGCAAUGGUUCCGAUUAGAUAGUCGAUACGCACAUUAUCCACAAUGGGCACCAAAAUACUCAAGUAGUCUGGUGUGGAAAGCUCCGGAUACAUGUAGG .(((((((.((((((((........))))))))..)).))...)))(((((((((.......((((((...(((....)))...))))))(((....)))))))).))))... ( -32.70, z-score = -0.84, R) >droPer1.super_6 1038869 113 + 6141320 GGCGCGCUCCUGAUUGGCAAUGGUUCCGAUUAGAUAGUCGAUACGCACAUUAUCCACAAUGGGCACCAAAAUACUCAAGUAGUCUGGUGUGGAAAGCUCCGGAUACAUGUAGG .(((((((.((((((((........))))))))..)).))...)))(((((((((.......((((((...(((....)))...))))))(((....)))))))).))))... ( -32.70, z-score = -0.84, R) >droWil1.scaffold_181089 5685743 113 - 12369635 GGCGCGUUCCUGAUUGGCAAUGGUGCCAAUUAGAUAAUCGAUACGCACAUUAUCCACAAUGGGCACCAAAAUGCUUAGAUAGUCUGGUGUGGAAAGCUCCGGAUACAUGUAGG ...((((((((((((((((....))))))))))......)).))))(((((((((.......((((((....(((.....))).))))))(((....)))))))).))))... ( -35.80, z-score = -1.78, R) >droVir3.scaffold_12855 5565992 113 + 10161210 GGCGCGCUCCUGAUUGGCAAUGGUGCCGAUCAGAUAGUCGAUACGCACAUUGUCCACAAUGGGCACCAGAAUGCUUAAAUAGUCCGGUGUGGAAAGCUCCGGAUACAUGUAGG ((.((((..((((((((((....))))))))))...((....)))).(((((....))))).)).))......((((....((((((.((.....)).)))))).....)))) ( -38.10, z-score = -1.28, R) >droMoj3.scaffold_6540 5888399 113 + 34148556 GGCGCGCUCCUGAUUGGCAAUGGUGCCGAUCAGAUAGUCGAUACGCACAUUAUCCACAAUGGGCACCAGAAUACUUAAAUAGUCCGGUGUGGAAAGCUCCGGAUACAUGUAGG .(((((((.((((((((((....))))))))))..)).))...)))(((((((((.......(((((.((.((......)).)).)))))(((....)))))))).))))... ( -37.10, z-score = -1.70, R) >droGri2.scaffold_14906 5738078 113 - 14172833 GGCGCGCUCCUGAUUGGCAAUGGUGCCGAUCAGAUAGUCGAUGCGCACAUUAUCCACAAUGGGCACUAGUAUGCUUAAAUAGUCCGGUGUGGAAAGCUCCGGAUACAUGUAGG .(((((((.((((((((((....))))))))))..)))....)))).......(((((.((((((......))))))....((((((.((.....)).))))))...))).)) ( -40.00, z-score = -1.75, R) >anoGam1.chr2R 34967398 113 + 62725911 GCCCCGCUCCUGCUUCACGAUCGUCUGGAUCAGGUAGUCGAUCCGCACGUUGUCCGCGAUCGGCACGAGUAUGCUCAGGUAGUCCGGCGUCGAGAGCUCCGGAUACACGUAUG .....((((.(((....(((((((..((((.(.((.((......)))).).)))))))))))))).))))((((....(((.(((((.(.(....)).))))))))..)))). ( -35.80, z-score = 1.13, R) >apiMel3.Group6 2770961 113 + 14581788 UGCUUUAUCUUGGCGACCAAUUAGAUCGAUUAGGUAUGUUAUUCUGACGUUAUCGGGGAUGGGAACCAAUAUGUUGCUAUAAUCGGACGUUGAAUAUUCAGAAUAGACGUAAU ((((((((..((((((((((((.....)))).))).)))(((((.((((((..(((..((((.(((......))).))))..))))))))))))))..))..))))).))).. ( -24.40, z-score = 0.07, R) >triCas2.ChLG3 12764392 113 - 32080666 GGCUUUAUUUUGUUUUGCCACAGUGUCGAUUAAAAACGCAGUUCGAACAUUGUCGAUAUUUGGCACCAAAAUAUUAAUAAAUUCCAAAACGCUGUCAGUGGGAUAAAUAAAUU .....(((((((...(((((.(((((((((......((.....))......)))))))))))))).))))))).......((((((..((...))...))))))......... ( -23.40, z-score = -1.15, R) >consensus GGCGCGCUCCUGAUUGGCAAUGGUGCCGAUCAGGUAGUCGAUACGCACAUUAUCCACGAUGGGCACCAGAAUGCUCAGAUAGUCUGGUGUGGAAAGCUCCGGAUACAUGUAGG ((.((....((((((((........))))))))...................((((((.(((((.................))))).))))))..)).))............. (-21.37 = -21.07 + -0.30)


Generated by rnazCluster.pl (part of RNAz 1.0) on Wed Apr 20 00:01:15 2011