| Sequence ID | dm3.chr3L |
|---|---|
| Location | 12,909,733 – 12,909,831 |
| Length | 98 |
| Max. P | 0.939618 |

| Location | 12,909,733 – 12,909,831 |
|---|---|
| Length | 98 |
| Sequences | 10 |
| Columns | 114 |
| Reading direction | reverse |
| Mean pairwise identity | 81.02 |
| Shannon entropy | 0.37329 |
| G+C content | 0.46863 |
| Mean single sequence MFE | -30.84 |
| Consensus MFE | -15.47 |
| Energy contribution | -14.89 |
| Covariance contribution | -0.58 |
| Combinations/Pair | 1.50 |
| Mean z-score | -2.64 |
| Structure conservation index | 0.50 |
| Background model | dinucleotide |
| Decision model | sequence based alignment quality |
| SVM decision value | 1.46 |
| SVM RNA-class probability | 0.939618 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
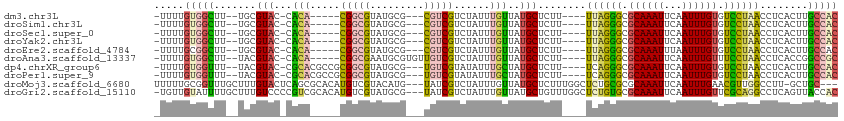
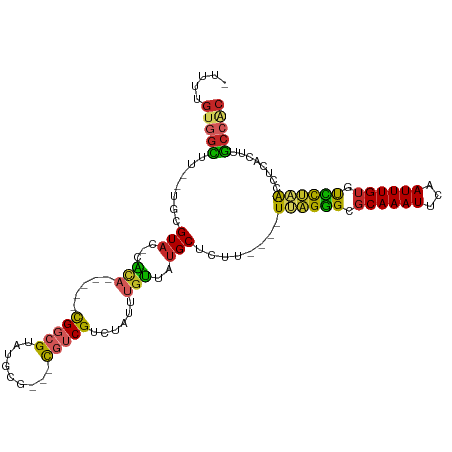
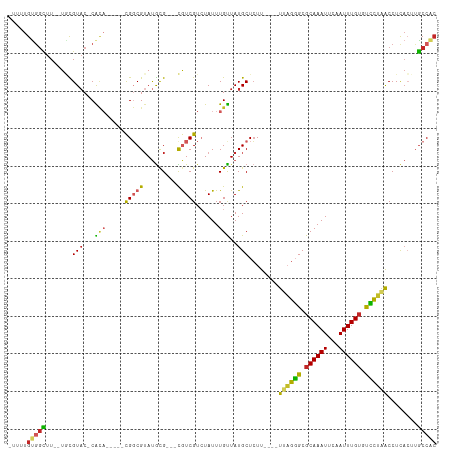
>dm3.chr3L 12909733 98 - 24543557 -UUUUGUGGCUU--UGCGUAC-CACA-----CGGCGUAUGCG---CGUCGUCUAUUUGUUAUGCUCUU----UUAGGGCGCAAAUUCAAUUUGUGUCCUAACCUCACUUGCCAC -....(((((..--.(((((.-((.(-----((((((....)---)))))).....)).)))))....----(((((((((((((...)))))))))))))........))))) ( -34.60, z-score = -4.39, R) >droSim1.chr3L 12294504 98 - 22553184 -UUUUGUGGCUU--UGCGUAC-CACA-----CGGCGUAUGCG---CGUCGUCUAUUUGUUAUGCUCUU----UUAGGGCGCAAAUUCAAUUUGUGUCCUAACCUCACUUGCCAC -....(((((..--.(((((.-((.(-----((((((....)---)))))).....)).)))))....----(((((((((((((...)))))))))))))........))))) ( -34.60, z-score = -4.39, R) >droSec1.super_0 5090445 98 - 21120651 -UUUUGUGGCUU--UGCGUAC-CACA-----CGGCGUAUGCG---CGUCGUCUAUUUGUUAUGCUCUU----UUAGGGCGCAAAUUCAAUUUGUGUCCUAACCUCACUUGCCAC -....(((((..--.(((((.-((.(-----((((((....)---)))))).....)).)))))....----(((((((((((((...)))))))))))))........))))) ( -34.60, z-score = -4.39, R) >droYak2.chr3L 12994590 98 - 24197627 -UUUUGUGGCUU--UGCGUAC-CACA-----CGGCGUAUGCG---CGUCGUCUAUUUGUUAUGCUCUU----UUAGGGCGCAAAUUCAAUUUGUGUCCUAACCUCACUUGCCAC -....(((((..--.(((((.-((.(-----((((((....)---)))))).....)).)))))....----(((((((((((((...)))))))))))))........))))) ( -34.60, z-score = -4.39, R) >droEre2.scaffold_4784 12924396 98 - 25762168 -UUUUGCGGCUU--UGCGUAC-CACA-----CGGCGUAUGCG---CGUCGUCUAUUUGUUAUGCUCUU----UUAGGGCGCAAAUUUAAUUUGUGUCCUAACCUCACUUGCCAC -......(((..--.(((((.-((.(-----((((((....)---)))))).....)).)))))....----(((((((((((((...)))))))))))))........))).. ( -32.30, z-score = -3.40, R) >droAna3.scaffold_13337 6459710 101 + 23293914 -UUUUGUGGCUU--UACGUAC-CACA-----CGGCGAAUGCGUGUUGUCGUCUAUUUGUUAUGCUCUU----UUAGGGCGCAAAUUCAAUUUGUUUCCUAACCUCACCGGCCGC -....((((((.--.(((.((-.(((-----((.......))))).))))).................----((((((.((((((...)))))).)))))).......)))))) ( -25.40, z-score = -0.88, R) >dp4.chrXR_group6 4289148 103 - 13314419 -UUUUGUGGUUU--UACGUAC-CGCACGCCGCGGCGUAUGCG---UGUCGUAUAUUUGCUAUGCUCUU----UCAGGGCGCAAAUUCAAUUUGUGUCCUAACCUCACUUGCCAC -....(((((..--((((.((-(((((((....))))..)))---.))))))................----..(((((((((((...)))))))))))..........))))) ( -32.20, z-score = -2.32, R) >droPer1.super_9 2577665 103 - 3637205 -UUUUGUGGUUU--UACGUAC-CGCACGCCGCGGCGUAUGCG---UGUCGUAUAUUUGCUAUGCUCUU----UCAGGGCGCAAAUUCAAUUUGUGUCCUAACCUCACUUGCCAC -....(((((..--((((.((-(((((((....))))..)))---.))))))................----..(((((((((((...)))))))))))..........))))) ( -32.20, z-score = -2.32, R) >droMoj3.scaffold_6680 7539231 107 + 24764193 UUUUUGCGGUUUGCUUUGUACUCAGCGCACAUGUCGUACAUG---UAUCGUCUAUUUGUUAUGCUCUUUGGCUCUGCGCGCAAAUUCAAUUUGAACGUUGGCCUU-GCUGC--- .....(((((..(((.(((.....(((((((((.....))))---)...........((...(((....)))...))))))....((.....)))))..)))...-)))))--- ( -24.10, z-score = 0.47, R) >droGri2.scaffold_15110 20937298 110 - 24565398 -UGUUGUAUUUUGCUUUGUCCCCGUCGCACAUGUCGUAUGCG---UAUCGUCUAUUUGUUAUGCUGUUUGGCUCUGUGCGCAAAUUCAAUUUGUUCGCAGGCCUCAGUUACCAC -.....................((.((((.........))))---...)).......((...((((...(((.(((((.((((((...)))))).)))))))).)))).))... ( -23.80, z-score = -0.42, R) >consensus _UUUUGUGGCUU__UGCGUAC_CACA_____CGGCGUAUGCG___CGUCGUCUAUUUGUUAUGCUCUU____UUAGGGCGCAAAUUCAAUUUGUGUCCUAACCUCACUUGCCAC .....(((((......................((((((.(((..............))))))))).......((((((.((((((...)))))).))))))........))))) (-15.47 = -14.89 + -0.58)
Generated by rnazCluster.pl (part of RNAz 1.0) on Tue Apr 19 23:22:15 2011