
| Sequence ID | dm3.chr3L |
|---|---|
| Location | 8,273,350 – 8,273,497 |
| Length | 147 |
| Max. P | 0.515783 |

| Location | 8,273,350 – 8,273,497 |
|---|---|
| Length | 147 |
| Sequences | 13 |
| Columns | 148 |
| Reading direction | reverse |
| Mean pairwise identity | 88.68 |
| Shannon entropy | 0.27660 |
| G+C content | 0.46013 |
| Mean single sequence MFE | -46.05 |
| Consensus MFE | -31.76 |
| Energy contribution | -32.50 |
| Covariance contribution | 0.74 |
| Combinations/Pair | 1.33 |
| Mean z-score | -1.66 |
| Structure conservation index | 0.69 |
| Background model | dinucleotide |
| Decision model | sequence based alignment quality |
| SVM decision value | 0.04 |
| SVM RNA-class probability | 0.515783 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
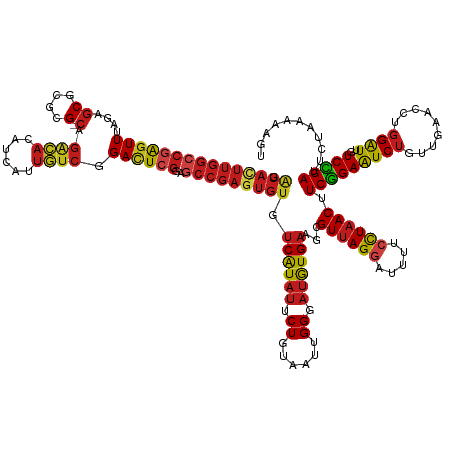
>dm3.chr3L 8273350 147 - 24543557 GAUACUUGGCCGAGUUUAGAGCUCGCG-CAGACACAUCAUUGUCGGACUCGGAGCCGAGUGUGUCAUAUUCUGUAAUUGGGAUGUGAAGCGUUAGGAUUUUCCUAACUUCGGAAUCUGUUGAACCUGGAUUGUCCGAUUCUAAAAAGU .((((((((((((((((...((....)-).((((......)))))))))))..))))))))).(((((((((......)))))))))...((((((.....)))))).(((((((((.........))))..)))))........... ( -48.60, z-score = -2.28, R) >anoGam1.chr2L 41973089 144 - 48795086 GGUAGUUGGACUGGUU-GGAGCGCGAG---GCAAUAUCGUUGUCAGAUUCGGAACCGAGUGUAUCAUAUUCUGUAAUCGGUAUAUGAAGUGUUAGUAUCUUCCUAACUUCGGAAUCUGUGGAUCCGGGAUUGUCUGAUUCUAUAAAUU ((.(((..(((...((-(((.(((..(---(((((...))))))((((((.(((.........((((((.(((....))).))))))...(((((.......)))))))).)))))))))..)))))....)))..)))))....... ( -38.70, z-score = -0.44, R) >droGri2.scaffold_15110 21039260 147 + 24565398 GAUAUUUGGCCGAGUUAAGAGCGCGUG-CAGACACAUCGUUGUCGGACUCGGAGCCGAGUGUGUCAUAUUCUGUAAUUGGUAUGUGAAGAGUUAGGAUUUUCCUAACUUCGGAAUCUGUUGAACCUGGAUUGUCCGAUUCUAAAAAGU .(((((((((((((((.(.((((.(((-....)))..)))).)..))))))..))))))))).((((((.((......)).))))))(((((((((.....)))))).(((((((((.........))))..))))).)))....... ( -42.70, z-score = -1.22, R) >droMoj3.scaffold_6654 1363100 147 - 2564135 GAUAUUUGGCCGAGUUAAGAGCGCGGG-CGGACACAUCAUUGUCGGACUCGGAGCCGAGUGUGUCAUAUUCUGUAAUUGGUAUGUGAAGCGUUAGGAUUUUCCUAACUUCGGAAUCUGUUGAACCUGGAUUGUCCGAUUCUAAAAAGU .(((((((((((((((....((....)-).((((......)))).))))))..))))))))).((((((.((......)).))))))...((((((.....)))))).(((((((((.........))))..)))))........... ( -42.00, z-score = -0.50, R) >droVir3.scaffold_13049 22707091 147 + 25233164 GAUAUUUGGCCGAGUUAAGAGCGCGCG-CGGACACAUCAUUGUCGGACUCGGAGCCGAGUGUGUCAUAUUCUGUAAUUGGUAUGUGAAGCGUUAGGAUUUUCCUAACUUCGGAAUCUGUUGAACCUGGAUUGUCCGAUUCUAAAAAGU .(((((((((((((((....((....)-).((((......)))).))))))..))))))))).((((((.((......)).))))))...((((((.....)))))).(((((((((.........))))..)))))........... ( -42.40, z-score = -0.65, R) >droWil1.scaffold_180698 2231789 147 - 11422946 GAUAUUUGGCCGAGUUAAGAGCGCGUG-CAGACACAUCAUUGUCGGACUCGGAGCCGAGUGUGUCAUAUUCUGUAAUUGGUAUGUGAAGUGUUAGGAUUUUCCUAACUUCGGAAUCUGUUGAACCUGGAUUGUCCGAUUCUAAAAAGU .(((((((((((((((....((....)-).((((......)))).))))))..))))))))).((((((.((......)).))))))...((((((.....)))))).(((((((((.........))))..)))))........... ( -41.40, z-score = -1.03, R) >dp4.chrXR_group3a 1427356 146 + 1468910 GAUACUUGGCCGAGUUUAGAGCGCGUG-CAGACACAUCAUUGUCGGACUCGGAGCCGAGUGUGUCAUAUUCUGUAAUUGGUAUGUGAAGCGUUAGGAUUUUCCUAACUUCGGAAUCUGUGGAACCUGGAUUGUCCGAUUCUAAAAGU- .((((((((((((((((...((....)-).((((......)))))))))))..))))))))).((((((.((......)).))))))...((((((.....)))))).((((((((((.(....))))))..)))))..........- ( -45.40, z-score = -1.50, R) >droAna3.scaffold_13337 3275038 147 - 23293914 GAUACUUGGCCGAGUUUAGCGCGCGUG-CAGACACAUCAUUGUCGGACUCGGAGCCGAGUGUGUCAUAUUCUGUAAUUGGGAUGUGAAGCGUUAGGAUUUUCCUAACUUCGGAAUCUGUUGAACCUGGAUUGUCCGAUUCUAAAAAGU .((((((((((((((((.(((....))-).((((......)))))))))))..))))))))).(((((((((......)))))))))...((((((.....)))))).(((((((((.........))))..)))))........... ( -50.10, z-score = -2.66, R) >droEre2.scaffold_4784 19998658 147 + 25762168 GAUACUUGGCCGAGUUUAGAGCGCGCG-CAGACACAUCAUUGUCGGACUCGGAGCCGAGUGUGUCAUAUUCUGUAAUUGGGAUGUGAAGCGUUAGGAUUUUCCUAACUUCGGAAUCUGUUGAACCUGGAUUGUCCGAUUCUAAAAAGU .((((((((((((((((...((....)-).((((......)))))))))))..))))))))).(((((((((......)))))))))...((((((.....)))))).(((((((((.........))))..)))))........... ( -49.20, z-score = -2.39, R) >droYak2.chr3L 20571834 147 + 24197627 GAUACUUGGCCGAGUUUAGAGCGCGCG-CAGACACAUCAUUGUCGGACUCGGAGCCGAGUGUGUCAUAUUCUGUAAUUGGGAUGUGAAGCGUUAGGAUUUUCCUAACUUCGGAAUCUGUUGAACCUGGAUUGUCCGAUUCUAAAAAGU .((((((((((((((((...((....)-).((((......)))))))))))..))))))))).(((((((((......)))))))))...((((((.....)))))).(((((((((.........))))..)))))........... ( -49.20, z-score = -2.39, R) >droSec1.super_0 554144 147 - 21120651 GAUACUUGGCCGAGUUUAGAGCGCGCG-CAGACACAUCAUUGUCGGACUCGGAGCCGAGUGUGUCAUAUUCUGUAAUUGGGAUGUGAAGCGUUAGGAUUUUCCUAACUUCGGAAUCUGUUGAACCUGGAUUGUCCGAUUCUAAAAAGU .((((((((((((((((...((....)-).((((......)))))))))))..))))))))).(((((((((......)))))))))...((((((.....)))))).(((((((((.........))))..)))))........... ( -49.20, z-score = -2.39, R) >droSim1.chr3L 7732590 147 - 22553184 GAUACUUGGCCGAGUUUAGAGCGCGCG-CAGACACAUCAUUGUCGGACUCGGAGCCGAGUGUGUCAUAUUCUGUAAUUGGGAUGUGAAGCGUUAGGAUUUUCCUAACUUCGGAAUCUGUUGAACCUGGAUUGUCCGAUUCUAAAAAGU .((((((((((((((((...((....)-).((((......)))))))))))..))))))))).(((((((((......)))))))))...((((((.....)))))).(((((((((.........))))..)))))........... ( -49.20, z-score = -2.39, R) >triCas2.ChLG7 14286350 133 + 17478683 ------------AGUUCUUGGCUGGUGGCGCGGCCGUCGCCCUCGGAAUCCGAACCGAGGGUGUCGUACUCUGAAAUAGGCAGGUGCAGAGUUAGUAUCUUCUUCACUUCUGAGUCAGUGCUGCCCAGGUUAUCAGACUCUGAAA--- ------------..(((..(((((((((((((((((.(((((((((........))))))))).))....((((....((.(((((.((((........)))).)))))))...)))).)))))....)))))))).))..))).--- ( -50.60, z-score = -1.78, R) >consensus GAUACUUGGCCGAGUUUAGAGCGCGCG_CAGACACAUCAUUGUCGGACUCGGAGCCGAGUGUGUCAUAUUCUGUAAUUGGGAUGUGAAGCGUUAGGAUUUUCCUAACUUCGGAAUCUGUUGAACCUGGAUUGUCCGAUUCUAAAAAGU .(((((((((((((((..(....)......((((......)))).))))))..))))))))).((((((.((......)).))))))...((((((.....)))))).(((((((((.........))))..)))))........... (-31.76 = -32.50 + 0.74)


Generated by rnazCluster.pl (part of RNAz 1.0) on Tue Apr 19 23:11:17 2011