| Sequence ID | dm3.chr2R |
|---|---|
| Location | 369,994 – 370,168 |
| Length | 174 |
| Max. P | 0.627560 |

| Location | 369,994 – 370,168 |
|---|---|
| Length | 174 |
| Sequences | 5 |
| Columns | 175 |
| Reading direction | reverse |
| Mean pairwise identity | 86.23 |
| Shannon entropy | 0.24361 |
| G+C content | 0.55035 |
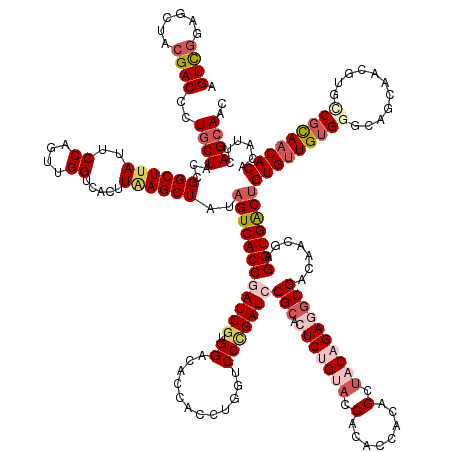
| Mean single sequence MFE | -58.94 |
| Consensus MFE | -40.48 |
| Energy contribution | -43.44 |
| Covariance contribution | 2.96 |
| Combinations/Pair | 1.12 |
| Mean z-score | -1.93 |
| Structure conservation index | 0.69 |
| Background model | dinucleotide |
| Decision model | sequence based alignment quality |
| SVM decision value | 0.28 |
| SVM RNA-class probability | 0.627560 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
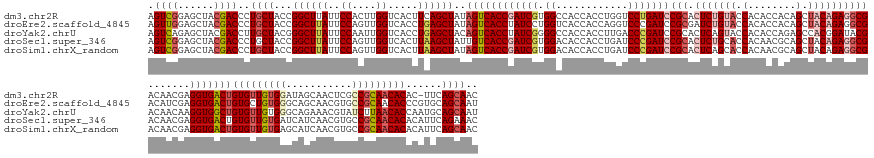
>dm3.chr2R 369994 174 - 21146708 AGUCGGAGCUACGACCCUGCUACCGGCUUAUUCCACUUGGUCACUUCAGCUAUAGUCACCGAUCGUGGCCACCACCUGGUCCUGAUCCGCACUCUGUACCACACCACAGCUACAGAGGCGACAACGAGGUGACUGUGUUGUGGAUAGCAACUCGCCGCAACACAC-UUCAGCAAC (((((((((.........))).))))))....((....))........(((..((((((((((((.(((((.....))))).)))))(((.(((((((.(........).)))))))))).......)))))))(((((((((..((...))..)))))))))..-...)))... ( -65.00, z-score = -3.60, R) >droEre2.scaffold_4845 1960395 175 - 22589142 AGUUGGAGCUACGACCCUGCUACCGGCUUAUUCCAGUUGGUCACCUGAGCUAUAGUCACCUAUCCUGGUCACCACCAGGUCCCGAUCCGCGAUCUGUACCACACCACAGCUACAGAGGCGACAUCGAGGUGACUGUGCUGUGGGCAGCAACGUGCCGCAACACCCGUGCAGCAAU .((((..((.(((...((((.(((((((......)))))))..((..(((.((((((((((..((((((....))))))...((((.(((..((((((.(........).)))))).)))..)))))))))))))))))..))))))...)))))..)))).............. ( -65.00, z-score = -1.68, R) >droYak2.chrU 2676732 175 - 28119190 AGUCAGAGCUACGACCUUGCUACGGGCUUAUUCCAAUUGGUCACCUGAGCUACAGUCACCUAUCGGGGCCACCACCUUGACCCGAUCCGCACUCAGUACCACACCAGAGCCACGGAUACGACAACAAGGUGGCUGUGUUGUGGGCAGAAACGUAUCUUAACACCAAUGCAGCAAU ........(((((((...(((.((((......((....))...))))))).((((((((((.((((((......))))))..(((((((..(((............)))...))))).))......)))))))))))))))))(((.....((......)).....)))...... ( -49.40, z-score = 0.13, R) >droSec1.super_346 8638 175 - 13895 AGUCGGAGCUACGACCCUGCUACCGGCUUAUUCCAGUUGGUCACUUAAGCUAUUGUCACCGAUCGUGGACACCACCUGAUCCCGAUCCGCACUCUGCACCACAACGCAGCUACAGAGGCGACAACGAGGUGACUGUGUUGUGAUCAUCAACGUGCCGCAACACACAUUCAGAAAC .((((......))))...((((((((((......)))))))......)))....(((((((((((.(((((.....)).))))))))(((.(((((................)))))))).......))))))(((((((((..(((....))).)))))))))........... ( -54.29, z-score = -1.53, R) >droSim1.chrX_random 96357 175 + 5698898 AGUCGGAGCUACGACCCUGCUACCGGCUUAUUCCAGUUGGUCACUUAAGCUAUAGUCACCGAUCGUGGACACCACCUGAUCCCGAUCCGCACUCAGCACCACAACGCAGCUACAGAGGCGACAACGAGGUGACUGUGUUGUGAGCAUCAACGUGCCGCAACACACAUUCAGCAAC (((((((((.........))).)))))).......(((((.............((((((((((((.(((((.....)).))))))))(((.((((((...........)))...)))))).......)))))))((((((((.((((....))))))))))))....)))))... ( -61.00, z-score = -2.99, R) >consensus AGUCGGAGCUACGACCCUGCUACCGGCUUAUUCCAGUUGGUCACUUAAGCUAUAGUCACCGAUCGUGGACACCACCUGGUCCCGAUCCGCACUCUGUACCACACCACAGCUACAGAGGCGACAACGAGGUGACUGUGUUGUGGGCAGCAACGUGCCGCAACACACAUUCAGCAAC .((((......))))..((((...((((((..((....)).....))))))..((((((((((((.((............)))))))(((.(((((((.(........).)))))))))).......)))))))(((((((((...........)))))))))......)))).. (-40.48 = -43.44 + 2.96)
Generated by rnazCluster.pl (part of RNAz 1.0) on Tue Apr 19 22:01:07 2011