| Sequence ID | dm3.chr2L |
|---|---|
| Location | 2,034,927 – 2,035,041 |
| Length | 114 |
| Max. P | 0.967398 |

| Location | 2,034,927 – 2,035,041 |
|---|---|
| Length | 114 |
| Sequences | 10 |
| Columns | 114 |
| Reading direction | forward |
| Mean pairwise identity | 75.65 |
| Shannon entropy | 0.52206 |
| G+C content | 0.52466 |
| Mean single sequence MFE | -41.95 |
| Consensus MFE | -20.96 |
| Energy contribution | -20.53 |
| Covariance contribution | -0.43 |
| Combinations/Pair | 1.58 |
| Mean z-score | -2.05 |
| Structure conservation index | 0.50 |
| Background model | dinucleotide |
| Decision model | sequence based alignment quality |
| SVM decision value | 1.78 |
| SVM RNA-class probability | 0.967398 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
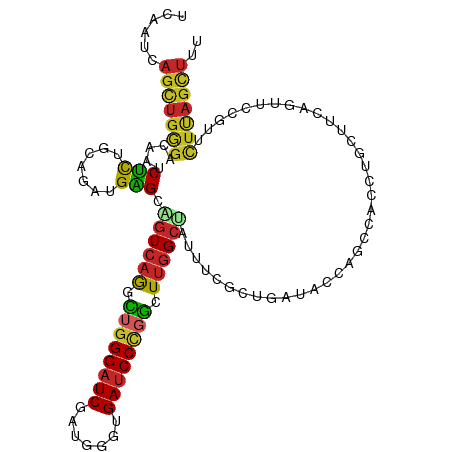
>dm3.chr2L 2034927 114 + 23011544 UCAAUCAGUUGGGACAAUCUCUGCAGGUGAGCAGUCAGGCUGGGAUCGAUGGGCGAUCCCGGCUUGGCUAUUUCGCUGAUACCAGCCACCUGUUUAAGUUCCGUUCUUAGCUUU ......((((((((....((..(((((((...((((((((((((((((.....)))))))))))))))).....((((....)))))))))))...))......)))))))).. ( -51.30, z-score = -4.70, R) >droSim1.chr2L 2004911 114 + 22036055 UCAAUCAGUUGGGACAAUCUCUGCAGGUGAGCAGUCAGGCUGGGAUCGAUGGGUGAUCCCGGUUUGGCUAUUUCGCUGAUACCAGCCACCUGUUUCAGUUCCGUUCUUAGCUUU ......((((((((......(((((((((...((((((((((((((((.....)))))))))))))))).....((((....))))))))))...)))......)))))))).. ( -47.00, z-score = -3.73, R) >droSec1.super_14 1981517 114 + 2068291 UCAAUCAGUUGGGACAAUCUCUGCAGGUGAGCAGUCAGGCUGGGAUCGAUAGGUGAUCCCGGUUUGGCUAUUUCGCUGAUACCAGCCACCUGUUUAAGUUCCGUUCUUAGCUUU ......((((((((....((..(((((((...((((((((((((((((.....)))))))))))))))).....((((....)))))))))))...))......)))))))).. ( -46.80, z-score = -4.18, R) >droYak2.chr2L 2020311 114 + 22324452 UCAAUCAGUUGGGAUAAUCUCUGCAGGUGAGCAGUCAAACUGGGAUCGAUCGGGGAUCCUGGCUUGGCUAUUUCGCUGAUACCAGCCACCUGCUUGAGUUCCGUUCUCAGCUUU ......((((((((....(((.(((((((...((((((.(..(((((.......)))))..).)))))).....((((....)))))))))))..)))......)))))))).. ( -47.90, z-score = -3.84, R) >droEre2.scaffold_4929 2082480 114 + 26641161 UCAAUCAGCUGGGAUAAUCUCUGCAGGUGAGCAGUCAAGCUGGGAUCGAUGGGAGAUCCUGGCUUGGCUAUUUCGCUGAUACCAGCCGCCUGCUUAAGUUCCGUUCUCAGCUUU ......((((((((....((..(((((((...((((((((..(((((.......)))))..)))))))).....((((....)))))))))))...))......)))))))).. ( -53.60, z-score = -4.63, R) >droAna3.scaffold_12916 9751209 114 - 16180835 UCUAUCAGUUGAGACAGUCUCUGUAAAUGGGCCGUCAGCUUGGGAUCAAUGGGUGAUCCCGGCUUGGCCAGUUCACUGACUCCAGCCGCCUGUGUCAGUUCGGUUUUCAGUUUC ..........(((((((((...((.(((.(((((..((((.(((((((.....)))))))))))))))).))).)).))))..(((((.(((...)))..)))))....))))) ( -37.90, z-score = -1.17, R) >dp4.chr4_group3 8823392 114 + 11692001 UCAAUCAGCUGGGAGAGCCUCUGGAGAUGAGCCGUCAGCUGGGGAUCGAUCUGGGAUCCCGGCUUGGCCAAUUCACUCACACUCGCCGCUUGCUUCAGCUCCGCCUUUAGCUGC .....((((((((.((((...(((((.(((((.((.((.((((((((.......))))))(((...)))..........)))).)).))))))))))))))..)))..))))). ( -39.70, z-score = 0.50, R) >droPer1.super_1 10275275 114 + 10282868 UCAAUCAGCUGGGAGAGCCUCUGGAGAUGAGCCGUCAGCUGGGGAUCGAUCUGGGAUCCCGGCUUGGCCAAUUCACUCACACUCGCCGCUUGCUUCAGCUCCGCCUUUAGCUGC .....((((((((.((((...(((((.(((((.((.((.((((((((.......))))))(((...)))..........)))).)).))))))))))))))..)))..))))). ( -39.70, z-score = 0.50, R) >droWil1.scaffold_180708 11689062 114 - 12563649 UCAAUAAGCUGGGAUAAUCUUUGCAAAUGGGCCGUCAAAUUGGGAUCAAUUGGUGAUCCUGGCUUGGAGCUUUCACUUACACCCUGCACUUGUUUCAGUUCGGCUUUCAGUUUC ......(((((..((((....((((...(((....(((.(..((((((.....))))))..).)))(((......)))...))))))).))))..))))).............. ( -28.00, z-score = 0.06, R) >droVir3.scaffold_12963 7625371 97 - 20206255 UCAAUCAGCUGGGAGAGACGCUGCAGAUGCGCGGUGAGAUUCGGAUCGAUGGGUGAGCCCGACU-GGCUAUUA----AAUGUCAUAUGCUCGCCACUGUUUG------------ .(((.((((((((.....((((((......))))))...))))).......(((((((.....(-(((.....----...))))...))))))).))).)))------------ ( -27.60, z-score = 0.71, R) >consensus UCAAUCAGCUGGGACAAUCUCUGCAGAUGAGCAGUCAGGCUGGGAUCGAUGGGUGAUCCCGGCUUGGCUAUUUCGCUGAUACCAGCCACCUGCUUCAGUUCCGUUCUUAGCUUU ......(((((((.....(((.......))).((((((.((((((((.......)))))))).))))))....................................))))))).. (-20.96 = -20.53 + -0.43)

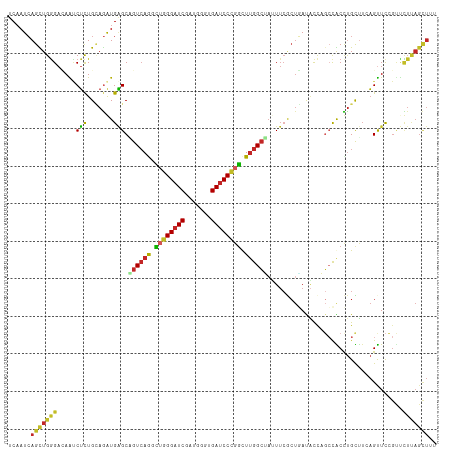
Generated by rnazCluster.pl (part of RNAz 1.0) on Tue Apr 19 21:09:59 2011