
| Sequence ID | dm3.chr2L |
|---|---|
| Location | 12,298,975 – 12,299,108 |
| Length | 133 |
| Max. P | 0.847264 |

| Location | 12,298,975 – 12,299,108 |
|---|---|
| Length | 133 |
| Sequences | 15 |
| Columns | 133 |
| Reading direction | reverse |
| Mean pairwise identity | 71.18 |
| Shannon entropy | 0.69172 |
| G+C content | 0.62868 |
| Mean single sequence MFE | -60.70 |
| Consensus MFE | -22.60 |
| Energy contribution | -22.63 |
| Covariance contribution | 0.03 |
| Combinations/Pair | 1.75 |
| Mean z-score | -1.50 |
| Structure conservation index | 0.37 |
| Background model | dinucleotide |
| Decision model | sequence based alignment quality |
| SVM decision value | 0.90 |
| SVM RNA-class probability | 0.847264 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>dm3.chr2L 12298975 133 - 23011544 GCAACAACUGGUGCUGCAGUCCCACCGCCUGCAGCUGCUGCAGCAGUUGAAUGGAGGCCGGGGUAAUGGCAUCUGCGCCGAGAACCGGCGAAGGCUGCUGCGGCGGAUUGGGCAGGAUGGGCGUGGUCACGCU ..........((((..(.(.((((...(((((..((((((((((((((....(((.((((......)))).))).(((((.....)))))..)))))))))))))).....))))).))))))..).)))... ( -64.60, z-score = -1.38, R) >droSim1.chr2L 12099422 133 - 22036055 GCAACAACUGAUGCUGCAGUCCCACCGCCUGCAGCUGCUGCAGCAGUUGGAUGGAGGCCGGGGUGAUGGCAUCUGCGCCGAGGACCGGCGAAGGCUGCUGCGGCGGAUUGGGCAGGAUGGGCGUGGUCACGCU (((.((.....)).))).(.((((...(((((..((((((((((((((....(((.((((......)))).))).(((((.....)))))..)))))))))))))).....))))).)))))(((....))). ( -63.00, z-score = -0.70, R) >droSec1.super_16 488680 133 - 1878335 GCAACAACUGGUGCUGCAGUCCCACCGCCUGCAGCUGCUGCAGCAGUUGGAUGGAGGCCGGGGUGAUGGCAUCUGCGCCGAGAACCGGCGAAGGCUGCUGCGGCGGAUUGGGCAGGAUGGGCGUGGUCACGCU ..........((((..(.(.((((...(((((..((((((((((((((....(((.((((......)))).))).(((((.....)))))..)))))))))))))).....))))).))))))..).)))... ( -64.60, z-score = -0.98, R) >droYak2.chr2L 8729401 133 - 22324452 GCAGCAACUGCUGCUGCAGCCCAACCGCCUGCAGUUGCUGCAGCAGUUGGAUGGAGGCCGGGGUGAUGGCAUCGGCGCCGAGCACCGGCGAAGGCUGCUGGGGCGGAUUGGGCAGGAUGGGCGUGGUCACGCU ((((((.....)))))).((((((((((((((....))..((((((((........(((((.((..((((......)))).)).)))))...)))))))))))))).))))))......(((((....))))) ( -67.70, z-score = -1.15, R) >droEre2.scaffold_4929 13521876 133 + 26641161 GCAGCAACUGCUGCUGCAAGCCAACCGCCUGCAGUUGCUGCAGCAGCUGGAUGGAGGCCGGGGUGAUGGCAUCGGCGCCGAGGACCGGCGAAGGCUGCUGCGGCGGGUUGGGCAGGAUGGGCGUGGUCACGCU ((((((.....))))))...(((.(((((((.(.((((((((((((((........((((..((....))..))))((((.....))))...)))))))))))))).)))))).)).)))((((....)))). ( -69.60, z-score = -1.45, R) >droAna3.scaffold_12916 3082550 133 + 16180835 GCAAUAGCUGCUGCUGCAACCCAACCGCCUGCAACUGCUGCAACAGUUGGAUGGAGGCCGGGGUUAUGGCAUCGGCUCCUAGGACUGGUGACGGCUGCUGCGGCGGAUUGGGCAGUAUCGGUGUGGCCACACU ((....((((.((((((...(((((((((.(((.(.((((((.(((((...(((..((((..((....))..))))..))).))))).)).)))).).)))))))).)))))))))).))))...))...... ( -59.60, z-score = -1.37, R) >dp4.chr4_group3 5874845 133 + 11692001 GCAGCAACUGCUGCUGCAGGCCCACGGCCUGCAACUGUUGCAGCAAUUGUAUGGAGGCCGGUGUCAGUGCAUCGGCGCCCAGAACGGGCGACUGCUGCUGCGGUGGGUUCGGCAGUAUCGGUGUGGACACACU ......(((((((.((((((((...))))))))(((((.((((((...........((((((((....))))))))((((.....))))...)))))).))))).....)))))))...(((((....))))) ( -65.20, z-score = -1.70, R) >droPer1.super_1 2977231 133 + 10282868 GCAGCAACUGCUGCUGCAGGCCCACGGCCUGCAACUGUUGCAGCAAUUGUAUGGAGGCCGGUGUCAGUGCAUCGGCGCCCAGAACGGGCGACUGCUGCUGCGGUGGGUUCGGCAGUAUCGGUGUGGACACACU ......(((((((.((((((((...))))))))(((((.((((((...........((((((((....))))))))((((.....))))...)))))).))))).....)))))))...(((((....))))) ( -65.20, z-score = -1.70, R) >droWil1.scaffold_180708 9994475 133 - 12563649 GCAGCAAUUGCUGUUGCAAUCCCACUGCCUGCAACUGUUGCAGCAAUUGAAUGGAGGCGGGUGUUAAGGCAUCUGCUCCCAAAACUGGCGACGGUUGUUGCGGUGGGUUUGGCAAUAUAGACGUGGAAACACU (((((....)))))(((...((((((((..(((((((((((..((.((...(((..((((((((....))))))))..))).)).))))))))))))).))))))))....)))........(((....))). ( -63.70, z-score = -5.29, R) >droVir3.scaffold_12963 17379721 133 - 20206255 GAAGCAGCUGUUGCUGCAGUCCAACUGUUUGGAGCUGCUGUAGCAACUGAAUGCUGGCGGGCGUCAACGCAUCGGCGCCCAUCACCGGCGACGGCUGUUGCGGUGGGUUUGGCAGUAUCGGUGUGGAUACAGU ...(((((....))))).(((((((((.(..((.(..((((((((.(((..((((((.(((((((........)))))))....)))))).))).))))))))..).))..))))).......)))))..... ( -60.11, z-score = -1.92, R) >droMoj3.scaffold_6500 22429504 133 - 32352404 GCAGCAGCUGUUGCUGCAGUCCAACUGUUUGCAGCUGCUGCAGCAACUGAAUGCUGGCGGGCGUCAGAGCAUCGGCGCCCAUUACCGGCGACGGUUGUUGCGGUGGGUUUGGCAGUAUCGGUGUGGAAACUGU (((((((((((....((((.....))))..))))))))))).(((.((((.(((((.((((((((........))))))).((((((.((((....))))))))))....).))))))))))))(....)... ( -65.90, z-score = -2.98, R) >droGri2.scaffold_15252 14814559 133 - 17193109 GCAACAGCUGCUGCUGCAGUCCAACUGUUUGCAGCUGCUGCAGCAAUUGAAUGCUGGCUGGUGUCAGAGCAUCGGCUCCCAACACUGGCGACGGCUGUUGCGGUGGGUUUGGCAGUAUCGGUGUGGACACUGU ((..((((.(((((.((((.....))))..))))).))))(((((......))))))).((((((...(((((((((.(((((((((.((((....)))))))))...)))).)))..)))))).)))))).. ( -58.60, z-score = -1.16, R) >anoGam1.chr3R 34924486 130 - 53272125 GCAAAAGAUGCUGCUGCUGGGCGACGGCCUGCAGCUGCUGCAGCAGCGAGA--GCGGCGGG-GAGAUCGCAUCGGCCGCCAGGAACGGGGUCUGCUGCUGCGGUGGGUUCGGAUGGGCGGACGCGGUCAGCGG ........(((((((((.((((....))))....(..(((((((((((.((--...((((.-....)))).))((((.((......)))))))))))))))))..)(((((......))))))))).))))). ( -61.50, z-score = -0.41, R) >apiMel3.Group4 3316078 125 - 10796202 GCAGCAGAUGCCGCAAAGGACAAGCUGGUUUCGGAUACGAGAGAAAUUGGUGAGAGG--------AUCGAGUCUGCGGCGAGAGACGGCAAAGAUCGAGUCGGCGAAAAAGUGAAAAUGGCCGAGGACGAGAC ((..(...(((((((...(((..((..(((((..........)))))..))((....--------.))..))))))))))...)...)).....(((..(((((.(...........).)))))...)))... ( -32.50, z-score = -0.36, R) >triCas2.ChLG9 10407444 121 + 15222296 GCGCCAACAGGUUCU-CGGCGC--CGGUUAAAAGCUGCUGCGGCA---GAA--GCGCCGAGCCGCCGCUCAUCGCCUGCAACAGUUGCAG--GGACGUCGCGUCG--UUCGACAGGACCGGACUGAACUGUUG ....((((((....(-(((..(--(((((....((.((((..(((---(..--(((..((((....))))..)))))))..)))).))..--(((((......))--))).....)))))).)))).)))))) ( -48.70, z-score = 0.04, R) >consensus GCAGCAACUGCUGCUGCAGUCCAACCGCCUGCAGCUGCUGCAGCAAUUGGAUGGAGGCCGGGGUCAUGGCAUCGGCGCCCAGAACCGGCGACGGCUGCUGCGGCGGGUUGGGCAGGAUCGGCGUGGACACGCU (((........)))............(((.....(((((((((((...........(((........))).....((((.......)))).....)))))))))))....))).................... (-22.60 = -22.63 + 0.03)

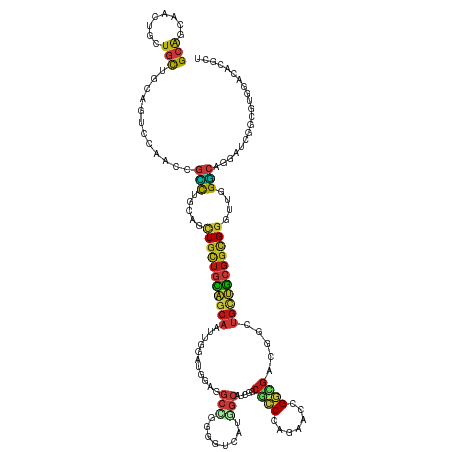
Generated by rnazCluster.pl (part of RNAz 1.0) on Tue Apr 19 21:34:50 2011