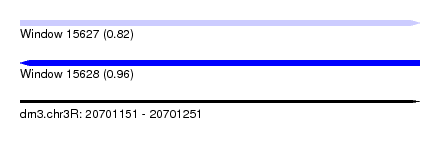
| Sequence ID | dm3.chr3R |
|---|---|
| Location | 20,701,151 – 20,701,251 |
| Length | 100 |
| Max. P | 0.959050 |

| Location | 20,701,151 – 20,701,251 |
|---|---|
| Length | 100 |
| Sequences | 11 |
| Columns | 107 |
| Reading direction | forward |
| Mean pairwise identity | 67.84 |
| Shannon entropy | 0.70050 |
| G+C content | 0.65126 |
| Mean single sequence MFE | -48.65 |
| Consensus MFE | -14.86 |
| Energy contribution | -14.85 |
| Covariance contribution | -0.02 |
| Combinations/Pair | 1.88 |
| Mean z-score | -1.79 |
| Structure conservation index | 0.31 |
| Background model | dinucleotide |
| Decision model | sequence based alignment quality |
| SVM decision value | 0.81 |
| SVM RNA-class probability | 0.823917 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
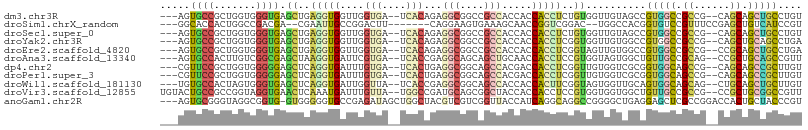
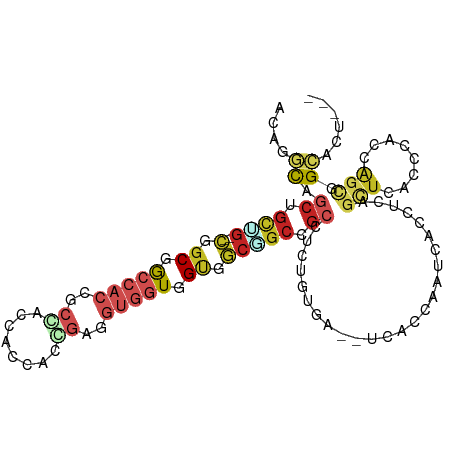
>dm3.chr3R 20701151 100 + 27905053 ---AGUGCCGCUGGUGGGUGAGCUGAGGUGGUUGGUGA--UCACAGAGGCGGCCGCCACCACCACCUCUGUGGUUGUAGCCGUGGCCGCCG--CAGCAGCUGCCUGU ---((.((.((((.((((((.(((..(((.....(..(--(((((((((.((.........)).))))))))))..).)))..))))))).--)).)))).)))).. ( -48.60, z-score = -0.86, R) >droSim1.chrX_random 2423945 93 + 5698898 ---GGCACCACUGGCCGACGA--CGAAUUGCCGGACUU-------CAGGAAGUGAAAGCAACCGGUCGGAC--UGGCCACGGUGUCCGUUUCCGAGCUGUCAUCCGU ---((((((..((((((.(((--(...((((...((((-------....))))....))))...))))...--)))))).))))))..................... ( -28.70, z-score = 1.06, R) >droSec1.super_0 21049171 100 + 21120651 ---AGUGCCGCUGGUGGGUGAGCUGAGGUGGUUGGUGA--UCACAGAGGCGGCCGCCACCACCACCUCUGUGGUUGUAGCCGUGGCCGCCG--CAGCAGCUGCCUGU ---((.((.((((.((((((.(((..(((.....(..(--(((((((((.((.........)).))))))))))..).)))..))))))).--)).)))).)))).. ( -48.60, z-score = -0.86, R) >droYak2.chr3R 3037209 100 - 28832112 ---AGUGCCGCUGGUGGGUGAGCUGAGGUGGUUGGUGA--UCACAGAGGCGGCCGCCACCACCACCUCGGUGGUUGUGGCCGUGGCCGCCG--CAGCUGCAGCCUGA ---...(((...)))((.(((((((.(((((((.((..--..))....((((((((.((((((.....)))))).))))))))))))))).--))))).)).))... ( -52.60, z-score = -1.42, R) >droEre2.scaffold_4820 3117333 100 - 10470090 ---AGUGCCGCUGGUGGGUGAGCUGAGGUGGUUGGUGA--UCACAGAGGCGGCCGCCACCACCACCUCGGUAGUUGUGGCCGUGGCCGCCG--CCGCAGCUGCCUGA ---...((((((....)))).)).(((((((((((((.--.(.(....).)..)))))..))))))))((((((((((((.((....)).)--)))))))))))... ( -51.30, z-score = -1.34, R) >droAna3.scaffold_13340 4749711 100 - 23697760 ---AGUGCCACUUGUCGGCGAGCUAAGGUGAUUCGUGA--UCACCGAGGCAGCAGCUGCAACCACCUCCGUGGUAGUGGCUGUUGCCGCAG--CCGCUGCAGCCGUU ---........(((.(((((.(((..(((((((...))--)))))(.(((((((((..(.(((((....))))).)..))))))))).)))--)))))))))..... ( -50.70, z-score = -3.63, R) >dp4.chr2 6567911 100 - 30794189 ---CGUUCCGCUGGUGGGGGAGCUCAGGUGAUUUGUGA--UCACUGAGGCGGCAGCCACGACCACCUCGGUUGUGGUCGCGGUGGCAGCCG--CAGCAGCCGCUUGU ---.(((((.(.....).)))))...(((((((...))--))))).(((((((.(((((((((.....))))))))).(((((....))))--)....))))))).. ( -49.70, z-score = -1.96, R) >droPer1.super_3 382125 100 - 7375914 ---CGUUCCGCUGGUGGGGGAGCUCAGGUGAUUUGUGA--UCACUGAGGCGGCAGCCACGACCACCUCGGUUGUGGUCGCGGUGGCAGCCG--CAGCAGCCGCUUGU ---.(((((.(.....).)))))...(((((((...))--))))).(((((((.(((((((((.....))))))))).(((((....))))--)....))))))).. ( -49.70, z-score = -1.96, R) >droWil1.scaffold_181130 8574748 100 - 16660200 ---UGUGCCACUAGUGGGUGAGCUCAGGUGAUUGGUUA--UCACCGAGGCGGCAGCCACCACCACUUCGGUAGUGGUUGCAGUGGCAGCAG--CUGCAGCUGCUUGU ---..(((((((.........(((..((((((.....)--)))))..))).((((((((.(((.....))).)))))))))))))))((((--(....))))).... ( -51.40, z-score = -3.33, R) >droVir3.scaffold_12855 8856907 103 + 10161210 UGUACUGCCGCCGGUAGGUGAACUCAAAUGAUUUGUUA--UGGCCGAUGCAGCGGCUACCACCACCUCCGUGGUGGUGGCUGUUGCCGCCG--CCGCUGCGGCCGUU ...((.(((((((((.((((..........(((.((..--..)).)))(((((((((((((((((....))))))))))))))))))))))--)))..))))).)). ( -52.60, z-score = -3.86, R) >anoGam1.chr2R 29591957 103 - 62725911 ---AGUGCGGGUAGGCGGUG-GUGGGGGUGCCGAGAUAGCUGGCUACGUCGUCGGUUACCAUCAGGCAGGCCGGGGCUGAGGAGCUCGCCGGACCACUGCUACCCGU ---...((((((((.(((((-((.....((((((..((((((((......))))))))...)).))))(((..(((((....))))))))..))))))))))))))) ( -51.30, z-score = -1.53, R) >consensus ___AGUGCCGCUGGUGGGUGAGCUGAGGUGAUUGGUGA__UCACAGAGGCGGCAGCCACCACCACCUCGGUGGUGGUGGCCGUGGCCGCCG__CAGCAGCUGCCUGU .....((((.......)))).((..(((((....(((....)))...(((....))).....)))))..))..........(((((.((......)).))))).... (-14.86 = -14.85 + -0.02)
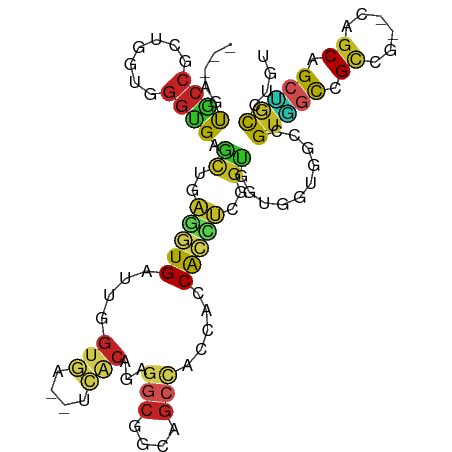
| Location | 20,701,151 – 20,701,251 |
|---|---|
| Length | 100 |
| Sequences | 11 |
| Columns | 107 |
| Reading direction | reverse |
| Mean pairwise identity | 67.84 |
| Shannon entropy | 0.70050 |
| G+C content | 0.65126 |
| Mean single sequence MFE | -44.69 |
| Consensus MFE | -13.04 |
| Energy contribution | -13.57 |
| Covariance contribution | 0.54 |
| Combinations/Pair | 1.95 |
| Mean z-score | -2.35 |
| Structure conservation index | 0.29 |
| Background model | dinucleotide |
| Decision model | sequence based alignment quality |
| SVM decision value | 1.66 |
| SVM RNA-class probability | 0.959050 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>dm3.chr3R 20701151 100 - 27905053 ACAGGCAGCUGCUG--CGGCGGCCACGGCUACAACCACAGAGGUGGUGGUGGCGGCCGCCUCUGUGA--UCACCAACCACCUCAGCUCACCCACCAGCGGCACU--- .......(((((((--.(((((((...(((((.(((((....))))).))))))))))))...((((--.(.............).))))....)))))))...--- ( -44.22, z-score = -1.24, R) >droSim1.chrX_random 2423945 93 - 5698898 ACGGAUGACAGCUCGGAAACGGACACCGUGGCCA--GUCCGACCGGUUGCUUUCACUUCCUG-------AAGUCCGGCAAUUCG--UCGUCGGCCAGUGGUGCC--- ..((........(((....))).((((((((((.--...((((..((((((...((((....-------))))..))))))..)--)))..))))).)))))))--- ( -34.60, z-score = -0.57, R) >droSec1.super_0 21049171 100 - 21120651 ACAGGCAGCUGCUG--CGGCGGCCACGGCUACAACCACAGAGGUGGUGGUGGCGGCCGCCUCUGUGA--UCACCAACCACCUCAGCUCACCCACCAGCGGCACU--- .......(((((((--.(((((((...(((((.(((((....))))).))))))))))))...((((--.(.............).))))....)))))))...--- ( -44.22, z-score = -1.24, R) >droYak2.chr3R 3037209 100 + 28832112 UCAGGCUGCAGCUG--CGGCGGCCACGGCCACAACCACCGAGGUGGUGGUGGCGGCCGCCUCUGUGA--UCACCAACCACCUCAGCUCACCCACCAGCGGCACU--- ....((((((((((--.(((((((...(((((.(((((....))))).))))))))))))...(((.--........)))..))))).........)))))...--- ( -46.90, z-score = -1.83, R) >droEre2.scaffold_4820 3117333 100 + 10470090 UCAGGCAGCUGCGG--CGGCGGCCACGGCCACAACUACCGAGGUGGUGGUGGCGGCCGCCUCUGUGA--UCACCAACCACCUCAGCUCACCCACCAGCGGCACU--- .......(((((((--((((.(((((.(((((..(....)..))))).))))).))))))...((((--.(.............).))))......)))))...--- ( -47.22, z-score = -1.86, R) >droAna3.scaffold_13340 4749711 100 + 23697760 AACGGCUGCAGCGG--CUGCGGCAACAGCCACUACCACGGAGGUGGUUGCAGCUGCUGCCUCGGUGA--UCACGAAUCACCUUAGCUCGCCGACAAGUGGCACU--- ...(((((((((((--(((((((....)))((((((.....)))))).)))))))))))...(((((--(.....))))))..)))).((((.....))))...--- ( -49.90, z-score = -3.81, R) >dp4.chr2 6567911 100 + 30794189 ACAAGCGGCUGCUG--CGGCUGCCACCGCGACCACAACCGAGGUGGUCGUGGCUGCCGCCUCAGUGA--UCACAAAUCACCUGAGCUCCCCCACCAGCGGAACG--- .....(.((((..(--((((.(((...((((((((.......))))))))))).)))))((((((((--(.....)))).))))).........)))).)....--- ( -42.90, z-score = -2.64, R) >droPer1.super_3 382125 100 + 7375914 ACAAGCGGCUGCUG--CGGCUGCCACCGCGACCACAACCGAGGUGGUCGUGGCUGCCGCCUCAGUGA--UCACAAAUCACCUGAGCUCCCCCACCAGCGGAACG--- .....(.((((..(--((((.(((...((((((((.......))))))))))).)))))((((((((--(.....)))).))))).........)))).)....--- ( -42.90, z-score = -2.64, R) >droWil1.scaffold_181130 8574748 100 + 16660200 ACAAGCAGCUGCAG--CUGCUGCCACUGCAACCACUACCGAAGUGGUGGUGGCUGCCGCCUCGGUGA--UAACCAAUCACCUGAGCUCACCCACUAGUGGCACA--- ...((((((....)--)))))(((((((((.((((((((.....)))))))).))).((.(((((((--(.....)))))).)))).........))))))...--- ( -47.40, z-score = -4.12, R) >droVir3.scaffold_12855 8856907 103 - 10161210 AACGGCCGCAGCGG--CGGCGGCAACAGCCACCACCACGGAGGUGGUGGUAGCCGCUGCAUCGGCCA--UAACAAAUCAUUUGAGUUCACCUACCGGCGGCAGUACA .((.(((((.((((--(((((....).(((((((((.....))))))))).))))))))..(((...--.......((....)).........)))))))).))... ( -51.61, z-score = -4.46, R) >anoGam1.chr2R 29591957 103 + 62725911 ACGGGUAGCAGUGGUCCGGCGAGCUCCUCAGCCCCGGCCUGCCUGAUGGUAACCGACGACGUAGCCAGCUAUCUCGGCACCCCCAC-CACCGCCUACCCGCACU--- .((((((((.(((((..((.(((...))).(((.(((..((((....)))).)))..((.((((....)))).)))))..))..))-))).).)))))))....--- ( -39.70, z-score = -1.46, R) >consensus ACAGGCAGCUGCUG__CGGCGGCCACCGCCACCACCACCGAGGUGGUGGUGGCGGCCGCCUCUGUGA__UCACCAAUCACCUCAGCUCACCCACCAGCGGCACU___ ...(((.((.(((....))).))....(((((.(((.....))).))))).)))(((((.....................................)))))...... (-13.04 = -13.57 + 0.54)

Generated by rnazCluster.pl (part of RNAz 1.0) on Wed Apr 20 00:41:39 2011