
| Sequence ID | X_DroMel_CAF1 |
|---|---|
| Location | 20,190,600 – 20,190,718 |
| Length | 118 |
| Max. P | 0.987464 |

| Location | 20,190,600 – 20,190,718 |
|---|---|
| Length | 118 |
| Sequences | 5 |
| Columns | 118 |
| Reading direction | forward |
| Mean pairwise identity | 89.07 |
| Mean single sequence MFE | -39.52 |
| Consensus MFE | -34.32 |
| Energy contribution | -34.40 |
| Covariance contribution | 0.08 |
| Combinations/Pair | 1.21 |
| Mean z-score | -2.07 |
| Structure conservation index | 0.87 |
| SVM decision value | 2.08 |
| SVM RNA-class probability | 0.987464 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
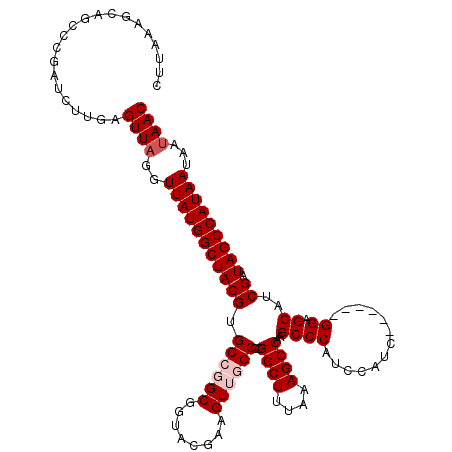
>X_DroMel_CAF1 20190600 118 + 22224390 GUUAUUAUUAUGGCUAUCGAUGCUCCCCGAUGGAUGGAUGGGCUUGGCUUUAAAGCCGAGCCAACUUCGUAUCGCCGGCACGUAGCCAUAACCUAACUCAAGAUCGGACUGCUUUAAG ((((...(((((((((.((.((((...((((..(((((..(((((((((....)))))))))...)))))))))..)))))))))))))))..))))..................... ( -42.00) >DroSec_CAF1 12253 112 + 1 GUUAUUAUUAUGGCUAUCGAUGCCCC------AGUGGAUGGGCUUGGCUUUAAAGCCGGGCCAACUUCGCACCGCCGGCACGUAGCCAUAACCUAACUCAAGAUCGGGCUGCUUUAAG ((((...(((((((((.((.((((..------.(((((..(((((((((....)))))))))....)).)))....)))))))))))))))..))))..................... ( -41.20) >DroSim_CAF1 10372 112 + 1 GUUAUUAUUAUGGCUAUCGAUGCCCC------AAUGGAUGGGCUUGGCUUUAAAGCCGGGCCAACUUCGCACCGCCGGCACGUAGCCAUAACCUAACUCAAGAUCGGGCUGCUUUAAG ((((...(((((((((.((.((((..------..((((..(((((((((....)))))))))....)).)).....)))))))))))))))..))))..................... ( -38.10) >DroEre_CAF1 10111 111 + 1 GUUAUUAUUAUGGCUAUCGAUGCUCC------GAUGGAUGGGCAUGGCUUUAAAGCCG-GCAAACUUUGUACCGCGGGCACGUAGCCAUAAGCAAACUCAGGACCGGGCGGCUUUAAG .......(((((((((.((.(((.((------(.((((..(((.(((((....)))))-)).....)..).))))))))))))))))))))((...(((......)))..))...... ( -35.90) >DroYak_CAF1 9793 112 + 1 GUUAUUAUUAUGGCUAUCGAUGCUCC------GUCGAAUGGGCGUGGCUUUAAAGCCGUGCCAACUUCGUACCGCGUGCACGUAGCCAUAACCUAACCCAAGAUCGGGCGGCUUUAAG .......(((((((((.((.(((.((------(.((((..(((((((((....)))))))))...))))...)).).))))))))))))))((...(((......))).))....... ( -40.40) >consensus GUUAUUAUUAUGGCUAUCGAUGCUCC______GAUGGAUGGGCUUGGCUUUAAAGCCGGGCCAACUUCGUACCGCCGGCACGUAGCCAUAACCUAACUCAAGAUCGGGCUGCUUUAAG ((((...(((((((((.((.((((.........(((((..(((((((((....)))))))))...)))))......)))))))))))))))..))))..................... (-34.32 = -34.40 + 0.08)


| Location | 20,190,600 – 20,190,718 |
|---|---|
| Length | 118 |
| Sequences | 5 |
| Columns | 118 |
| Reading direction | reverse |
| Mean pairwise identity | 89.07 |
| Mean single sequence MFE | -37.44 |
| Consensus MFE | -26.98 |
| Energy contribution | -27.98 |
| Covariance contribution | 1.00 |
| Combinations/Pair | 1.00 |
| Mean z-score | -1.79 |
| Structure conservation index | 0.72 |
| SVM decision value | 0.12 |
| SVM RNA-class probability | 0.594413 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>X_DroMel_CAF1 20190600 118 - 22224390 CUUAAAGCAGUCCGAUCUUGAGUUAGGUUAUGGCUACGUGCCGGCGAUACGAAGUUGGCUCGGCUUUAAAGCCAAGCCCAUCCAUCCAUCGGGGAGCAUCGAUAGCCAUAAUAAUAAC (((((..(((.......)))..)))))(((((((((((((((..((((.....((.((((.((((....)))).)))).))......))))..).))).)).)))))))))....... ( -35.20) >DroSec_CAF1 12253 112 - 1 CUUAAAGCAGCCCGAUCUUGAGUUAGGUUAUGGCUACGUGCCGGCGGUGCGAAGUUGGCCCGGCUUUAAAGCCAAGCCCAUCCACU------GGGGCAUCGAUAGCCAUAAUAAUAAC (((((..(((.......)))..)))))(((((((((((((((..(((((.((....(((..((((....))))..)))..))))))------).)))).)).)))))))))....... ( -39.30) >DroSim_CAF1 10372 112 - 1 CUUAAAGCAGCCCGAUCUUGAGUUAGGUUAUGGCUACGUGCCGGCGGUGCGAAGUUGGCCCGGCUUUAAAGCCAAGCCCAUCCAUU------GGGGCAUCGAUAGCCAUAAUAAUAAC (((((..(((.......)))..)))))((((((((((((((((((((.((.......))))((((....))))..)))((.....)------).)))).)).)))))))))....... ( -37.60) >DroEre_CAF1 10111 111 - 1 CUUAAAGCCGCCCGGUCCUGAGUUUGCUUAUGGCUACGUGCCCGCGGUACAAAGUUUGC-CGGCUUUAAAGCCAUGCCCAUCCAUC------GGAGCAUCGAUAGCCAUAAUAAUAAC ((((..(((....)))..)))).....(((((((((((((((((.((((.......)))-)((((....))))............)------)).))).)).)))))))))....... ( -35.10) >DroYak_CAF1 9793 112 - 1 CUUAAAGCCGCCCGAUCUUGGGUUAGGUUAUGGCUACGUGCACGCGGUACGAAGUUGGCACGGCUUUAAAGCCACGCCCAUUCGAC------GGAGCAUCGAUAGCCAUAAUAAUAAC ......((((((((....)))))..)))(((((((((((((...(.((.((((...(((..((((....))))..)))..))))))------.).))).)).))))))))........ ( -40.00) >consensus CUUAAAGCAGCCCGAUCUUGAGUUAGGUUAUGGCUACGUGCCGGCGGUACGAAGUUGGCCCGGCUUUAAAGCCAAGCCCAUCCAUC______GGAGCAUCGAUAGCCAUAAUAAUAAC .....................((((..(((((((((((.((((((........))))))..((((....))))..((((.............)).))..)).)))))))))...)))) (-26.98 = -27.98 + 1.00)


Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 12:56:03 2006