
| Sequence ID | X_DroMel_CAF1 |
|---|---|
| Location | 16,220,920 – 16,221,184 |
| Length | 264 |
| Max. P | 0.998550 |

| Location | 16,220,920 – 16,221,024 |
|---|---|
| Length | 104 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 83.66 |
| Mean single sequence MFE | -36.60 |
| Consensus MFE | -31.62 |
| Energy contribution | -31.27 |
| Covariance contribution | -0.36 |
| Combinations/Pair | 1.19 |
| Mean z-score | -3.10 |
| Structure conservation index | 0.86 |
| SVM decision value | 1.74 |
| SVM RNA-class probability | 0.974831 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
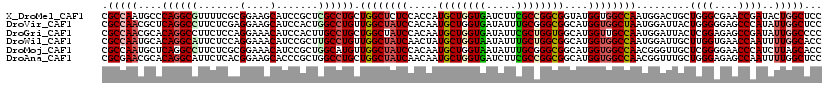
>X_DroMel_CAF1 16220920 104 + 22224390 ----------------AAGGCAGGACACAAGAUCGGCUGUGAUCAUGGACCCGGAAGCAUUUUUGGACGUGGCCAACCAGGUCAUCAAGCUGAAAAUGUUUCCGUUCUUCGACAUCGCUC ----------------..((((((((.((.(((((....))))).)).....(((((((((((..(..((((((.....))))))....)..))))))))))))))))..(....)))). ( -35.70) >DroVir_CAF1 1 104 + 1 ----------------AAGGCAGGAUACAAGAUCGGCUGUGAUCAUGGACCCGGAAGCGUUUUUGGAUGUGGCCAAUCAGGUCAUCAAGCUAAAAAUGUUUCCGUUCUUUGAUAUCGCGC ----------------..(((..(((.....))).)))(((((((.(((..(((((((((((((((..((((((.....))))))....))))))))))))))).))).)))..)))).. ( -37.90) >DroGri_CAF1 1 104 + 1 ----------------AAGGCAGGACACAAGAUCAGCUCUGAUCAUGGACCCGGAAGCAUUUUUGGAUGUGGCCAAUCAGGUCAUCAAGCUGAAAAUGUUUCCGUUCUUUGAUAUCGCGC ----------------...((.((...((.(((((....))))).))..))((((((((((((..(..((((((.....))))))....)..))))))))))))............)).. ( -36.70) >DroWil_CAF1 8441 120 + 1 AGAUUAUCCAUCCGUGAAAACAGGAUAUAAGAACAGCUGUGAUCAUGGAUCCGGAAGCAUUUUUGGAUGUGGCCAAUCAGGUCAUUAAGCUAAAAAUGUUUCCGUUUUUCGAUAUCGCGC .(((.(((.((((((((..((((.............))))..)))))))).(((((((((((((((..((((((.....))))))....)))))))))))))))......)))))).... ( -43.92) >DroMoj_CAF1 1 104 + 1 ----------------AAGACAGGAUACAAAAUCAGCUGUGAUCAUGGACCCGGAAGCGUUUUUGGAUGUGGCCAAUCAGGUCAUCAAGCUAAAAAUGUUUCCGUUCUUUGAUAUCGCGC ----------------.......(((.....))).((.(((((((.(((..(((((((((((((((..((((((.....))))))....))))))))))))))).))).)))..)))))) ( -34.80) >DroAna_CAF1 1 104 + 1 ----------------GAGGCGUAAUUAAAUAUCGGCUGCGAUCAUGGAUCCAGAGGCAUUUUUAGACGUGGCCAAUCAGGUCAUCAAACUGAAAAUGUUUCCGUUUUUUGACAUUGCUC ----------------..((((...(((((...((((((.((((...)))))))((((((((((((..((((((.....))))))....)))))))))))))))...)))))...)))). ( -30.60) >consensus ________________AAGGCAGGAUACAAGAUCAGCUGUGAUCAUGGACCCGGAAGCAUUUUUGGAUGUGGCCAAUCAGGUCAUCAAGCUAAAAAUGUUUCCGUUCUUUGAUAUCGCGC ...................................((.(((.(((.(((..(((((((((((((((..((((((.....))))))....))))))))))))))).))).)))))).)).. (-31.62 = -31.27 + -0.36)


| Location | 16,220,944 – 16,221,064 |
|---|---|
| Length | 120 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 92.17 |
| Mean single sequence MFE | -45.58 |
| Consensus MFE | -41.67 |
| Energy contribution | -41.53 |
| Covariance contribution | -0.14 |
| Combinations/Pair | 1.20 |
| Mean z-score | -2.56 |
| Structure conservation index | 0.91 |
| SVM decision value | 3.14 |
| SVM RNA-class probability | 0.998550 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>X_DroMel_CAF1 16220944 120 + 22224390 GAUCAUGGACCCGGAAGCAUUUUUGGACGUGGCCAACCAGGUCAUCAAGCUGAAAAUGUUUCCGUUCUUCGACAUCGCUCACAGUCUACUUGCCGCGCUGGCCGUGCGUGAGGACUUGGG (((..((((..((((((((((((..(..((((((.....))))))....)..))))))))))))...))))..))).((((.((((..((..(.((((.....)))))..)))))))))) ( -43.20) >DroVir_CAF1 25 120 + 1 GAUCAUGGACCCGGAAGCGUUUUUGGAUGUGGCCAAUCAGGUCAUCAAGCUAAAAAUGUUUCCGUUCUUUGAUAUCGCGCACAGUUUACUUGCCGCGCUGGCCGUGCGCGAGGAUUUAGG .((((.(((..(((((((((((((((..((((((.....))))))....))))))))))))))).))).)))).((((((((((....)).(((.....))).))))))))......... ( -49.30) >DroGri_CAF1 25 120 + 1 GAUCAUGGACCCGGAAGCAUUUUUGGAUGUGGCCAAUCAGGUCAUCAAGCUGAAAAUGUUUCCGUUCUUUGAUAUCGCGCACAGUUUACUUGCCGCGCUGGCCGUGCGCGAGGAUUUGGG .((((.(((..((((((((((((..(..((((((.....))))))....)..)))))))))))).))).)))).((((((((((....)).(((.....))).))))))))......... ( -49.20) >DroWil_CAF1 8481 120 + 1 GAUCAUGGAUCCGGAAGCAUUUUUGGAUGUGGCCAAUCAGGUCAUUAAGCUAAAAAUGUUUCCGUUUUUCGAUAUCGCGCACAGUUUACUUGCAGCGCUGGCCGUACGCGAGGAUUUGGG ......((((((((((((((((((((..((((((.....))))))....))))))))))))))...........(((((.((.((......)).((....)).)).)))))))))))... ( -42.60) >DroMoj_CAF1 25 120 + 1 GAUCAUGGACCCGGAAGCGUUUUUGGAUGUGGCCAAUCAGGUCAUCAAGCUAAAAAUGUUUCCGUUCUUUGAUAUCGCGCACAGUUUACUUGCCGCGCUGGCCGUGCGCGAGGAUUUGGG .((((.(((..(((((((((((((((..((((((.....))))))....))))))))))))))).))).)))).((((((((((....)).(((.....))).))))))))......... ( -49.30) >DroAna_CAF1 25 120 + 1 GAUCAUGGAUCCAGAGGCAUUUUUAGACGUGGCCAAUCAGGUCAUCAAACUGAAAAUGUUUCCGUUUUUUGACAUUGCUCACAGUCUCCUUGCCGCGCUGGCCGUGCGCGAGGACUUGGG ..(((.(((..(.(((((((((((((..((((((.....))))))....))))))))))))).)..)))))).....((((.((..(((((((.((((.....))))))))))))))))) ( -39.90) >consensus GAUCAUGGACCCGGAAGCAUUUUUGGAUGUGGCCAAUCAGGUCAUCAAGCUAAAAAUGUUUCCGUUCUUUGAUAUCGCGCACAGUUUACUUGCCGCGCUGGCCGUGCGCGAGGAUUUGGG .((((.(((..(((((((((((((((..((((((.....))))))....))))))))))))))).))).)))).((((((((.(((..(.......)..))).))))))))......... (-41.67 = -41.53 + -0.14)



| Location | 16,221,064 – 16,221,184 |
|---|---|
| Length | 120 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 83.67 |
| Mean single sequence MFE | -47.92 |
| Consensus MFE | -33.61 |
| Energy contribution | -34.72 |
| Covariance contribution | 1.11 |
| Combinations/Pair | 1.28 |
| Mean z-score | -1.86 |
| Structure conservation index | 0.70 |
| SVM decision value | 0.04 |
| SVM RNA-class probability | 0.554617 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>X_DroMel_CAF1 16221064 120 + 22224390 CGCCAAUGCCCAGGCGUUUUCGCGGAAGCAUCCGCUCGCCUGCUGGCUCUCCACCAUGCUGGUGAUCUUCGCCGGCGGUAUGGUGGCCAAUGGACUGCUGGGCGAACCGAUACUGGCUCC .((((.((((((((((.....(((((....))))).)))((..(((((..(((...((((((((.....))))))))...))).)))))..))....))))))).........))))... ( -51.70) >DroVir_CAF1 145 120 + 1 CGCCAACGCUCAGGCCUUCUCGAGGAAGCAUCCACUGGCCUGUUGGCUAUCCACAAUGCUGGUGAUAUUUGCGGGCGGCAUGGUGGCUAAUGGAUUACUGGGGGAGCCCAUAUUGGCUCC .(((........)))((((.....))))..((((.((..((((((((((.(((...((((.(..(...)..).))))...)))))))))))))..)).))))((((((......)))))) ( -43.10) >DroGri_CAF1 145 120 + 1 CGCCAACGCACAGGCCUUCUCCAGGAAACAUCCACUUGCCUGCUGGCUAUCCACAAUGCUGGUGAUAUUCGCUGGUGGCAUGGUUGCCAAUGGAUUACUCGGAGAGCCGAUAUUGGCCCC .(((((......(((..(((((.(((....)))....(((....))).(((((....((..(((.....)))..))((((....))))..))))).....))))))))....)))))... ( -42.80) >DroWil_CAF1 8601 120 + 1 CGCCAAUGCACAGGCAUUCUCCAGGAAACAUCCGCUUGCCUGUUGGCUAUCAACUAUGCUGGUAAUAUUUGCUGGCGGCAUGGUGGCCAAUGGAUUGCUUGGUGAACCAAUUUUGGCACC .(((((.(((((((((.......(((....)))...))))))((((((((((....(((..(((.....)))..)))...)))))))))).....)))((((....))))..)))))... ( -47.40) >DroMoj_CAF1 145 120 + 1 CGCCAAUGCUCAGGCCUUCUCGCGGAAACAUCCGCUGGCAUGUUGGCUAUCCACAAUGCUGGUAAUAUUUGCGGGCGGCAUGGUGGCCAACGGGUUGCUCGGGGAACCCAUCUUAGCACC ......((((.(((((.....(((((....))))).)))..((((((((.(((...((((.(((.....))).))))...)))))))))))(((((.(....).)))))..)).)))).. ( -49.20) >DroAna_CAF1 145 120 + 1 CGCGAACGCACAGGCAUUCUCACGGAAGCACCCGCUGGCCUGCUGGCUAUCAACAAUGCUGGUGAUCUUCGCCGGCGGCAUGGUGGCCAACGGUUUGCUGGGAGAGCCAAUUUUGGCUCC .((((((...(((((.......(((......)))...))))).(((((((((....((((((((.....))))))))...)))))))))...)))))).....((((((....)))))). ( -53.30) >consensus CGCCAACGCACAGGCCUUCUCGAGGAAACAUCCGCUGGCCUGCUGGCUAUCCACAAUGCUGGUGAUAUUCGCCGGCGGCAUGGUGGCCAAUGGAUUGCUGGGAGAACCAAUAUUGGCUCC .(((((....((((((.......(....).......)))))).((((((((.....((((((((.....))))))))....)))))))).........((((....))))..)))))... (-33.61 = -34.72 + 1.11)

Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 12:14:27 2006