
| Sequence ID | X_DroMel_CAF1 |
|---|---|
| Location | 16,131,070 – 16,131,199 |
| Length | 129 |
| Max. P | 0.701388 |

| Location | 16,131,070 – 16,131,168 |
|---|---|
| Length | 98 |
| Sequences | 5 |
| Columns | 100 |
| Reading direction | forward |
| Mean pairwise identity | 93.72 |
| Mean single sequence MFE | -28.90 |
| Consensus MFE | -21.36 |
| Energy contribution | -20.72 |
| Covariance contribution | -0.64 |
| Combinations/Pair | 1.21 |
| Mean z-score | -2.27 |
| Structure conservation index | 0.74 |
| SVM decision value | 0.35 |
| SVM RNA-class probability | 0.701388 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>X_DroMel_CAF1 16131070 98 + 22224390 CUAUUGGUAUAUAUGUGCGUGCGUAUGUAAUGCAGCGACACACAAAUAUGUGCAUACUAUAUAUUGCGCACCUUGUGGAACUGCAACUGUG--UGUGCUC ......((((.(((((((....)))))))))))(((.(((((((....((((((..........))))))((....)).........))))--)))))). ( -27.20) >DroSec_CAF1 4151 100 + 1 CUAUUGGUAUAUAUGUGCGUGCGUAUGUAAUGCAGCGACAUAUAUAUAUGUGCAUACUAUAUAUUGCGCACCUUGUGGAACUGCAACUGUGUGUGUGCUC ......((((((((((((((((((.....))))).)).)))))))))))..((((((.((((((((((..((....))...))))).))))))))))).. ( -33.50) >DroSim_CAF1 4166 98 + 1 CUAUUCGUAUAUAUGUGCGUGCGUAUGUAAUGCAGCGACAUAUAUAUAUGUGCAUACUAUAUAUUGCGCACCUUGUGGAACUGCAACUGUG--UGUGCUC .....(((((((((((((((((((.....))))).)).)))))))))))).((((((.(((..(((((..((....))...))))).))))--))))).. ( -31.30) >DroEre_CAF1 4205 98 + 1 CUAUUGGUAUAUAUGUGCGUGCGUAUGUAAUGCAGUGACAUACAUAUAUGUGCAUACUAUGUAUUGCGCACCUUGUCGAACUGCAACUGUG--UGCGCUC .....(((((((((((((..(..((((((.((......))))))))..)..))))).))))))))(((((((((((......))))..).)--))))).. ( -28.30) >DroYak_CAF1 4235 98 + 1 CUAUUGGUAUAUAUGUGAGUGCGUAUGUAAUGCAGCAAUAUACAUAUAUGUGCAUACUAUGUAUUGCGCACCUUGUCGAACUACAACUGUG--UGUGCUC ........(((((((((..(((((((...)))).)))...)))))))))(..(((((..((((...(((.....).))...))))...)))--))..).. ( -24.20) >consensus CUAUUGGUAUAUAUGUGCGUGCGUAUGUAAUGCAGCGACAUACAUAUAUGUGCAUACUAUAUAUUGCGCACCUUGUGGAACUGCAACUGUG__UGUGCUC ......(((((((((((.((((((.((.....))))).))).)))))))))))............(((((..((((......)))).......))))).. (-21.36 = -20.72 + -0.64)



| Location | 16,131,100 – 16,131,199 |
|---|---|
| Length | 99 |
| Sequences | 5 |
| Columns | 101 |
| Reading direction | reverse |
| Mean pairwise identity | 92.59 |
| Mean single sequence MFE | -26.28 |
| Consensus MFE | -18.44 |
| Energy contribution | -18.80 |
| Covariance contribution | 0.36 |
| Combinations/Pair | 1.14 |
| Mean z-score | -2.67 |
| Structure conservation index | 0.70 |
| SVM decision value | 0.20 |
| SVM RNA-class probability | 0.632210 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>X_DroMel_CAF1 16131100 99 - 22224390 UGUACAAUGUACAAUGAACAUACAUUUAUGUGAGCACA--CACAGUUGCAGUUCCACAAGGUGCGCAAUAUAUAGUAUGCACAUAUUUGUGUGUCGCUGCA (((((...)))))..((.((((((..((((((...((.--....(((((.((.((....)).))))))).....))...))))))..))))))))...... ( -26.30) >DroSec_CAF1 4181 101 - 1 UGUACAAUGUACAAUGUACAUACAUUUAUGUGAGCACACACACAGUUGCAGUUCCACAAGGUGCGCAAUAUAUAGUAUGCACAUAUAUAUAUGUCGCUGCA ((((((........)))))).((((.((((((.(((.((.....(((((.((.((....)).))))))).....)).))).))))))...))))....... ( -23.50) >DroSim_CAF1 4196 99 - 1 UGUACAAUGUACAAUGUACAUACAUUUAUGUGAGCACA--CACAGUUGCAGUUCCACAAGGUGCGCAAUAUAUAGUAUGCACAUAUAUAUAUGUCGCUGCA ((((((........)))))).((((.((((((.(((.(--(...(((((.((.((....)).))))))).....)).))).))))))...))))....... ( -22.70) >DroEre_CAF1 4235 99 - 1 UGUACAAUAUACGAUUCACAUACAUUUAUGUGAGCGCA--CACAGUUGCAGUUCGACAAGGUGCGCAAUACAUAGUAUGCACAUAUAUGUAUGUCACUGCA .................((((((((.((((((.(((((--(...((((.....))))...)))))).((((...)))).)))))).))))))))....... ( -29.70) >DroYak_CAF1 4265 99 - 1 UGUACAAUGUACAAUGCACAUACAUUUAUGUGAGCACA--CACAGUUGUAGUUCGACAAGGUGCGCAAUACAUAGUAUGCACAUAUAUGUAUAUUGCUGCA .(((((((((((((((..(((((...((((((.((.((--(...((((.....))))...))).))..)))))))))))..)))...))))))))).))). ( -29.20) >consensus UGUACAAUGUACAAUGCACAUACAUUUAUGUGAGCACA__CACAGUUGCAGUUCCACAAGGUGCGCAAUAUAUAGUAUGCACAUAUAUGUAUGUCGCUGCA (((((...)))))....((((((((.((((((...((.......(((((.((.(......).))))))).....))...)))))).))))))))....... (-18.44 = -18.80 + 0.36)

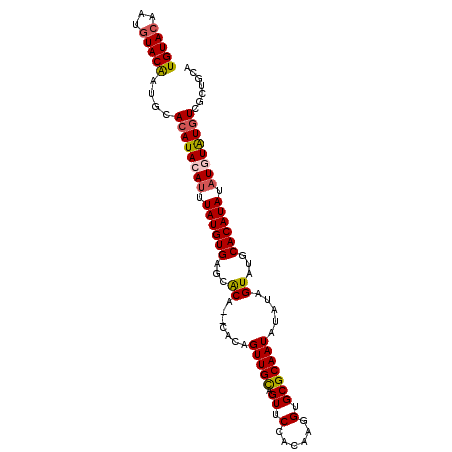

Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 12:13:39 2006