
| Sequence ID | X_DroMel_CAF1 |
|---|---|
| Location | 15,741,258 – 15,741,394 |
| Length | 136 |
| Max. P | 0.999301 |

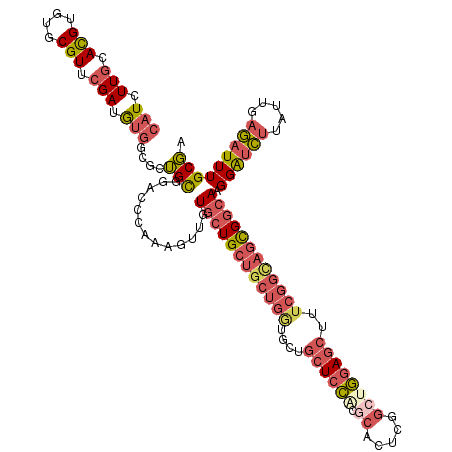
| Location | 15,741,258 – 15,741,378 |
|---|---|
| Length | 120 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 79.17 |
| Mean single sequence MFE | -45.17 |
| Consensus MFE | -29.93 |
| Energy contribution | -31.55 |
| Covariance contribution | 1.62 |
| Combinations/Pair | 1.29 |
| Mean z-score | -1.31 |
| Structure conservation index | 0.66 |
| SVM decision value | 0.13 |
| SVM RNA-class probability | 0.597999 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>X_DroMel_CAF1 15741258 120 + 22224390 CAUCUUGCACGUGUGCGUCCGAUGUGGCGCUGCGGACCCAAAGUUGUGCUGCUGCUGGUGUUGCUCCACGCACUCGGCAGGAGCUUUCGGUAGCGGCAAGGGUCUAAUUGAGAUUUGCGA ....(((((((((.(((((......)))))))))(((((.......((((((((((((....(((((..((.....)).)))))..)))))))))))).)))))...........))))) ( -49.70) >DroSec_CAF1 53 120 + 1 CAUCUUGCACGUGUGCGUUCGAUGUGGCGCUGCGGACCCAAAGUUGUGCUGCUGCUGGUGCUGCUCCACGCACUCGGCUGGAGCUUUCGGCAGCGGCAAGGGUCUUAUUGAGAUUUGCGA ....(((((((((.(((((......)))))))))(((((.......((((((((((((....((((((.((.....))))))))..)))))))))))).)))))...........))))) ( -52.50) >DroSim_CAF1 50 120 + 1 CAUCUUGCACGUGUGCGUUCGAUGUGGCGCUGCGGACCCAAAGUUGUGCUGCUGCUGGUGCUGCUCCACGCACUCGGCUGGAGCUUUCGGCAGCGGCAAGGGUCUUAUUGAGAUUUGCGA ....(((((((((.(((((......)))))))))(((((.......((((((((((((....((((((.((.....))))))))..)))))))))))).)))))...........))))) ( -52.50) >DroEre_CAF1 49 120 + 1 CAUCUUGCACGUAUGCGUUCGAUGUGGCGCUGCCGACCCAAAGUUGUGCUGCUGCUGAUGCUGCUCCGCGCAGUCGGCUGGAGCCUUCGGCAGCGGCAUGGAUCUUAUUGAGAUUUGCGA .........((((....(((((((((((...))))........(..((((((((((((....((((((.((.....))))))))..))))))))))))..)....)))))))...)))). ( -47.60) >DroYak_CAF1 44 120 + 1 CAUCUUGCACGUAUGCGUUCGAUGUGGUGCUGCGGACCCAAAGUUGUGCUGCUGCUGGUGCUGCUCCGCACAGUCGGCUGGAGCUUUCGGCAGUGGCAAGGAUCUUAUUGAGAUUUGCGA .........((((....(((((((.(((.((...(((.....))).(((..(((((((....(((((((.......)).)))))..)))))))..))))).))).)))))))...)))). ( -42.70) >DroPer_CAF1 5511 105 + 1 AAUCUUAAAUGUUUGCGUCCGAUAGGGUAGGGUAGCCUUAAAGCAAUUUUGA------------UCAGC---GUUGGCGUCAGCAGUAGUAAAUGUUAAGGAGGGUAUUGGCAUUUGCCU .........((((.(((.((((((((((......)))))...((........------------...))---)))))))).))))...(((((((((((........))))))))))).. ( -26.00) >consensus CAUCUUGCACGUGUGCGUUCGAUGUGGCGCUGCGGACCCAAAGUUGUGCUGCUGCUGGUGCUGCUCCACGCACUCGGCUGGAGCUUUCGGCAGCGGCAAGGAUCUUAUUGAGAUUUGCGA (((.(((.(((....))).))).)))....(((.............((((((((((((....((((((.((.....))))))))..)))))))))))).((((((.....))))))))). (-29.93 = -31.55 + 1.62)


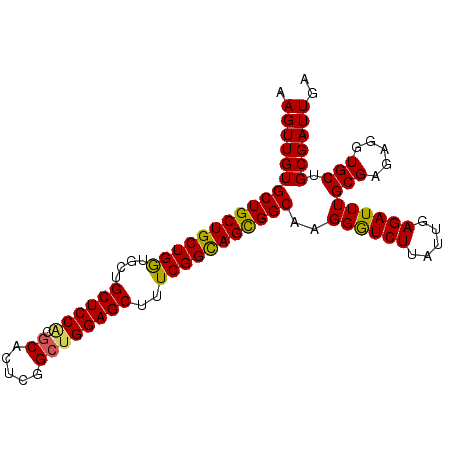
| Location | 15,741,298 – 15,741,394 |
|---|---|
| Length | 96 |
| Sequences | 5 |
| Columns | 96 |
| Reading direction | forward |
| Mean pairwise identity | 93.33 |
| Mean single sequence MFE | -38.30 |
| Consensus MFE | -36.68 |
| Energy contribution | -36.20 |
| Covariance contribution | -0.48 |
| Combinations/Pair | 1.15 |
| Mean z-score | -2.00 |
| Structure conservation index | 0.96 |
| SVM decision value | 3.50 |
| SVM RNA-class probability | 0.999301 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>X_DroMel_CAF1 15741298 96 + 22224390 AAGUUGUGCUGCUGCUGGUGUUGCUCCACGCACUCGGCAGGAGCUUUCGGUAGCGGCAAGGGUCUAAUUGAGAUUUGCGAGAGAUGCUGCGAUUGA .(((((((((((((((((....(((((..((.....)).)))))..))))))))))).((.((((..(((.......))).)))).)))))))).. ( -36.40) >DroSec_CAF1 93 96 + 1 AAGUUGUGCUGCUGCUGGUGCUGCUCCACGCACUCGGCUGGAGCUUUCGGCAGCGGCAAGGGUCUUAUUGAGAUUUGCGAGAGGUGCUGCGAUUGA .(((((((((((((((((....((((((.((.....))))))))..)))))))))))..(((((((...)))))))(((.....))).)))))).. ( -39.40) >DroSim_CAF1 90 96 + 1 AAGUUGUGCUGCUGCUGGUGCUGCUCCACGCACUCGGCUGGAGCUUUCGGCAGCGGCAAGGGUCUUAUUGAGAUUUGCGAGAGGUGCUGCGAUUGA .(((((((((((((((((....((((((.((.....))))))))..)))))))))))..(((((((...)))))))(((.....))).)))))).. ( -39.40) >DroEre_CAF1 89 96 + 1 AAGUUGUGCUGCUGCUGAUGCUGCUCCGCGCAGUCGGCUGGAGCCUUCGGCAGCGGCAUGGAUCUUAUUGAGAUUUGCGAGAGGUGCUGCGAUUGG .(((((((((((((((((....((((((.((.....))))))))..)))))))))))..(.(((((.(((.......)))))))).).)))))).. ( -39.50) >DroYak_CAF1 84 96 + 1 AAGUUGUGCUGCUGCUGGUGCUGCUCCGCACAGUCGGCUGGAGCUUUCGGCAGUGGCAAGGAUCUUAUUGAGAUUUGCGAGAGGUGCUGCGAUUGG .((((((((..(((((((....(((((((.......)).)))))..)))))))..)).((.(((((.(((.......)))))))).)))))))).. ( -36.80) >consensus AAGUUGUGCUGCUGCUGGUGCUGCUCCACGCACUCGGCUGGAGCUUUCGGCAGCGGCAAGGGUCUUAUUGAGAUUUGCGAGAGGUGCUGCGAUUGA .(((((((((((((((((....((((((.((.....))))))))..)))))))))))..((((((.....))))))(((.....))).)))))).. (-36.68 = -36.20 + -0.48)

Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 12:06:14 2006