
| Sequence ID | X_DroMel_CAF1 |
|---|---|
| Location | 10,640,961 – 10,641,063 |
| Length | 102 |
| Max. P | 0.994258 |

| Location | 10,640,961 – 10,641,063 |
|---|---|
| Length | 102 |
| Sequences | 5 |
| Columns | 102 |
| Reading direction | forward |
| Mean pairwise identity | 93.99 |
| Mean single sequence MFE | -23.08 |
| Consensus MFE | -20.10 |
| Energy contribution | -20.14 |
| Covariance contribution | 0.04 |
| Combinations/Pair | 1.05 |
| Mean z-score | -2.07 |
| Structure conservation index | 0.87 |
| SVM decision value | 2.46 |
| SVM RNA-class probability | 0.994258 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
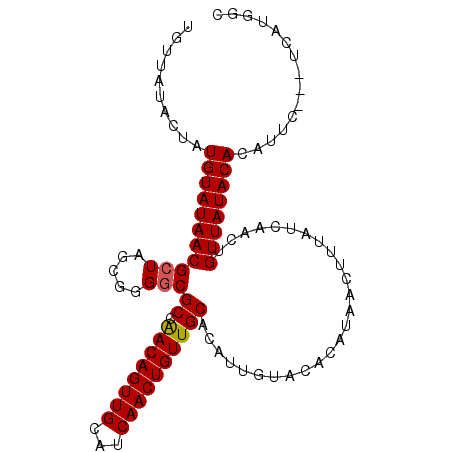
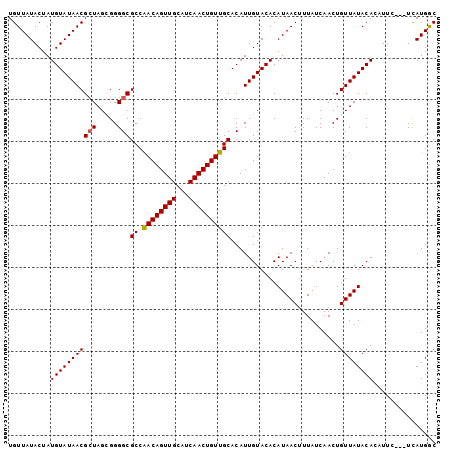
>X_DroMel_CAF1 10640961 102 + 22224390 UGUUAUACUAUGUAUAACGAUAGCGGGGCGCCAACAGUUGCAUCAACUGUUGCACAUUGUACACAUAACAUUAUCAACUGUUAUACACAUUCUUCUUAUGGC .(((((((...))))))).(((((((.(.((.((((((((...)))))))))).)..(((.......))).......))))))).................. ( -21.60) >DroSec_CAF1 22418 99 + 1 UGUUAUACUAUGUAUAACGCUAGCGGGGCGCCAACAGUUGCAUCAACUGUUGCACAUUGUACACAUAACUUUAUCAACUGUUAUACACAUUA---UCAUGGC .(((((((...)))))))((((((((.(.((.((((((((...)))))))))).).))))....(((((..........)))))........---...)))) ( -22.00) >DroSim_CAF1 21110 99 + 1 UGUUAUACUAUGUAUAACGCUAGCGGGGCGCCGACAGUUGCAUCAACUGUUGCACAUUGUACACAUAACUUUAUCAACUGUUAUACACAUUC---UCAUGGC .(((((((...)))))))((((..((((.((.((((((((...))))))))))...........(((((..........)))))......))---)).)))) ( -22.80) >DroEre_CAF1 23292 96 + 1 UGUUAUACUAUGUAUAACGCUAG-GGGGCGCCAACAGUUGCAUCAACUGUUGCACAUUGUACACAUAACUUUAUCAACUGUUAUACA--UUU---UCAUGAC .(((((...((((((((((((..-..)))((.((((((((...))))))))))..........................))))))))--)..---..))))) ( -24.50) >DroYak_CAF1 22957 96 + 1 UGUUAUACUAUGUAUAACGCUAG-GGGGCGCCAACAGUUGCAUCAACUGUUGCACAUUGUACACAUAACUUUAUCAACUGUUAUACA--UUU---UCAUGAC .(((((...((((((((((((..-..)))((.((((((((...))))))))))..........................))))))))--)..---..))))) ( -24.50) >consensus UGUUAUACUAUGUAUAACGCUAGCGGGGCGCCAACAGUUGCAUCAACUGUUGCACAUUGUACACAUAACUUUAUCAACUGUUAUACACAUUC___UCAUGGC ..........(((((((((((.....)))((.((((((((...))))))))))..........................))))))))............... (-20.10 = -20.14 + 0.04)

| Location | 10,640,961 – 10,641,063 |
|---|---|
| Length | 102 |
| Sequences | 5 |
| Columns | 102 |
| Reading direction | reverse |
| Mean pairwise identity | 93.99 |
| Mean single sequence MFE | -26.04 |
| Consensus MFE | -22.30 |
| Energy contribution | -23.30 |
| Covariance contribution | 1.00 |
| Combinations/Pair | 1.00 |
| Mean z-score | -2.13 |
| Structure conservation index | 0.86 |
| SVM decision value | 2.34 |
| SVM RNA-class probability | 0.992674 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
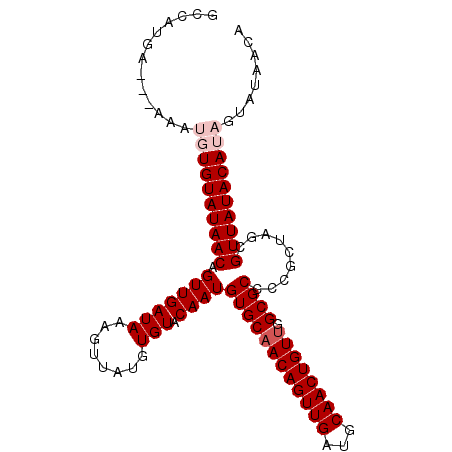
>X_DroMel_CAF1 10640961 102 - 22224390 GCCAUAAGAAGAAUGUGUAUAACAGUUGAUAAUGUUAUGUGUACAAUGUGCAACAGUUGAUGCAACUGUUGGCGCCCCGCUAUCGUUAUACAUAGUAUAACA ((...........((..(((((((........)))))))..))....((((((((((((...)))))))).))))...))....(((((((...))))))). ( -27.10) >DroSec_CAF1 22418 99 - 1 GCCAUGA---UAAUGUGUAUAACAGUUGAUAAAGUUAUGUGUACAAUGUGCAACAGUUGAUGCAACUGUUGGCGCCCCGCUAGCGUUAUACAUAGUAUAACA ......(---((.(((((((((((((((.........(((((((...)))).))).......)))))(((((((...))))))))))))))))).))).... ( -28.09) >DroSim_CAF1 21110 99 - 1 GCCAUGA---GAAUGUGUAUAACAGUUGAUAAAGUUAUGUGUACAAUGUGCAACAGUUGAUGCAACUGUCGGCGCCCCGCUAGCGUUAUACAUAGUAUAACA .......---...(((((((((((((((.........(((((((...)))).))).......)))))((..(((...)))..))))))))))))........ ( -24.79) >DroEre_CAF1 23292 96 - 1 GUCAUGA---AAA--UGUAUAACAGUUGAUAAAGUUAUGUGUACAAUGUGCAACAGUUGAUGCAACUGUUGGCGCCCC-CUAGCGUUAUACAUAGUAUAACA ((.(((.---..(--((((((((.(((((((........))).))))((((((((((((...)))))))).))))...-.....)))))))))..))).)). ( -25.10) >DroYak_CAF1 22957 96 - 1 GUCAUGA---AAA--UGUAUAACAGUUGAUAAAGUUAUGUGUACAAUGUGCAACAGUUGAUGCAACUGUUGGCGCCCC-CUAGCGUUAUACAUAGUAUAACA ((.(((.---..(--((((((((.(((((((........))).))))((((((((((((...)))))))).))))...-.....)))))))))..))).)). ( -25.10) >consensus GCCAUGA___AAAUGUGUAUAACAGUUGAUAAAGUUAUGUGUACAAUGUGCAACAGUUGAUGCAACUGUUGGCGCCCCGCUAGCGUUAUACAUAGUAUAACA .............((((((((((.(((((((........))).))))((((((((((((...)))))))).)))).........))))))))))........ (-22.30 = -23.30 + 1.00)


Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 11:14:30 2006