
| Sequence ID | X_DroMel_CAF1 |
|---|---|
| Location | 6,617,033 – 6,617,153 |
| Length | 120 |
| Max. P | 0.739560 |

| Location | 6,617,033 – 6,617,153 |
|---|---|
| Length | 120 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 78.39 |
| Mean single sequence MFE | -46.90 |
| Consensus MFE | -29.53 |
| Energy contribution | -30.62 |
| Covariance contribution | 1.09 |
| Combinations/Pair | 1.41 |
| Mean z-score | -1.59 |
| Structure conservation index | 0.63 |
| SVM decision value | 0.45 |
| SVM RNA-class probability | 0.739560 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
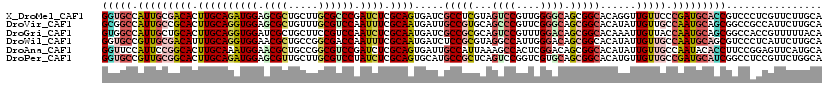
>X_DroMel_CAF1 6617033 120 + 22224390 GGUGCCAUUGCGACACUUGCAGAUGGAGCGCUGCUUGCGCCCGAUCUCGCAGUGAUCGCCUCGUAGUCCGUUGGGGCAGCGGCACAGGUUGUUCCCGAUGCACCGUCCCUCGUUCUUGCA (((((....((((((((.((((((((.((((.....)))))).)))).)))))).))))..........(((((((((((.......)))).))))))))))))................ ( -47.30) >DroVir_CAF1 76 120 + 1 GCGGCCAUUGCCGCACUUGCAGGUGGAGCGCUGUUUGCGUCCAAUUUCGCAAUGAUUGCCGUGCAGCCCGUUCGGGCAGCGGCACAUAUUGUUGCCAAUGCAGCGGCCGCCAUUCUUGCA ((((((..((((((...((((.(((((.(((.....))))))).....(((.....)))).))))((((....)))).))))))......(((((....))))))))))).......... ( -55.50) >DroGri_CAF1 61 120 + 1 GUGGCCAUUGCUGCACUUGCAGGUGGAUCGCUGCUUCCGUCCAAUCUCGCAAUGAUCGCCGCGCAGUCCGUUUGGACAGCGGCACAAAUUGUUACCAAUGCAGCGGCCACCGUUUUUACA ((((((...((((((.(((..((((((........)))).))......(((((....(((((...((((....)))).)))))....)))))...))))))))))))))).......... ( -46.80) >DroWil_CAF1 70 120 + 1 GGUGCCGUUGCGACAUUUGCAGGUGGAACGCUGCCGGCGACCAAUUUCGCAAUGAUCUCCGCGUAGGCCAUUGGGACAGCGGCACAUAUUGUUGCCAAUGCAGCGUCCCUCAUUCUUGCA .(((((((((......((((.((..(....)..)).))))......((.(((((..((......))..))))).))))))))))).....(((((....)))))................ ( -40.20) >DroAna_CAF1 6138 120 + 1 GGUUCCAUUCCGGCACUUGCAAAUGGAACGCUGCCGGCGUCCGAUCUCGCAGUGAUUGCCAUUAAAGCCACUCGGACAGCGGCACAUAUUGUUGCCAAUACACCUUCCGGAGUUCAUGCA .((((((((...((....)).))))))))(((.((((.((((((....((..((((....))))..))...)))))).((((((.....))))))...........)))))))....... ( -37.20) >DroPer_CAF1 26173 120 + 1 GGUGCCGUUGCGGCACUUGCAGAUGGAGCGUUGCUUGCGUCCUAUCUCGCAGUGCAUGCCGCUCAGUCCGGUCGUGCAGCGGCACAUGUUGUUGCCGAUGCAUCGGCCUCCGUUCUGGCA ..(((((..((((((((.((((((((..(((.....)))..)))))).)))))))..............(((((((((.(((((........))))).)))).)))))..)))..))))) ( -54.40) >consensus GGUGCCAUUGCGGCACUUGCAGAUGGAGCGCUGCUUGCGUCCAAUCUCGCAAUGAUCGCCGCGCAGUCCGUUCGGACAGCGGCACAUAUUGUUGCCAAUGCAGCGGCCCCCGUUCUUGCA (((((.(((((((((.((((((((((.((((.....)))))).)))).)))).....(((((...((((....)))).)))))......))))).)))))))))................ (-29.53 = -30.62 + 1.09)

| Location | 6,617,033 – 6,617,153 |
|---|---|
| Length | 120 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 78.39 |
| Mean single sequence MFE | -48.38 |
| Consensus MFE | -20.13 |
| Energy contribution | -20.30 |
| Covariance contribution | 0.17 |
| Combinations/Pair | 1.38 |
| Mean z-score | -2.25 |
| Structure conservation index | 0.42 |
| SVM decision value | -0.02 |
| SVM RNA-class probability | 0.522687 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
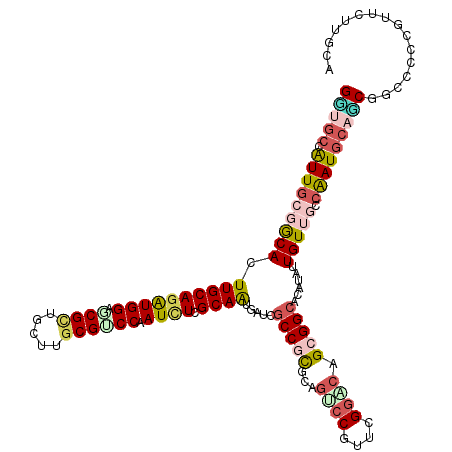
>X_DroMel_CAF1 6617033 120 - 22224390 UGCAAGAACGAGGGACGGUGCAUCGGGAACAACCUGUGCCGCUGCCCCAACGGACUACGAGGCGAUCACUGCGAGAUCGGGCGCAAGCAGCGCUCCAUCUGCAAGUGUCGCAAUGGCACC (((.((..((.(((.(((((((.((((.....)))))).))))).)))..))..)).((..((((.((((((.((((.((((((.....)))))).)))))).))))))))..))))).. ( -50.00) >DroVir_CAF1 76 120 - 1 UGCAAGAAUGGCGGCCGCUGCAUUGGCAACAAUAUGUGCCGCUGCCCGAACGGGCUGCACGGCAAUCAUUGCGAAAUUGGACGCAAACAGCGCUCCACCUGCAAGUGCGGCAAUGGCCGC ..........((((((((((((((.(((.((((...((((((.((((....)))).))..))))...))))......(((((((.....))).))))..))).))))))))...)))))) ( -53.40) >DroGri_CAF1 61 120 - 1 UGUAAAAACGGUGGCCGCUGCAUUGGUAACAAUUUGUGCCGCUGUCCAAACGGACUGCGCGGCGAUCAUUGCGAGAUUGGACGGAAGCAGCGAUCCACCUGCAAGUGCAGCAAUGGCCAC ..........((((((((((((((.(((.((((...((((((.((((....))))...))))))...)))).(.(((((..(....)...))))))...))).))))))))...)))))) ( -47.80) >DroWil_CAF1 70 120 - 1 UGCAAGAAUGAGGGACGCUGCAUUGGCAACAAUAUGUGCCGCUGUCCCAAUGGCCUACGCGGAGAUCAUUGCGAAAUUGGUCGCCGGCAGCGUUCCACCUGCAAAUGUCGCAACGGCACC (((........((((((((((((((....))))..((((((...((.(((((..((......))..))))).))...))).)))..))))))))))...(((.......)))...))).. ( -42.40) >DroAna_CAF1 6138 120 - 1 UGCAUGAACUCCGGAAGGUGUAUUGGCAACAAUAUGUGCCGCUGUCCGAGUGGCUUUAAUGGCAAUCACUGCGAGAUCGGACGCCGGCAGCGUUCCAUUUGCAAGUGCCGGAAUGGAACC .((.......((....)).((((((....)))))).(((((.(((((((....(((.....(((.....)))))).))))))).)))))))(((((((((((....))..))))))))). ( -45.90) >DroPer_CAF1 26173 120 - 1 UGCCAGAACGGAGGCCGAUGCAUCGGCAACAACAUGUGCCGCUGCACGACCGGACUGAGCGGCAUGCACUGCGAGAUAGGACGCAAGCAACGCUCCAUCUGCAAGUGCCGCAACGGCACC ((((....(((.((.((.((((.(((((........))))).)))))).))...))).(((((((....(((.((((.(((.((.......)))))))))))).)))))))...)))).. ( -50.80) >consensus UGCAAGAACGGCGGACGCUGCAUUGGCAACAAUAUGUGCCGCUGCCCGAACGGACUGCGCGGCAAUCACUGCGAGAUUGGACGCAAGCAGCGCUCCACCUGCAAGUGCCGCAAUGGCACC .((........(((.....(((.(((((........))))).))))))..........((((((.....((((.....((((((.....))).)))...))))..))))))....))... (-20.13 = -20.30 + 0.17)


Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 10:36:07 2006