
| Sequence ID | 3R_DroMel_CAF1 |
|---|---|
| Location | 13,636,325 – 13,636,445 |
| Length | 120 |
| Max. P | 0.790186 |

| Location | 13,636,325 – 13,636,445 |
|---|---|
| Length | 120 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 76.83 |
| Mean single sequence MFE | -41.77 |
| Consensus MFE | -22.70 |
| Energy contribution | -24.04 |
| Covariance contribution | 1.34 |
| Combinations/Pair | 1.53 |
| Mean z-score | -1.64 |
| Structure conservation index | 0.54 |
| SVM decision value | 0.04 |
| SVM RNA-class probability | 0.554412 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
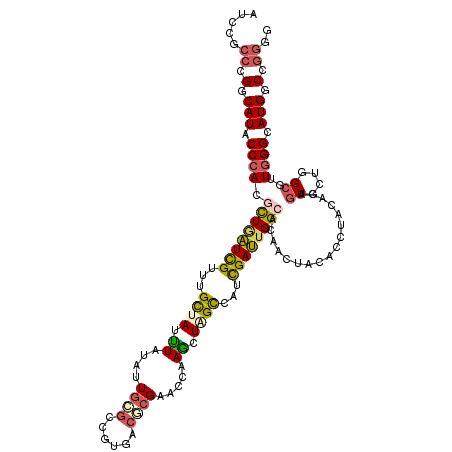
>3R_DroMel_CAF1 13636325 120 + 27905053 CCUUCGACAUUCCCAAUGCCAGCACUGUGUACGUGUAGUUGUGCCAAUCGAUGGCCAGCUUGGUUCGUGUGACCGCACAGUACAGAUAGCACACAAUCAGCGUGGGAAUGCCGGGCGGAU ((((((.((((((((.(((..(.(((((((......(((((.((((.....))))))))).((((.....))))))))))).).(((........))).))))))))))).)))).)).. ( -43.90) >DroVir_CAF1 3042 120 + 1 CGCCGGCCAUACCCAGCGCCAGCACCGUGUAGGUGUAGUUGUGCCAGUCGAUGACUAGCUUGGUGCGCGUCAAGGCGCAAUAAAAAUAGCAGACGACCAGUGUGGGUAUGCCGGGUGGAU ..(((((.((((((((((((((((((.....)))))......((.((((...)))).)).))))))((((....))))........................))))))))))))...... ( -50.00) >DroGri_CAF1 2725 120 + 1 CACCGGCCAUGCCCAUCGCCAGAACCGUAUAGCUGUAGUUGUGCCAAUCGAUGGCGAGCUUGGUGCGCGUUACUGCGCAAUACAAAUAGCACACGAUGAGCGUGGGAAUGCCGGGCGGAU ..(((((....((((.(((((....(((...(((((.(((.(((((.....))))))))(((.((((((....))))))...))))))))..))).)).)))))))...)))))...... ( -46.10) >DroWil_CAF1 2093 120 + 1 CCCCCGCCAUGCCGAGGGCCAGCACUGUAAACGUAUAAUUGUGCCAAUCAAUGACCAAUUUGCAUCUGGUCACGGCACAAUAUAAAUAGCAAACAAUCAAAGUGGGUAUGCCCGGAGGAU ...((.((.(((((..((((((...((((((......((((.......))))......)))))).)))))).)))))..........................(((....))))).)).. ( -33.00) >DroMoj_CAF1 2704 120 + 1 CUCCGGCCAUGCCCAACGCCAAGAUAGUGUAGGUGUAAUUAUGCCAAUCGAUGGCUAGCUUAGUUCGCGUCAAGGCGCAGUAUAAAUAGCAAACAAUCAACGUGGGUAUGCCGGGGGGGU (((((((.(((((((..((((.(((.((((((......))))))..)))..))))..(((.....(((((....)))).).......)))............)))))))))))))).... ( -42.30) >DroAna_CAF1 1224 120 + 1 CCCCGGACAUUCCCAAUGCCAAAACAGUGUAGGUGUAGUUGUGCCAAUCAAUAACAAACUUGGUUCGUGUCAGAGUGCAAUAGAGGUAACAAACGAUUAGCGUGGGAAUGCCCGGCGGAU ((((((.((((((((.(((..........(((((...(((((........)))))..)))))..((((.......(((.......)))....))))...))))))))))).)))).)).. ( -35.30) >consensus CCCCGGCCAUGCCCAACGCCAGCACAGUGUAGGUGUAGUUGUGCCAAUCGAUGACCAGCUUGGUUCGCGUCACGGCGCAAUACAAAUAGCAAACAAUCAGCGUGGGAAUGCCGGGCGGAU .(((((.((((((((.(((........(((...((((.((((((....((...(((.....)))...)).....))))))))))....)))........))))))))))))))))..... (-22.70 = -24.04 + 1.34)



| Location | 13,636,325 – 13,636,445 |
|---|---|
| Length | 120 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 76.83 |
| Mean single sequence MFE | -42.63 |
| Consensus MFE | -17.87 |
| Energy contribution | -17.93 |
| Covariance contribution | 0.06 |
| Combinations/Pair | 1.37 |
| Mean z-score | -2.31 |
| Structure conservation index | 0.42 |
| SVM decision value | 0.58 |
| SVM RNA-class probability | 0.790186 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>3R_DroMel_CAF1 13636325 120 - 27905053 AUCCGCCCGGCAUUCCCACGCUGAUUGUGUGCUAUCUGUACUGUGCGGUCACACGAACCAAGCUGGCCAUCGAUUGGCACAACUACACGUACACAGUGCUGGCAUUGGGAAUGUCGAAGG ..((...((((((((((((((.....))))((((...((((((((.((((....).))).((.((((((.....)))).)).)).......))))))))))))...))))))))))..)) ( -46.20) >DroVir_CAF1 3042 120 - 1 AUCCACCCGGCAUACCCACACUGGUCGUCUGCUAUUUUUAUUGCGCCUUGACGCGCACCAAGCUAGUCAUCGACUGGCACAACUACACCUACACGGUGCUGGCGCUGGGUAUGGCCGGCG ......((((((((((((.....((((..(((..........)))...))))((((.....(((((((...)))))))....(..((((.....))))..)))))))))))).))))).. ( -47.30) >DroGri_CAF1 2725 120 - 1 AUCCGCCCGGCAUUCCCACGCUCAUCGUGUGCUAUUUGUAUUGCGCAGUAACGCGCACCAAGCUCGCCAUCGAUUGGCACAACUACAGCUAUACGGUUCUGGCGAUGGGCAUGGCCGGUG ......(((((...((((((((.((((((((((..((((..(((((......)))))........((((.....))))))))....))).)))))))...)))).))))....))))).. ( -46.90) >DroWil_CAF1 2093 120 - 1 AUCCUCCGGGCAUACCCACUUUGAUUGUUUGCUAUUUAUAUUGUGCCGUGACCAGAUGCAAAUUGGUCAUUGAUUGGCACAAUUAUACGUUUACAGUGCUGGCCCUCGGCAUGGCGGGGG ..((((((((....)))......(((((..(((((....((((((((((((((((.......)))))))).....)))))))).))).))..)))))(((((((...))).))))))))) ( -41.90) >DroMoj_CAF1 2704 120 - 1 ACCCCCCCGGCAUACCCACGUUGAUUGUUUGCUAUUUAUACUGCGCCUUGACGCGAACUAAGCUAGCCAUCGAUUGGCAUAAUUACACCUACACUAUCUUGGCGUUGGGCAUGGCCGGAG ......(((((...((((.((..((((...((((((((...((((......))))...)))).))))...))))..))......((.((...........)).))))))....))))).. ( -34.20) >DroAna_CAF1 1224 120 - 1 AUCCGCCGGGCAUUCCCACGCUAAUCGUUUGUUACCUCUAUUGCACUCUGACACGAACCAAGUUUGUUAUUGAUUGGCACAACUACACCUACACUGUUUUGGCAUUGGGAAUGUCCGGGG ..((.(((((((((((((.(((((((((((((..........)))....)))((((((...))))))....))))))).(((..(((.......))).)))....))))))))))))))) ( -39.30) >consensus AUCCGCCCGGCAUACCCACGCUGAUCGUUUGCUAUUUAUAUUGCGCCGUGACGCGAACCAAGCUAGCCAUCGAUUGGCACAACUACACCUACACAGUGCUGGCGUUGGGCAUGGCCGGGG .....((.(.(((.((((.((((((((...((((.((....((((......)))).....)).))))...)))))))).................((....))..)))).))).).)).. (-17.87 = -17.93 + 0.06)


Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 11:49:03 2006