
| Sequence ID | 3R_DroMel_CAF1 |
|---|---|
| Location | 8,587,272 – 8,587,448 |
| Length | 176 |
| Max. P | 0.992772 |

| Location | 8,587,272 – 8,587,390 |
|---|---|
| Length | 118 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 96.57 |
| Mean single sequence MFE | -26.13 |
| Consensus MFE | -24.75 |
| Energy contribution | -24.70 |
| Covariance contribution | -0.05 |
| Combinations/Pair | 1.06 |
| Mean z-score | -1.24 |
| Structure conservation index | 0.95 |
| SVM decision value | 1.29 |
| SVM RNA-class probability | 0.938439 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
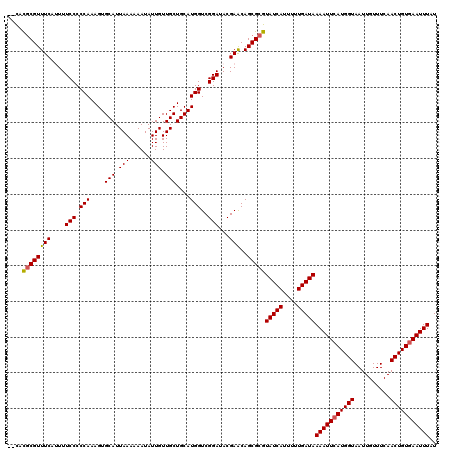
>3R_DroMel_CAF1 8587272 118 + 27905053 --CUUGCGUUUCAUUUUCCCCCAAAGUGCAUUAAAAAAUAUUGUUGCUGCAUGGUCGGAUACGAACAGCGCGUAUCAUUUUUGAUAAAAUUCAUGGUAAUUGUUUCAACUGUGAAUUUAU --...(((((((....(((.(((....(((.(((......))).)))....)))..)))...)))..)))).(((((....)))))(((((((((((..........))))))))))).. ( -25.40) >DroVir_CAF1 20452 118 + 1 --CACGCGUUUCAGUUUCCCCCAAAGUGCAUUAAAAAAUAUUGUUGCUGCAUGGUCGGAUACGAACAGCGCGUAUCAUUUUUGAUAAAAUUCAUGGUAAUUGUUUCAACUGUGAAUUUAU --.(((((((...((.(((.(((....(((.(((......))).)))....)))..))).))....)))))))((((....)))).(((((((((((..........))))))))))).. ( -29.60) >DroGri_CAF1 15352 118 + 1 --CACGCGUUUCAGUUUCCCCCAAAGUGCAUUAAAAAAUAUUGUUGCUGCAUGGUCGGAUACGAGCAGCGCGUAUCAUUUUUGAUAAAAUUCAUGGUAAUUGUUUCAACUGUGAAUUUAU --.(((((((.(.((.(((.(((....(((.(((......))).)))....)))..))).))..).)))))))((((....)))).(((((((((((..........))))))))))).. ( -29.80) >DroWil_CAF1 38686 118 + 1 --UUUGCGUUUCAUUUUCCCCCAAAGUGCAUUAAAAAAUAUUGUUGCUGCAUGGUCGGAUACGAACAGCGCGUAUCAUUUUUGAUAAAAUUCAUGGUAAUUGUUUCAACUGUAAAUUUAU --...(((((((....(((.(((....(((.(((......))).)))....)))..)))...)))..)))).(((((....)))))(((((.(((((..........))))).))))).. ( -19.20) >DroMoj_CAF1 40506 118 + 1 --CACGCGUUUCAUUUUCCCCCAAAGUGCAUUAAAAAAUAUUGUUGCUGCAUGGUCGGAUACGAACAGCGCGUAUCAUUUUUGAUAAAAUUCAUGGUAAUUGUUUCAACUGUGAAUUUAU --.(((((((((....(((.(((....(((.(((......))).)))....)))..)))...)))..))))))((((....)))).(((((((((((..........))))))))))).. ( -27.40) >DroAna_CAF1 13661 120 + 1 CUCUUUCGUUUCGUUUUCCCCCAAAGUGCAUUAAAAAAUAUUGUUGCUGCAUGGUCGGAUACGAACAGCGCGUAUCAUUUUUGAUAAAAUUCAUGGUAAUUGUUUCAACUGUGAAUUUAU ......((((((((..(((.(((....(((.(((......))).)))....)))..))).)))))..)))..(((((....)))))(((((((((((..........))))))))))).. ( -25.40) >consensus __CACGCGUUUCAUUUUCCCCCAAAGUGCAUUAAAAAAUAUUGUUGCUGCAUGGUCGGAUACGAACAGCGCGUAUCAUUUUUGAUAAAAUUCAUGGUAAUUGUUUCAACUGUGAAUUUAU ....((((((((....(((.(((....(((.(((......))).)))....)))..)))...)))..)))))(((((....)))))(((((((((((..........))))))))))).. (-24.75 = -24.70 + -0.05)


| Location | 8,587,310 – 8,587,425 |
|---|---|
| Length | 115 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 94.85 |
| Mean single sequence MFE | -29.25 |
| Consensus MFE | -26.35 |
| Energy contribution | -26.72 |
| Covariance contribution | 0.36 |
| Combinations/Pair | 1.03 |
| Mean z-score | -2.14 |
| Structure conservation index | 0.90 |
| SVM decision value | 2.35 |
| SVM RNA-class probability | 0.992772 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
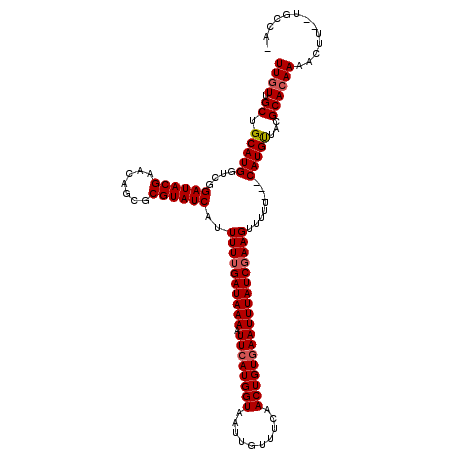
>3R_DroMel_CAF1 8587310 115 + 27905053 UUGUUGCUGCAUGGUCGGAUACGAACAGCGCGUAUCAUUUUUGAUAAAAUUCAUGGUAAUUGUUUCAACUGUGAAUUUAUCGAAGUUUUU---CAUGUUACGCACAAAACUU--UGCCAA ((((.((.((((((...((((((.......))))))..((((((((((.((((((((..........))))))))))))))))))....)---)))))...)))))).....--...... ( -29.20) >DroPse_CAF1 21794 113 + 1 UUGUUGCUGCAUGGUCGGAUACGAACAGCGCGUAUCAUUUUUGAUAAAAUUCAUGGUAAUUGUUUCAACUGUGAAUUUAUCGAAGUUUUU---CAUGUUACGCACAA-ACUU--UGGCA- ....((((((.((.(((....))).))))(((((.(((((((((((((.((((((((..........)))))))))))))))))).....---.))).)))))....-....--.))))- ( -30.10) >DroGri_CAF1 15390 114 + 1 UUGUUGCUGCAUGGUCGGAUACGAGCAGCGCGUAUCAUUUUUGAUAAAAUUCAUGGUAAUUGUUUCAACUGUGAAUUUAUCGAAGUUUUU---CAUGUUACGCACAAAACUU--UGCCC- ((((.(((((....(((....))))))))(((((.(((((((((((((.((((((((..........)))))))))))))))))).....---.))).))))))))).....--.....- ( -32.00) >DroWil_CAF1 38724 120 + 1 UUGUUGCUGCAUGGUCGGAUACGAACAGCGCGUAUCAUUUUUGAUAAAAUUCAUGGUAAUUGUUUCAACUGUAAAUUUAUCCAAGUUUUUUUCCAUGCAACGCAGAAAACUUUUUGCCAA .....(.(((((((...((((((.......))))))......((((((.((.(((((..........))))))).))))))...........))))))).)((((((....))))))... ( -24.90) >DroYak_CAF1 17057 115 + 1 UUGUUGCUGCAUGGUCGGAUACGAACAGCGCGUAUCAUUUUUGAUAAAAUUCAUGGUAAUUGUUUCAACUGUGAAUUUAUCGAAGUUUUU---CAUGUUACGCACAAAACUU--UUCCAA ((((.((.((((((...((((((.......))))))..((((((((((.((((((((..........))))))))))))))))))....)---)))))...)))))).....--...... ( -29.20) >DroPer_CAF1 18717 113 + 1 UUGUUGCUGCAUGGUCGGAUACGAACAGCGCGUAUCAUUUUUGAUAAAAUUCAUGGUAAUUGUUUCAACUGUGAAUUUAUCGAAGUUUUU---CAUGUUACGCACAA-ACUU--UGGCA- ....((((((.((.(((....))).))))(((((.(((((((((((((.((((((((..........)))))))))))))))))).....---.))).)))))....-....--.))))- ( -30.10) >consensus UUGUUGCUGCAUGGUCGGAUACGAACAGCGCGUAUCAUUUUUGAUAAAAUUCAUGGUAAUUGUUUCAACUGUGAAUUUAUCGAAGUUUUU___CAUGUUACGCACAAAACUU__UGCCA_ ((((.((.(((((....((((((.......))))))..((((((((((.((((((((..........))))))))))))))))))........)))))...))))))............. (-26.35 = -26.72 + 0.36)


| Location | 8,587,350 – 8,587,448 |
|---|---|
| Length | 98 |
| Sequences | 6 |
| Columns | 110 |
| Reading direction | forward |
| Mean pairwise identity | 78.93 |
| Mean single sequence MFE | -17.72 |
| Consensus MFE | -14.23 |
| Energy contribution | -14.40 |
| Covariance contribution | 0.17 |
| Combinations/Pair | 1.00 |
| Mean z-score | -0.88 |
| Structure conservation index | 0.80 |
| SVM decision value | -0.05 |
| SVM RNA-class probability | 0.508271 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>3R_DroMel_CAF1 8587350 98 + 27905053 UUGAUAAAAUUCAUGGUAAUUGUUUCAACUGUGAAUUUAUCGAAGUUUUUCAUGUUACGCACAAAACUUUGCCAAAGCCAAC-CACUGAGA--CU---------UCUCCG ..((((((.((((((((..........))))))))))))))((((((((....(((..((................)).)))-....))))--))---------)).... ( -18.39) >DroVir_CAF1 20530 82 + 1 UUGAUAAAAUUCAUGGUAAUUGUUUCAACUGUGAAUUUAUCGAAGUUUUUCAUGUUACGCACAAAACUUUGCCC-UGCUCU---------------------------CG ..((((((.((((((((..........))))))))))))))((((((((...((.....)).))))))))....-......---------------------------.. ( -14.70) >DroPse_CAF1 21834 106 + 1 UUGAUAAAAUUCAUGGUAAUUGUUUCAACUGUGAAUUUAUCGAAGUUUUUCAUGUUACGCACAA-ACUUUGGCA-AGCUAACAGAAAGAGA--AGGCCACAUAGCCGGAG ((((((((.((((((((..........))))))))))))))))..((((((.(((((.((....-.........-.)))))))))))))..--.(((......))).... ( -23.64) >DroGri_CAF1 15430 80 + 1 UUGAUAAAAUUCAUGGUAAUUGUUUCAACUGUGAAUUUAUCGAAGUUUUUCAUGUUACGCACAAAACUUUGCCC-UGCU-----------------------------CG ..((((((.((((((((..........))))))))))))))((((((((...((.....)).))))))))....-....-----------------------------.. ( -14.70) >DroMoj_CAF1 40584 82 + 1 UUGAUAAAAUUCAUGGUAAUUGUUUCAACUGUGAAUUUAUCGAAGUUUUUCAUGUUACGCACAAAACUUUGCCC-UGCUCU---------------------------CG ..((((((.((((((((..........))))))))))))))((((((((...((.....)).))))))))....-......---------------------------.. ( -14.70) >DroAna_CAF1 13741 110 + 1 UUGAUAAAAUUCAUGGUAAUUGUUUCAACUGUGAAUUUAUCGAAGUUUUUCAUGUUACGCACAAAACUUUGCCAAAGCCAACACACAGAGAGACAGCCGCAGAGACUCUG .(((......))).(((...((((((..(((((........((((((((...((.....)).))))))))((....)).....))))).))))))))).(((.....))) ( -20.20) >consensus UUGAUAAAAUUCAUGGUAAUUGUUUCAACUGUGAAUUUAUCGAAGUUUUUCAUGUUACGCACAAAACUUUGCCA_AGCUAA___________________________CG ..((((((.((((((((..........))))))))))))))((((((((...((.....)).))))))))........................................ (-14.23 = -14.40 + 0.17)



Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 10:56:02 2006