
| Sequence ID | 3R_DroMel_CAF1 |
|---|---|
| Location | 6,103,762 – 6,103,859 |
| Length | 97 |
| Max. P | 0.934001 |

| Location | 6,103,762 – 6,103,859 |
|---|---|
| Length | 97 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 84.01 |
| Mean single sequence MFE | -29.88 |
| Consensus MFE | -29.07 |
| Energy contribution | -29.07 |
| Covariance contribution | -0.00 |
| Combinations/Pair | 1.00 |
| Mean z-score | -1.70 |
| Structure conservation index | 0.97 |
| SVM decision value | 1.23 |
| SVM RNA-class probability | 0.934001 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
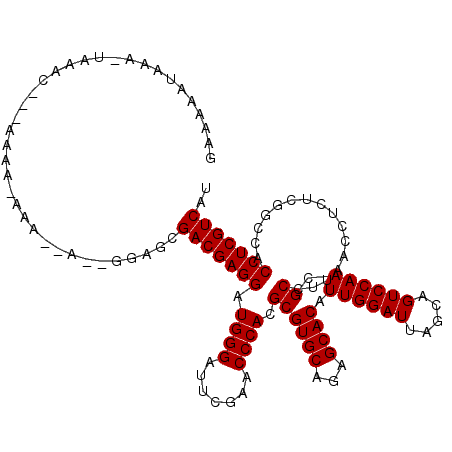
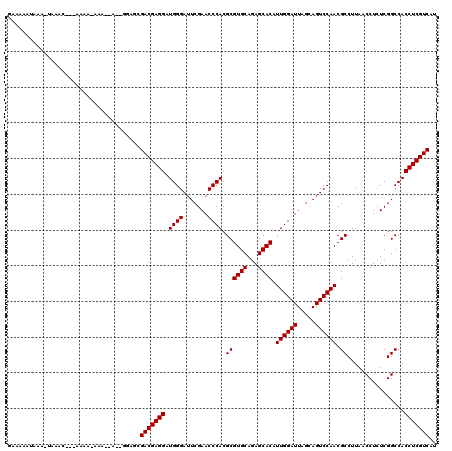
>3R_DroMel_CAF1 6103762 97 + 27905053 GAAAA-------------------AAA--A--GGAUCGACGAGGAUGGGAUUCGAACCCACGCGUGCAGAGCACAUUGGAUUAGCAGUCCAACGCCUUAACCUCUCGGCCACCUCGUCAU .....-------------------...--.--.....(((((((.((((.......)))).((((((...)))).((((((.....)))))).))................))))))).. ( -29.30) >DroVir_CAF1 14414 114 + 1 GAAAAUUAAA-UAAACUG-AAAAAAUA--A--ACCUCGACGAGGAUGGGAUUCGAACCCACGCGUGCAGAGCACAUUGGAUUAGCAGUCCAACGCCUUAACCUCUCGGCCACCUCGUCAU ..........-.......-........--.--.....(((((((.((((.......)))).((((((...)))).((((((.....)))))).))................))))))).. ( -29.30) >DroGri_CAF1 16575 116 + 1 ACAAAAAAAGU----AUAUAAUAAAAACAGUUGUUGCGACGAGGAUGGGAUUCGAACCCACGCGUGCAGAGCACAUUGGAUUAGCAGUCCAACGCCUUAACCUCUCGGCCACCUCGUCUG .........((----(.(((((.......))))))))(((((((.((((.......)))).((((((...)))).((((((.....)))))).))................))))))).. ( -30.60) >DroSim_CAF1 16454 110 + 1 GAAAAAUAAA-UAAAC---AAAA--AA--A--GGAGCGACGAGGAUGGGAUUCGAACCCACGCGUGCAGAGCACAUUGGAUUAGCAGUCCAACGCCUUAACCUCUCGGCCACCUCGUCAU ..........-.....---....--..--.--.....(((((((.((((.......)))).((((((...)))).((((((.....)))))).))................))))))).. ( -29.30) >DroEre_CAF1 16130 112 + 1 GAAAAAUAAA-UAAAC---AAAAAAGA--A--CGGACGACGAGGAUGGGAUUCGAACCCACGCGUGCAGAGCACAUUGGAUUAGCAGUCCAACGCCUUAACCUCUCGGCCACCUCGUCAC ..........-.....---........--.--.....(((((((.((((.......)))).((((((...)))).((((((.....)))))).))................))))))).. ( -29.30) >DroAna_CAF1 12733 109 + 1 -AAUAAUAAU-AAUGC---AAA--AUA--A--GGCCCGACGAGGAUGGGAUUCGAACCCACGCGUGCAGAGCACAUUGGAUUAGCAGUCCAACGCCUUAACCUCUCGGCCACCUCGUCCU -.........-.....---...--...--.--((((.((.((((.((((.......)))).((((((...)))).((((((.....)))))).)).....)))))))))).......... ( -31.50) >consensus GAAAAAUAAA_UAAAC___AAAA_AAA__A__GGAGCGACGAGGAUGGGAUUCGAACCCACGCGUGCAGAGCACAUUGGAUUAGCAGUCCAACGCCUUAACCUCUCGGCCACCUCGUCAU .....................................(((((((.((((.......)))).((((((...)))).((((((.....)))))).))................))))))).. (-29.07 = -29.07 + -0.00)

| Location | 6,103,762 – 6,103,859 |
|---|---|
| Length | 97 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 84.01 |
| Mean single sequence MFE | -35.45 |
| Consensus MFE | -35.23 |
| Energy contribution | -35.23 |
| Covariance contribution | -0.00 |
| Combinations/Pair | 1.00 |
| Mean z-score | -1.59 |
| Structure conservation index | 0.99 |
| SVM decision value | 1.19 |
| SVM RNA-class probability | 0.927761 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
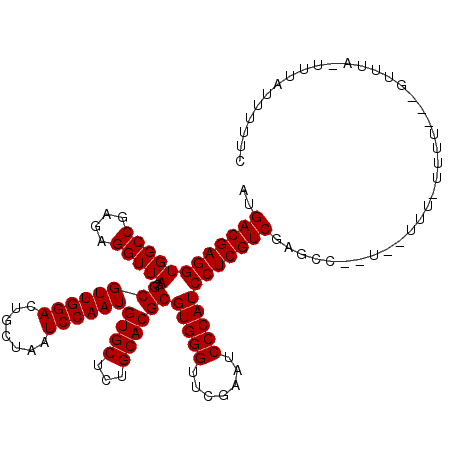
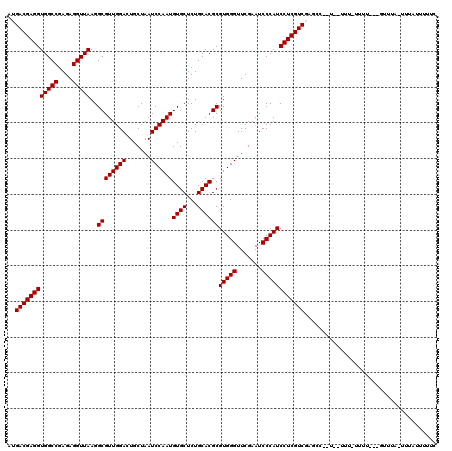
>3R_DroMel_CAF1 6103762 97 - 27905053 AUGACGAGGUGGCCGAGAGGUUAAGGCGUUGGACUGCUAAUCCAAUGUGCUCUGCACGCGUGGGUUCGAAUCCCAUCCUCGUCGAUCC--U--UUU-------------------UUUUC .(((((((((((((....)))))..((((((((.......))))))((((...))))))(((((.......)))))))))))))....--.--...-------------------..... ( -35.50) >DroVir_CAF1 14414 114 - 1 AUGACGAGGUGGCCGAGAGGUUAAGGCGUUGGACUGCUAAUCCAAUGUGCUCUGCACGCGUGGGUUCGAAUCCCAUCCUCGUCGAGGU--U--UAUUUUUU-CAGUUUA-UUUAAUUUUC ..((((((((((((....)))))..((((((((.......))))))((((...))))))(((((.......))))))))))))((((.--.--.....)))-)......-.......... ( -35.90) >DroGri_CAF1 16575 116 - 1 CAGACGAGGUGGCCGAGAGGUUAAGGCGUUGGACUGCUAAUCCAAUGUGCUCUGCACGCGUGGGUUCGAAUCCCAUCCUCGUCGCAACAACUGUUUUUAUUAUAU----ACUUUUUUUGU ..((((((((((((....)))))..((((((((.......))))))((((...))))))(((((.......))))))))))))......................----........... ( -35.40) >DroSim_CAF1 16454 110 - 1 AUGACGAGGUGGCCGAGAGGUUAAGGCGUUGGACUGCUAAUCCAAUGUGCUCUGCACGCGUGGGUUCGAAUCCCAUCCUCGUCGCUCC--U--UU--UUUU---GUUUA-UUUAUUUUUC ..((((((((((((....)))))..((((((((.......))))))((((...))))))(((((.......)))))))))))).....--.--..--....---.....-.......... ( -35.20) >DroEre_CAF1 16130 112 - 1 GUGACGAGGUGGCCGAGAGGUUAAGGCGUUGGACUGCUAAUCCAAUGUGCUCUGCACGCGUGGGUUCGAAUCCCAUCCUCGUCGUCCG--U--UCUUUUUU---GUUUA-UUUAUUUUUC ..((((((((((((....)))))..((((((((.......))))))((((...))))))(((((.......)))))))))))).....--.--........---.....-.......... ( -35.20) >DroAna_CAF1 12733 109 - 1 AGGACGAGGUGGCCGAGAGGUUAAGGCGUUGGACUGCUAAUCCAAUGUGCUCUGCACGCGUGGGUUCGAAUCCCAUCCUCGUCGGGCC--U--UAU--UUU---GCAUU-AUUAUUAUU- ..((((((((((((....)))))..((((((((.......))))))((((...))))))(((((.......))))))))))))..((.--.--...--...---))...-.........- ( -35.50) >consensus AUGACGAGGUGGCCGAGAGGUUAAGGCGUUGGACUGCUAAUCCAAUGUGCUCUGCACGCGUGGGUUCGAAUCCCAUCCUCGUCGAGCC__U__UUU_UUUU___GUUUA_UUUAUUUUUC ..((((((((((((....)))))..((((((((.......))))))((((...))))))(((((.......))))))))))))..................................... (-35.23 = -35.23 + -0.00)

Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 10:28:19 2006