
| Sequence ID | 3R_DroMel_CAF1 |
|---|---|
| Location | 5,365,969 – 5,366,101 |
| Length | 132 |
| Max. P | 0.802189 |

| Location | 5,365,969 – 5,366,067 |
|---|---|
| Length | 98 |
| Sequences | 6 |
| Columns | 108 |
| Reading direction | reverse |
| Mean pairwise identity | 80.82 |
| Mean single sequence MFE | -50.24 |
| Consensus MFE | -31.73 |
| Energy contribution | -33.62 |
| Covariance contribution | 1.89 |
| Combinations/Pair | 1.17 |
| Mean z-score | -1.88 |
| Structure conservation index | 0.63 |
| SVM decision value | 0.42 |
| SVM RNA-class probability | 0.728123 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
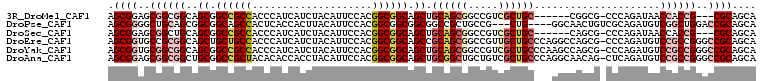
>3R_DroMel_CAF1 5365969 98 - 27905053 AGCGGAGCGGCGGCAGCGGCCGCCACCCAUCAUCUACAUUCCACGGCGGCAGCUGCAGCGGCCGUCGCUGC------CGGCG-CCCAGAUAACCACCG---CGCAGCA .((((.(((.((((((((((.(((....................)))(((.((....)).)))))))))))------)).))-)...(.....).)))---)...... ( -45.05) >DroPse_CAF1 865 101 - 1 AGCGGGGCUGCAGCGGCGGCAGCCACUCACCACUUACAUUCCACGGCGGCGGCGGCCGCUGCCG---CUG----GGCAACUGUCGCAGAUGUCGGCUGGACCGCAGCA .((((((((((.......)))))).....(((((.(((((...((((((((((....)))))))---)))----(((....)))...))))).)).))).)))).... ( -50.50) >DroSec_CAF1 1166 98 - 1 AGCGGAGCGGCUGCAGCGGCCGCCACCCAUCAUCUACAUUCCACGGCGGCAGCUGCAGCGGCCGUCGCUGC------CAGCG-CCCAGAUAACCACCG---CGCAGCA (((((.((.((((((((.((((((....................)))))).)))))))).))..)))))((------..(((-(.............)---))).)). ( -46.57) >DroEre_CAF1 1252 107 - 1 AGCGGUGCCGCGGCAGCUGCUGCCACCCAUCAUCUACAUUCCACGGCGGCAGCCGCAGCGGCCGUUGCUGCCCAGGCCAGCG-CCCAGAUGUCCGCCGGGCCGCAGCA ....(.(((((.((.(((((((((....................))))))))).)).))))))(((((.((((.(((..(((-......)))..))))))).))))). ( -54.05) >DroYak_CAF1 3790 107 - 1 AGCGGUGCGGCGGCAGCGGCCGCCACCCAUCAUCUACAUUCCACGGCGGCAGCUGCAGCGGCCGUCGCUGCCCAAGCCAGCG-CCCAGAUGUCCGCCGGGCCGCAGCA .(((((.((((((((((.((((((....................)))))).)))))...((.(((.(((.....)))..)))-.)).......))))).))))).... ( -53.45) >DroAna_CAF1 1504 107 - 1 AGCGGAGCGGCGGCUGCGGCCGCUACACACCACCUACAUUCCACGGCGGCAGCUGCGGCUGCUGUCGCUGCCCAGGCAACAG-CUCAGAUGUCCGCCGGGCCGCAGCA .((((.(..(((((....)))))..)..............((.((((((((.(((.(((((.((((........)))).)))-))))).)).)))))))))))).... ( -51.80) >consensus AGCGGAGCGGCGGCAGCGGCCGCCACCCAUCAUCUACAUUCCACGGCGGCAGCUGCAGCGGCCGUCGCUGC___GGCCAGCG_CCCAGAUGUCCGCCGGGCCGCAGCA .((((..((((((..((.((((((....................)))))).)).((((((.....)))))).....................))))))..)))).... (-31.73 = -33.62 + 1.89)

| Location | 5,365,996 – 5,366,101 |
|---|---|
| Length | 105 |
| Sequences | 6 |
| Columns | 108 |
| Reading direction | forward |
| Mean pairwise identity | 84.05 |
| Mean single sequence MFE | -58.35 |
| Consensus MFE | -39.51 |
| Energy contribution | -41.40 |
| Covariance contribution | 1.89 |
| Combinations/Pair | 1.17 |
| Mean z-score | -2.55 |
| Structure conservation index | 0.68 |
| SVM decision value | 0.22 |
| SVM RNA-class probability | 0.639574 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
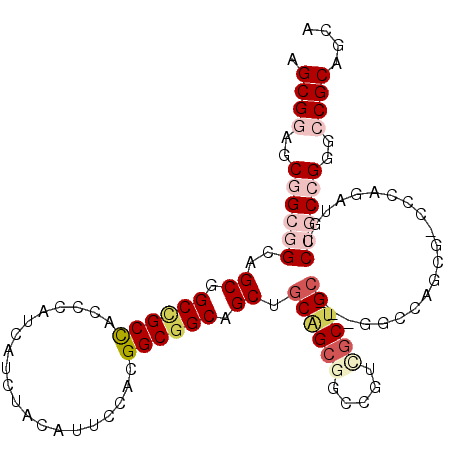
>3R_DroMel_CAF1 5365996 105 + 27905053 ---GCAGCGACGGCCGCUGCAGCUGCCGCCGUGGAAUGUAGAUGAUGGGUGGCGGCCGCUGCCGCCGCUCCGCUCAGCGGCGUGAUAUGGAUGCCCGGCGGCAGCUGG ---((((((.....))))))(((((((((((.((.((.((.((.((((((((((((....)))))))))((((...))))))).)).)).)).))))))))))))).. ( -64.00) >DroPse_CAF1 899 101 + 1 ----CAG---CGGCAGCGGCCGCCGCCGCCGUGGAAUGUAAGUGGUGAGUGGCUGCCGCCGCUGCAGCCCCGCUAAUAGGUGUGAUGUGAAUUCCGGGCGGCAGCUGG ----(((---((((.((((((((((((((............)))))).)))))))).)))))))((((.(((((....((.((.......)).)).)))))..)))). ( -54.50) >DroSec_CAF1 1193 105 + 1 ---GCAGCGACGGCCGCUGCAGCUGCCGCCGUGGAAUGUAGAUGAUGGGUGGCGGCCGCUGCAGCCGCUCCGCUCAGCGGCGUGAUGUGGAUGCCCGGCGGCAGCUGG ---((((((.....))))))(((((((((((.((.((.((.((.(((((((((.((....)).))))))((((...))))))).)).)).)).))))))))))))).. ( -60.00) >DroEre_CAF1 1285 108 + 1 UGGGCAGCAACGGCCGCUGCGGCUGCCGCCGUGGAAUGUAGAUGAUGGGUGGCAGCAGCUGCCGCGGCACCGCUCAACGGGGUGAUGUGGAUGCCCGGCGGCAGCUGG ...(((((.......))))).(((((((((.................)))))))))((((((((((((((((((((......))).)))).))))..))))))))).. ( -58.03) >DroYak_CAF1 3823 108 + 1 UGGGCAGCGACGGCCGCUGCAGCUGCCGCCGUGGAAUGUAGAUGAUGGGUGGCGGCCGCUGCCGCCGCACCGCUCAACGGAGUGAUGUGGAUGCCCGGCGGCAGCUGG ...((((((.....))))))(((((((((((.((.((.((.((...((((((((((....)))))))).))((((....)))).)).)).)).))))))))))))).. ( -63.80) >DroAna_CAF1 1537 108 + 1 UGGGCAGCGACAGCAGCCGCAGCUGCCGCCGUGGAAUGUAGGUGGUGUGUAGCGGCCGCAGCCGCCGCUCCGCUCAGUGGCGUAAUAUGGAUGCCGUGCGGAAGCUGA ..(((.((....((.(((((.(((((((((..........))))))).)).))))).)).)).)))(((((((....((((((.......)))))).)))).)))... ( -49.80) >consensus ___GCAGCGACGGCCGCUGCAGCUGCCGCCGUGGAAUGUAGAUGAUGGGUGGCGGCCGCUGCCGCCGCUCCGCUCAGCGGCGUGAUGUGGAUGCCCGGCGGCAGCUGG ...(((((.......)))))(((((((((((.((.((((.(.((.(((((((((((.......)))))..)))))).)).)...)))).....))))))))))))).. (-39.51 = -41.40 + 1.89)



| Location | 5,365,996 – 5,366,101 |
|---|---|
| Length | 105 |
| Sequences | 6 |
| Columns | 108 |
| Reading direction | reverse |
| Mean pairwise identity | 84.05 |
| Mean single sequence MFE | -50.82 |
| Consensus MFE | -37.65 |
| Energy contribution | -39.65 |
| Covariance contribution | 2.00 |
| Combinations/Pair | 1.21 |
| Mean z-score | -2.70 |
| Structure conservation index | 0.74 |
| SVM decision value | 0.62 |
| SVM RNA-class probability | 0.802189 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>3R_DroMel_CAF1 5365996 105 - 27905053 CCAGCUGCCGCCGGGCAUCCAUAUCACGCCGCUGAGCGGAGCGGCGGCAGCGGCCGCCACCCAUCAUCUACAUUCCACGGCGGCAGCUGCAGCGGCCGUCGCUGC--- ..((((((((((((((...........)))(.(((..((.(.((((((....)))))).))).))).).........)))))))))))((((((.....))))))--- ( -56.20) >DroPse_CAF1 899 101 - 1 CCAGCUGCCGCCCGGAAUUCACAUCACACCUAUUAGCGGGGCUGCAGCGGCGGCAGCCACUCACCACUUACAUUCCACGGCGGCGGCGGCCGCUGCCG---CUG---- ...(((((((((................(((......)))((....)))))))))))....................((((((((((....)))))))---)))---- ( -44.00) >DroSec_CAF1 1193 105 - 1 CCAGCUGCCGCCGGGCAUCCACAUCACGCCGCUGAGCGGAGCGGCUGCAGCGGCCGCCACCCAUCAUCUACAUUCCACGGCGGCAGCUGCAGCGGCCGUCGCUGC--- ..((((((((((((((...........)))(.(((..((.(((((((...)))))))...)).))).).........)))))))))))((((((.....))))))--- ( -52.30) >DroEre_CAF1 1285 108 - 1 CCAGCUGCCGCCGGGCAUCCACAUCACCCCGUUGAGCGGUGCCGCGGCAGCUGCUGCCACCCAUCAUCUACAUUCCACGGCGGCAGCCGCAGCGGCCGUUGCUGCCCA ...((((((((((((((.((.(.(((......)))).))))))(((((....)))))....................)))))))))).((((((.....))))))... ( -49.70) >DroYak_CAF1 3823 108 - 1 CCAGCUGCCGCCGGGCAUCCACAUCACUCCGUUGAGCGGUGCGGCGGCAGCGGCCGCCACCCAUCAUCUACAUUCCACGGCGGCAGCUGCAGCGGCCGUCGCUGCCCA ..(((((((((((((......((((.(((....))).)))).((((((....))))))................)).)))))))))))((((((.....))))))... ( -56.50) >DroAna_CAF1 1537 108 - 1 UCAGCUUCCGCACGGCAUCCAUAUUACGCCACUGAGCGGAGCGGCGGCUGCGGCCGCUACACACCACCUACAUUCCACGGCGGCAGCUGCGGCUGCUGUCGCUGCCCA ......(((((.((((...........)))...).)))))((((((((.((((((((......((.((..........)).)).....)))))))).))))))))... ( -46.20) >consensus CCAGCUGCCGCCGGGCAUCCACAUCACGCCGCUGAGCGGAGCGGCGGCAGCGGCCGCCACCCAUCAUCUACAUUCCACGGCGGCAGCUGCAGCGGCCGUCGCUGC___ ...((((((((((((.............((((...))))...((((((....))))))................)).)))))))))).((((((.....))))))... (-37.65 = -39.65 + 2.00)


Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 10:21:36 2006