
| Sequence ID | 3R_DroMel_CAF1 |
|---|---|
| Location | 4,777,137 – 4,777,281 |
| Length | 144 |
| Max. P | 0.999345 |

| Location | 4,777,137 – 4,777,243 |
|---|---|
| Length | 106 |
| Sequences | 5 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 78.34 |
| Mean single sequence MFE | -28.52 |
| Consensus MFE | -9.72 |
| Energy contribution | -10.68 |
| Covariance contribution | 0.96 |
| Combinations/Pair | 1.21 |
| Mean z-score | -2.67 |
| Structure conservation index | 0.34 |
| SVM decision value | 1.91 |
| SVM RNA-class probability | 0.982294 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>3R_DroMel_CAF1 4777137 106 - 27905053 CAGGAUAAUGUCCGAGUAUCGUUCAGAACC--CGGAGAUUUU----CCAG--UCUAUAUAUUA-AU-AUAUAUAUAGAGAAACACU----UAAUAGGUCACGCAGUGACAUACACACACU ..(((.(((.((((.((.((.....)))).--)))).))).)----))..--(((((((((..-..-..)))))))))........----......(((((...)))))........... ( -27.10) >DroSec_CAF1 12655 107 - 1 CAGGAUAAUGUCCGAGUAUCGUUCAGAACU--CGGAGAUUUU----CCAG--UCUAUAUAUUU-GUGGUAUAUAUAGAGAAACACU----UAAUAAGUCACGCAGUGACAUACACACACU ..(((.(((.(((((((.((.....)))))--)))).))).)----))..--(((((((((..-.....)))))))))........----......(((((...)))))........... ( -31.60) >DroEre_CAF1 12780 107 - 1 CAGGAUUAUGUCUGAGUAUCGUUCAGAACU--CGGGGAUUUU----CCAG--CCUAUAUAUUA-GUGGUAUAUAUAGAGAAACUAU----AAGUCGGCCACGCAGUGACAUACAUACACC ..(((..((.(((((((.((.....)))))--)))).))..)----))..--......((((.-(((((...(((((.....))))----).....)))))..))))............. ( -26.10) >DroYak_CAF1 12952 107 - 1 CAGGAUAAUGUCCGAGUAUCGUUCAGAACU--CGGAGAUUUU----CCAG--UCUAUAUAUUA-GUGGUAUAUAUAGAGCAAUACU----UAAUGGGCCACGCAGUGACAUACACACACC ..(((.(((.(((((((.((.....)))))--)))).))).)----))..--...........-(((((...(((.(((.....))----).))).)))))...(((.....)))..... ( -30.50) >DroAna_CAF1 12660 111 - 1 CAGGCUAAU--------AUCGUUUAUAUCUAUCCGAUAUUUGGUUAUUAGCCCCUAUAUAUCAUGUGGGAUAUAUAGAAUA-UAUUUUUUGAAAAGGUCACGCAGUGGCAUACACACACC ..(((((((--------((((...(((((.....))))).))).)))))))).(((((((((......)))))))))....-..............(((((...)))))........... ( -27.30) >consensus CAGGAUAAUGUCCGAGUAUCGUUCAGAACU__CGGAGAUUUU____CCAG__UCUAUAUAUUA_GUGGUAUAUAUAGAGAAACACU____UAAUAGGUCACGCAGUGACAUACACACACC ..((..(((.((((....((.....)).....)))).)))......)).....((((((((........))))))))...................(((((...)))))........... ( -9.72 = -10.68 + 0.96)


| Location | 4,777,173 – 4,777,281 |
|---|---|
| Length | 108 |
| Sequences | 5 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 77.12 |
| Mean single sequence MFE | -23.56 |
| Consensus MFE | -7.18 |
| Energy contribution | -7.90 |
| Covariance contribution | 0.72 |
| Combinations/Pair | 1.15 |
| Mean z-score | -3.41 |
| Structure conservation index | 0.30 |
| SVM decision value | 3.53 |
| SVM RNA-class probability | 0.999345 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>3R_DroMel_CAF1 4777173 108 + 27905053 UCUCUAUAUAUAU-AU-UAAUAUAUAGA--CUGG----AAAAUCUCCG--GGUUCUGAACGAUACUCGGACAUUAUCCUGGCCCAGCACUGACACACACACAC--AUAUAUAUAUAUAGA ..(((((((((((-((-...........--(.((----(.(((.((((--(((((.....)).))))))).))).))).)((...))................--..))))))))))))) ( -25.60) >DroSec_CAF1 12691 101 + 1 UCUCUAUAUAUACCAC-AAAUAUAUAGA--CUGG----AAAAUCUCCG--AGUUCUGAACGAUACUCGGACAUUAUCCUGGUCCAGCACUGACACACACACAC--AC--------ACAGA ..(((((((((.....-..)))))))))--(.((----(.(((.((((--(((((.....)).))))))).))).))).)(((.......)))..........--..--------..... ( -23.40) >DroEre_CAF1 12816 103 + 1 UCUCUAUAUAUACCAC-UAAUAUAUAGG--CUGG----AAAAUCCCCG--AGUUCUGAACGAUACUCAGACAUAAUCCUGGCCCAGCACUGACUCACACACACGCAC--------ACAGA ...((((((((.....-..))))))))(--((((----.....((..(--(..(((((.......))))).....))..)).)))))....................--------..... ( -17.70) >DroYak_CAF1 12988 98 + 1 GCUCUAUAUAUACCAC-UAAUAUAUAGA--CUGG----AAAAUCUCCG--AGUUCUGAACGAUACUCGGACAUUAUCCUG-CCCAGCACUGACUCACACAC----AC--------ACAGA (((((((((((.....-..)))))))))--..((----(.(((.((((--(((((.....)).))))))).))).)))..-....)).(((..........----..--------.))). ( -24.02) >DroAna_CAF1 12699 100 + 1 AUUCUAUAUAUCCCACAUGAUAUAUAGGGGCUAAUAACCAAAUAUCGGAUAGAUAUAAACGAU--------AUUAGCCUGGUCCAGCACUGGCACACACGC----AC--------CCAGA ...(((((((((......)))))))))(((..........(((((((..((....))..))))--------))).((.(((((((....))).)).)).))----.)--------))... ( -27.10) >consensus UCUCUAUAUAUACCAC_UAAUAUAUAGA__CUGG____AAAAUCUCCG__AGUUCUGAACGAUACUCGGACAUUAUCCUGGCCCAGCACUGACACACACACAC__AC________ACAGA ..(((((((((........)))))))))..(((....................(((((.......))))).......(((...)))..............................))). ( -7.18 = -7.90 + 0.72)



| Location | 4,777,173 – 4,777,281 |
|---|---|
| Length | 108 |
| Sequences | 5 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 77.12 |
| Mean single sequence MFE | -30.98 |
| Consensus MFE | -10.14 |
| Energy contribution | -10.78 |
| Covariance contribution | 0.64 |
| Combinations/Pair | 1.19 |
| Mean z-score | -2.49 |
| Structure conservation index | 0.33 |
| SVM decision value | 1.89 |
| SVM RNA-class probability | 0.981567 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
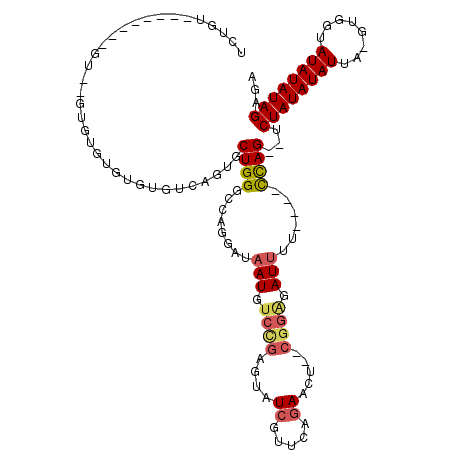
>3R_DroMel_CAF1 4777173 108 - 27905053 UCUAUAUAUAUAUAU--GUGUGUGUGUGUCAGUGCUGGGCCAGGAUAAUGUCCGAGUAUCGUUCAGAACC--CGGAGAUUUU----CCAG--UCUAUAUAUUA-AU-AUAUAUAUAGAGA (((((((((((((..--(((((((((.(((.......)))))(((.(((.((((.((.((.....)))).--)))).))).)----))..--..)))))))..-))-))))))))))).. ( -32.90) >DroSec_CAF1 12691 101 - 1 UCUGU--------GU--GUGUGUGUGUGUCAGUGCUGGACCAGGAUAAUGUCCGAGUAUCGUUCAGAACU--CGGAGAUUUU----CCAG--UCUAUAUAUUU-GUGGUAUAUAUAGAGA (((((--------((--(((.(..(......)..)(((((..(((.(((.(((((((.((.....)))))--)))).))).)----)).)--)))).......-....)))))))))).. ( -32.10) >DroEre_CAF1 12816 103 - 1 UCUGU--------GUGCGUGUGUGUGAGUCAGUGCUGGGCCAGGAUUAUGUCUGAGUAUCGUUCAGAACU--CGGGGAUUUU----CCAG--CCUAUAUAUUA-GUGGUAUAUAUAGAGA (((((--------(((..(..(..(......)..)(((((..(((..((.(((((((.((.....)))))--)))).))..)----)).)--)))).......-...)..)))))))).. ( -28.70) >DroYak_CAF1 12988 98 - 1 UCUGU--------GU----GUGUGUGAGUCAGUGCUGGG-CAGGAUAAUGUCCGAGUAUCGUUCAGAACU--CGGAGAUUUU----CCAG--UCUAUAUAUUA-GUGGUAUAUAUAGAGC (((((--------((----(((..(......)..)((((-(.(((.(((.(((((((.((.....)))))--)))).))).)----)).)--)))).......-.....))))))))).. ( -31.60) >DroAna_CAF1 12699 100 - 1 UCUGG--------GU----GCGUGUGUGCCAGUGCUGGACCAGGCUAAU--------AUCGUUUAUAUCUAUCCGAUAUUUGGUUAUUAGCCCCUAUAUAUCAUGUGGGAUAUAUAGAAU ....(--------((----.((.(..(....)..))).))).(((((((--------((((...(((((.....))))).))).)))))))).(((((((((......)))))))))... ( -29.60) >consensus UCUGU________GU__GUGUGUGUGUGUCAGUGCUGGGCCAGGAUAAUGUCCGAGUAUCGUUCAGAACU__CGGAGAUUUU____CCAG__UCUAUAUAUUA_GUGGUAUAUAUAGAGA ..................................((((........(((.((((....((.....)).....)))).)))......))))...((((((((........))))))))... (-10.14 = -10.78 + 0.64)


Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 10:15:33 2006