
| Sequence ID | 3L_DroMel_CAF1 |
|---|---|
| Location | 20,185,318 – 20,185,423 |
| Length | 105 |
| Max. P | 0.847627 |

| Location | 20,185,318 – 20,185,423 |
|---|---|
| Length | 105 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 78.81 |
| Mean single sequence MFE | -35.35 |
| Consensus MFE | -18.99 |
| Energy contribution | -19.80 |
| Covariance contribution | 0.81 |
| Combinations/Pair | 1.21 |
| Mean z-score | -2.22 |
| Structure conservation index | 0.54 |
| SVM decision value | 0.78 |
| SVM RNA-class probability | 0.847627 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
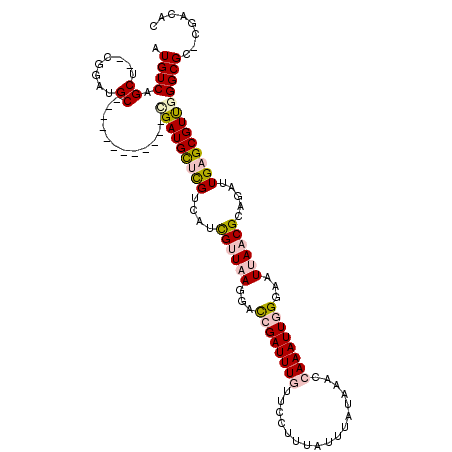
>3L_DroMel_CAF1 20185318 105 - 23771897 AUGUCAGCU--CGGAUGC------------CGAUGCUCGUCAUCGUUAAGGACCGAUUUGUUCUUUUAUUUAUAAACCAAAUUGGGAAUUAACGCAGAUUGAGCGUUGGGCGC-CGACAC ......(.(--(((.(((------------(((((((((((..((((((...((((((((.................))))))))...))))))..)).)))))))).)))))-)))).. ( -36.53) >DroPse_CAF1 18191 116 - 1 AUGUCAGCUCUCGGAUGC-GGUGCUCAUGUGGAUGUGUGUCAAUGCUGAGAGUCGAUUU---UCGUUAUUUAUAAACCAAAUUAGGGAUAAACGGAAAUUGGGCGUCAGGCGUUUGGCAC .(((((((((((((....-((..(.(((....))).)..))....))))))))((((((---((((((((..(((......)))..))).)))))))))))((((.....))))))))). ( -35.10) >DroSim_CAF1 18751 105 - 1 AUGUCAGCU--CGGAUGC------------CGAUGCUCGUCAUCGUUAAGGACCGAUUUGUUCUUUUAUUUAUAAACCAAAUUGGGAAUUAACGCAGAUUGAGCGUUGGGCGC-CGACAC ......(.(--(((.(((------------(((((((((((..((((((...((((((((.................))))))))...))))))..)).)))))))).)))))-)))).. ( -36.53) >DroEre_CAF1 18289 105 - 1 AUGUCAGCU--CGGAUGC------------CGAUGCUCGUCAUCGUUAAGCACCGAUUUGUUCUUUUAUUUAUAAACCAAAUUGGGAAUUAACGCAGAUUGAGCGUUGGGCGC-CAACAC .........--.((.(((------------(((((((((((..((((((...((((((((.................))))))))...))))))..)).)))))))).)))))-)..... ( -33.43) >DroYak_CAF1 17703 111 - 1 AUGUCAGCU--CGGAUGCUGGUGC------UGAUGCUCGUCAUCGUUAAGGACCGAUUUGUUCCUUUAUUUAUAAACCAAAUUGGGAAUUAACGCAGAUUGAGCGUUGGGCGG-CAACAC .(..((((.--.....))))..)(------..(((((((((..((((((...((((((((.................))))))))...))))))..)).)))))))..)..(.-...).. ( -35.43) >DroPer_CAF1 18128 116 - 1 AUGUCAGCUCUCGGAUGC-GGUGCUCAUGUGGAUGUGUGUCAAUGCUGAGAGUCGAUUU---UCGUUAUUUAUAAACCAAAUUAGGGAUAAACGGAAAUUGGGCGUCAGGCGUUUGGCAC .(((((((((((((....-((..(.(((....))).)..))....))))))))((((((---((((((((..(((......)))..))).)))))))))))((((.....))))))))). ( -35.10) >consensus AUGUCAGCU__CGGAUGC____________CGAUGCUCGUCAUCGUUAAGGACCGAUUUGUUCCUUUAUUUAUAAACCAAAUUGGGAAUUAACGCAGAUUGAGCGUUGGGCGC_CGACAC .((((.((........))............(((((((((....((((((...((((((((.................))))))))...)))))).....)))))))))))))........ (-18.99 = -19.80 + 0.81)


Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 12:49:07 2006