
| Sequence ID | 3L_DroMel_CAF1 |
|---|---|
| Location | 11,725,099 – 11,725,193 |
| Length | 94 |
| Max. P | 0.794355 |

| Location | 11,725,099 – 11,725,193 |
|---|---|
| Length | 94 |
| Sequences | 5 |
| Columns | 96 |
| Reading direction | forward |
| Mean pairwise identity | 80.23 |
| Mean single sequence MFE | -19.08 |
| Consensus MFE | -6.00 |
| Energy contribution | -7.04 |
| Covariance contribution | 1.04 |
| Combinations/Pair | 1.12 |
| Mean z-score | -2.26 |
| Structure conservation index | 0.31 |
| SVM decision value | 0.36 |
| SVM RNA-class probability | 0.705719 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>3L_DroMel_CAF1 11725099 94 + 23771897 UCAUACU--AUUAAUAGUAUCAUAUUAUUACGCCUAUUUGCUGUUUAUGACAGCUAAUUAAAGGUACUAAUACAGUAAGCCUGCUACUCAGUUAAU ..(((((--(....)))))).....(((((.(((((((.((((((...)))))).)))...))))..))))).((((....))))........... ( -14.20) >DroSec_CAF1 37982 90 + 1 -AA---U--AUUAAUAGCAUCAUAUUAUUACGUCUAUUUGCUGUUAAUGACAGCUAAUUAAAUGUACUAAUAGAGUAAGCCUGCUACUCAGUUAAU -..---.--.....((((....(((((.(((((..(((.((((((...)))))).)))...))))).)))))(((((.(....)))))).)))).. ( -19.90) >DroSim_CAF1 32690 93 + 1 -CAUACU--AUCAAUAGCAUCAUAUUAUUACGUCUAUUUGCUGUUUAUGACAGCUAAUUAAAGGUAGUAAUAGAGCAAGCCUGCUACUCAGUUAAU -......--.....((((....(((((((((.(..(((.((((((...)))))).)))...).))))))))).((((....)))).....)))).. ( -19.90) >DroEre_CAF1 34433 92 + 1 UCUUUCC--UUUAAUAGCAUCGUAUUAUUACGUCCAUUAUUUGGAUGUGACAGCUAAUAAAAGAUACUAAUAGAGCAAGC--GCUACUAAGUUUAU ......(--((((.(((.(((.((((((((((((((.....)))))))))....)))))...))).))).))))).((((--........)))).. ( -20.60) >DroYak_CAF1 35009 95 + 1 UCAUACAUUUUUAAUAGCAACGUAUUAUUACAUUCAUUCUCUGUUUAUGACAGUUAAUGAAUGCUACUAAUAGCGUAAGC-UGCCACUAAGUUAAU ..........(((.((((...(((....)))(((((((..(((((...)))))..))))))))))).)))((((....))-))............. ( -20.80) >consensus UCAUACU__AUUAAUAGCAUCAUAUUAUUACGUCUAUUUGCUGUUUAUGACAGCUAAUUAAAGGUACUAAUAGAGUAAGCCUGCUACUCAGUUAAU ..............((((....(((((.(((....(((.(((((.....))))).))).....))).))))).((((....)))).....)))).. ( -6.00 = -7.04 + 1.04)

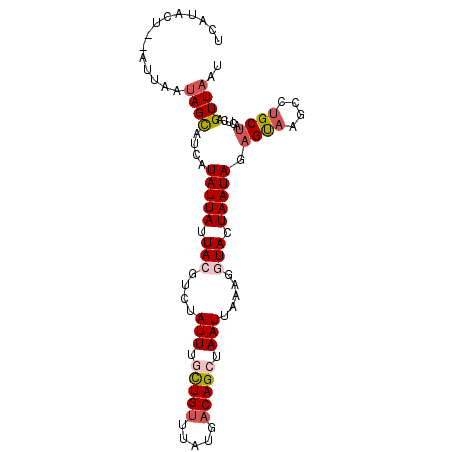
| Location | 11,725,099 – 11,725,193 |
|---|---|
| Length | 94 |
| Sequences | 5 |
| Columns | 96 |
| Reading direction | reverse |
| Mean pairwise identity | 80.23 |
| Mean single sequence MFE | -20.30 |
| Consensus MFE | -9.63 |
| Energy contribution | -10.31 |
| Covariance contribution | 0.68 |
| Combinations/Pair | 1.21 |
| Mean z-score | -2.26 |
| Structure conservation index | 0.47 |
| SVM decision value | 0.60 |
| SVM RNA-class probability | 0.794355 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>3L_DroMel_CAF1 11725099 94 - 23771897 AUUAACUGAGUAGCAGGCUUACUGUAUUAGUACCUUUAAUUAGCUGUCAUAAACAGCAAAUAGGCGUAAUAAUAUGAUACUAUUAAU--AGUAUGA ....(((((...((((.....)))).))))).(((...(((.(((((.....))))).))))))((((....))))((((((....)--))))).. ( -18.40) >DroSec_CAF1 37982 90 - 1 AUUAACUGAGUAGCAGGCUUACUCUAUUAGUACAUUUAAUUAGCUGUCAUUAACAGCAAAUAGACGUAAUAAUAUGAUGCUAUUAAU--A---UU- ........(((((((.......(((((((.(((.((((.((.(((((.....))))))).)))).))).))))).)))))))))...--.---..- ( -17.01) >DroSim_CAF1 32690 93 - 1 AUUAACUGAGUAGCAGGCUUGCUCUAUUACUACCUUUAAUUAGCUGUCAUAAACAGCAAAUAGACGUAAUAAUAUGAUGCUAUUGAU--AGUAUG- ....(((((((((((.......(((((((.(((.((((.((.(((((.....))))))).)))).))).))))).)))))))))..)--)))...- ( -18.41) >DroEre_CAF1 34433 92 - 1 AUAAACUUAGUAGC--GCUUGCUCUAUUAGUAUCUUUUAUUAGCUGUCACAUCCAAAUAAUGGACGUAAUAAUACGAUGCUAUUAAA--GGAAAGA ....(((.(((((.--(....).)))))))).(((((((.((((.(((...((((.....)))).(((....)))))))))).))))--))).... ( -20.70) >DroYak_CAF1 35009 95 - 1 AUUAACUUAGUGGCA-GCUUACGCUAUUAGUAGCAUUCAUUAACUGUCAUAAACAGAGAAUGAAUGUAAUAAUACGUUGCUAUUAAAAAUGUAUGA ......(((((((((-((.(((.......)))(((((((((..((((.....))))..)))))))))........))))))))))).......... ( -27.00) >consensus AUUAACUGAGUAGCAGGCUUACUCUAUUAGUACCUUUAAUUAGCUGUCAUAAACAGCAAAUAGACGUAAUAAUAUGAUGCUAUUAAU__AGUAUGA ........(((((((.......(((((((.(((.(((.(((.(((((.....))))).)))))).))).))))).)))))))))............ ( -9.63 = -10.31 + 0.68)



Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 11:12:34 2006