
| Sequence ID | 3L_DroMel_CAF1 |
|---|---|
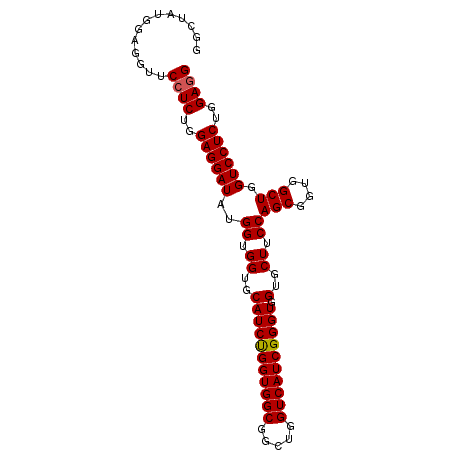
| Location | 10,775,563 – 10,775,695 |
| Length | 132 |
| Max. P | 0.979313 |

| Location | 10,775,563 – 10,775,655 |
|---|---|
| Length | 92 |
| Sequences | 4 |
| Columns | 92 |
| Reading direction | forward |
| Mean pairwise identity | 97.83 |
| Mean single sequence MFE | -42.07 |
| Consensus MFE | -41.44 |
| Energy contribution | -41.50 |
| Covariance contribution | 0.06 |
| Combinations/Pair | 1.04 |
| Mean z-score | -3.01 |
| Structure conservation index | 0.98 |
| SVM decision value | 1.83 |
| SVM RNA-class probability | 0.979313 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
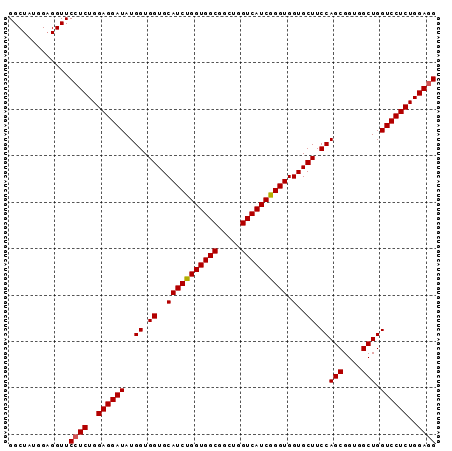
>3L_DroMel_CAF1 10775563 92 + 23771897 GGCUAUGGAGGUUCGUCUGGAGGAUAUGGUGGUGCAUCUGGUGGCGGUUGGUCAUCGGGUGGUGCUUCCAGCGGUGGCUGGUCCUCUGGAGG .............(.((..((((((..((.((..(((((((((((.....)))))))))).)..)).))(((....))).))))))..)).) ( -37.90) >DroSec_CAF1 109146 92 + 1 GGCUAUGGAGGUUCCUCUGGAGGAUAUGGUGGUGCAUCUGGUGGCGGCUGGUCAUCGGGUGGUGCUUCCAGCGGUGGCUGGUCCUCUGGAGG .............((((..((((((..((.((..(((((((((((.....)))))))))).)..)).))(((....))).))))))..)))) ( -42.30) >DroSim_CAF1 112120 92 + 1 GGCUAUGGAGGUUCCUCUGGAGGAUAUGGUGGUGCAUCUGGUGGCGGCUGGUCAUCGGGUGGUGCUUCCAGCGGUGGCUGGUCCUCUGGAGG .............((((..((((((..((.((..(((((((((((.....)))))))))).)..)).))(((....))).))))))..)))) ( -42.30) >DroYak_CAF1 125828 92 + 1 GGCUAUGGCGGUUCCUCUGGAGGAUAUGGUGGUGCAUCCGGUGGCGGCUGGUCAUCGGGUGGUGCUUCCAGCGGUGGCUGGUCCUCUGGAGG .((....))....((((..((((((..((.((..(((((((((((.....)))))))))).)..)).))(((....))).))))))..)))) ( -45.80) >consensus GGCUAUGGAGGUUCCUCUGGAGGAUAUGGUGGUGCAUCUGGUGGCGGCUGGUCAUCGGGUGGUGCUUCCAGCGGUGGCUGGUCCUCUGGAGG .............((((..((((((..((.((..(((((((((((.....)))))))))).)..)).))(((....))).))))))..)))) (-41.44 = -41.50 + 0.06)

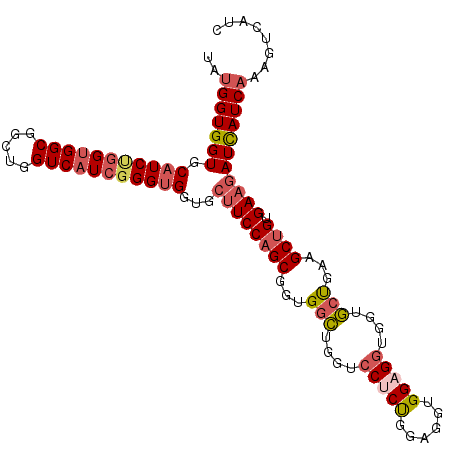
| Location | 10,775,587 – 10,775,695 |
|---|---|
| Length | 108 |
| Sequences | 5 |
| Columns | 108 |
| Reading direction | forward |
| Mean pairwise identity | 88.15 |
| Mean single sequence MFE | -42.54 |
| Consensus MFE | -33.28 |
| Energy contribution | -34.76 |
| Covariance contribution | 1.48 |
| Combinations/Pair | 1.15 |
| Mean z-score | -1.47 |
| Structure conservation index | 0.78 |
| SVM decision value | 0.02 |
| SVM RNA-class probability | 0.544315 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
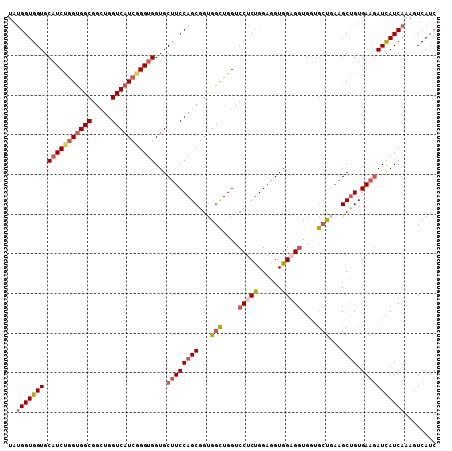
>3L_DroMel_CAF1 10775587 108 + 23771897 UAUGGUGGUGCAUCUGGUGGCGGUUGGUCAUCGGGUGGUGCUUCCAGCGGUGGCUGGUCCUCUGGAGGUGGAGGUGGUGCUGAAGCUGUGAAGAUCAUCAAAAUCAUC ..(((((((.(((((((((((.....)))))))))))...((((((((..((((....(((((......)))))....))))..)))).)))))))))))........ ( -45.10) >DroSec_CAF1 109170 108 + 1 UAUGGUGGUGCAUCUGGUGGCGGCUGGUCAUCGGGUGGUGCUUCCAGCGGUGGCUGGUCCUCUGGAGGUGGAGGUGGUGCUGAGGCUGUGAAGAUCAUCAAAGUCAUC ..(((((((.(((((((((((.....)))))))))))...((((((((..((((....(((((......)))))....))))..)))).)))))))))))........ ( -44.40) >DroSim_CAF1 112144 108 + 1 UAUGGUGGUGCAUCUGGUGGCGGCUGGUCAUCGGGUGGUGCUUCCAGCGGUGGCUGGUCCUCUGGAGGUGGCGGUGGUGCUGAAGCUGUGAAGAUCAUCAAAGUCAUC ..(((((((.(((((((((((.....)))))))))))...((((((((..((((....((.(((.......))).)).))))..)))).)))))))))))........ ( -41.50) >DroYak_CAF1 125852 108 + 1 UAUGGUGGUGCAUCCGGUGGCGGCUGGUCAUCGGGUGGUGCUUCCAGCGGUGGCUGGUCCUCUGGAGGUGGAGGUGCUGCUCAAGCCGUGAAGAUUAUCAAAGUCAUC ..(((.((..(((((((((((.....)))))))))).)..)).)))((((((((.((((((((......))))).))))))...)))))...((((.....))))... ( -42.60) >DroAna_CAF1 110002 108 + 1 UCCGGUGGUGCCUCCAGCGGCGGUUGGUCUUCCGGUGGUGCCUCCAGCGGCGGUUGGUCCUCCGGCGGUGGUGAUGCCAACACGGCUGUGAAAAUCAUCAAAAUCAUC .(((.((((..(.(((.((.(((..(..(..(((.((.((....)).)).)))..)..)..))).)).))).)..))))...)))....................... ( -39.10) >consensus UAUGGUGGUGCAUCUGGUGGCGGCUGGUCAUCGGGUGGUGCUUCCAGCGGUGGCUGGUCCUCUGGAGGUGGAGGUGGUGCUGAAGCUGUGAAGAUCAUCAAAGUCAUC ..(((((((.(((((((((((.....)))))))))))...((((((((...(((....(((((......)))))....)))...)))).)))))))))))........ (-33.28 = -34.76 + 1.48)

Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 11:04:59 2006