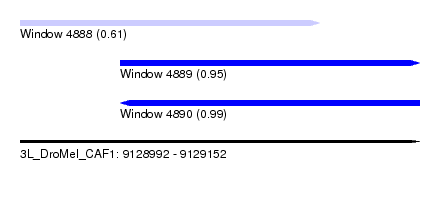
| Sequence ID | 3L_DroMel_CAF1 |
|---|---|
| Location | 9,128,992 – 9,129,152 |
| Length | 160 |
| Max. P | 0.993818 |

| Location | 9,128,992 – 9,129,112 |
|---|---|
| Length | 120 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 97.61 |
| Mean single sequence MFE | -33.85 |
| Consensus MFE | -31.75 |
| Energy contribution | -32.12 |
| Covariance contribution | 0.36 |
| Combinations/Pair | 1.03 |
| Mean z-score | -0.90 |
| Structure conservation index | 0.94 |
| SVM decision value | 0.16 |
| SVM RNA-class probability | 0.610649 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
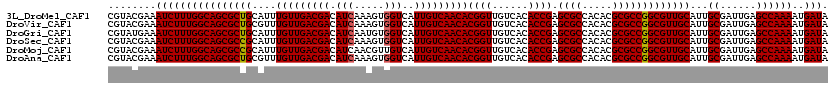
>3L_DroMel_CAF1 9128992 120 + 23771897 AUAACGAAGCAUGUUCCCAGAUAGACGUCAAUCGAUUUGACGUACGAAAUCUUUGGCAGCGCUGCAUUUGUUGACGACAUCAAAGUGGUCAUUGUCAACACGGUUGUCACACCGAGCGCC ...........((((...((((.((((((((.....))))))).)...))))..))))(((((.....(((((((((.(((.....)))..)))))))))((((......))))))))). ( -34.30) >DroVir_CAF1 7295 120 + 1 AUAACGAAGCAUGUUCCCAGAUAGACGUCAAUCGAUUUGACGUACGAAAUCUUUGGCAGCGCUGCGUUUGUUGACGACAUCAAAGUGGUCAUUGUCAACACGGUUGUCACACCGAGCGCC .......(((.((((...((((.((((((((.....))))))).)...))))..))))..)))((((((((((((((.(((.....)))..)))))))))((((......))))))))). ( -35.10) >DroGri_CAF1 4843 120 + 1 AUAACGAAGCAUGUUCCCAGAUAGACGUCAAUCGAUUUGACGUAUGAAAUCUUUGGCAGCGCUGCAUUUGUUGACGACAUCAAUGUGGUCAUUGUCAACACGGUUGUCACACCGAGCGCC ...........((((...((((..(((((((.....))))))).....))))..))))(((((.....(((((((((.(((.....)))..)))))))))((((......))))))))). ( -34.00) >DroSec_CAF1 4046 120 + 1 AUAACGAAGCAUGUUCCCAGAUAGACGUCAAUCGACUUGACGUACGAAAUCUUUGGCAGCGCCGCAUUUGUUGACGACAUCAAAGUGGUCAUUGUCAACACGGUUGUCACACCGAGCGCC ........((.((((...((((.((((((((.....))))))).)...))))..))))))..(((...(((((((((.(((.....)))..)))))))))((((......)))).))).. ( -32.00) >DroMoj_CAF1 4963 120 + 1 AUAACGAAGCAUGUUCCCAGAUAGACGUCAAUCGAUUUGACGUACGAAAUCUUUGGCAGCGCCGCAUUUGUUGACGACAUCAACGUUGUCAUUGUCAACACGGUUGUCACACCGAGCGCC ........((.((((...((((.((((((((.....))))))).)...))))..))))))..(((...(((((((((((.......))))...)))))))((((......)))).))).. ( -33.40) >DroAna_CAF1 4582 120 + 1 AUAACGAAGCAUGUUCCCAGAUAGACGUCAAUCGACUUGACGUACGAAAUCUUUGGCAGCGCUGCGUUUGUUGACGACAUCAAAGUGGUCAUUGUCAACACGGUUGUCACACCGAGCGCC .......(((.((((...((((.((((((((.....))))))).)...))))..))))..)))((((((((((((((.(((.....)))..)))))))))((((......))))))))). ( -34.30) >consensus AUAACGAAGCAUGUUCCCAGAUAGACGUCAAUCGAUUUGACGUACGAAAUCUUUGGCAGCGCUGCAUUUGUUGACGACAUCAAAGUGGUCAUUGUCAACACGGUUGUCACACCGAGCGCC ...........((((...((((.((((((((.....))))))).)...))))..))))(((((.....(((((((((.(((.....)))..)))))))))((((......))))))))). (-31.75 = -32.12 + 0.36)

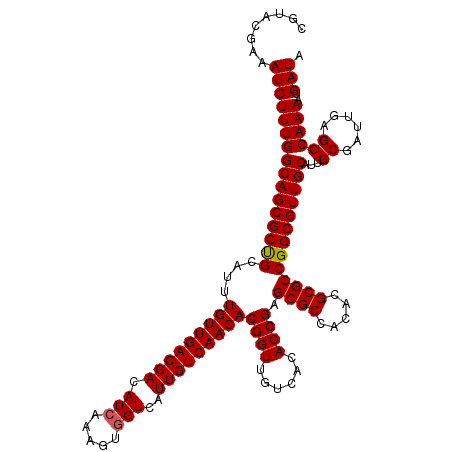
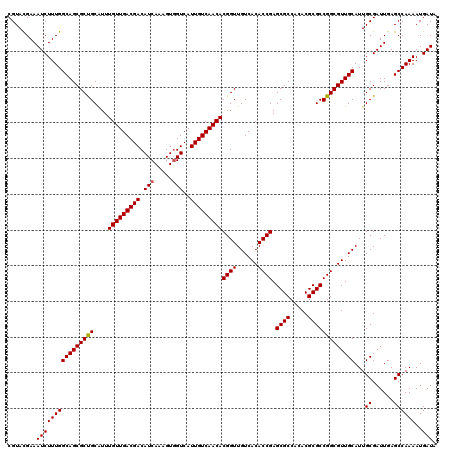
| Location | 9,129,032 – 9,129,152 |
|---|---|
| Length | 120 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 98.06 |
| Mean single sequence MFE | -38.63 |
| Consensus MFE | -38.04 |
| Energy contribution | -37.98 |
| Covariance contribution | -0.06 |
| Combinations/Pair | 1.03 |
| Mean z-score | -1.07 |
| Structure conservation index | 0.98 |
| SVM decision value | 1.38 |
| SVM RNA-class probability | 0.948404 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
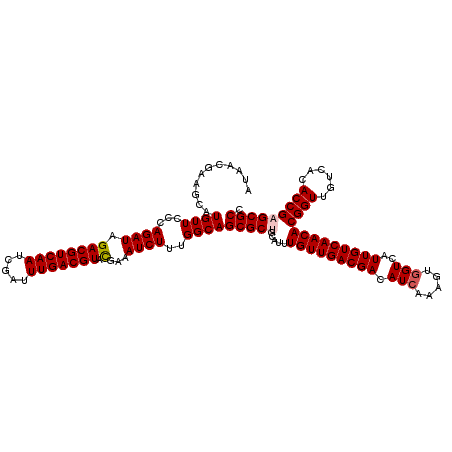
>3L_DroMel_CAF1 9129032 120 + 23771897 CGUACGAAAUCUUUGGCAGCGCUGCAUUUGUUGACGACAUCAAAGUGGUCAUUGUCAACACGGUUGUCACACCGAGCGCCACACGCGCCGGCGUUGCAUUGCGAUUGAGCCAAAAUGAUA ........((((((((((((((((....(((((((((.(((.....)))..)))))))))((((......)))).((((.....)))))))))))))...((......))))))..))). ( -37.80) >DroVir_CAF1 7335 120 + 1 CGUACGAAAUCUUUGGCAGCGCUGCGUUUGUUGACGACAUCAAAGUGGUCAUUGUCAACACGGUUGUCACACCGAGCGCCACACGCGCCGGCGUUGCAUUGCGAUUGAGCCAAAAUGAUA ........((((((((((((((((....(((((((((.(((.....)))..)))))))))((((......)))).((((.....)))))))))))))...((......))))))..))). ( -37.80) >DroGri_CAF1 4883 120 + 1 CGUAUGAAAUCUUUGGCAGCGCUGCAUUUGUUGACGACAUCAAUGUGGUCAUUGUCAACACGGUUGUCACACCGAGCGCCACACGCGCCGGCGUUGCAUUGCGAUUGAGCCAAAAUGAUA ........((((((((((((((((....(((((((((.(((.....)))..)))))))))((((......)))).((((.....)))))))))))))...((......))))))..))). ( -37.80) >DroSec_CAF1 4086 120 + 1 CGUACGAAAUCUUUGGCAGCGCCGCAUUUGUUGACGACAUCAAAGUGGUCAUUGUCAACACGGUUGUCACACCGAGCGCCACACGCGCCGGCGUUGCAUUGCGAUUGAGCCAAAAUGAUA ........((((((((((((((((....(((((((((.(((.....)))..)))))))))((((......)))).((((.....)))))))))))))...((......))))))..))). ( -40.00) >DroMoj_CAF1 5003 120 + 1 CGUACGAAAUCUUUGGCAGCGCCGCAUUUGUUGACGACAUCAACGUUGUCAUUGUCAACACGGUUGUCACACCGAGCGCCACACGCGCCGGCGUUGCAUUGCGAUUGAGCCAAAAUGAUA ........((((((((((((((((....(((((((((((.......))))...)))))))((((......)))).((((.....)))))))))))))...((......))))))..))). ( -40.60) >DroAna_CAF1 4622 120 + 1 CGUACGAAAUCUUUGGCAGCGCUGCGUUUGUUGACGACAUCAAAGUGGUCAUUGUCAACACGGUUGUCACACCGAGCGCCACACGCGCCGGCGUUGCAUUGCGAUUGAGCCAAAAUGAUA ........((((((((((((((((....(((((((((.(((.....)))..)))))))))((((......)))).((((.....)))))))))))))...((......))))))..))). ( -37.80) >consensus CGUACGAAAUCUUUGGCAGCGCUGCAUUUGUUGACGACAUCAAAGUGGUCAUUGUCAACACGGUUGUCACACCGAGCGCCACACGCGCCGGCGUUGCAUUGCGAUUGAGCCAAAAUGAUA ........((((((((((((((((....(((((((((.(((.....)))..)))))))))((((......)))).((((.....)))))))))))))...((......))))))..))). (-38.04 = -37.98 + -0.06)
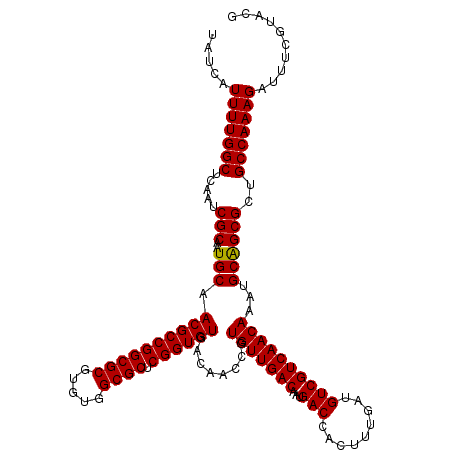
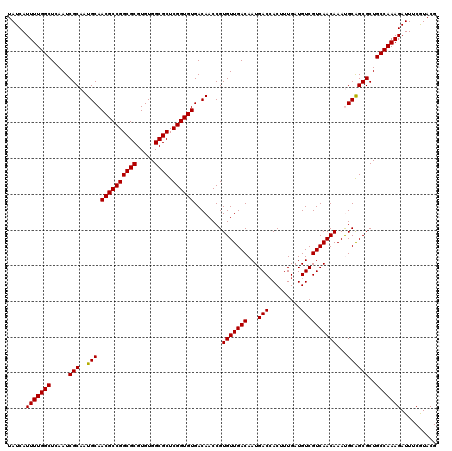
| Location | 9,129,032 – 9,129,152 |
|---|---|
| Length | 120 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 98.06 |
| Mean single sequence MFE | -40.92 |
| Consensus MFE | -39.35 |
| Energy contribution | -39.13 |
| Covariance contribution | -0.22 |
| Combinations/Pair | 1.03 |
| Mean z-score | -1.59 |
| Structure conservation index | 0.96 |
| SVM decision value | 2.43 |
| SVM RNA-class probability | 0.993818 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>3L_DroMel_CAF1 9129032 120 - 23771897 UAUCAUUUUGGCUCAAUCGCAAUGCAACGCCGGCGCGUGUGGCGCUCGGUGUGACAACCGUGUUGACAAUGACCACUUUGAUGUCGUCAACAAAUGCAGCGCUGCCAAAGAUUUCGUACG .....(((((((.....(((..((((((((((((((.....)))).))))))........(((((((...(((.........))))))))))..)))))))..))))))).......... ( -40.10) >DroVir_CAF1 7335 120 - 1 UAUCAUUUUGGCUCAAUCGCAAUGCAACGCCGGCGCGUGUGGCGCUCGGUGUGACAACCGUGUUGACAAUGACCACUUUGAUGUCGUCAACAAACGCAGCGCUGCCAAAGAUUUCGUACG .....(((((((.....(((..((..((((((((((.....)))).))))))..))...(((((.....((((.((......)).))))...))))).)))..))))))).......... ( -40.10) >DroGri_CAF1 4883 120 - 1 UAUCAUUUUGGCUCAAUCGCAAUGCAACGCCGGCGCGUGUGGCGCUCGGUGUGACAACCGUGUUGACAAUGACCACAUUGAUGUCGUCAACAAAUGCAGCGCUGCCAAAGAUUUCAUACG .....(((((((.....(((..((((((((((((((.....)))).))))))........(((((((...(((.........))))))))))..)))))))..))))))).......... ( -40.10) >DroSec_CAF1 4086 120 - 1 UAUCAUUUUGGCUCAAUCGCAAUGCAACGCCGGCGCGUGUGGCGCUCGGUGUGACAACCGUGUUGACAAUGACCACUUUGAUGUCGUCAACAAAUGCGGCGCUGCCAAAGAUUUCGUACG .....(((((((....(((((.((..((((((((((.....)))).))))))..))....(((((((...(((.........))))))))))..)))))....))))))).......... ( -41.50) >DroMoj_CAF1 5003 120 - 1 UAUCAUUUUGGCUCAAUCGCAAUGCAACGCCGGCGCGUGUGGCGCUCGGUGUGACAACCGUGUUGACAAUGACAACGUUGAUGUCGUCAACAAAUGCGGCGCUGCCAAAGAUUUCGUACG .....(((((((....(((((.((..((((((((((.....)))).))))))..))....(((((((...((((.......)))))))))))..)))))....))))))).......... ( -43.60) >DroAna_CAF1 4622 120 - 1 UAUCAUUUUGGCUCAAUCGCAAUGCAACGCCGGCGCGUGUGGCGCUCGGUGUGACAACCGUGUUGACAAUGACCACUUUGAUGUCGUCAACAAACGCAGCGCUGCCAAAGAUUUCGUACG .....(((((((.....(((..((..((((((((((.....)))).))))))..))...(((((.....((((.((......)).))))...))))).)))..))))))).......... ( -40.10) >consensus UAUCAUUUUGGCUCAAUCGCAAUGCAACGCCGGCGCGUGUGGCGCUCGGUGUGACAACCGUGUUGACAAUGACCACUUUGAUGUCGUCAACAAAUGCAGCGCUGCCAAAGAUUUCGUACG .....(((((((.....(((..(((.((((((((((.....)))).))))))........(((((((...(((.........))))))))))...))))))..))))))).......... (-39.35 = -39.13 + -0.22)

Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 10:50:25 2006