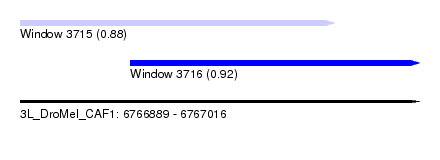
| Sequence ID | 3L_DroMel_CAF1 |
|---|---|
| Location | 6,766,889 – 6,767,016 |
| Length | 127 |
| Max. P | 0.922726 |

| Location | 6,766,889 – 6,766,989 |
|---|---|
| Length | 100 |
| Sequences | 6 |
| Columns | 100 |
| Reading direction | forward |
| Mean pairwise identity | 85.71 |
| Mean single sequence MFE | -49.33 |
| Consensus MFE | -40.55 |
| Energy contribution | -39.92 |
| Covariance contribution | -0.63 |
| Combinations/Pair | 1.29 |
| Mean z-score | -2.50 |
| Structure conservation index | 0.82 |
| SVM decision value | 0.91 |
| SVM RNA-class probability | 0.880022 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
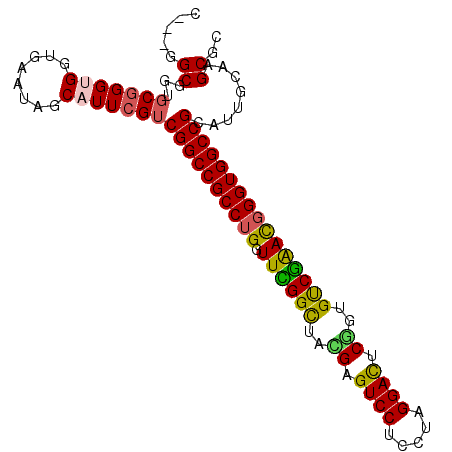
>3L_DroMel_CAF1 6766889 100 + 23771897 GGCGGGCGGAGCGGGUGGCGAAUAGCAUUCGUCGGCCGCCUGGUUCGGCUAUGAGUCCUCCUAGGAUUCGGCGUCGAAUGGGUGGCCGCAUUUCAAGCGG .((((.((..((((.((((((((...)))))))).))))((.(((((((..(((((((.....)))))))..))))))).)))).))))........... ( -47.60) >DroVir_CAF1 41859 97 + 1 C---GGCGGUGCGGGCGGUGAAUAGCAUUCGUCGGCCGCCUGGUUUGGUUACGAGUCCUCCUAGGACACAAUGCCAGACGGGUGGCCGGAAUGCAAGCGC .---.(((.(((((((((((.....)).)))))(((((((((.((((((...(.((((.....)))).)...)))))))))))))))....))))..))) ( -44.60) >DroGri_CAF1 38998 97 + 1 C---GGCGGUGCGGGUGGUGAAUAGCAUUCGUCGGCCGCCUGGUUUGGCUAUGAGUCCUCCUAGGACCCACUGCCGGACCGGUGGCCGCAUUGCAAGCGU .---.((((((((((((........)))))...(((((((.((((((((..((.((((.....)))).))..))))))))))))))))))))))...... ( -52.70) >DroMoj_CAF1 42106 97 + 1 C---GGCGGUUCGGGUGGUGAAUAGCAUUCGUCGGCCGCCUGGUUCGGCUACGAGUCCUCCUAGGACACGCUGUCGGACGGGUGGCCGCAAUGCAAGCGC .---.((((((((.....))))).(((((.(.((((((((((.((((((..((.((((.....)))).))..))))))))))))))))))))))...))) ( -47.80) >DroAna_CAF1 37279 100 + 1 GGCGGGCGGAGCGGGCGGCGAAUAGCAUUCGUCGGCCGCCUGGUUCGGCUAUGAGUCCUCCUAGGACUCGGUGUCGAACGGGUGGCCGCAGUUCAAGCGG .((.....((((..(((((((((...)))))))(((((((((.((((((..(((((((.....)))))))..))))))))))))))))).))))..)).. ( -55.00) >DroPer_CAF1 36166 100 + 1 UGCGGGCGGCGCCGGUGGGGAAUAGCAUUCGUCGGCCGCCUGGUUUGGCUACGAGUCCUCCUAGGAUUCGGUGUCGAACGGGUGGCCGCAUUUCAAGCGU .((..(((((((((..(((........)))..))))((((((.((((((..(((((((.....)))))))..))))))))))))))))).......)).. ( -48.30) >consensus C___GGCGGUGCGGGUGGUGAAUAGCAUUCGUCGGCCGCCUGGUUCGGCUACGAGUCCUCCUAGGACUCGGUGUCGAACGGGUGGCCGCAUUGCAAGCGC .....((...(((((((........)))))))((((((((((.((((((..((.((((.....)))).))..))))))))))))))))........)).. (-40.55 = -39.92 + -0.63)

| Location | 6,766,924 – 6,767,016 |
|---|---|
| Length | 92 |
| Sequences | 6 |
| Columns | 102 |
| Reading direction | forward |
| Mean pairwise identity | 76.24 |
| Mean single sequence MFE | -36.15 |
| Consensus MFE | -31.04 |
| Energy contribution | -30.15 |
| Covariance contribution | -0.89 |
| Combinations/Pair | 1.30 |
| Mean z-score | -1.33 |
| Structure conservation index | 0.86 |
| SVM decision value | 1.15 |
| SVM RNA-class probability | 0.922726 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
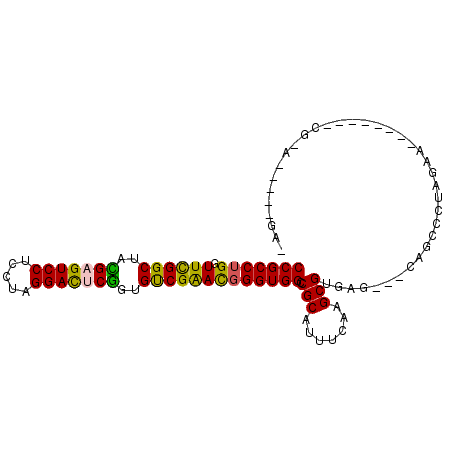
>3L_DroMel_CAF1 6766924 92 + 23771897 CCGCCUGGUUCGGCUAUGAGUCCUCCUAGGAUUCGGCGUCGAAUGGGUGGCCGCAUUUCAAGCGGGAG---CAGCCCUAGAAU-------CGUACAGUCGAA .((.((((((((((..(((((((.....)))))))..)))))))((((..((((.......))))...---..))))......-------....))).)).. ( -34.00) >DroPse_CAF1 36529 82 + 1 CCGCCUGGUUUGGCUACGAGUCCUCCUAGGAUUCGGUGUCGAACGGGUGGCCGCAUUUCAAGCGUGAGCCGCAGCCGUAGGA-------------------- ...(((((((((((..(((((((.....)))))))..)))))))((((((((((.........))).)))))..)).)))).-------------------- ( -34.80) >DroGri_CAF1 39030 92 + 1 CCGCCUGGUUUGGCUAUGAGUCCUCCUAGGACCCACUGCCGGACCGGUGGCCGCAUUGCAAGCGUGAG---CAGCCCUAGAU-------UCGUAUCCUCGAA (((((.((((((((..((.((((.....)))).))..)))))))))))))...........((....)---).........(-------(((......)))) ( -36.30) >DroMoj_CAF1 42138 97 + 1 CCGCCUGGUUCGGCUACGAGUCCUCCUAGGACACGCUGUCGGACGGGUGGCCGCAAUGCAAGCGCGAG---CAGCCCUGAAAACCAGAUGCAGAUCU--GAC (((((((.((((((..((.((((.....)))).))..)))))))))))))......((((.((....)---)....(((.....))).)))).....--... ( -37.80) >DroAna_CAF1 37314 92 + 1 CCGCCUGGUUCGGCUAUGAGUCCUCCUAGGACUCGGUGUCGAACGGGUGGCCGCAGUUCAAGCGGGAG---CAGCCCUAGAGC-------CGAACAGUCGAG (((((((.((((((..(((((((.....)))))))..))))))))))))).(((.((((..((....)---).((......))-------.)))).).)).. ( -39.20) >DroPer_CAF1 36201 82 + 1 CCGCCUGGUUUGGCUACGAGUCCUCCUAGGAUUCGGUGUCGAACGGGUGGCCGCAUUUCAAGCGUGAGCCGCAGCCGUAGGA-------------------- ...(((((((((((..(((((((.....)))))))..)))))))((((((((((.........))).)))))..)).)))).-------------------- ( -34.80) >consensus CCGCCUGGUUCGGCUACGAGUCCUCCUAGGACUCGGUGUCGAACGGGUGGCCGCAUUUCAAGCGUGAG___CAGCCCUAGAA________CG_A_____GA_ (((((((.((((((..(((((((.....)))))))..))))))))))))).(((.......)))...................................... (-31.04 = -30.15 + -0.89)

Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 10:31:36 2006