
| Sequence ID | 3L_DroMel_CAF1 |
|---|---|
| Location | 6,044,784 – 6,044,904 |
| Length | 120 |
| Max. P | 0.941041 |

| Location | 6,044,784 – 6,044,904 |
|---|---|
| Length | 120 |
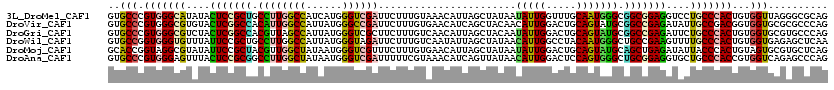
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 79.17 |
| Mean single sequence MFE | -46.47 |
| Consensus MFE | -30.98 |
| Energy contribution | -30.32 |
| Covariance contribution | -0.66 |
| Combinations/Pair | 1.53 |
| Mean z-score | -2.27 |
| Structure conservation index | 0.67 |
| SVM decision value | 1.31 |
| SVM RNA-class probability | 0.941041 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>3L_DroMel_CAF1 6044784 120 + 23771897 GUGCCCGUGGGCAUAUACUCCGCUGCCUUGGCCAUCAUGGGUCGAUUCUUUGUAAACAUUAGCUAUAAUAUUGGUUUGCAAUGGGCGGCGGAGGUCCUGCCCACUGUGGUUAGGGCGCAG (((((((((((((....((((((((((((((((......))))))....((((((((..((.......))...))))))))..))))))))))....)))))))((....)))))))).. ( -58.50) >DroVir_CAF1 149302 120 + 1 GUGCCCGUGGGCGUGUACUCGGCCACAUUGGCCAUUAUGGGCCGAUUCUUUGUGAACAUCAGCUACAACAUUGGACUGCAGUAUGCGGCCGAGAUAUUGCCGACGGUGGUGCGCGCCCAG .......(((((((((.(((((((..(((((((......))))))).....(((.((..((((((......))).)))..)).))))))))))..((..((...))..))))))))))). ( -50.40) >DroGri_CAF1 147064 120 + 1 GUGCCCGUGGGCGUCUACUCGGCCACGUUAGCCAUUAUGGGUCGCUUCUUUGUCAACAUUAGCUACAAUAUUGGACUGCAGUAUGCGGCCGAGAUUCUGCCCACUGUGGUGCGUGCCCAG (..((((((((((....(((((((.(((((((((.(((..((.(((....((....))..))).)).))).))).)))....))).)))))))....))))))).).))..)........ ( -46.30) >DroWil_CAF1 223937 120 + 1 GUGCCGGUGGGUGUUUAUUCCGCUGCCUUGGCCAUUAUGGGUAGAUUCUUUGUCAAUAUUAGCUAUAACAUUGGCCUACAAUGGGCUGCCGAAGUUUUGCCCACUGUGGUGAGAGCUCAA ....(((((((((....(((.((.((((.(((((((((((.(((((.....))).....)).))))))...)))))......)))).)).)))....)))))))))((((....)).)). ( -39.70) >DroMoj_CAF1 117389 120 + 1 GCACCGGUAGGCGUAUAUUCCGCUACGUUGGCUAUAAUGGGUCGUUUCUUUGUGAACAUUAGCUAUAAUAUUGGACUGCAGUAUGCAGCUGAGAUAUUACCCACUGUAGUGCGUGCUCAG (((((.((((.((.......))))))....((((((.(((((.((.((..((....))((((((...((((((.....))))))..)))))))).)).))))).))))))).)))).... ( -35.80) >DroAna_CAF1 107894 120 + 1 GUGCCCGUGGGAGUUUACUCCGCGGCCUUGGCUAUAAUGGGUCGAUUUUUCGUAAACAUCAGUUAUAACAUUGGACUCCAGUGGGCUGCGGAGGUGCUGCCCACCGUGGUCAGAGCCCAG ..((((((((((((...((((((((((.(((((...(((..((((....))).)..))).)))))...((((((...))))))))))))))))..))).)))).)).))).......... ( -48.10) >consensus GUGCCCGUGGGCGUAUACUCCGCUACCUUGGCCAUUAUGGGUCGAUUCUUUGUAAACAUUAGCUAUAACAUUGGACUGCAGUAGGCGGCCGAGAUACUGCCCACUGUGGUGAGAGCCCAG ..(((.(((((((....(((((((.((((((((......)))))).......................(((((.....))))))).)))))))....)))))))...))).......... (-30.98 = -30.32 + -0.66)

| Location | 6,044,784 – 6,044,904 |
|---|---|
| Length | 120 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 79.17 |
| Mean single sequence MFE | -38.72 |
| Consensus MFE | -21.94 |
| Energy contribution | -21.58 |
| Covariance contribution | -0.36 |
| Combinations/Pair | 1.42 |
| Mean z-score | -1.94 |
| Structure conservation index | 0.57 |
| SVM decision value | 0.44 |
| SVM RNA-class probability | 0.736229 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
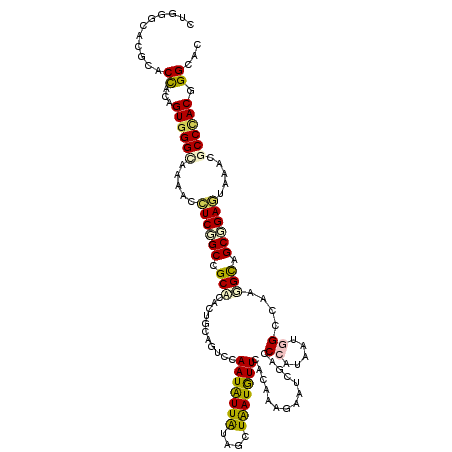
>3L_DroMel_CAF1 6044784 120 - 23771897 CUGCGCCCUAACCACAGUGGGCAGGACCUCCGCCGCCCAUUGCAAACCAAUAUUAUAGCUAAUGUUUACAAAGAAUCGACCCAUGAUGGCCAAGGCAGCGGAGUAUAUGCCCACGGGCAC ....((((........(((((((....((((((.(((....((.....(((((((....)))))))........((((.....)))).))...))).))))))....))))))))))).. ( -40.30) >DroVir_CAF1 149302 120 - 1 CUGGGCGCGCACCACCGUCGGCAAUAUCUCGGCCGCAUACUGCAGUCCAAUGUUGUAGCUGAUGUUCACAAAGAAUCGGCCCAUAAUGGCCAAUGUGGCCGAGUACACGCCCACGGGCAC .(((.......)))((((.(((.....(((((((((((.((((((.......))))))...................((((......)))).))))))))))).....))).)))).... ( -46.50) >DroGri_CAF1 147064 120 - 1 CUGGGCACGCACCACAGUGGGCAGAAUCUCGGCCGCAUACUGCAGUCCAAUAUUGUAGCUAAUGUUGACAAAGAAGCGACCCAUAAUGGCUAACGUGGCCGAGUAGACGCCCACGGGCAC ........((.((...((((((.....(((((((((........(((.(((((((....)))))))))).....(((.(.......).)))...))))))))).....)))))))))).. ( -42.70) >DroWil_CAF1 223937 120 - 1 UUGAGCUCUCACCACAGUGGGCAAAACUUCGGCAGCCCAUUGUAGGCCAAUGUUAUAGCUAAUAUUGACAAAGAAUCUACCCAUAAUGGCCAAGGCAGCGGAAUAAACACCCACCGGCAC ....((.....(((((((((((....(....)..))))))))).(((((.(((((..........)))))..(........)....)))))..))...(((............))))).. ( -29.70) >DroMoj_CAF1 117389 120 - 1 CUGAGCACGCACUACAGUGGGUAAUAUCUCAGCUGCAUACUGCAGUCCAAUAUUAUAGCUAAUGUUCACAAAGAAACGACCCAUUAUAGCCAACGUAGCGGAAUAUACGCCUACCGGUGC ....((((...(((.(((((((....(((..(((((.....)))))..(((((((....))))))).....)))....))))))).))).....((((((.......)).))))..)))) ( -30.30) >DroAna_CAF1 107894 120 - 1 CUGGGCUCUGACCACGGUGGGCAGCACCUCCGCAGCCCACUGGAGUCCAAUGUUAUAACUGAUGUUUACGAAAAAUCGACCCAUUAUAGCCAAGGCCGCGGAGUAAACUCCCACGGGCAC ...((((..(((..((((((((.((......)).))))))))..)))............(((((..(.(((....))))..))))).))))..(.(((.((((....))))..))).).. ( -42.80) >consensus CUGGGCACGCACCACAGUGGGCAAAACCUCGGCCGCACACUGCAGUCCAAUAUUAUAGCUAAUGUUCACAAAGAAUCGACCCAUAAUGGCCAAGGCAGCGGAGUAAACGCCCACGGGCAC ...........((...((((((.....((((((.(((...........(((((((....)))))))..............((.....))....))).)))))).....)))))).))... (-21.94 = -21.58 + -0.36)


Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 10:26:37 2006