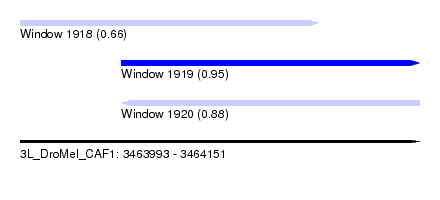
| Sequence ID | 3L_DroMel_CAF1 |
|---|---|
| Location | 3,463,993 – 3,464,151 |
| Length | 158 |
| Max. P | 0.945926 |

| Location | 3,463,993 – 3,464,111 |
|---|---|
| Length | 118 |
| Sequences | 4 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 88.33 |
| Mean single sequence MFE | -30.19 |
| Consensus MFE | -19.42 |
| Energy contribution | -20.23 |
| Covariance contribution | 0.81 |
| Combinations/Pair | 1.03 |
| Mean z-score | -2.46 |
| Structure conservation index | 0.64 |
| SVM decision value | 0.25 |
| SVM RNA-class probability | 0.655178 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>3L_DroMel_CAF1 3463993 118 + 23771897 UAGCGUAAGGAAUCCAUAAAUUUAAAAUGAAGCCGUCGUAGUAAAUCGCUUCGCAAAUUGUAAUAGAACCCUAAGCGACUGCGUAGAAUUCUAUA--AAUAUGAUAUUGAAUGGUUUGCC ..(((...((....(((.........)))...))..))).((((((((.((((...((..((((((((..(((.((....)).)))..)))))).--..))..))..)))))))))))). ( -21.20) >DroSec_CAF1 11161 117 + 1 UAGCGUACGGAAU-CAUAAAUUUAAAAUGAAGCCGUCGUGGUAAAUCGCUCCGCAAAUUGUAAUAGAACCCUAAGCGACUGCGGAGCAUUCUAUA--AAUAUGAUAUUGAAUGGUUUGCC ..(((.((((..(-(((.........))))..)))))))((((((((((((((((..((((..(((....))).)))).))))))))((((.(((--.......))).)))))))))))) ( -38.00) >DroSim_CAF1 11266 117 + 1 UAGCGUACGGAAU-CAUAAAUUUAAAAUGAAGCCGUCGUGGUAAAUCGCUCCGCAAAUUGUAAUAGAACCCUAAGCGACUGCGGAGCAUUCUAUA--AAUAUGAUAUUGAAUGGUUUGCC ..(((.((((..(-(((.........))))..)))))))((((((((((((((((..((((..(((....))).)))).))))))))((((.(((--.......))).)))))))))))) ( -38.00) >DroYak_CAF1 11627 109 + 1 CAGC-----------AUAAAUUUAAAAUGAAGGUGUCGUGGUAAAUCGCUCUGCAAAUUGCAAAAGAACACUAAGCGAUUGCCGAGCAUUCUAAAAAAAUAUGAUAUUGAAUGGUUUGCC ..((-----------((...(((.....))).))))...((((((((((((.((((.((((.............)))))))).))))((((.................)))))))))))) ( -23.55) >consensus UAGCGUACGGAAU_CAUAAAUUUAAAAUGAAGCCGUCGUGGUAAAUCGCUCCGCAAAUUGUAAUAGAACCCUAAGCGACUGCGGAGCAUUCUAUA__AAUAUGAUAUUGAAUGGUUUGCC ..........................((((.....))))((((((((((((((((..((((...((....))..)))).))))))))((((.................)))))))))))) (-19.42 = -20.23 + 0.81)

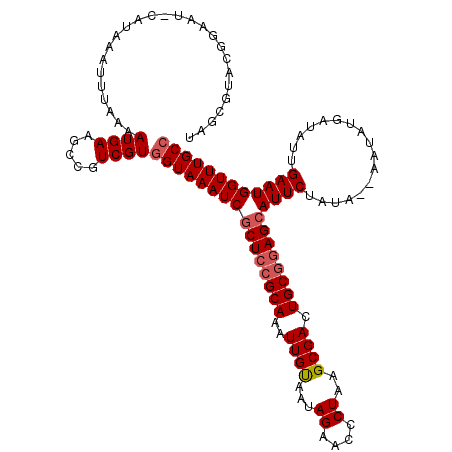
| Location | 3,464,033 – 3,464,151 |
|---|---|
| Length | 118 |
| Sequences | 4 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 94.54 |
| Mean single sequence MFE | -24.93 |
| Consensus MFE | -21.89 |
| Energy contribution | -22.45 |
| Covariance contribution | 0.56 |
| Combinations/Pair | 1.04 |
| Mean z-score | -2.36 |
| Structure conservation index | 0.88 |
| SVM decision value | 1.36 |
| SVM RNA-class probability | 0.945926 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>3L_DroMel_CAF1 3464033 118 + 23771897 GUAAAUCGCUUCGCAAAUUGUAAUAGAACCCUAAGCGACUGCGUAGAAUUCUAUA--AAUAUGAUAUUGAAUGGUUUGCCACUGCAACCAUUAUCCUAAUUACACAGCCACACACCCAAC ((((.........(((((..((((((((..(((.((....)).)))..)))))).--..))..)).)))(((((((.((....))))))))).......))))................. ( -19.60) >DroSec_CAF1 11200 118 + 1 GUAAAUCGCUCCGCAAAUUGUAAUAGAACCCUAAGCGACUGCGGAGCAUUCUAUA--AAUAUGAUAUUGAAUGGUUUGCCACUGCAACCAUUAUCCUAAUUACACAGCCACACACCCAAC ((((...((((((((..((((..(((....))).)))).))))))))........--............(((((((.((....))))))))).......))))................. ( -28.00) >DroSim_CAF1 11305 118 + 1 GUAAAUCGCUCCGCAAAUUGUAAUAGAACCCUAAGCGACUGCGGAGCAUUCUAUA--AAUAUGAUAUUGAAUGGUUUGCCACUGCAACCAUUAUCCUAAUUACACAGCCACACACCCAAC ((((...((((((((..((((..(((....))).)))).))))))))........--............(((((((.((....))))))))).......))))................. ( -28.00) >DroYak_CAF1 11656 120 + 1 GUAAAUCGCUCUGCAAAUUGCAAAAGAACACUAAGCGAUUGCCGAGCAUUCUAAAAAAAUAUGAUAUUGAAUGGUUUGCCAGUGCAACCAUUAUCCUAAUUACACAGCCACACACCCAAC ((((...((((.((((.((((.............)))))))).))))......................(((((((.((....))))))))).......))))................. ( -24.12) >consensus GUAAAUCGCUCCGCAAAUUGUAAUAGAACCCUAAGCGACUGCGGAGCAUUCUAUA__AAUAUGAUAUUGAAUGGUUUGCCACUGCAACCAUUAUCCUAAUUACACAGCCACACACCCAAC ((((...((((((((..((((...((....))..)))).))))))))......................(((((((.((....))))))))).......))))................. (-21.89 = -22.45 + 0.56)


| Location | 3,464,033 – 3,464,151 |
|---|---|
| Length | 118 |
| Sequences | 4 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 94.54 |
| Mean single sequence MFE | -34.17 |
| Consensus MFE | -30.29 |
| Energy contribution | -31.10 |
| Covariance contribution | 0.81 |
| Combinations/Pair | 1.03 |
| Mean z-score | -1.97 |
| Structure conservation index | 0.89 |
| SVM decision value | 0.92 |
| SVM RNA-class probability | 0.882299 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>3L_DroMel_CAF1 3464033 118 - 23771897 GUUGGGUGUGUGGCUGUGUAAUUAGGAUAAUGGUUGCAGUGGCAAACCAUUCAAUAUCAUAUU--UAUAGAAUUCUACGCAGUCGCUUAGGGUUCUAUUACAAUUUGCGAAGCGAUUUAC .....(((.((.(((.(((((....((((((((((((....)).))))))....)))).....--.(((((((((((.((....)).)))))))))))......))))).))).)).))) ( -30.80) >DroSec_CAF1 11200 118 - 1 GUUGGGUGUGUGGCUGUGUAAUUAGGAUAAUGGUUGCAGUGGCAAACCAUUCAAUAUCAUAUU--UAUAGAAUGCUCCGCAGUCGCUUAGGGUUCUAUUACAAUUUGCGGAGCGAUUUAC ((((((((.((.((((((((((((......)))))))).))))..))))))))))........--..((((.((((((((((.....(((....))).......)))))))))).)))). ( -35.40) >DroSim_CAF1 11305 118 - 1 GUUGGGUGUGUGGCUGUGUAAUUAGGAUAAUGGUUGCAGUGGCAAACCAUUCAAUAUCAUAUU--UAUAGAAUGCUCCGCAGUCGCUUAGGGUUCUAUUACAAUUUGCGGAGCGAUUUAC ((((((((.((.((((((((((((......)))))))).))))..))))))))))........--..((((.((((((((((.....(((....))).......)))))))))).)))). ( -35.40) >DroYak_CAF1 11656 120 - 1 GUUGGGUGUGUGGCUGUGUAAUUAGGAUAAUGGUUGCACUGGCAAACCAUUCAAUAUCAUAUUUUUUUAGAAUGCUCGGCAAUCGCUUAGUGUUCUUUUGCAAUUUGCAGAGCGAUUUAC ((((((((.((.((((((((((((......))))))))).)))..))))))))))(((..........((((((((.(((....))).))))))))(((((.....)))))..))).... ( -35.10) >consensus GUUGGGUGUGUGGCUGUGUAAUUAGGAUAAUGGUUGCAGUGGCAAACCAUUCAAUAUCAUAUU__UAUAGAAUGCUCCGCAGUCGCUUAGGGUUCUAUUACAAUUUGCGGAGCGAUUUAC ((((((((.((.((((((((((((......)))))))).))))..))))))))))............((((.((((((((((.....(((....))).......)))))))))).)))). (-30.29 = -31.10 + 0.81)


Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 10:02:28 2006