
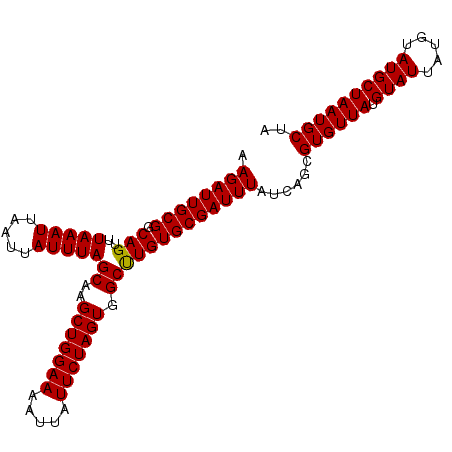
| Sequence ID | 3L_DroMel_CAF1 |
|---|---|
| Location | 382,473 – 382,574 |
| Length | 101 |
| Max. P | 0.819307 |

| Location | 382,473 – 382,574 |
|---|---|
| Length | 101 |
| Sequences | 5 |
| Columns | 101 |
| Reading direction | forward |
| Mean pairwise identity | 98.02 |
| Mean single sequence MFE | -22.48 |
| Consensus MFE | -22.04 |
| Energy contribution | -21.80 |
| Covariance contribution | -0.24 |
| Combinations/Pair | 1.03 |
| Mean z-score | -1.29 |
| Structure conservation index | 0.98 |
| SVM decision value | 0.68 |
| SVM RNA-class probability | 0.819307 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
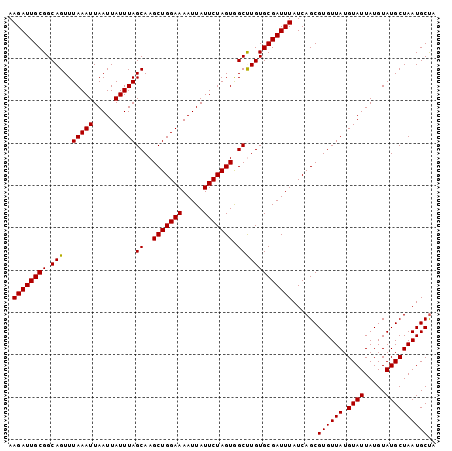
>3L_DroMel_CAF1 382473 101 + 23771897 AAGAUUGCGGCAGUUUAAAUUAAUUAUUUAGCAAGCUGGAAAAUUAUUCUAGUGGCUUGUGCGAUUUAUCAGCGUGUUAUGUAUUAUGUAUGCUAAUGCUA .(((((((.......(((((.....)))))(((((((((((.....))))...))))))))))))))...(((((.....((((.....))))..))))). ( -22.10) >DroSec_CAF1 36569 101 + 1 AAGAUUGCGGCAGUUUAAAUUAAUUAUUUAGCAAGCUGGAAAAUUAUUCUAGUAGCUUGUGCGAUUUAUCAGCGUGUUAUGUAUUAUGUAUGCUAAUGCUA .(((((((.......(((((.....)))))(((((((((((.....))))...))))))))))))))...(((((.....((((.....))))..))))). ( -22.10) >DroSim_CAF1 37321 101 + 1 AAGAUUGCGGCAGUUUAAAUUAAUUAUUUAGCAAGCUGGAAAAUUAUUCUAGUGGCUUGUGCGAUUUAUCAGCGUGUUAUGUAUUAUGUAUGCUAAUGCUA .(((((((.......(((((.....)))))(((((((((((.....))))...))))))))))))))...(((((.....((((.....))))..))))). ( -22.10) >DroEre_CAF1 39992 101 + 1 AAGAUUGCGGCAGUUUAAAUUAAUUAUUUAGCAAGCUGGAAAAUUAUUCUAGUGGCCUGUGCGAUUUAUCAGCGUGUUAUGUAUUAUGUAUGCUAAUGCUU .((((((((.(((..(((((.....)))))((..(((((((.....))))))).)))))))))))))......((((((.((((.....)))))))))).. ( -23.10) >DroYak_CAF1 38529 101 + 1 AAGAUUGCGGCAGUUUAAAUUAAUUAUUUAGCAAGCUGGAAAAUUAUUCUAGUGGCCUGUGCGAUUUAUCAGCGUGUUAUGUAUUAUGUAUGCUAAUGCCU .((((((((.(((..(((((.....)))))((..(((((((.....))))))).)))))))))))))...((.((((((.((((.....)))))))))))) ( -23.00) >consensus AAGAUUGCGGCAGUUUAAAUUAAUUAUUUAGCAAGCUGGAAAAUUAUUCUAGUGGCUUGUGCGAUUUAUCAGCGUGUUAUGUAUUAUGUAUGCUAAUGCUA .((((((((.(((..(((((.....)))))((..(((((((.....))))))).)))))))))))))......((((((.((((.....)))))))))).. (-22.04 = -21.80 + -0.24)

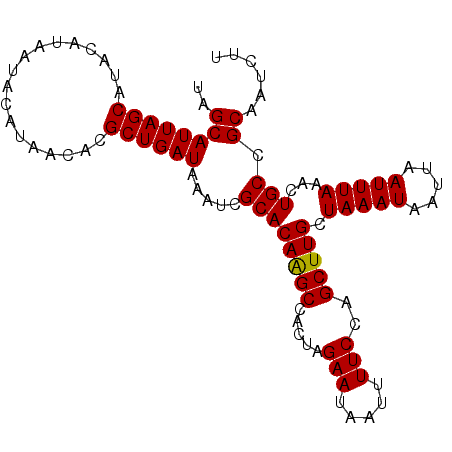
| Location | 382,473 – 382,574 |
|---|---|
| Length | 101 |
| Sequences | 5 |
| Columns | 101 |
| Reading direction | reverse |
| Mean pairwise identity | 98.02 |
| Mean single sequence MFE | -13.29 |
| Consensus MFE | -12.65 |
| Energy contribution | -12.41 |
| Covariance contribution | -0.24 |
| Combinations/Pair | 1.04 |
| Mean z-score | -1.17 |
| Structure conservation index | 0.95 |
| SVM decision value | 0.04 |
| SVM RNA-class probability | 0.554265 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
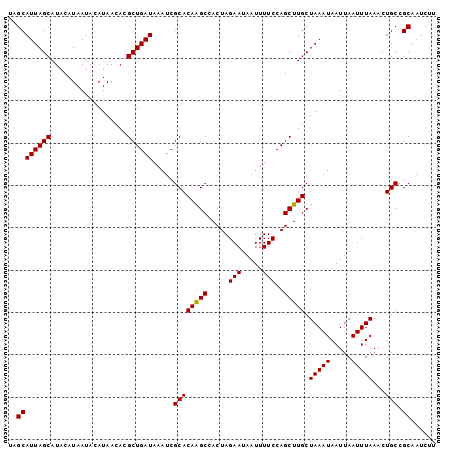
>3L_DroMel_CAF1 382473 101 - 23771897 UAGCAUUAGCAUACAUAAUACAUAACACGCUGAUAAAUCGCACAAGCCACUAGAAUAAUUUUCCAGCUUGCUAAAUAAUUAAUUUAAACUGCCGCAAUCUU ..((((((((..................)))))).....((((((((.....(((.....)))..))))).(((((.....)))))...))).))...... ( -12.57) >DroSec_CAF1 36569 101 - 1 UAGCAUUAGCAUACAUAAUACAUAACACGCUGAUAAAUCGCACAAGCUACUAGAAUAAUUUUCCAGCUUGCUAAAUAAUUAAUUUAAACUGCCGCAAUCUU ..((((((((..................)))))).....(((((((((....(((.....))).)))))).(((((.....)))))...))).))...... ( -14.37) >DroSim_CAF1 37321 101 - 1 UAGCAUUAGCAUACAUAAUACAUAACACGCUGAUAAAUCGCACAAGCCACUAGAAUAAUUUUCCAGCUUGCUAAAUAAUUAAUUUAAACUGCCGCAAUCUU ..((((((((..................)))))).....((((((((.....(((.....)))..))))).(((((.....)))))...))).))...... ( -12.57) >DroEre_CAF1 39992 101 - 1 AAGCAUUAGCAUACAUAAUACAUAACACGCUGAUAAAUCGCACAGGCCACUAGAAUAAUUUUCCAGCUUGCUAAAUAAUUAAUUUAAACUGCCGCAAUCUU ..((((((((..................))))))..........(((...((((.(((((....((....))....))))).))))....)))))...... ( -13.27) >DroYak_CAF1 38529 101 - 1 AGGCAUUAGCAUACAUAAUACAUAACACGCUGAUAAAUCGCACAGGCCACUAGAAUAAUUUUCCAGCUUGCUAAAUAAUUAAUUUAAACUGCCGCAAUCUU .(((((((((..................))))))........(((((.....(((.....)))..)))))....................)))........ ( -13.67) >consensus UAGCAUUAGCAUACAUAAUACAUAACACGCUGAUAAAUCGCACAAGCCACUAGAAUAAUUUUCCAGCUUGCUAAAUAAUUAAUUUAAACUGCCGCAAUCUU ..((((((((..................)))))).....((((((((.....(((.....)))..))))).(((((.....)))))...))).))...... (-12.65 = -12.41 + -0.24)

Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 09:32:50 2006