
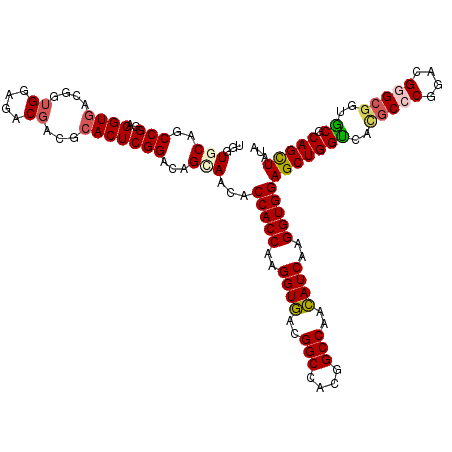
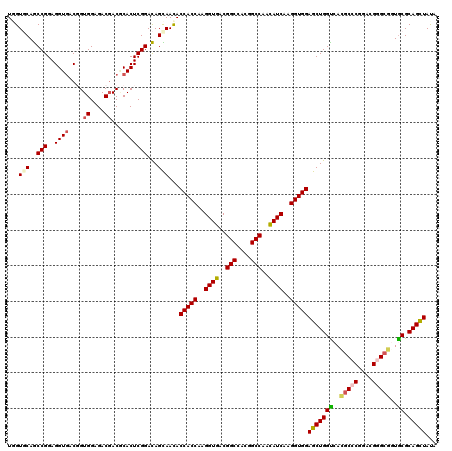
| Sequence ID | 2R_DroMel_CAF1 |
|---|---|
| Location | 4,176,015 – 4,176,174 |
| Length | 159 |
| Max. P | 0.977878 |

| Location | 4,176,015 – 4,176,135 |
|---|---|
| Length | 120 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 90.72 |
| Mean single sequence MFE | -52.58 |
| Consensus MFE | -44.39 |
| Energy contribution | -44.70 |
| Covariance contribution | 0.31 |
| Combinations/Pair | 1.17 |
| Mean z-score | -2.16 |
| Structure conservation index | 0.84 |
| SVM decision value | 0.85 |
| SVM RNA-class probability | 0.867337 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2R_DroMel_CAF1 4176015 120 + 20766785 UGGUGCAGCCGGAGGUGACGGUGGAGACGACGCACUCGGACAGCAACACCACCAAGGUGACGGCCACGGCCAACAUCAAGGUGGAGCUGGCCAUGCCCGGCAGGGCGGUGCGCAGCUAUA ((.(((..(((..((((.((.((....)).)))))))))...))).))(((((..((((..(((....)))..))))..)))))(((((((..(((((....)))))..)).)))))... ( -55.20) >DroVir_CAF1 1426 120 + 1 UCGUGCAGCCGGAGGUGACCGUGGAGACGACACACUCGGACAGCAACACCACCAAGGUGACGGCCACGGCCAACAUCAAGGUGGAGCUGGUCACGCCCGGACGUGCGGUGCGCAGCUACA (((..(..((((..(((((((((.......)))........(((....(((((..((((..(((....)))..))))..))))).)))))))))..))))..)..)))............ ( -49.40) >DroWil_CAF1 3377 120 + 1 UGGUUCAACCGGAGGUUACUGUGGAGACCACCCACUCGGAUAGUAAUACCACCAAGGUAACGGCCACGGCCAAUAUCAAGGUGGAGCUGGUCACACCCGGACGAGCCGUACGCAGUUAUA .(((((..((((((....))(((..(((((((((((..((((....((((.....))))..(((....)))..))))..))))).).))))).)))))))..)))))............. ( -46.60) >DroYak_CAF1 3342 120 + 1 UGGUGCAGCCGGAGGUGACGGUGGAGACGACCCACUCGGACAGCAACACCACCAAGGUGACGGCCACGGCCAACAUCAAGGUGGAGCUGGCCAUGCCCGGCAGGGCGUUGCGCAGCUAUA ((.(((..(((..((((..((((....).))))))))))...))).))(((((..((((..(((....)))..))))..)))))(((((((.((((((....)))))).)).)))))... ( -56.00) >DroAna_CAF1 3417 120 + 1 UGGUGCAGCCGGAGGUGACGGUGGAGACGACGCACUCGGACAGUAACACCACCAAGGUGACGGCCACGGCCAACAUCAAGGUGGAGCUGGUGACGCCCGGACGGGCGAUGCGCAGCUACA ((.(((..(((..((((.((.((....)).)))))))))...))).))(((((..((((..(((....)))..))))..)))))((((((((.(((((....))))).))).)))))... ( -53.50) >DroPer_CAF1 3785 120 + 1 UUGUCCAGCCGGAGGUGACGGUGGAGACGACGCACUCGGACAGCAACACCACCAAGGUGACGGCCACGGCCAACAUCAAGGUGGAGCUGGUCACGCCCGGGCGGGCGGUGCGCAGCUAUA ((((((.((((.......)))).(((........))))))))).....(((((..((((..(((....)))..))))..)))))(((((((..(((((....)))))..)).)))))... ( -54.80) >consensus UGGUGCAGCCGGAGGUGACGGUGGAGACGACGCACUCGGACAGCAACACCACCAAGGUGACGGCCACGGCCAACAUCAAGGUGGAGCUGGUCACGCCCGGACGGGCGGUGCGCAGCUAUA ...(((..(((..((((....((....))...)))))))...)))...(((((..((((..(((....)))..))))..)))))(((((((..(((((....)))))..)).)))))... (-44.39 = -44.70 + 0.31)

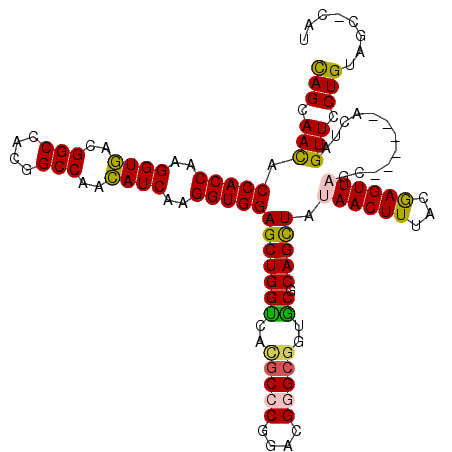
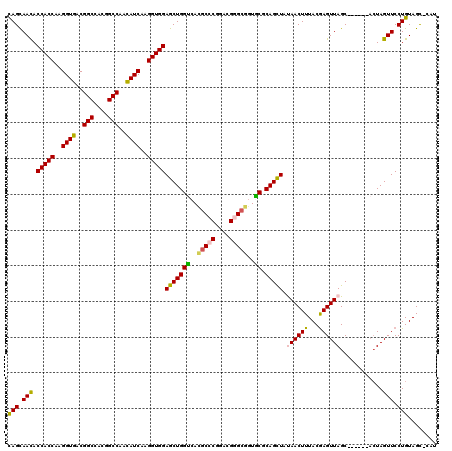
| Location | 4,176,055 – 4,176,174 |
|---|---|
| Length | 119 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 88.77 |
| Mean single sequence MFE | -42.68 |
| Consensus MFE | -39.75 |
| Energy contribution | -39.53 |
| Covariance contribution | -0.22 |
| Combinations/Pair | 1.22 |
| Mean z-score | -1.90 |
| Structure conservation index | 0.93 |
| SVM decision value | 1.80 |
| SVM RNA-class probability | 0.977878 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2R_DroMel_CAF1 4176055 119 + 20766785 CAGCAACACCACCAAGGUGACGGCCACGGCCAACAUCAAGGUGGAGCUGGCCAUGCCCGGCAGGGCGGUGCGCAGCUAUAACUUUACGAGUUAGCACUAGCACUAGUUCCUGUAGC-UAU ..((....(((((..((((..(((....)))..))))..)))))(((((((..(((((....)))))..)).))))).((((((...))))))))..((((((........)).))-)). ( -47.30) >DroVir_CAF1 1466 119 + 1 CAGCAACACCACCAAGGUGACGGCCACGGCCAACAUCAAGGUGGAGCUGGUCACGCCCGGACGUGCGGUGCGCAGCUACAACUUUACGAGUUAGCCCUGGCACUAGUUCCUGUAGC-CAU ..((.(((..(((..((((..(((....)))..))))..)))(((((((((...(((.((..((((...)))).((((..((((...)))))))))).))))))))))))))).))-... ( -43.30) >DroPse_CAF1 3318 113 + 1 CAGCAACACCACCAAGGUGACGGCCACGGCCAACAUCAAGGUGGAGCUGGUCACGCCCGGGCGGGCGGUGCGCAGCUAUAACUUUACGAGUUAGC------ACUAGUUCCUGUAGC-CAU (((.(((.(((((..((((..(((....)))..))))..)))))(((((((..(((((....)))))..)).))))).((((((...))))))..------....))).)))....-... ( -45.80) >DroWil_CAF1 3417 115 + 1 UAGUAAUACCACCAAGGUAACGGCCACGGCCAAUAUCAAGGUGGAGCUGGUCACACCCGGACGAGCCGUACGCAGUUAUAACUUUACGAGUUAGCACU-----UAGUUCCUGUAGUAUCC ........(((((..((((..(((....)))..))))..))))).(((.(((.......))).))).((((((((...((((((...))))))((...-----..))..)))).)))).. ( -30.50) >DroAna_CAF1 3457 113 + 1 CAGUAACACCACCAAGGUGACGGCCACGGCCAACAUCAAGGUGGAGCUGGUGACGCCCGGACGGGCGAUGCGCAGCUACAACUUUACAAGUUAGC------ACUAGUUCCUGUAGC-CAU (((.(((.(((((..((((..(((....)))..))))..)))))((((((((.(((((....))))).))).)))))..................------....))).)))....-... ( -43.40) >DroPer_CAF1 3825 113 + 1 CAGCAACACCACCAAGGUGACGGCCACGGCCAACAUCAAGGUGGAGCUGGUCACGCCCGGGCGGGCGGUGCGCAGCUAUAACUUUACGAGUUAGC------ACUAGUUCCUGUAGC-CAU (((.(((.(((((..((((..(((....)))..))))..)))))(((((((..(((((....)))))..)).))))).((((((...))))))..------....))).)))....-... ( -45.80) >consensus CAGCAACACCACCAAGGUGACGGCCACGGCCAACAUCAAGGUGGAGCUGGUCACGCCCGGACGGGCGGUGCGCAGCUAUAACUUUACGAGUUAGC______ACUAGUUCCUGUAGC_CAU (((.(((.(((((..((((..(((....)))..))))..)))))(((((((..(((((....)))))..)).))))).((((((...))))))............))).)))........ (-39.75 = -39.53 + -0.22)

Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 09:53:38 2006