
| Sequence ID | 2R_DroMel_CAF1 |
|---|---|
| Location | 18,414,161 – 18,414,281 |
| Length | 120 |
| Max. P | 0.957613 |

| Location | 18,414,161 – 18,414,262 |
|---|---|
| Length | 101 |
| Sequences | 5 |
| Columns | 118 |
| Reading direction | forward |
| Mean pairwise identity | 80.34 |
| Mean single sequence MFE | -27.58 |
| Consensus MFE | -14.90 |
| Energy contribution | -15.58 |
| Covariance contribution | 0.68 |
| Combinations/Pair | 1.17 |
| Mean z-score | -1.93 |
| Structure conservation index | 0.54 |
| SVM decision value | 0.13 |
| SVM RNA-class probability | 0.595677 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2R_DroMel_CAF1 18414161 101 + 20766785 UGGAUAUAUCCAAAAUACAACUGCU-----------------UAAAACCUAGUCUAUCGAGUUCCACGAUCUAUCUGCAGAUAGGUCGCUGUAUACAGUUGUAUCUGCAACCGACAGU ((((....))))..(((((((((..-----------------((........((....))....(((((((((((....))))))))).))))..)))))))))((((....).))). ( -24.30) >DroSec_CAF1 2176 106 + 1 ---AUGUAUCCA-AAUACAACUGCU-------UU-AAAUGUUUAAUACCUAGUUCAUCUAGUUCCACGAUCUAUCUGCAGAUGGGUCGCUGCAUGCAGAUGUAUCUGCAACCGACAGU ---.(((((...-.)))))(((((.-------..-..((((.......((((.....)))).....(((((((((....)))))))))..))))(((((....)))))....).)))) ( -26.00) >DroSim_CAF1 2255 109 + 1 UGGAUGUAUCCA-AAUACAACUGCU-------UU-AAAUGCUUAAAACCUAGUUCAUCUAGUUCCACGAUCUAUCUGCAGAUGGGUCGCUGCAUGCAGAUGUAUCUGCAACCGACAGU .((.((((....-.(((((.((((.-------..-..((((.......((((.....)))).....(((((((((....)))))))))..)))))))).))))).)))).))...... ( -29.60) >DroEre_CAF1 2372 110 + 1 UGGAUGUAUCCA-AGUACAUCUAAU-------UCAAGAUGUUUAAGACUUAGUGCAUCUAGUUCCAUGAUCUAUCUGCGAAUGGGUCGCUGUAUACAGCUGUAUCUGCAAGCGACAGU (((((((((..(-(((((((((...-------...)))))).....)))).)))))))))...((((...(.....)...))))((((((((((((....))))..)).))))))... ( -30.60) >DroYak_CAF1 2274 116 + 1 UGGAUGUAUCCA-AU-UCAACUAAUUAGGUGUUCAAAAUGUAUAAAAGCUAGUCCAUCUAGUUACAUGAUCUAUCUGCAGAUGGUUCGCUGUAUACAGAUGUAUCUGCAGCUGACAGU ((((....))))-..-(((..((((((((((..(.....((......))..)..))))))))))..)))((...(((((((((.....(((....)))...)))))))))..)).... ( -27.40) >consensus UGGAUGUAUCCA_AAUACAACUGCU_______UC_AAAUGUUUAAAACCUAGUCCAUCUAGUUCCACGAUCUAUCUGCAGAUGGGUCGCUGUAUACAGAUGUAUCUGCAACCGACAGU .(((((((((......................................((((.....))))...(((((((((((....))))))))).))......)))))))))............ (-14.90 = -15.58 + 0.68)

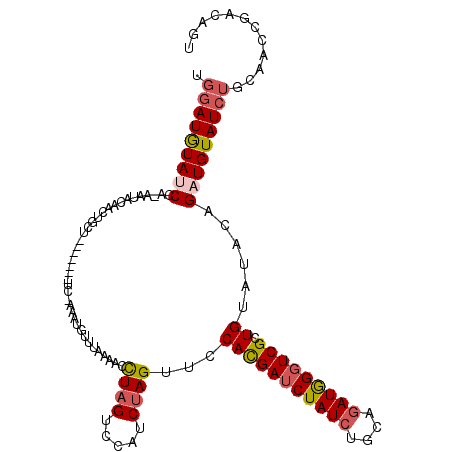

| Location | 18,414,186 – 18,414,281 |
|---|---|
| Length | 95 |
| Sequences | 5 |
| Columns | 97 |
| Reading direction | forward |
| Mean pairwise identity | 88.87 |
| Mean single sequence MFE | -27.42 |
| Consensus MFE | -19.10 |
| Energy contribution | -18.74 |
| Covariance contribution | -0.36 |
| Combinations/Pair | 1.17 |
| Mean z-score | -1.88 |
| Structure conservation index | 0.70 |
| SVM decision value | 0.03 |
| SVM RNA-class probability | 0.546495 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2R_DroMel_CAF1 18414186 95 + 20766785 --UAAAACCUAGUCUAUCGAGUUCCACGAUCUAUCUGCAGAUAGGUCGCUGUAUACAGUUGUAUCUGCAACCGACAGUGACAACCAAAUGAGGCUGA --.......((((((((((.......))))(((((....)))))((((((((.....(((((....)))))..)))))))).........)))))). ( -26.40) >DroSec_CAF1 2204 97 + 1 UUUAAUACCUAGUUCAUCUAGUUCCACGAUCUAUCUGCAGAUGGGUCGCUGCAUGCAGAUGUAUCUGCAACCGACAGUGACAACCAAAUGGGGCUGA ..................((((((((....(((((....)))))((((((((.((((((....))))))...).))))))).......)))))))). ( -30.60) >DroSim_CAF1 2286 97 + 1 CUUAAAACCUAGUUCAUCUAGUUCCACGAUCUAUCUGCAGAUGGGUCGCUGCAUGCAGAUGUAUCUGCAACCGACAGUGACAACCAAAUGGGGCUGA ..................((((((((....(((((....)))))((((((((.((((((....))))))...).))))))).......)))))))). ( -30.60) >DroEre_CAF1 2404 97 + 1 UUUAAGACUUAGUGCAUCUAGUUCCAUGAUCUAUCUGCGAAUGGGUCGCUGUAUACAGCUGUAUCUGCAAGCGACAGUGACAACCAAAUGAGGCUGA ....((.((((.((((..(((.((...)).)))..))))..(((((((((((.....(((((....)).))).))))))))..)))..)))).)).. ( -23.70) >DroYak_CAF1 2312 97 + 1 UAUAAAAGCUAGUCCAUCUAGUUACAUGAUCUAUCUGCAGAUGGUUCGCUGUAUACAGAUGUAUCUGCAGCUGACAGUGACAACCAAAUGAGGCUGA .........((((((((...(((((.((.((...(((((((((.....(((....)))...)))))))))..)))))))))......))).))))). ( -25.80) >consensus UUUAAAACCUAGUCCAUCUAGUUCCACGAUCUAUCUGCAGAUGGGUCGCUGUAUACAGAUGUAUCUGCAACCGACAGUGACAACCAAAUGAGGCUGA .........((((((((...(((.(((((((((((....))))))))((.(.((((....))))).))........)))..)))...))).))))). (-19.10 = -18.74 + -0.36)

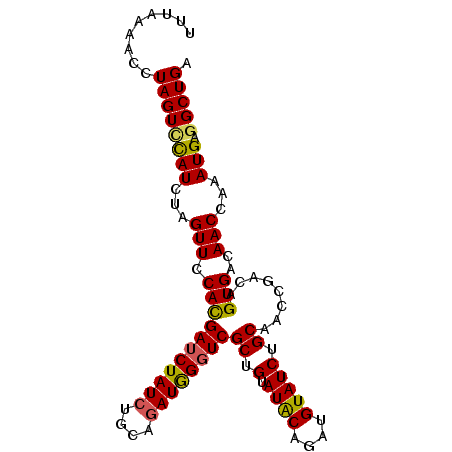
| Location | 18,414,186 – 18,414,281 |
|---|---|
| Length | 95 |
| Sequences | 5 |
| Columns | 97 |
| Reading direction | reverse |
| Mean pairwise identity | 88.87 |
| Mean single sequence MFE | -28.06 |
| Consensus MFE | -23.28 |
| Energy contribution | -24.16 |
| Covariance contribution | 0.88 |
| Combinations/Pair | 1.07 |
| Mean z-score | -1.99 |
| Structure conservation index | 0.83 |
| SVM decision value | 1.48 |
| SVM RNA-class probability | 0.957613 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2R_DroMel_CAF1 18414186 95 - 20766785 UCAGCCUCAUUUGGUUGUCACUGUCGGUUGCAGAUACAACUGUAUACAGCGACCUAUCUGCAGAUAGAUCGUGGAACUCGAUAGACUAGGUUUUA-- .(((((......)))))...(((((((((.(..((((....))))...((((.(((((....))))).))))).))).))))))...........-- ( -28.50) >DroSec_CAF1 2204 97 - 1 UCAGCCCCAUUUGGUUGUCACUGUCGGUUGCAGAUACAUCUGCAUGCAGCGACCCAUCUGCAGAUAGAUCGUGGAACUAGAUGAACUAGGUAUUAAA ...(((.(((((((((.((((.(((..((((((((...((.((.....))))...))))))))...))).))))))))))))).....)))...... ( -29.50) >DroSim_CAF1 2286 97 - 1 UCAGCCCCAUUUGGUUGUCACUGUCGGUUGCAGAUACAUCUGCAUGCAGCGACCCAUCUGCAGAUAGAUCGUGGAACUAGAUGAACUAGGUUUUAAG ..((((.(((((((((.((((.(((..((((((((...((.((.....))))...))))))))...))).))))))))))))).....))))..... ( -29.50) >DroEre_CAF1 2404 97 - 1 UCAGCCUCAUUUGGUUGUCACUGUCGCUUGCAGAUACAGCUGUAUACAGCGACCCAUUCGCAGAUAGAUCAUGGAACUAGAUGCACUAAGUCUUAAA .(((((......)))))..((((((((((((((......)))))...))))))......(((..(((.((...)).)))..)))....)))...... ( -24.80) >DroYak_CAF1 2312 97 - 1 UCAGCCUCAUUUGGUUGUCACUGUCAGCUGCAGAUACAUCUGUAUACAGCGAACCAUCUGCAGAUAGAUCAUGUAACUAGAUGGACUAGCUUUUAUA ..(((.(((((((((((.((..(((..((((((((....(((....)))......))))))))...)))..)))))))))))))....)))...... ( -28.00) >consensus UCAGCCUCAUUUGGUUGUCACUGUCGGUUGCAGAUACAUCUGUAUACAGCGACCCAUCUGCAGAUAGAUCGUGGAACUAGAUGAACUAGGUUUUAAA .......(((((((((.((((.(((..((((((((....(((....)))......))))))))...))).))))))))))))).............. (-23.28 = -24.16 + 0.88)


Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 11:55:08 2006