
| Sequence ID | 2R_DroMel_CAF1 |
|---|---|
| Location | 16,074,643 – 16,074,759 |
| Length | 116 |
| Max. P | 0.925964 |

| Location | 16,074,643 – 16,074,759 |
|---|---|
| Length | 116 |
| Sequences | 4 |
| Columns | 116 |
| Reading direction | forward |
| Mean pairwise identity | 90.72 |
| Mean single sequence MFE | -43.15 |
| Consensus MFE | -33.42 |
| Energy contribution | -34.41 |
| Covariance contribution | 1.00 |
| Combinations/Pair | 1.11 |
| Mean z-score | -2.67 |
| Structure conservation index | 0.77 |
| SVM decision value | 1.17 |
| SVM RNA-class probability | 0.925964 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
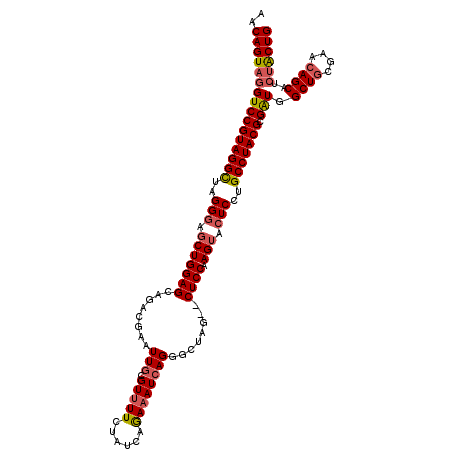
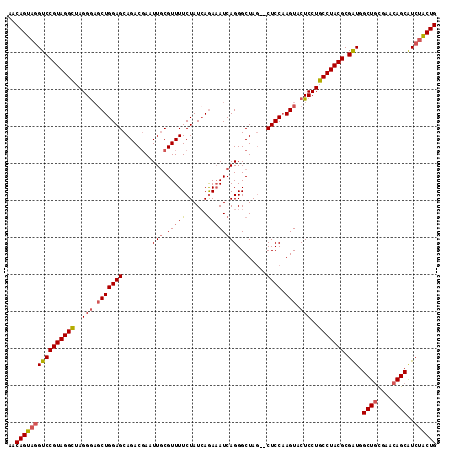
>2R_DroMel_CAF1 16074643 116 + 20766785 AACAGUAGGUCCGUAGGCUAGGGAUCUGGAGCAGACGAAUUGCGUUUUCUAUCAGAAAUCAGGGCUAGUACUCCAAGUACUCCUGCCUACGCGAUGGCUGCGAACAGCGUCUACUG ..((((((((((((((((..((..(((((((.(((((.....))))).)).)))))..)).(((..(((((.....))))))))))))))).))).((((....))))..)))))) ( -44.30) >DroSec_CAF1 2785 114 + 1 AACAGUAGGUCCGUAGGCUAGGAAGCUGGAGCAGACGAAUUCCGUUUUCUAUCAGAAAUCAGGGCUAG--CUCCAAGUACUCCUGCCUACGCGGUGGCUGCGAACAGCAUCUACUG ..((((((((((((((((.((((.((((((((((......(((..((((.....))))...))))).)--)))).)))..))))))))))).)...((((....)))))))))))) ( -44.80) >DroSim_CAF1 2799 114 + 1 AACAGUAGGUCCGUAGGCGAGGGAGCUGGAGCAGACGAAUUGCGUUUUCUAUCAGAAAUCAGGGCUAG--CUCCAAGUACUCCUGCCUACGCGAUGGCUGCGAACAGCAUCUACUG ..(((((((((((((((((.(((.((((((((.((((.....))))(((.....)))..........)--)))).))).))).)))))))).))).((((....))))..)))))) ( -46.10) >DroYak_CAF1 2868 114 + 1 AACAGUAAGUCCGUAGGUUAGGGUGCUGGAGCAGACCAAUUGCGUUUUCUAUAAAAUAUCAGGGCUAU--CUCCCAGUACUCCUGCCUACGCGAUGGCUUUGAACAGCGUCGGCUG ..(((...((((((((((..(((((((((((.((.((......(((((....))))).....))))..--)).)))))))))..))))))).)))....)))..((((....)))) ( -37.40) >consensus AACAGUAGGUCCGUAGGCUAGGGAGCUGGAGCAGACGAAUUGCGUUUUCUAUCAGAAAUCAGGGCUAG__CUCCAAGUACUCCUGCCUACGCGAUGGCUGCGAACAGCAUCUACUG ..((((((((((((((((..(((.(((((((........(((.(((((......))))))))........)))).))).)))..))))))).))).((((....))))..)))))) (-33.42 = -34.41 + 1.00)

| Location | 16,074,643 – 16,074,759 |
|---|---|
| Length | 116 |
| Sequences | 4 |
| Columns | 116 |
| Reading direction | reverse |
| Mean pairwise identity | 90.72 |
| Mean single sequence MFE | -39.85 |
| Consensus MFE | -28.24 |
| Energy contribution | -28.92 |
| Covariance contribution | 0.69 |
| Combinations/Pair | 1.09 |
| Mean z-score | -2.27 |
| Structure conservation index | 0.71 |
| SVM decision value | 0.29 |
| SVM RNA-class probability | 0.672284 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
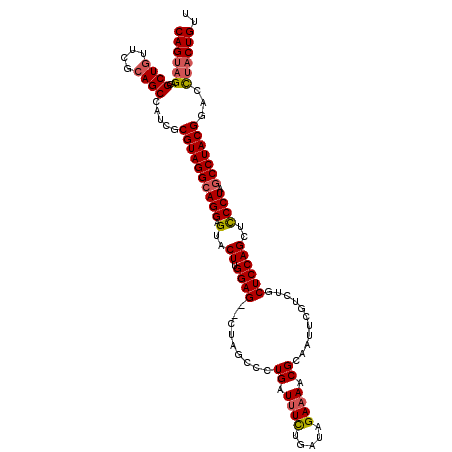
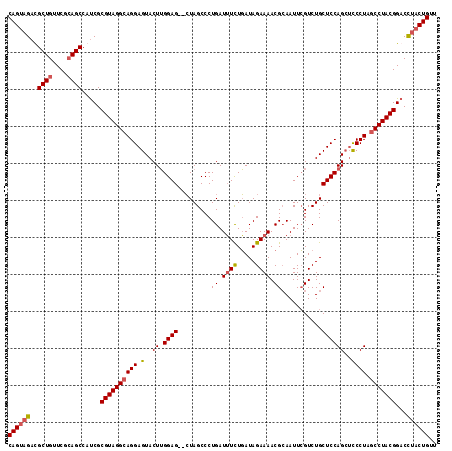
>2R_DroMel_CAF1 16074643 116 - 20766785 CAGUAGACGCUGUUCGCAGCCAUCGCGUAGGCAGGAGUACUUGGAGUACUAGCCCUGAUUUCUGAUAGAAAACGCAAUUCGUCUGCUCCAGAUCCCUAGCCUACGGACCUACUGUU ((((((..((((....))))..((.((((((((((.(...((((((((.......((.((((.....))))...)).......))))))))..)))).))))))))).)))))).. ( -40.14) >DroSec_CAF1 2785 114 - 1 CAGUAGAUGCUGUUCGCAGCCACCGCGUAGGCAGGAGUACUUGGAG--CUAGCCCUGAUUUCUGAUAGAAAACGGAAUUCGUCUGCUCCAGCUUCCUAGCCUACGGACCUACUGUU ((((((..((((....)))).....((((((((((((...((((((--(..((...((.(((((........))))).))))..))))))).))))).)))))))...)))))).. ( -47.00) >DroSim_CAF1 2799 114 - 1 CAGUAGAUGCUGUUCGCAGCCAUCGCGUAGGCAGGAGUACUUGGAG--CUAGCCCUGAUUUCUGAUAGAAAACGCAAUUCGUCUGCUCCAGCUCCCUCGCCUACGGACCUACUGUU ((((((..((((....))))..((.(((((((.(((((...(((((--(..((..((.((((.....))))...))....))..)))))))))))...))))))))).)))))).. ( -44.00) >DroYak_CAF1 2868 114 - 1 CAGCCGACGCUGUUCAAAGCCAUCGCGUAGGCAGGAGUACUGGGAG--AUAGCCCUGAUAUUUUAUAGAAAACGCAAUUGGUCUGCUCCAGCACCCUAACCUACGGACUUACUGUU (((.(((.(((......)))..)))((((((.(((.((.((((.((--.(((.((........................)).))))))))).)))))..))))))......))).. ( -28.26) >consensus CAGUAGACGCUGUUCGCAGCCAUCGCGUAGGCAGGAGUACUUGGAG__CUAGCCCUGAUUUCUGAUAGAAAACGCAAUUCGUCUGCUCCAGCUCCCUAGCCUACGGACCUACUGUU ((((((..((((....)))).....((((((((((.(..((.((((.........((.((((.....)))).))...........))))))..)))).)))))))...)))))).. (-28.24 = -28.92 + 0.69)

Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 11:32:18 2006