| Sequence ID | 2R_DroMel_CAF1 |
|---|---|
| Location | 15,176,287 – 15,176,385 |
| Length | 98 |
| Max. P | 0.977441 |

| Location | 15,176,287 – 15,176,385 |
|---|---|
| Length | 98 |
| Sequences | 6 |
| Columns | 119 |
| Reading direction | forward |
| Mean pairwise identity | 78.33 |
| Mean single sequence MFE | -23.99 |
| Consensus MFE | -14.36 |
| Energy contribution | -14.53 |
| Covariance contribution | 0.17 |
| Combinations/Pair | 1.00 |
| Mean z-score | -2.72 |
| Structure conservation index | 0.60 |
| SVM decision value | 1.79 |
| SVM RNA-class probability | 0.977441 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2R_DroMel_CAF1 15176287 98 + 20766785 UUAAAAUUAUAGCACGAGUGUUCGGUCUAGUCACUUCG---CUU-AAUC------G----AAAC---C----UUUCUUUGAAAAAGAGACCAUACCGACAUUCGCCAUUCAAUUUUAAA ((((((((......(((((((.((((...(((..((((---...-...)------)----))..---.----..((((.....)))))))...)))))))))))......)))))))). ( -22.40) >DroVir_CAF1 4974 100 + 1 UUAAAAUUAUAGCACGAGUGUUCGGUCUAGUCACUUUA---UAUAGAUA--A--UG----GUAU---A----UUG-UUUGAAAAAGCGACCAUACCGACAAUCGCCAUUUAAUUUUAAA (((((((((.....(((.(((.((((...(((.((((.---..((((((--(--((----...)---)----)))-))))..)))).)))...))))))).))).....))))))))). ( -24.50) >DroPse_CAF1 11510 95 + 1 CUAAAAUUAUAGCACGAGUGUUCGGUCUAGUCACUUCG---CUU-GAUC------G----GAAC---C----CU---GGUAAAAAGCGACCAAACCGACAAUCGCCAUUUAAUUUUAAA .((((((((.....(((.(((.((((.........(((---(((-.(((------(----(...---.----))---)))...))))))....))))))).))).....)))))))).. ( -24.02) >DroGri_CAF1 3066 103 + 1 UUAAAAUUAUAGCACGAGUGUUCGGUCUAGUCACUUUA---UAUAUAUUGUAUAUA----GAGU---U----UAG-GUUC-AAAAGCGACCAUACCGACAAUCGCCAUUUAAUUUUAAA (((((((((.....(((.(((.((((...(((((((((---(((((...)))))))----))))---.----...-((..-....)))))...))))))).))).....))))))))). ( -26.00) >DroWil_CAF1 36701 111 + 1 UUAAAAUUAUAGCACGAGUGUUCGGUCUAGUCACUUUCUUAUUA-GAUU------GGCAAAAACAAACAAGAUUU-UUGGAAAAAGAGACUAUACCGACAAUCGCCAUUCAAUUUUAAA ((((((((......(((.(((.((((.(((((.(..(((....)-))..------).(((((((......).)))-)))........))))).))))))).)))......)))))))). ( -24.40) >DroAna_CAF1 2694 102 + 1 UUAAAAUUAUAGCACGAGUGUUCGGUCUAGUCACUUCG---CUU-GUUG------G----UAAC---CAAUUUUUUUGUGAAAAAGCGACCAUACCGACAAUCGCCAUUCAAUUUUAAA ((((((((......(((.(((.((((...(((.(((((---(..-((((------(----...)---))))......))))...)).)))...))))))).)))......)))))))). ( -22.60) >consensus UUAAAAUUAUAGCACGAGUGUUCGGUCUAGUCACUUCG___CUU_GAUC______G____GAAC___C____UUU_UUUGAAAAAGCGACCAUACCGACAAUCGCCAUUCAAUUUUAAA ((((((((......(((.(((.((((...(((.(((...............................................))).)))...))))))).)))......)))))))). (-14.36 = -14.53 + 0.17)


| Location | 15,176,287 – 15,176,385 |
|---|---|
| Length | 98 |
| Sequences | 6 |
| Columns | 119 |
| Reading direction | reverse |
| Mean pairwise identity | 78.33 |
| Mean single sequence MFE | -28.72 |
| Consensus MFE | -25.87 |
| Energy contribution | -25.43 |
| Covariance contribution | -0.44 |
| Combinations/Pair | 1.13 |
| Mean z-score | -3.55 |
| Structure conservation index | 0.90 |
| SVM decision value | 1.64 |
| SVM RNA-class probability | 0.969476 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
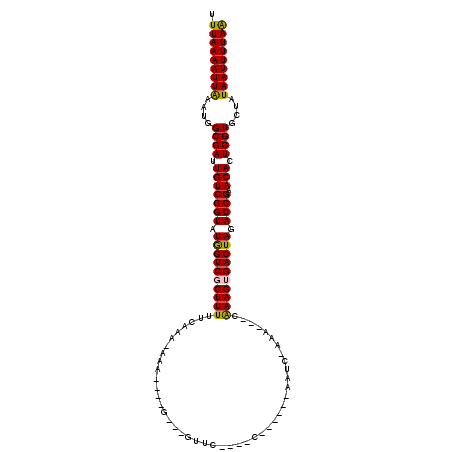
>2R_DroMel_CAF1 15176287 98 - 20766785 UUUAAAAUUGAAUGGCGAAUGUCGGUAUGGUCUCUUUUUCAAAGAAA----G---GUUU----C------GAUU-AAG---CGAAGUGACUAGACCGAACACUCGUGCUAUAAUUUUAA .(((((((((....((((.(((((((.(((((((((((.....))))----)---)(((----(------(...-...---))))).))))).)))).))).))))....))))))))) ( -27.30) >DroVir_CAF1 4974 100 - 1 UUUAAAAUUAAAUGGCGAUUGUCGGUAUGGUCGCUUUUUCAAA-CAA----U---AUAC----CA--U--UAUCUAUA---UAAAGUGACUAGACCGAACACUCGUGCUAUAAUUUUAA .(((((((((....((((.(((((((.((((((((((......-..(----(---(((.----..--.--....))))---))))))))))).)))).))).))))....))))))))) ( -28.10) >DroPse_CAF1 11510 95 - 1 UUUAAAAUUAAAUGGCGAUUGUCGGUUUGGUCGCUUUUUACC---AG----G---GUUC----C------GAUC-AAG---CGAAGUGACUAGACCGAACACUCGUGCUAUAAUUUUAG ..((((((((....((((.((((((((((((((((((.....---.(----(---...)----)------....-...---.))))))))))))))).))).))))....)))))))). ( -32.44) >DroGri_CAF1 3066 103 - 1 UUUAAAAUUAAAUGGCGAUUGUCGGUAUGGUCGCUUUU-GAAC-CUA----A---ACUC----UAUAUACAAUAUAUA---UAAAGUGACUAGACCGAACACUCGUGCUAUAAUUUUAA .(((((((((....((((.(((((((.(((((((((..-((..-...----.---..))----((((((.....))))---))))))))))).)))).))).))))....))))))))) ( -28.30) >DroWil_CAF1 36701 111 - 1 UUUAAAAUUGAAUGGCGAUUGUCGGUAUAGUCUCUUUUUCCAA-AAAUCUUGUUUGUUUUUGCC------AAUC-UAAUAAGAAAGUGACUAGACCGAACACUCGUGCUAUAAUUUUAA .(((((((((....((((.(((((((.(((((.((((((.(((-((((.......)))))))..------....-.....)))))).))))).)))).))).))))....))))))))) ( -27.50) >DroAna_CAF1 2694 102 - 1 UUUAAAAUUGAAUGGCGAUUGUCGGUAUGGUCGCUUUUUCACAAAAAAAUUG---GUUA----C------CAAC-AAG---CGAAGUGACUAGACCGAACACUCGUGCUAUAAUUUUAA .(((((((((....((((.(((((((.((((((((((....(((.....)))---(((.----.------....-.))---))))))))))).)))).))).))))....))))))))) ( -28.70) >consensus UUUAAAAUUAAAUGGCGAUUGUCGGUAUGGUCGCUUUUUCAAA_AAA____G___GUUC____C______AAUC_AAA___CAAAGUGACUAGACCGAACACUCGUGCUAUAAUUUUAA .(((((((((....((((.(((((((.((((((((((.............................................)))))))))).)))).))).))))....))))))))) (-25.87 = -25.43 + -0.44)

Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 11:25:43 2006