
| Sequence ID | 2R_DroMel_CAF1 |
|---|---|
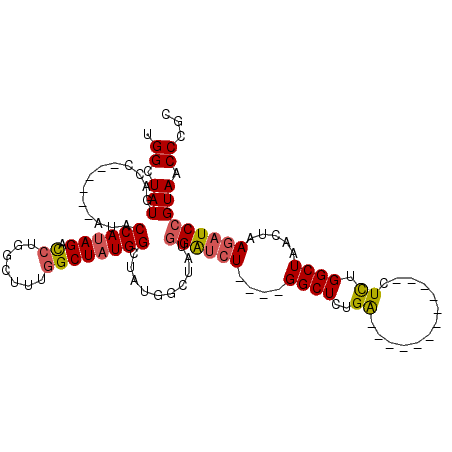
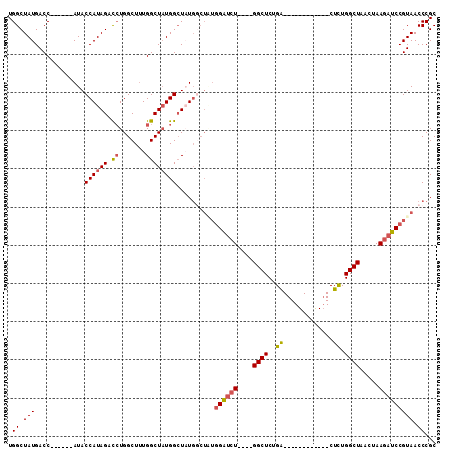
| Location | 14,454,618 – 14,454,708 |
| Length | 90 |
| Max. P | 0.972632 |

| Location | 14,454,618 – 14,454,708 |
|---|---|
| Length | 90 |
| Sequences | 5 |
| Columns | 112 |
| Reading direction | forward |
| Mean pairwise identity | 79.56 |
| Mean single sequence MFE | -34.48 |
| Consensus MFE | -17.20 |
| Energy contribution | -17.56 |
| Covariance contribution | 0.36 |
| Combinations/Pair | 1.16 |
| Mean z-score | -2.65 |
| Structure conservation index | 0.50 |
| SVM decision value | 1.70 |
| SVM RNA-class probability | 0.972632 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2R_DroMel_CAF1 14454618 90 + 20766785 UGGCUAUGACC------AUACCAUAGAUCUGGCUUUGGCUAUGGCUAUGGCUAUGGAUCU----GGCUCUGA------------CUCUGGCUAACUAAGAUCCGUAACCCGC .(((((((.((------((((((.((......)).))).))))).)))))))((((((((----((((....------------....)))).....))))))))....... ( -29.60) >DroSec_CAF1 86806 90 + 1 UGGCUAUGACCAUAGCCAUACCAUAGACCUGGCUUUGGCUAUGGCUAU------GGAUCU----GGCUCUGA------------CUCUGGCUAACUAAGAUCCGUAACCCGC (((((((....)))))))..((((((.((.......)))))))).(((------((((((----((((....------------....)))).....)))))))))...... ( -31.60) >DroSim_CAF1 88089 96 + 1 UGGCUAUGACCAUAGCCAUACCAUAGACCUGGCUUUGGCUAUGGCUAUGGCUGUGGAUCU----GGCUCUGA------------CUCUGGCUAACUAAGAUCCGUAACCCGC .((.((((.(((((((((((((((((.((.......)))))))).)))))))))))...(----((((....------------....))))).........)))).))... ( -37.30) >DroEre_CAF1 88324 102 + 1 UGGCUAUGACC------AUACCAUAGACCUGGCUUUGGCUUUGGCUUUGGCUAUGGAUCU----GGCUCUGACUCUGGCUCUAGCUCUGGCUAACUAAGAUCCGUAACCCGC .(((((((...------....))))).)).((((..(((....)))..))))((((((((----((((........)))).((((....))))....))))))))....... ( -30.50) >DroYak_CAF1 89376 106 + 1 UGGCUAUGACC------AUACCAUAGCCAUGGCUAUGGCUAUGGAUCUGCCUCUCGGAGUCAGAGGCUCUGGCUCUGGCUUUUGCUUUGGCUAACUAAGAUCCGUAACCCGC ((((((((...------....)))))))).......((.(((((((((((((((.......))))))..(((((..(((....)))..)))))....))))))))).))... ( -43.40) >consensus UGGCUAUGACC______AUACCAUAGACCUGGCUUUGGCUAUGGCUAUGGCUAUGGAUCU____GGCUCUGA____________CUCUGGCUAACUAAGAUCCGUAACCCGC .((.(((.............((((((.((.......))))))))..........((((((....((((..((.............)).)))).....))))))))).))... (-17.20 = -17.56 + 0.36)

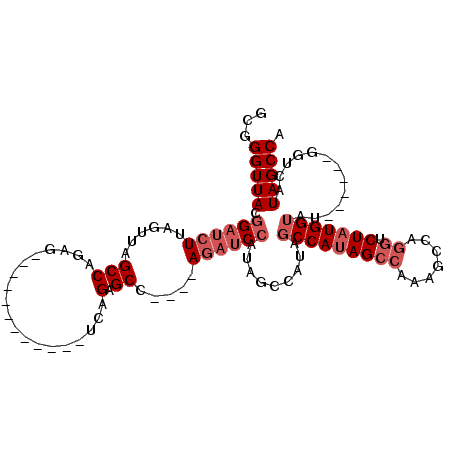
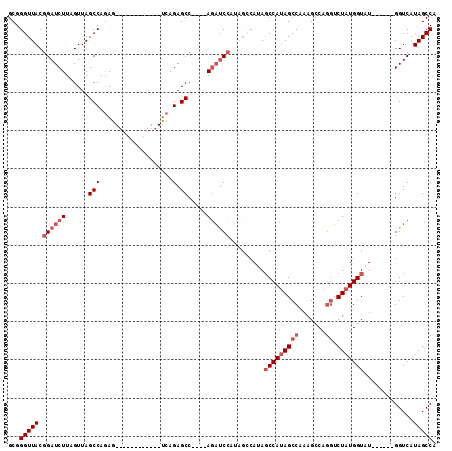
| Location | 14,454,618 – 14,454,708 |
|---|---|
| Length | 90 |
| Sequences | 5 |
| Columns | 112 |
| Reading direction | reverse |
| Mean pairwise identity | 79.56 |
| Mean single sequence MFE | -32.50 |
| Consensus MFE | -15.59 |
| Energy contribution | -17.19 |
| Covariance contribution | 1.60 |
| Combinations/Pair | 1.00 |
| Mean z-score | -2.04 |
| Structure conservation index | 0.48 |
| SVM decision value | 0.25 |
| SVM RNA-class probability | 0.655102 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2R_DroMel_CAF1 14454618 90 - 20766785 GCGGGUUACGGAUCUUAGUUAGCCAGAG------------UCAGAGCC----AGAUCCAUAGCCAUAGCCAUAGCCAAAGCCAGAUCUAUGGUAU------GGUCAUAGCCA ((.(((((.((((((..(((.((....)------------)...))).----)))))).)))))((..(((((.(((.((......)).))))))------))..)).)).. ( -25.50) >DroSec_CAF1 86806 90 - 1 GCGGGUUACGGAUCUUAGUUAGCCAGAG------------UCAGAGCC----AGAUCC------AUAGCCAUAGCCAAAGCCAGGUCUAUGGUAUGGCUAUGGUCAUAGCCA ...(((((.((((((..(((.((....)------------)...))).----))))))------...((((((((((..((((......)))).))))))))))..))))). ( -33.90) >DroSim_CAF1 88089 96 - 1 GCGGGUUACGGAUCUUAGUUAGCCAGAG------------UCAGAGCC----AGAUCCACAGCCAUAGCCAUAGCCAAAGCCAGGUCUAUGGUAUGGCUAUGGUCAUAGCCA ...(((((.((((((..(((.((....)------------)...))).----))))))...((((((((((((.(((.((......)).)))))))))))))))..))))). ( -35.90) >DroEre_CAF1 88324 102 - 1 GCGGGUUACGGAUCUUAGUUAGCCAGAGCUAGAGCCAGAGUCAGAGCC----AGAUCCAUAGCCAAAGCCAAAGCCAAAGCCAGGUCUAUGGUAU------GGUCAUAGCCA ((.(((((.((((((...(((((....))))).(((.......).)).----)))))).)))))...))..............((.((((((...------..)))))))). ( -27.40) >DroYak_CAF1 89376 106 - 1 GCGGGUUACGGAUCUUAGUUAGCCAAAGCAAAAGCCAGAGCCAGAGCCUCUGACUCCGAGAGGCAGAUCCAUAGCCAUAGCCAUGGCUAUGGUAU------GGUCAUAGCCA ((.(((((.((((((......((....((....))....))....((((((.......)))))))))))).)))))...))..(((((((((...------..))))))))) ( -39.80) >consensus GCGGGUUACGGAUCUUAGUUAGCCAGAG____________UCAGAGCC____AGAUCCAUAGCCAUAGCCAUAGCCAAAGCCAGGUCUAUGGUAU______GGUCAUAGCCA ...(((((.((((((......(((...................).)).....)))))).........(((((((((.......)).))))))).............))))). (-15.59 = -17.19 + 1.60)

Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 11:18:32 2006