
| Sequence ID | 2R_DroMel_CAF1 |
|---|---|
| Location | 12,346,274 – 12,346,408 |
| Length | 134 |
| Max. P | 0.983613 |

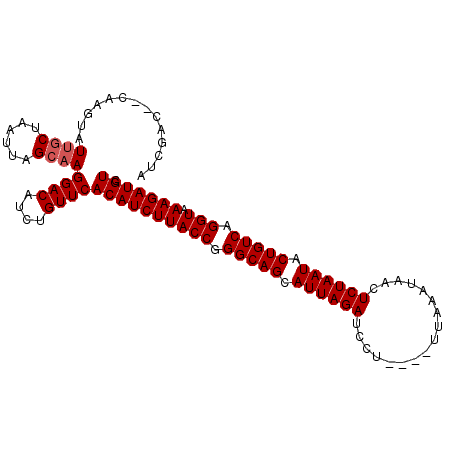
| Location | 12,346,274 – 12,346,369 |
|---|---|
| Length | 95 |
| Sequences | 6 |
| Columns | 105 |
| Reading direction | forward |
| Mean pairwise identity | 83.03 |
| Mean single sequence MFE | -29.95 |
| Consensus MFE | -25.91 |
| Energy contribution | -26.25 |
| Covariance contribution | 0.33 |
| Combinations/Pair | 1.00 |
| Mean z-score | -3.91 |
| Structure conservation index | 0.87 |
| SVM decision value | 1.91 |
| SVM RNA-class probability | 0.982309 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
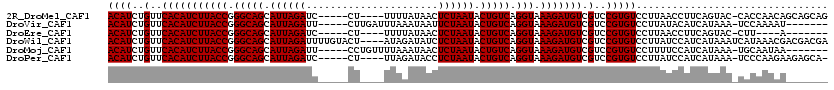
>2R_DroMel_CAF1 12346274 95 + 20766785 ACC------GAAUCUUGCUAAUUAGCAAGGACAUCUGUUCACAUCUUACCGGGCAGCAUUAGAUCCU----UUUUAUAACUCUAAUACUGUCAGGUAAAGAUGUC ...------...(((((((....)))))))..........((((((((((.(((((.((((((....----.........)))))).))))).))).))))))). ( -29.32) >DroVir_CAF1 13812 103 + 1 GUUUGC--UUGCAAUUACUUAUUUGCAAGGACAUCUGUUCACAUCUUACCGGGCAGCAUUAGAUUCUUGAUUUAAAUAAUUCUAAUACUGUCAGGUAAAGAUGUC .....(--((((((........)))))))((((((((....)...(((((.(((((.((((((.................)))))).))))).)))))))))))) ( -31.33) >DroPse_CAF1 32466 100 + 1 GACGAAAACACGUUUUGCUA-UUCGCAAGGACAUCUGUUCACAUCUUACCGGGCAGCAUUAGAUCCU----UUAGAUACCUCUAAUACUGUCAGGUAAAGAUGUC ((((......))))((((..-...))))((((....))))((((((((((.(((((.((((((....----.........)))))).))))).))).))))))). ( -28.72) >DroEre_CAF1 6949 99 + 1 AUCGAC--CGAGUCUUGCUAAUUAGCAAGGACAUCUGUUCACAUCUUACCGGGCAGCAUUAGAUCCU----UUUUAUAACUCUAAUACUGUCAGGUAAAGAUGUC ...(((--.((.(((((((....)))))))...)).))).((((((((((.(((((.((((((....----.........)))))).))))).))).))))))). ( -32.22) >DroMoj_CAF1 9413 103 + 1 AUUUAC--CUGCAAUUGCCUAUUUGCUAGGACAUCUGUUCACAUCUUACCGGGCAGCAUUAGAUUCCUGUUUUAAAUAACUCUAAUACUGUCAGGUAAAGAUGUC .....(--((((((........)))).)))..........((((((((((.(((((.((((((.....(((......))))))))).))))).))).))))))). ( -29.40) >DroPer_CAF1 32477 100 + 1 GACGAAAACACGUUUUGCUA-UUCGCAAGGACAUCUGUUCACAUCUUACCGGGCAGCAUUAGAUCCU----UUAGAUACCUCUAAUACUGUCAGGUAAAGAUGUC ((((......))))((((..-...))))((((....))))((((((((((.(((((.((((((....----.........)))))).))))).))).))))))). ( -28.72) >consensus AUCGAC__CAAGUAUUGCUAAUUAGCAAGGACAUCUGUUCACAUCUUACCGGGCAGCAUUAGAUCCU____UUAAAUAACUCUAAUACUGUCAGGUAAAGAUGUC ..............((((......))))((((....))))((((((((((.(((((.((((((.................)))))).))))).))).))))))). (-25.91 = -26.25 + 0.33)

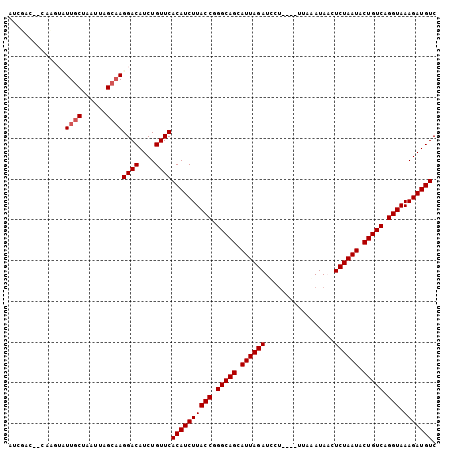
| Location | 12,346,274 – 12,346,369 |
|---|---|
| Length | 95 |
| Sequences | 6 |
| Columns | 105 |
| Reading direction | reverse |
| Mean pairwise identity | 83.03 |
| Mean single sequence MFE | -31.92 |
| Consensus MFE | -27.85 |
| Energy contribution | -27.88 |
| Covariance contribution | 0.03 |
| Combinations/Pair | 1.03 |
| Mean z-score | -3.84 |
| Structure conservation index | 0.87 |
| SVM decision value | 1.95 |
| SVM RNA-class probability | 0.983613 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2R_DroMel_CAF1 12346274 95 - 20766785 GACAUCUUUACCUGACAGUAUUAGAGUUAUAAAA----AGGAUCUAAUGCUGCCCGGUAAGAUGUGAACAGAUGUCCUUGCUAAUUAGCAAGAUUC------GGU ((((((((((((.(.((((((((((.........----....)))))))))).).)))))).((....))))))))((((((....))))))....------... ( -32.92) >DroVir_CAF1 13812 103 - 1 GACAUCUUUACCUGACAGUAUUAGAAUUAUUUAAAUCAAGAAUCUAAUGCUGCCCGGUAAGAUGUGAACAGAUGUCCUUGCAAAUAAGUAAUUGCAA--GCAAAC ((((((((((((.(.((((((((((.((...........)).)))))))))).).)))))).((....))))))))(((((((........))))))--)..... ( -32.10) >DroPse_CAF1 32466 100 - 1 GACAUCUUUACCUGACAGUAUUAGAGGUAUCUAA----AGGAUCUAAUGCUGCCCGGUAAGAUGUGAACAGAUGUCCUUGCGAA-UAGCAAAACGUGUUUUCGUC .(((((((.(((.(.((((((((((.........----....)))))))))).).))))))))))(((.(.((((..((((...-..)))).)))).).)))... ( -31.92) >DroEre_CAF1 6949 99 - 1 GACAUCUUUACCUGACAGUAUUAGAGUUAUAAAA----AGGAUCUAAUGCUGCCCGGUAAGAUGUGAACAGAUGUCCUUGCUAAUUAGCAAGACUCG--GUCGAU .(((((((.(((.(.((((((((((.........----....)))))))))).).))))))))))((...((.(((.(((((....)))))))))).--.))... ( -33.72) >DroMoj_CAF1 9413 103 - 1 GACAUCUUUACCUGACAGUAUUAGAGUUAUUUAAAACAGGAAUCUAAUGCUGCCCGGUAAGAUGUGAACAGAUGUCCUAGCAAAUAGGCAAUUGCAG--GUAAAU .(((((((.(((.(.((((((((((.................)))))))))).).))))))))))...(((.((.((((.....)))))).)))...--...... ( -28.93) >DroPer_CAF1 32477 100 - 1 GACAUCUUUACCUGACAGUAUUAGAGGUAUCUAA----AGGAUCUAAUGCUGCCCGGUAAGAUGUGAACAGAUGUCCUUGCGAA-UAGCAAAACGUGUUUUCGUC .(((((((.(((.(.((((((((((.........----....)))))))))).).))))))))))(((.(.((((..((((...-..)))).)))).).)))... ( -31.92) >consensus GACAUCUUUACCUGACAGUAUUAGAGUUAUAUAA____AGGAUCUAAUGCUGCCCGGUAAGAUGUGAACAGAUGUCCUUGCAAAUUAGCAAAACCAG__GUCGAC ((((((((((((.(.((((((((((.................)))))))))).).)))))).((....)))))))).((((......)))).............. (-27.85 = -27.88 + 0.03)


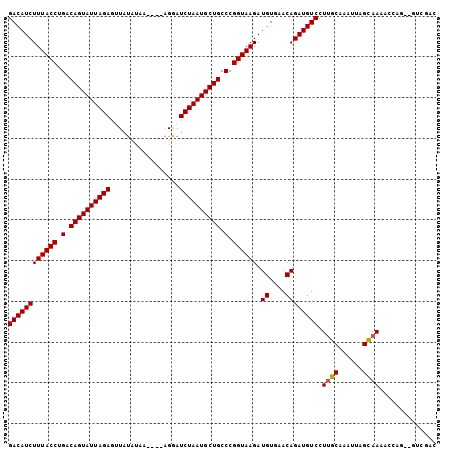
| Location | 12,346,298 – 12,346,408 |
|---|---|
| Length | 110 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 81.32 |
| Mean single sequence MFE | -24.70 |
| Consensus MFE | -22.38 |
| Energy contribution | -22.38 |
| Covariance contribution | 0.00 |
| Combinations/Pair | 1.00 |
| Mean z-score | -2.42 |
| Structure conservation index | 0.91 |
| SVM decision value | 1.58 |
| SVM RNA-class probability | 0.965383 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2R_DroMel_CAF1 12346298 110 + 20766785 ACAUCUGUUCACAUCUUACCGGGCAGCAUUAGAUC-----CU----UUUUAUAACUCUAAUACUGUCAGGUAAAGAUGUCGUCCGUGUCCUUAACCUUCAGUAC-CACCAACAGCAGCAG ....((((((((((((((((.(((((.((((((..-----..----.........)))))).))))).))).))))))).((..(((..((........))...-)))..)).).))))) ( -26.02) >DroVir_CAF1 13840 107 + 1 ACAUCUGUUCACAUCUUACCGGGCAGCAUUAGAUU-----CUUGAUUUAAAUAAUUCUAAUACUGUCAGGUAAAGAUGUCGUCCGUGUCCUUAUACAUCAUAAA-UCCAAAAU------- ......(..(((((((((((.(((((.((((((..-----...............)))))).))))).))).))))))).)..)((((....))))........-........------- ( -24.03) >DroEre_CAF1 6977 99 + 1 ACAUCUGUUCACAUCUUACCGGGCAGCAUUAGAUC-----CU----UUUUAUAACUCUAAUACUGUCAGGUAAAGAUGUCGUCCGUGUCCUUAACCUUCAGUAC-CUU----A------- ((((..(..(((((((((((.(((((.((((((..-----..----.........)))))).))))).))).))))))).)..)))))................-...----.------- ( -22.82) >DroWil_CAF1 52456 116 + 1 ACAUCUGUUCACAUCUUACCGGGCAGCAUUAGAUUUUGUACU----AUAGAUAUCUCUAAUACUGUCAGGUAAAGAUGUCGUCCGUGUCCUUAUCCAUCAUAAAUCAUAAACGACGACGA ............((((((((.(((((.((((((.(((((...----)))))....)))))).))))).))).)))))((((((.(((...((((.....))))..)))....)))))).. ( -26.90) >DroMoj_CAF1 9441 107 + 1 ACAUCUGUUCACAUCUUACCGGGCAGCAUUAGAUU-----CCUGUUUUAAAUAACUCUAAUACUGUCAGGUAAAGAUGUCGUCCGUGUCCUUUUCCAUCAUAAA-UGCAAUAA------- ((((..(..(((((((((((.(((((.((((((..-----...(((......))))))))).))))).))).))))))).)..)))))................-........------- ( -23.30) >DroPer_CAF1 32506 109 + 1 ACAUCUGUUCACAUCUUACCGGGCAGCAUUAGAUC-----CU----UUAGAUACCUCUAAUACUGUCAGGUAAAGAUGUCGUCCGUGUCCUUAUCCAUCAUAAA-UCCCAAGAAGAGCA- ......((((((((((((((.(((((.((((((..-----..----.........)))))).))))).))).))))))).....(((...........)))...-.........)))).- ( -25.12) >consensus ACAUCUGUUCACAUCUUACCGGGCAGCAUUAGAUC_____CU____UUAAAUAACUCUAAUACUGUCAGGUAAAGAUGUCGUCCGUGUCCUUAUCCAUCAUAAA_CACAAAAA_______ ((((..(..(((((((((((.(((((.((((((......................)))))).))))).))).))))))).)..)))))................................ (-22.38 = -22.38 + 0.00)
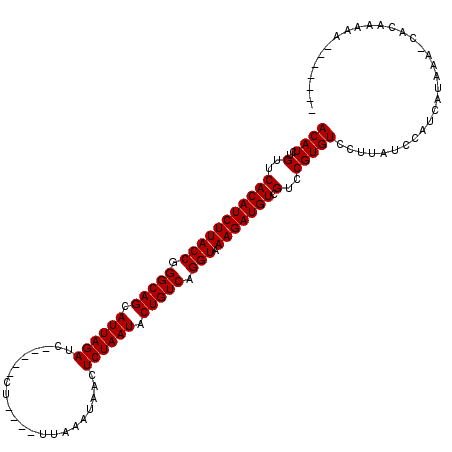

| Location | 12,346,298 – 12,346,408 |
|---|---|
| Length | 110 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 81.32 |
| Mean single sequence MFE | -28.48 |
| Consensus MFE | -22.92 |
| Energy contribution | -22.92 |
| Covariance contribution | 0.00 |
| Combinations/Pair | 1.00 |
| Mean z-score | -1.78 |
| Structure conservation index | 0.80 |
| SVM decision value | 0.72 |
| SVM RNA-class probability | 0.831385 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2R_DroMel_CAF1 12346298 110 - 20766785 CUGCUGCUGUUGGUG-GUACUGAAGGUUAAGGACACGGACGACAUCUUUACCUGACAGUAUUAGAGUUAUAAAA----AG-----GAUCUAAUGCUGCCCGGUAAGAUGUGAACAGAUGU ...(((.((((.(((-...((........))..))).))))(((((((.(((.(.((((((((((.........----..-----..)))))))))).).))))))))))...))).... ( -33.62) >DroVir_CAF1 13840 107 - 1 -------AUUUUGGA-UUUAUGAUGUAUAAGGACACGGACGACAUCUUUACCUGACAGUAUUAGAAUUAUUUAAAUCAAG-----AAUCUAAUGCUGCCCGGUAAGAUGUGAACAGAUGU -------....((..-((((((...))))))..)).(..(.(((((((.(((.(.((((((((((.((...........)-----).)))))))))).).)))))))))))..)...... ( -24.90) >DroEre_CAF1 6977 99 - 1 -------U----AAG-GUACUGAAGGUUAAGGACACGGACGACAUCUUUACCUGACAGUAUUAGAGUUAUAAAA----AG-----GAUCUAAUGCUGCCCGGUAAGAUGUGAACAGAUGU -------.----...-...(((...(((..(....).))).(((((((.(((.(.((((((((((.........----..-----..)))))))))).).))))))))))...))).... ( -25.72) >DroWil_CAF1 52456 116 - 1 UCGUCGUCGUUUAUGAUUUAUGAUGGAUAAGGACACGGACGACAUCUUUACCUGACAGUAUUAGAGAUAUCUAU----AGUACAAAAUCUAAUGCUGCCCGGUAAGAUGUGAACAGAUGU .((((((((((..((.(((((.....)))))..))..))))))(((((.(((.(.((((((((((.........----.........)))))))))).).)))))))).......)))). ( -33.97) >DroMoj_CAF1 9441 107 - 1 -------UUAUUGCA-UUUAUGAUGGAAAAGGACACGGACGACAUCUUUACCUGACAGUAUUAGAGUUAUUUAAAACAGG-----AAUCUAAUGCUGCCCGGUAAGAUGUGAACAGAUGU -------.....(((-(((....((........)).(..(.(((((((.(((.(.((((((((((...............-----..)))))))))).).)))))))))))..))))))) ( -25.73) >DroPer_CAF1 32506 109 - 1 -UGCUCUUCUUGGGA-UUUAUGAUGGAUAAGGACACGGACGACAUCUUUACCUGACAGUAUUAGAGGUAUCUAA----AG-----GAUCUAAUGCUGCCCGGUAAGAUGUGAACAGAUGU -..((.(((((((..-(((((.....)))))..).)))...(((((((.(((.(.((((((((((.........----..-----..)))))))))).).))))))))))))).)).... ( -26.92) >consensus _______UGUUUGGA_UUUAUGAUGGAUAAGGACACGGACGACAUCUUUACCUGACAGUAUUAGAGUUAUAUAA____AG_____AAUCUAAUGCUGCCCGGUAAGAUGUGAACAGAUGU ....................................(..(.(((((((.(((.(.((((((((((......................)))))))))).).)))))))))))..)...... (-22.92 = -22.92 + 0.00)


Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 11:03:02 2006