
| Sequence ID | 2R_DroMel_CAF1 |
|---|---|
| Location | 10,278,924 – 10,279,084 |
| Length | 160 |
| Max. P | 0.999510 |

| Location | 10,278,924 – 10,279,044 |
|---|---|
| Length | 120 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 90.28 |
| Mean single sequence MFE | -46.75 |
| Consensus MFE | -45.01 |
| Energy contribution | -42.82 |
| Covariance contribution | -2.19 |
| Combinations/Pair | 1.31 |
| Mean z-score | -2.44 |
| Structure conservation index | 0.96 |
| SVM decision value | 3.67 |
| SVM RNA-class probability | 0.999510 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
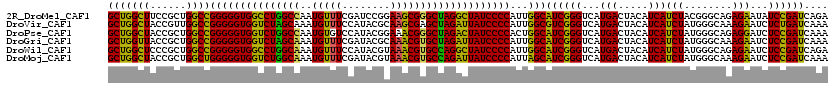
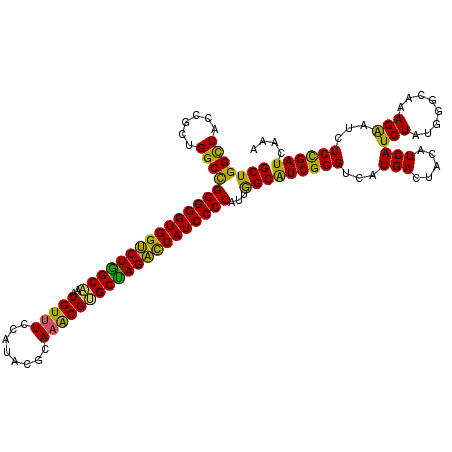
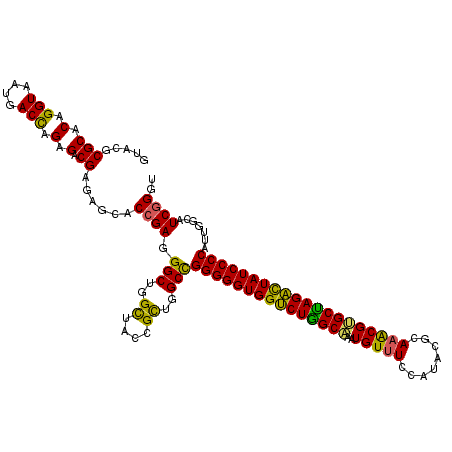
>2R_DroMel_CAF1 10278924 120 - 20766785 GCUGGCUUCCGCUGGCCGGGGGUGGCCUGGCCAAUGUUUCGAUCCGGAAGCGGGCUAGGCUAUCCCCAUUGGCAUCGGGUCAUGACUACAUCAUCUACGGGCAGAGAAUAUCCGAUCAGA (((((((......))))(((((((((((((((...(((((......))))).)))))))))))))))...)))(((((((.((((.....))))(....).........))))))).... ( -53.70) >DroVir_CAF1 27602 120 - 1 GCUGGCUACCGUUGGCCGGGGGUGGUCUAGCAAAUGUUUCCAUACGCAAGCGAGCUAGAUUAUCCCCAUUGGCGUCGGGUCAUGACUACAUCAUCUAUGGGCAAAGAAUCUCUGAUCAAA ((((((((....)))))((((((((((((((..(((....))).((....)).))))))))))))))...)))(((.(...((((.....))))...).))).................. ( -40.10) >DroPse_CAF1 22178 120 - 1 GCUGGCUACCGCUGGCCGGGGGUGGUCUGGCCAAUGUGUCCAUACGGAAACGGGCUAGACUAUCCCCACUGGCAUCGGGUCAUGACUACAUCAUCUAUGGGCAGAGGAUCUCCGAUCAAA ((..((....))..)).(((((((((((((((...((.(((....))).)).))))))))))))))).(((.(...((((.(((....))).))))...).)))..((((...))))... ( -52.70) >DroGri_CAF1 22576 120 - 1 GCUGGUUACCGCUGGCCGGGGGUGGUCUAGCAAAUGUUUCGAUACGCAAACGUGCUAGAUUAUCCCCAUUGGCAUCGGGUCAUGACUACAUCAUCUAUGGGCAAAGAAUCUCCGAUCAAA ((((((((....)))))(((((((((((((((...((((((...)).)))).)))))))))))))))...)))((((((...(((.....)))(((........)))...)))))).... ( -40.30) >DroWil_CAF1 22042 120 - 1 GCUGGCUCCCGCUGGCCGGGGGUGGCCUGGCAAAUGUUUCCAUACGUAAACGUGCCAGGCUAUCCCCAUUGGCAUCGGGUCAUGACUACAUCAUCUAUGGGCAGAGAAUCUCCGAUCAGA .((((..((((...((((((((((((((((((...((((.(....).)))).)))))))))))))))...)))..))))((((((.....)))).....((.((.....)))))))))). ( -49.10) >DroMoj_CAF1 24229 120 - 1 GCUGGCUACCGCUGGCUGGGGGUGGUCUGGCAAAUGUUUCGAUACGUAAACGUGCCAGAUUAUCCCCAUUAGCAUCGGGUCAUGACUACAUCAUCUAUGGGCAAAGAAUCUCCGAUCAAA ((..((....))..))((((((((((((((((...((((((...)).)))).))))))))))))))))...(.((((((...(((.....)))(((........)))...)))))))... ( -44.60) >consensus GCUGGCUACCGCUGGCCGGGGGUGGUCUGGCAAAUGUUUCCAUACGCAAACGUGCUAGACUAUCCCCAUUGGCAUCGGGUCAUGACUACAUCAUCUAUGGGCAAAGAAUCUCCGAUCAAA (((((((......))))(((((((((((((((..(((((........))))))))))))))))))))...)))((((((...(((.....)))(((........)))...)))))).... (-45.01 = -42.82 + -2.19)
| Location | 10,278,964 – 10,279,084 |
|---|---|
| Length | 120 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 90.22 |
| Mean single sequence MFE | -52.80 |
| Consensus MFE | -49.54 |
| Energy contribution | -47.80 |
| Covariance contribution | -1.74 |
| Combinations/Pair | 1.28 |
| Mean z-score | -2.58 |
| Structure conservation index | 0.94 |
| SVM decision value | 3.37 |
| SVM RNA-class probability | 0.999097 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
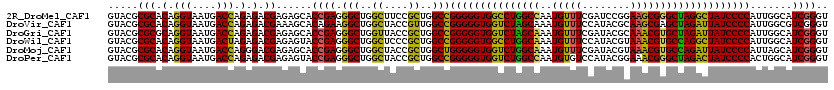
>2R_DroMel_CAF1 10278964 120 - 20766785 GUACGCGCACAGGUAAUGACCAGAGACGAGAGCACCGAGGGCUGGCUUCCGCUGGCCGGGGGUGGCCUGGCCAAUGUUUCGAUCCGGAAGCGGGCUAGGCUAUCCCCAUUGGCAUCGGGU ((.(.(((.(.(((....))).).).)).).)).((((.(((..((....))..)))(((((((((((((((...(((((......))))).))))))))))))))).......)))).. ( -59.40) >DroVir_CAF1 27642 120 - 1 GUACGCGCACAGGUAAUGACCAGAGACGAAAGCACAGAAGGCUGGCUACCGUUGGCCGGGGGUGGUCUAGCAAAUGUUUCCAUACGCAAGCGAGCUAGAUUAUCCCCAUUGGCGUCGGGU ...(((((...(((....)))...(.(....)).(((..(((..((....))..)))((((((((((((((..(((....))).((....)).)))))))))))))).)))))).))... ( -46.90) >DroGri_CAF1 22616 120 - 1 GUACGCGCGCAGGUAAUGACCAGAGACGAGAGCACCGAGGGCUGGUUACCGCUGGCCGGGGGUGGUCUAGCAAAUGUUUCGAUACGCAAACGUGCUAGAUUAUCCCCAUUGGCAUCGGGU ((.(.(((...(((....)))...).)).).)).((((.(((..((....))..)))(((((((((((((((...((((((...)).)))).))))))))))))))).......)))).. ( -48.40) >DroWil_CAF1 22082 120 - 1 GUACGCGCACAGGUAAUGACUAGAGACGAGAGUACCGAGGGCUGGCUCCCGCUGGCCGGGGGUGGCCUGGCAAAUGUUUCCAUACGUAAACGUGCCAGGCUAUCCCCAUUGGCAUCGGGU .(((.(((.(.(((....))).).).))...)))((((.(((..((....))..)))(((((((((((((((...((((.(....).)))).))))))))))))))).......)))).. ( -54.80) >DroMoj_CAF1 24269 120 - 1 GUACGCGCACAGGUAAUGACCAGGGACGAGAGCACCGAGGGCUGGCUACCGCUGGCUGGGGGUGGUCUGGCAAAUGUUUCGAUACGUAAACGUGCCAGAUUAUCCCCAUUAGCAUCGGGU ((.(.((..(.(((....)))..)..)).).)).((((.(((..((....))..)))(((((((((((((((...((((((...)).)))).))))))))))))))).......)))).. ( -50.50) >DroPer_CAF1 22185 120 - 1 GUACGCGCACAGGUAAUGACCAGAGACGAGAGUACCGAGGGCUGGCUACCGCUGGCCGGGGGUGGUCUGGCCAAUGUGUCCAUACGGAAACGGGCUAGACUAUCCCCACUGGCAUCGGGU .(((.(((.(.(((....))).).).))...)))((((.(((..((....))..)))(((((((((((((((...((.(((....))).)).))))))))))))))).......)))).. ( -56.80) >consensus GUACGCGCACAGGUAAUGACCAGAGACGAGAGCACCGAGGGCUGGCUACCGCUGGCCGGGGGUGGUCUGGCAAAUGUUUCCAUACGCAAACGUGCUAGACUAUCCCCAUUGGCAUCGGGU .....(((.(.(((....))).).).))......((((.(((..((....))..)))(((((((((((((((..(((((........)))))))))))))))))))).......)))).. (-49.54 = -47.80 + -1.74)
Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 10:44:27 2006