
| Sequence ID | 2R_DroMel_CAF1 |
|---|---|
| Location | 10,165,541 – 10,165,701 |
| Length | 160 |
| Max. P | 0.707905 |

| Location | 10,165,541 – 10,165,661 |
|---|---|
| Length | 120 |
| Sequences | 5 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 90.60 |
| Mean single sequence MFE | -46.46 |
| Consensus MFE | -37.58 |
| Energy contribution | -38.80 |
| Covariance contribution | 1.22 |
| Combinations/Pair | 1.07 |
| Mean z-score | -1.35 |
| Structure conservation index | 0.81 |
| SVM decision value | -0.01 |
| SVM RNA-class probability | 0.528963 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
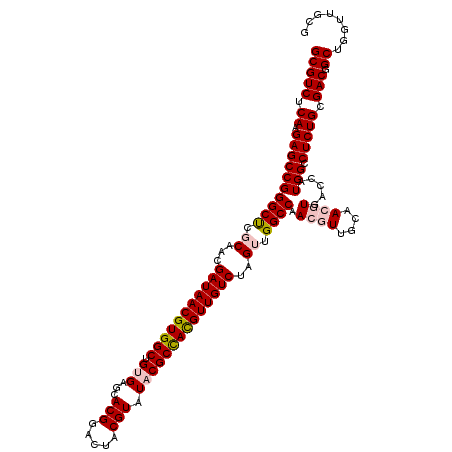
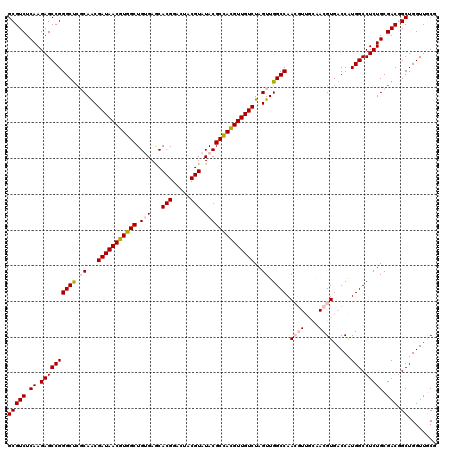
>2R_DroMel_CAF1 10165541 120 - 20766785 GCGUCUCAAGAGCCGGGCUCGCAACGAUAACGUGGCUGUGAGCACGGACUACGUAUACGCCACGUUGUCUAGUUGGCCAACGUUGCAACGUGACCAUGGCCUCUGCGACGGCUGGUUGCG ..........((((((.((((((..(((((((((((.(((...(((.....))).)))))))))))))).....(((((..((..(...)..))..)))))..))))).).))))))... ( -49.80) >DroSec_CAF1 5279 120 - 1 GCGUCUCAAGAGCCGGGCUCGCAACGAUAACGUGGCUGUGAGCACGGAAUACGUAUACGCCAUGUUGUCUAGUUGGCCAACGUUGCAACGUGACCAUGGCCUCUGCGACGGCUGGUUCCU .........(((((((.((((((..(((((((((((.(((...(((.....))).)))))))))))))).....(((((..((..(...)..))..)))))..))))).).))))))).. ( -50.80) >DroSim_CAF1 5211 120 - 1 GCGUCUCAAGAGCCGGGCUCGCAACGAUAACGUGGCUGUGAACACGGAAUACGUAUACGCUACGUUGUCUAGUUGGCCAACGUUGCAACGUGACCAUGGCCUCUGCGACGGCUGGUUCCU .........(((((((.((((((..(((((((((((.(((...(((.....))).)))))))))))))).....(((((..((..(...)..))..)))))..))))).).))))))).. ( -50.30) >DroEre_CAF1 5351 111 - 1 GCGUCUCAAGAGCCGGGCU-CCAGCGAUAACGUGGCUGAGAGCACGGACUACGUAUACGCCACGUUGUCUAGUUGGCCAA--------CGUGACCAUGGCCUCUGCGACUGCUGGUUGCG .((.((....)).)).((.-((((((((((((((((....(..(((.....))).)..)))))))))))..((.(((((.--------........)))))...))....)))))..)). ( -41.00) >DroYak_CAF1 5146 112 - 1 GCGUCUCAAGAGCCGGGCCCCCAACGAUAACGUGGCUGAGAGCACGGACUACGUAUACGCCACGUUGUCUAGUUGGCCAA--------CGUGACCGUGGCCUCUGCGACUGCUGGUUGCG ........((((((.((((......(((((((((((....(..(((.....))).)..))))))))))).....)))).(--------((....))))).))))(((((.....))))). ( -40.40) >consensus GCGUCUCAAGAGCCGGGCUCGCAACGAUAACGUGGCUGUGAGCACGGACUACGUAUACGCCACGUUGUCUAGUUGGCCAACGUUGCAACGUGACCAUGGCCUCUGCGACGGCUGGUUGCG (((((.((.((((((((((.((...(((((((((((.(((...(((.....))).))))))))))))))..)).)))).((((....)))).....))).))))).))).))........ (-37.58 = -38.80 + 1.22)

| Location | 10,165,581 – 10,165,701 |
|---|---|
| Length | 120 |
| Sequences | 5 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 95.83 |
| Mean single sequence MFE | -37.38 |
| Consensus MFE | -34.24 |
| Energy contribution | -34.56 |
| Covariance contribution | 0.32 |
| Combinations/Pair | 1.09 |
| Mean z-score | -1.22 |
| Structure conservation index | 0.92 |
| SVM decision value | 0.37 |
| SVM RNA-class probability | 0.707905 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
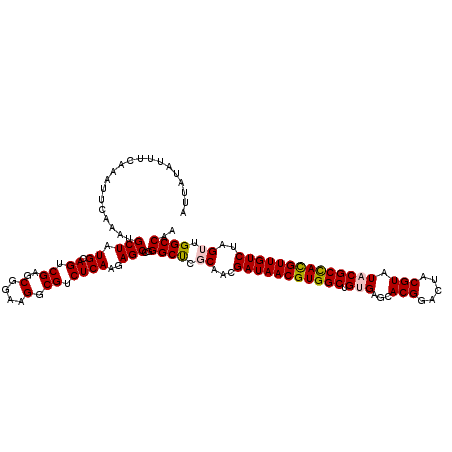
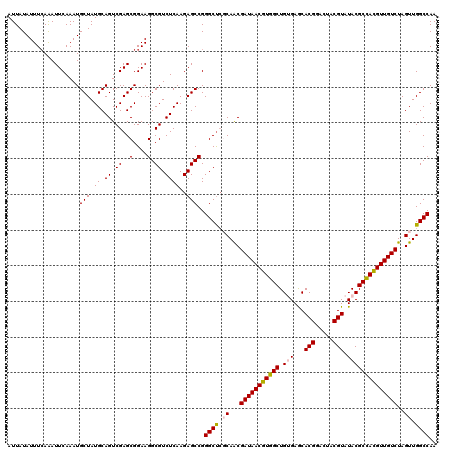
>2R_DroMel_CAF1 10165581 120 - 20766785 AUUAUAUUUCAAAUUCAAAUGCUAUGCAGUCGAGCGGAAGGCGUCUCAAGAGCCGGGCUCGCAACGAUAACGUGGCUGUGAGCACGGACUACGUAUACGCCACGUUGUCUAGUUGGCCAA ....................((((.((.(.(((((....(((.((....)))))..))))))...(((((((((((.(((...(((.....))).))))))))))))))..))))))... ( -39.20) >DroSec_CAF1 5319 120 - 1 AUUAUAUUUCAAAUUCAAAUGCUAUGCAGUCGAGCGGAAGGCGUCUCAAGAGCCGGGCUCGCAACGAUAACGUGGCUGUGAGCACGGAAUACGUAUACGCCAUGUUGUCUAGUUGGCCAA ....................((((.((.(.(((((....(((.((....)))))..))))))...(((((((((((.(((...(((.....))).))))))))))))))..))))))... ( -37.40) >DroSim_CAF1 5251 120 - 1 AUUAUAUUUGAAAUUCAAAUGCUAUGCAGUCGAGCGGAAGGCGUCUCAAGAGCCGGGCUCGCAACGAUAACGUGGCUGUGAACACGGAAUACGUAUACGCUACGUUGUCUAGUUGGCCAA .....(((((.....)))))((((.((.(.(((((....(((.((....)))))..))))))...(((((((((((.(((...(((.....))).))))))))))))))..))))))... ( -38.80) >DroEre_CAF1 5383 119 - 1 AUUAUAUUUCAGAUUCAAAUGCUAUGCAGUCGAGCGGAAGGCGUCUCAAGAGCCGGGCU-CCAGCGAUAACGUGGCUGAGAGCACGGACUACGUAUACGCCACGUUGUCUAGUUGGCCAA ....................((((.((((.(.((((...(((((......(((((.(((-(((((.((...)).)))).)))).))).))......))))).))))).)).))))))... ( -36.40) >DroYak_CAF1 5178 120 - 1 AUUAUAUUUCAAAUUCAAAUGCUAUGCAGUCGAGCGGAAGGCGUCUCAAGAGCCGGGCCCCCAACGAUAACGUGGCUGAGAGCACGGACUACGUAUACGCCACGUUGUCUAGUUGGCCAA .......(((...(((...(((...)))...)))..)))(((.((....))))).((((......(((((((((((....(..(((.....))).)..))))))))))).....)))).. ( -35.10) >consensus AUUAUAUUUCAAAUUCAAAUGCUAUGCAGUCGAGCGGAAGGCGUCUCAAGAGCCGGGCUCGCAACGAUAACGUGGCUGUGAGCACGGACUACGUAUACGCCACGUUGUCUAGUUGGCCAA ....................(((.((.((.((..(....).)).))))..)))..((((.((...(((((((((((.(((...(((.....))).))))))))))))))..)).)))).. (-34.24 = -34.56 + 0.32)

Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 10:43:15 2006