
| Sequence ID | 2R_DroMel_CAF1 |
|---|---|
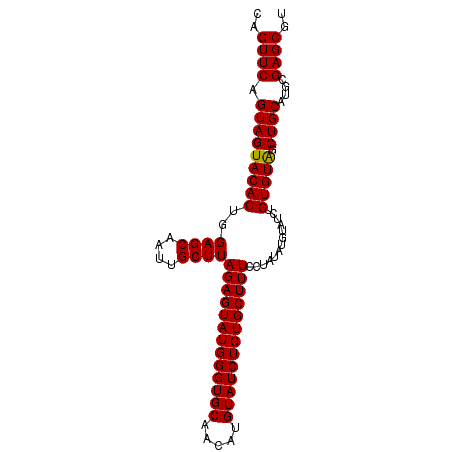
| Location | 1,641,000 – 1,641,116 |
| Length | 116 |
| Max. P | 0.946870 |

| Location | 1,641,000 – 1,641,094 |
|---|---|
| Length | 94 |
| Sequences | 3 |
| Columns | 94 |
| Reading direction | forward |
| Mean pairwise identity | 97.16 |
| Mean single sequence MFE | -30.23 |
| Consensus MFE | -29.62 |
| Energy contribution | -29.40 |
| Covariance contribution | -0.22 |
| Combinations/Pair | 1.03 |
| Mean z-score | -2.25 |
| Structure conservation index | 0.98 |
| SVM decision value | 1.37 |
| SVM RNA-class probability | 0.946870 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
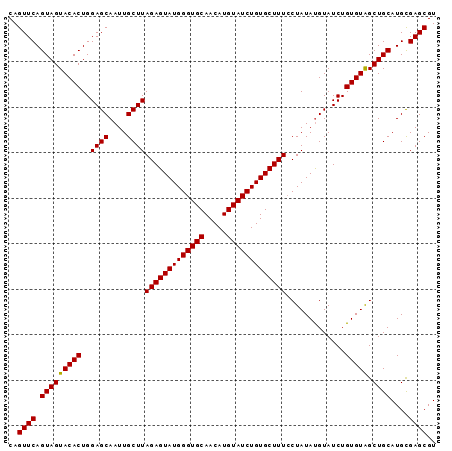
>2R_DroMel_CAF1 1641000 94 + 20766785 CAGUUCAGUAGUACACUGGAGCAAUUGCUUAGAGUAUGGGUGCAACAUGUAUCUGUGCUUUCCUAUAUGUAUCUGUGUAGCUGCAUGCGAGCGU ..((((.(((((((((..((((....))))(((((((((((((.....))))))))))))).............)))).)))))....)))).. ( -29.20) >DroSec_CAF1 26815 94 + 1 CAGUUCAGUAGUACACUGGAGCAAUUGCUUAGAGUAUGGGUGCAACAUGUAUCUGUGCUUUCCUAUACGUAUCUGUGUAGCUGCAUGCGAGCGU ..((((.(((((((((..((((....))))(((((((((((((.....))))))))))))).............)))).)))))....)))).. ( -29.20) >DroEre_CAF1 29596 94 + 1 CAGUUCAGUAGUACACUGGAGCAAUUGCUUAGAGUAUGGGUGCAACAUGUAUCUGUGCUUUGCUAUAUGUAUCUGUGUGGCUGCAUGUGAGCGU ..((((((((((((((.((.(((...((..(((((((((((((.....)))))))))))))))....))).)).)))).)))))...))))).. ( -32.30) >consensus CAGUUCAGUAGUACACUGGAGCAAUUGCUUAGAGUAUGGGUGCAACAUGUAUCUGUGCUUUCCUAUAUGUAUCUGUGUAGCUGCAUGCGAGCGU ..((((.(((((((((..((((....))))(((((((((((((.....))))))))))))).............))))).))))....)))).. (-29.62 = -29.40 + -0.22)

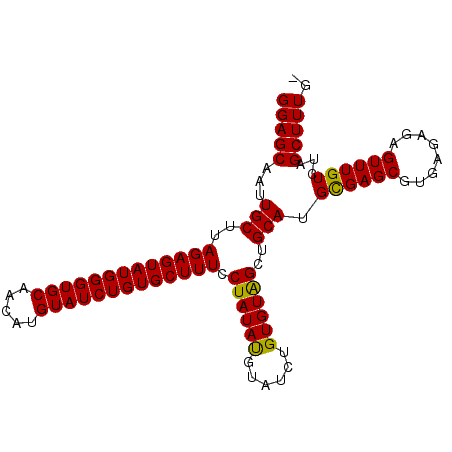
| Location | 1,641,017 – 1,641,116 |
|---|---|
| Length | 99 |
| Sequences | 3 |
| Columns | 99 |
| Reading direction | forward |
| Mean pairwise identity | 94.95 |
| Mean single sequence MFE | -29.37 |
| Consensus MFE | -27.49 |
| Energy contribution | -26.83 |
| Covariance contribution | -0.66 |
| Combinations/Pair | 1.09 |
| Mean z-score | -1.70 |
| Structure conservation index | 0.94 |
| SVM decision value | 0.25 |
| SVM RNA-class probability | 0.652059 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
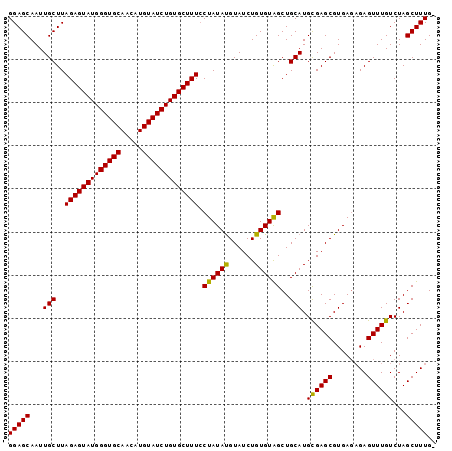
>2R_DroMel_CAF1 1641017 99 + 20766785 GGAGCAAUUGCUUAGAGUAUGGGUGCAACAUGUAUCUGUGCUUUCCUAUAUGUAUCUGUGUAGCUGCAUGCGAGCGUGAGAGAGUUUGUCUAGCUUUGA (((((...(((..(((((((((((((.....))))))))))))).((((((......))))))..))).((((((........))))))...))))).. ( -28.20) >DroSec_CAF1 26832 98 + 1 GGAGCAAUUGCUUAGAGUAUGGGUGCAACAUGUAUCUGUGCUUUCCUAUACGUAUCUGUGUAGCUGCAUGCGAGCGUGAGAGAGUUUGUCUAGCUUUG- (((((...(((..(((((((((((((.....))))))))))))).(((((((....)))))))..))).((((((........))))))...))))).- ( -29.80) >DroEre_CAF1 29613 97 + 1 GGAGCAAUUGCUUAGAGUAUGGGUGCAACAUGUAUCUGUGCUUUGCUAUAUGUAUCUGUGUGGCUGCAUGUGAGCGUGA--GAGUUUGUCUAGCUUUGG .((((....))))(((((((((((((.....)))))))))))))((((((((((.((....)).))))))).)))...(--(((((.....)))))).. ( -30.10) >consensus GGAGCAAUUGCUUAGAGUAUGGGUGCAACAUGUAUCUGUGCUUUCCUAUAUGUAUCUGUGUAGCUGCAUGCGAGCGUGAGAGAGUUUGUCUAGCUUUG_ (((((...(((..(((((((((((((.....))))))))))))).((((((......))))))..))).((((((........))))))...))))).. (-27.49 = -26.83 + -0.66)

Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 09:33:43 2006