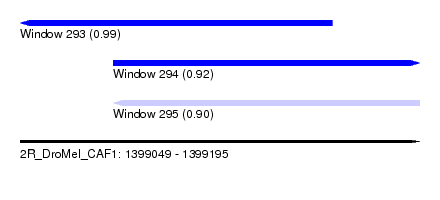
| Sequence ID | 2R_DroMel_CAF1 |
|---|---|
| Location | 1,399,049 – 1,399,195 |
| Length | 146 |
| Max. P | 0.993370 |

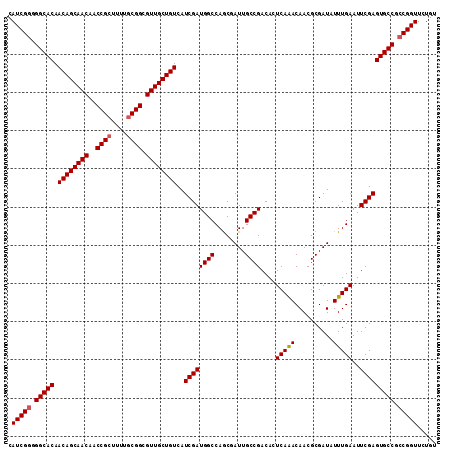
| Location | 1,399,049 – 1,399,163 |
|---|---|
| Length | 114 |
| Sequences | 5 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 90.98 |
| Mean single sequence MFE | -46.78 |
| Consensus MFE | -44.24 |
| Energy contribution | -43.72 |
| Covariance contribution | -0.52 |
| Combinations/Pair | 1.12 |
| Mean z-score | -1.77 |
| Structure conservation index | 0.95 |
| SVM decision value | 2.39 |
| SVM RNA-class probability | 0.993370 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2R_DroMel_CAF1 1399049 114 - 20766785 CGUUGUUUGAGUGUCGGCAAUCGCUGGCCAUCGAUGACAGCAACGCCGCAAAAGCGGUUGUUGCUGUUGUGCCCCCGAUGGCGUGCCUCUUGUCGCUGCUGCCUCUGCUGCUGC------ .((.((..(((.(.(((((.......((((((((..(((((((((((((....)))).)))))))))..).....)))))))(((.(....).)))))))))))).)).))...------ ( -47.70) >DroSec_CAF1 24878 114 - 1 CGUUGUUUGAGUGUCGGCAAUCGCUGGCCAUCGAUGACAGCAACGCCGUAAAAGCGGUUGUUGCUGUUGUGCCCCCGAUGGCGUGCCUCUUGUCGCUGCUGCCUCUGCUGCUGC------ .((.((..(((.(.(((((.......((((((((..(((((((((((((....)))).)))))))))..).....)))))))(((.(....).)))))))))))).)).))...------ ( -45.80) >DroSim_CAF1 29812 114 - 1 CGUUGUUUGAGUGUCGGCAAUCGCUGGCCAUCGAUGACAGCAACGCCGCAAAAGCGGUUGUUGCUGUUGUGCCCCCGAUGGCGUGCCUCUUGUCGCUGCUGCCUCUGCUGCUGC------ .((.((..(((.(.(((((.......((((((((..(((((((((((((....)))).)))))))))..).....)))))))(((.(....).)))))))))))).)).))...------ ( -47.70) >DroEre_CAF1 23869 120 - 1 CGUUGUCUGAGUGUCGGCAAUCGUUGGCCAUCGAUGACAGCAACGCCGCAAAAGCGGUUGUUGCUGUUGUGCCCCCGAUGGCGUGCCCCUUGUCGCCGCUGCCUCUGUUGCUGCCUCUGC ........(((.(.(((((((.(..(((((((((..(((((((((((((....)))).)))))))))..).....)))))(((.((........))))).))).).)))))))))))... ( -49.60) >DroYak_CAF1 25742 104 - 1 ---------AGUGUCGGCAAUCGUUGGCCAUCGAUGACAGCAACGCCGCAAAAGCGGUUGUUGCUGUUGUGCC-CCGAUGGUGUGCCUCUCGUCGCUGCUGCAUCUGCUGCUAC------ ---------((((.(((.....((..((((((((..(((((((((((((....)))).)))))))))..)...-.)))))))..))...))).))))((.((....)).))...------ ( -43.10) >consensus CGUUGUUUGAGUGUCGGCAAUCGCUGGCCAUCGAUGACAGCAACGCCGCAAAAGCGGUUGUUGCUGUUGUGCCCCCGAUGGCGUGCCUCUUGUCGCUGCUGCCUCUGCUGCUGC______ .........((((.((((((..((..((((((((..(((((((((((((....)))).)))))))))..).....)))))))..))...)))))).)))).................... (-44.24 = -43.72 + -0.52)

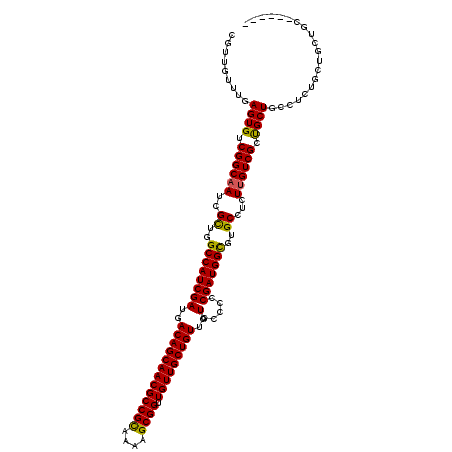
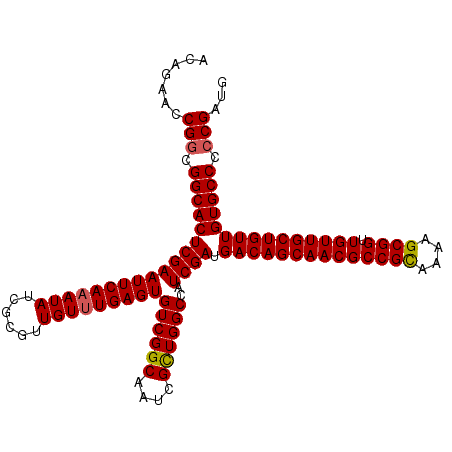
| Location | 1,399,083 – 1,399,195 |
|---|---|
| Length | 112 |
| Sequences | 4 |
| Columns | 112 |
| Reading direction | forward |
| Mean pairwise identity | 98.21 |
| Mean single sequence MFE | -42.90 |
| Consensus MFE | -41.14 |
| Energy contribution | -41.45 |
| Covariance contribution | 0.31 |
| Combinations/Pair | 1.03 |
| Mean z-score | -2.40 |
| Structure conservation index | 0.96 |
| SVM decision value | 1.16 |
| SVM RNA-class probability | 0.924619 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2R_DroMel_CAF1 1399083 112 + 20766785 CAUCGGGGGCACAACAGCAACAACCGCUUUUGCGGCGUUGCUGUCAUCGAUGGCCAGCGAUUGCCGACACUCAAACAACGCGAUAUUUGAAUUCGAGUGCCGCCGGUUCUGU .(((((.(((((.((((((((..((((....)))).))))))))..((((((((........))))....(((((..........)))))..))))))))).)))))..... ( -44.30) >DroSec_CAF1 24912 112 + 1 CAUCGGGGGCACAACAGCAACAACCGCUUUUACGGCGUUGCUGUCAUCGAUGGCCAGCGAUUGCCGACACUCAAACAACGCGAUAUUUGAAUUCGAGUGCCGCCGGUUCUGU .(((((.(((((.((((((((..(((......))).))))))))..((((((((........))))....(((((..........)))))..))))))))).)))))..... ( -40.20) >DroSim_CAF1 29846 112 + 1 CAUCGGGGGCACAACAGCAACAACCGCUUUUGCGGCGUUGCUGUCAUCGAUGGCCAGCGAUUGCCGACACUCAAACAACGCGAUAUUUGAAUUCGAGUGCCGCCGGUUCUGU .(((((.(((((.((((((((..((((....)))).))))))))..((((((((........))))....(((((..........)))))..))))))))).)))))..... ( -44.30) >DroEre_CAF1 23909 112 + 1 CAUCGGGGGCACAACAGCAACAACCGCUUUUGCGGCGUUGCUGUCAUCGAUGGCCAACGAUUGCCGACACUCAGACAACGCGAUAUUUGAAUUCGAGUGCCGGCGGUUCUGU .((((..(((.((((((((((..((((....)))).))))))))......)))))..))))(((((.(((((.(((((........)))...))))))).)))))....... ( -42.80) >consensus CAUCGGGGGCACAACAGCAACAACCGCUUUUGCGGCGUUGCUGUCAUCGAUGGCCAGCGAUUGCCGACACUCAAACAACGCGAUAUUUGAAUUCGAGUGCCGCCGGUUCUGU .(((((.(((((.((((((((..((((....)))).))))))))..((((((((........))))....(((((..........)))))..))))))))).)))))..... (-41.14 = -41.45 + 0.31)

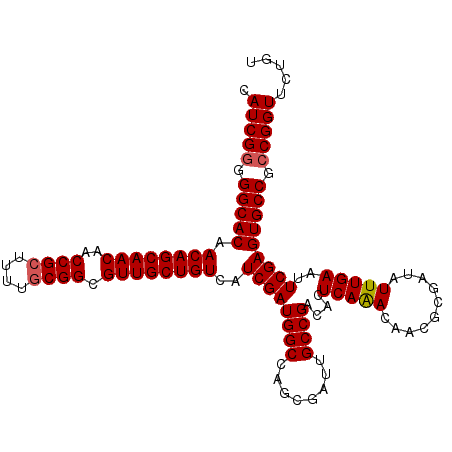
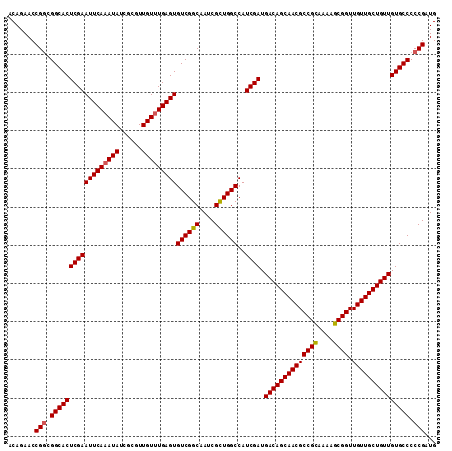
| Location | 1,399,083 – 1,399,195 |
|---|---|
| Length | 112 |
| Sequences | 4 |
| Columns | 112 |
| Reading direction | reverse |
| Mean pairwise identity | 98.21 |
| Mean single sequence MFE | -52.33 |
| Consensus MFE | -51.25 |
| Energy contribution | -51.38 |
| Covariance contribution | 0.12 |
| Combinations/Pair | 1.05 |
| Mean z-score | -4.62 |
| Structure conservation index | 0.98 |
| SVM decision value | 0.99 |
| SVM RNA-class probability | 0.896816 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2R_DroMel_CAF1 1399083 112 - 20766785 ACAGAACCGGCGGCACUCGAAUUCAAAUAUCGCGUUGUUUGAGUGUCGGCAAUCGCUGGCCAUCGAUGACAGCAACGCCGCAAAAGCGGUUGUUGCUGUUGUGCCCCCGAUG .......(((.((((((((((((((((((......)))))))))((((((....))))))..)))).((((((((((((((....)))).))))))))))))))).)))... ( -53.90) >DroSec_CAF1 24912 112 - 1 ACAGAACCGGCGGCACUCGAAUUCAAAUAUCGCGUUGUUUGAGUGUCGGCAAUCGCUGGCCAUCGAUGACAGCAACGCCGUAAAAGCGGUUGUUGCUGUUGUGCCCCCGAUG .......(((.((((((((((((((((((......)))))))))((((((....))))))..)))).((((((((((((((....)))).))))))))))))))).)))... ( -52.00) >DroSim_CAF1 29846 112 - 1 ACAGAACCGGCGGCACUCGAAUUCAAAUAUCGCGUUGUUUGAGUGUCGGCAAUCGCUGGCCAUCGAUGACAGCAACGCCGCAAAAGCGGUUGUUGCUGUUGUGCCCCCGAUG .......(((.((((((((((((((((((......)))))))))((((((....))))))..)))).((((((((((((((....)))).))))))))))))))).)))... ( -53.90) >DroEre_CAF1 23909 112 - 1 ACAGAACCGCCGGCACUCGAAUUCAAAUAUCGCGUUGUCUGAGUGUCGGCAAUCGUUGGCCAUCGAUGACAGCAACGCCGCAAAAGCGGUUGUUGCUGUUGUGCCCCCGAUG ........(((((((((((....(((........)))..))))))))))).((((..(((.....(..(((((((((((((....)))).)))))))))..))))..)))). ( -49.50) >consensus ACAGAACCGGCGGCACUCGAAUUCAAAUAUCGCGUUGUUUGAGUGUCGGCAAUCGCUGGCCAUCGAUGACAGCAACGCCGCAAAAGCGGUUGUUGCUGUUGUGCCCCCGAUG .......(((.((((((((((((((((((......)))))))))((((((....))))))..)))).((((((((((((((....)))).))))))))))))))).)))... (-51.25 = -51.38 + 0.12)

Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 09:29:03 2006