
| Sequence ID | 2L_DroMel_CAF1 |
|---|---|
| Location | 2,670,036 – 2,670,156 |
| Length | 120 |
| Max. P | 0.500000 |

| Location | 2,670,036 – 2,670,156 |
|---|---|
| Length | 120 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 79.83 |
| Mean single sequence MFE | -47.42 |
| Consensus MFE | -24.03 |
| Energy contribution | -22.78 |
| Covariance contribution | -1.24 |
| Combinations/Pair | 1.44 |
| Mean z-score | -2.00 |
| Structure conservation index | 0.51 |
| SVM decision value | -0.07 |
| SVM RNA-class probability | 0.500000 |
| Prediction | OTHER |
Download alignment: ClustalW | MAF
>2L_DroMel_CAF1 2670036 120 - 22407834 GUCUUUGCAGUUGCAACUCCGUCUGGACUCGCAGAUCCUCCAGCUGGCUGUGGGUCUUCUGCUUAAGGACACUCUCCAGCAGGAGCGCAAAUCCCAGCACGGAGUUUCCCACGAACAGCA .....(((.((((.((((((((((((((((((((..((.......))))))))))((((((((...(((.....)))))))))))........)))).)))))))).).....))).))) ( -42.20) >DroPse_CAF1 115033 120 - 1 GGCGCUGCAGCUGGAGCUGCGACUGGAAGCGCAGGUCCUCCAGCUGUCUGUGGGUCUUCUGCUUCAGCACGCUCUCCAGAAGAAGCAGCAGACCCAAAACGGUGCUGCCCAUGAAGAGCA (((((((((((((((((((((........)))))...)))))))))....(((((((.(((((((..(..........)..))))))).)))))))...)))))))((.(.....).)). ( -55.40) >DroSim_CAF1 91030 120 - 1 GUCUUUGCAGCUGCAACUCCGUCUGGACUCGCAGAUCCUCCAGCUGGCUGUGGGUCUUCUGCUUCAGGACACUCUCCAGCAGGAGCGCAAAUCCCAGCACGGAGUUUCCCACGAACAGCA .........((((.((((((((((((((((((((..((.......))))))))))((((((((...(((.....)))))))))))........)))).))))))))((....)).)))). ( -44.50) >DroYak_CAF1 93656 120 - 1 GUCUCUGCAGCUGCAACUCCGUCUGAACACGCAGAUCCUCCAGCUGGCUGUGGGUCUUUUGCUUAAGGACACUCUCCAGCAGGAGCGCAAGUCCCAGCACGGAGUUGCCCACGAACAGCG .........((((((((((((((((.....(((((.((..(((....)))..))...)))))....((((.(.((((....)))).)...))))))).))))))))))........))). ( -45.50) >DroAna_CAF1 147799 120 - 1 AACGUUGGAGCUGCAGUUCCGACUGGAAGCGCAGGGUCUCCAACUGGCCGUGGGCCGCCUGCUGCAGGACACUUUCCAGGAGUAGCAGCAGUCCUAGCACAGACUUUCCCGUGAAUAGUA ...(((((..((((.(((.(..((((((((.((.((((.......)))).)).)).(((((...)))).)...))))))..).))).))))..)))))....((((((....))).))). ( -43.60) >DroPer_CAF1 111773 120 - 1 GGCGCUGCAGCUGGAGCUGCGACUGGAAGCGCAGGUCUUCCAGCUGUCUGUGGGUCUUCUGCUUCAGCACGCUCUCCAGGAGGAGCAGCAGACCCAAAAUGGUGCUGCCCAUGAAGAGCA (((((((((((((((((((((........)))))...))))))))))...(((((((..(((....))).(((((((....)))).))))))))))....))))))((.(.....).)). ( -53.30) >consensus GUCGCUGCAGCUGCAACUCCGACUGGAAGCGCAGAUCCUCCAGCUGGCUGUGGGUCUUCUGCUUCAGGACACUCUCCAGCAGGAGCACAAGUCCCAGCACGGAGUUGCCCACGAACAGCA .........((((.....(((.(((((...........))))).))).((((((.....((((((.(((.....)))....)))))).(((..((.....))..)))))))))..)))). (-24.03 = -22.78 + -1.24)

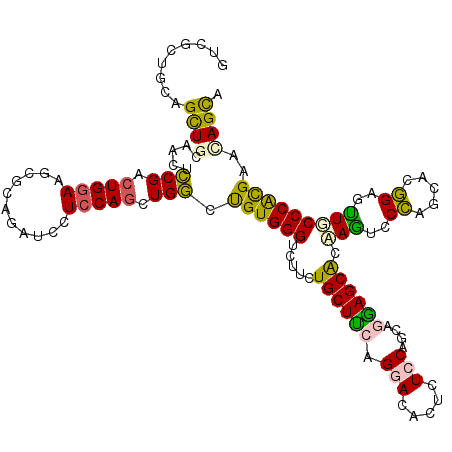
Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 09:49:01 2006