
| Sequence ID | 2L_DroMel_CAF1 |
|---|---|
| Location | 19,565,793 – 19,565,927 |
| Length | 134 |
| Max. P | 0.973645 |

| Location | 19,565,793 – 19,565,894 |
|---|---|
| Length | 101 |
| Sequences | 6 |
| Columns | 107 |
| Reading direction | reverse |
| Mean pairwise identity | 86.33 |
| Mean single sequence MFE | -27.73 |
| Consensus MFE | -24.28 |
| Energy contribution | -24.31 |
| Covariance contribution | 0.03 |
| Combinations/Pair | 1.04 |
| Mean z-score | -2.33 |
| Structure conservation index | 0.88 |
| SVM decision value | 1.37 |
| SVM RNA-class probability | 0.947470 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2L_DroMel_CAF1 19565793 101 - 22407834 UCUCAAAGUGGUUGUGAAAUGCAUUUC---CGCUUUGCGCGGCAUAUCACAGCCAGCUUUGAUGAGCUUAGCGUAAUGUAUCGUACAUCAAAUCAUAAUAAUAC--- ..(((((((((((((((.((((.....---(((.....))))))).))))))))).))))))(((.....(((........)))...)))..............--- ( -29.10) >DroPse_CAF1 19561 100 - 1 UCACAAAGUGGUUGUGAAAUGCAUUU----UGCUUUGCCC-GCAUAUCACAGCCAGCUUUGAUGAGCUCGGCGUAAUGUAUCGUACAUCAAUCAAUCAUAAUAUA-- ...((((((((((((((.((((....----..........-)))).))))))))).))))).(((.....(((........)))...)))...............-- ( -26.24) >DroEre_CAF1 6902 101 - 1 UCUCAAAGUGGUUGUGAAAUGCAUAUC---AGCUUUGCGCGGCAUAUCACAGCCAGCUUUGAUGAGCUUAGCGUAAUGUAUCGUACAUCAAAUCAUGGUAAUAC--- (((((((((((((((((.((((.....---.((.....)).)))).))))))))).)))))).)).......(((...((((((..........)))))).)))--- ( -28.30) >DroYak_CAF1 6239 99 - 1 UCUCAAAGUGGUUGUGAAAUGCAUUUC---CGCUUUGCGCGGCAUAUCACAGCCAGCUUUGAUGAGCUUAGCGUAAUGUAUCGUACAUCAAAUCAUGGUUUU----- ..(((((((((((((((.((((.....---(((.....))))))).))))))))).)))))).(((((.......(((((...)))))........))))).----- ( -29.46) >DroMoj_CAF1 28058 101 - 1 UCUCAAAGAGGCUGUGAAAUGCAUUUUGAAAGCUUUGCGA-GCAUAUCACAGCCAGCUUUGAUGAGCUUAGCGUAAUGUAACGUACAUCAAUCAAUCAAAUC----- ..((((((.((((((((.((((..................-)))).))))))))..))))))(((.....((((......))))...)))............----- ( -27.07) >DroPer_CAF1 19480 102 - 1 UCACAAAGUGGUUGUGAAAUGCAUUU----UGCUUUGCCC-GCAUAUCACAGCCAGCUUUGAUGAGCUCGGCGUAAUGUAUCGUACAUCAAUCAAUCAUAAUAUACG ...((((((((((((((.((((....----..........-)))).))))))))).))))).(((.....(((........)))...)))................. ( -26.24) >consensus UCUCAAAGUGGUUGUGAAAUGCAUUUC___AGCUUUGCGC_GCAUAUCACAGCCAGCUUUGAUGAGCUUAGCGUAAUGUAUCGUACAUCAAACAAUCAUAAUA____ ...((((((((((((((.((((...................)))).))))))))).))))).(((.....(((........)))...)))................. (-24.28 = -24.31 + 0.03)

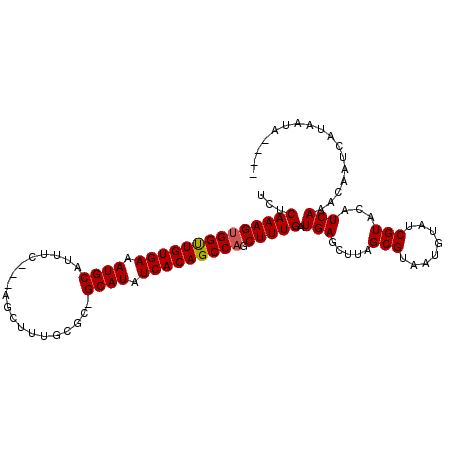
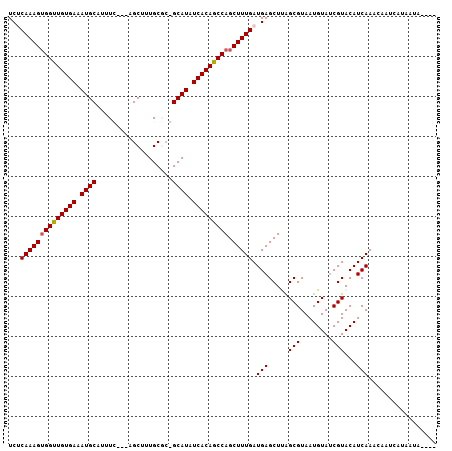
| Location | 19,565,818 – 19,565,927 |
|---|---|
| Length | 109 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 82.44 |
| Mean single sequence MFE | -38.33 |
| Consensus MFE | -28.23 |
| Energy contribution | -29.23 |
| Covariance contribution | 1.00 |
| Combinations/Pair | 1.00 |
| Mean z-score | -4.49 |
| Structure conservation index | 0.74 |
| SVM decision value | 1.61 |
| SVM RNA-class probability | 0.967366 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2L_DroMel_CAF1 19565818 109 + 22407834 ACAUUACGCUAAGCUCAUCAAAGCUGGCUGUGAUAUGCCGCGCAAAGCG---GA-AAUGCAUUUCACAACCACUUUGAGAGCCCAGCAUGAAUGCG-CCAA-UAUAGU----UU-UAUUG .((((..(((..((((.((((((.(((.(((((.(((((((.....)))---..-...)))).))))).)))))))))))))..)))...))))..-.(((-((....----..-))))) ( -37.70) >DroVir_CAF1 8361 108 + 1 ACAUUACGCUAAGCUCAUCAAAGCUGGCUGUGAUAUGC-GCGCAAAGCUUUCA--AAUGCAUUUCACAACCACUUUGAGAGCGCAGCAUGAAUGUG-CCAA-U--CUU----AU-GGUAA (((((..(((..((((.((((((.(((.(((((.((((-((.....)).....--...)))).))))).)))))))))))))..)))...)))))(-(((.-.--...----.)-))).. ( -38.80) >DroGri_CAF1 6979 114 + 1 ACAUUACGCUAAGCUCAUCAAAGCUGGCUGUGAUAUGC-GCGCAAAGCUUUCAAAAAUGCAUUUCACAACCACUUUGAGAGCGCAGCAUGAAUGUG-CCAA-U--CUUAGAUAU-GCUUG (((((..(((..((((.((((((.(((.(((((.((((-((.....))..........)))).))))).)))))))))))))..)))...))))).-....-.--.........-..... ( -35.40) >DroWil_CAF1 28106 109 + 1 ACAUUACGCAGAGCUCAUCAAAGCUGGCUGUGAUAUGCUGGAUAAAGCA---AAUAAUGCAUUUCACAACCACUUUGUGAGCUCAGCAUGAAUGUG-UCGU-G--UGU----UUUUCUUU ....(((((.(((((((.(((((.(((.(((((.((((...........---......)))).))))).))))))))))))))).((((....)))-).))-)--)).----........ ( -38.13) >DroMoj_CAF1 28081 111 + 1 ACAUUACGCUAAGCUCAUCAAAGCUGGCUGUGAUAUGC-UCGCAAAGCUUUCAA-AAUGCAUUUCACAGCCUCUUUGAGAGCUCAGCAUGAAUGUGGCCAAUU--CUU----AU-GAUAG (((((..(((.(((((.((((((..((((((((.((((-...............-...)))).)))))))).))))))))))).)))...)))))........--...----..-..... ( -41.17) >DroAna_CAF1 6618 106 + 1 ACAUAACGCUAAGCUCAUCAAAGCUGGCUGUGAUAUGC-GGGCAAAAUG---GA-AAUGCAUUUCACAACCACUUUGUGAGCCCAGCAGGAAUGUG-CCAA-UAU--U----UU-UGUUG ............(((((.(((((.(((.(((((.((((-(..(......---).-..))))).))))).))))))))))))).((((((((((((.-...)-)))--)----))-))))) ( -38.80) >consensus ACAUUACGCUAAGCUCAUCAAAGCUGGCUGUGAUAUGC_GCGCAAAGCU___AA_AAUGCAUUUCACAACCACUUUGAGAGCCCAGCAUGAAUGUG_CCAA_U__CUU____AU_GAUUG (((((..(((..((((.((((((.(((.(((((.((((....................)))).))))).)))))))))))))..)))...)))))......................... (-28.23 = -29.23 + 1.00)

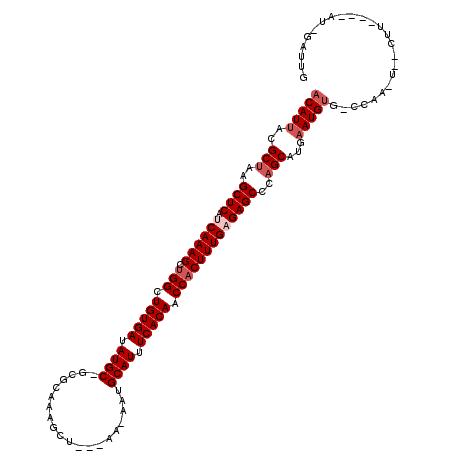
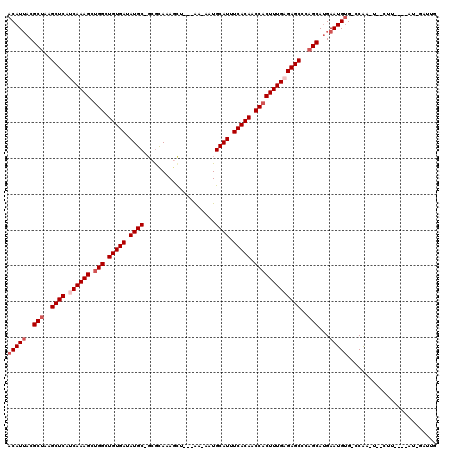
| Location | 19,565,818 – 19,565,927 |
|---|---|
| Length | 109 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 82.44 |
| Mean single sequence MFE | -44.69 |
| Consensus MFE | -40.42 |
| Energy contribution | -41.23 |
| Covariance contribution | 0.81 |
| Combinations/Pair | 1.11 |
| Mean z-score | -5.97 |
| Structure conservation index | 0.90 |
| SVM decision value | 1.71 |
| SVM RNA-class probability | 0.973645 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2L_DroMel_CAF1 19565818 109 - 22407834 CAAUA-AA----ACUAUA-UUGG-CGCAUUCAUGCUGGGCUCUCAAAGUGGUUGUGAAAUGCAUU-UC---CGCUUUGCGCGGCAUAUCACAGCCAGCUUUGAUGAGCUUAGCGUAAUGU (((((-..----....))-))).-.(((((.((((((((((((((((((((((((((.((((...-..---(((.....))))))).))))))))).)))))).)))))))))))))))) ( -50.20) >DroVir_CAF1 8361 108 - 1 UUACC-AU----AAG--A-UUGG-CACAUUCAUGCUGCGCUCUCAAAGUGGUUGUGAAAUGCAUU--UGAAAGCUUUGCGC-GCAUAUCACAGCCAGCUUUGAUGAGCUUAGCGUAAUGU ...((-(.----...--.-.)))-.(((((.((((((.(((((((((((((((((((.((((...--.....((.....))-)))).))))))))).)))))).)))).))))))))))) ( -43.50) >DroGri_CAF1 6979 114 - 1 CAAGC-AUAUCUAAG--A-UUGG-CACAUUCAUGCUGCGCUCUCAAAGUGGUUGUGAAAUGCAUUUUUGAAAGCUUUGCGC-GCAUAUCACAGCCAGCUUUGAUGAGCUUAGCGUAAUGU ...((-..(((...)--)-)..)-)(((((.((((((.(((((((((((((((((((.((((.((....)).((.....))-)))).))))))))).)))))).)))).))))))))))) ( -43.00) >DroWil_CAF1 28106 109 - 1 AAAGAAAA----ACA--C-ACGA-CACAUUCAUGCUGAGCUCACAAAGUGGUUGUGAAAUGCAUUAUU---UGCUUUAUCCAGCAUAUCACAGCCAGCUUUGAUGAGCUCUGCGUAAUGU ........----...--.-....-.(((((.((((.(((((((((((((((((((((.((((......---...........)))).))))))))).))))).))))))).))))))))) ( -43.33) >DroMoj_CAF1 28081 111 - 1 CUAUC-AU----AAG--AAUUGGCCACAUUCAUGCUGAGCUCUCAAAGAGGCUGUGAAAUGCAUU-UUGAAAGCUUUGCGA-GCAUAUCACAGCCAGCUUUGAUGAGCUUAGCGUAAUGU .....-..----...--........(((((.(((((((((((((((((.((((((((.((((...-...............-)))).))))))))..)))))).)))))))))))))))) ( -45.67) >DroAna_CAF1 6618 106 - 1 CAACA-AA----A--AUA-UUGG-CACAUUCCUGCUGGGCUCACAAAGUGGUUGUGAAAUGCAUU-UC---CAUUUUGCCC-GCAUAUCACAGCCAGCUUUGAUGAGCUUAGCGUUAUGU .....-..----.--...-....-.((((..(.((((((((((((((((((((((((.((((...-..---..........-)))).))))))))).))))).)))))))))))..)))) ( -42.46) >consensus CAACA_AA____AAG__A_UUGG_CACAUUCAUGCUGAGCUCUCAAAGUGGUUGUGAAAUGCAUU_UU___AGCUUUGCGC_GCAUAUCACAGCCAGCUUUGAUGAGCUUAGCGUAAUGU .........................(((((.((((((((((((((((((((((((((.((((....................)))).))))))))).)))))).)))))))))))))))) (-40.42 = -41.23 + 0.81)


Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 12:25:20 2006