
| Sequence ID | 2L_DroMel_CAF1 |
|---|---|
| Location | 19,565,392 – 19,565,500 |
| Length | 108 |
| Max. P | 0.999852 |

| Location | 19,565,392 – 19,565,500 |
|---|---|
| Length | 108 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 88.80 |
| Mean single sequence MFE | -37.60 |
| Consensus MFE | -36.30 |
| Energy contribution | -36.30 |
| Covariance contribution | 0.00 |
| Combinations/Pair | 1.00 |
| Mean z-score | -4.44 |
| Structure conservation index | 0.97 |
| SVM decision value | 4.26 |
| SVM RNA-class probability | 0.999852 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
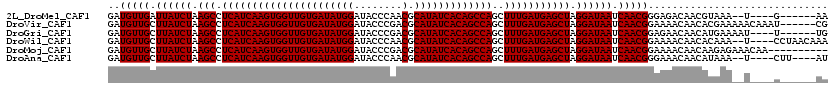
>2L_DroMel_CAF1 19565392 108 + 22407834 UU------C----A--UUUACGUUGUCUCCCGUUGAUUAUCCUAGCUCAUCAAAGCUGGCUGUGAUAUGCGUUGGGUAUCCAUAUCACAACCACUUGAUGAGGCUUAGAUAAUCAACAUC ..------.----.--...............((((((((((..((((((((((.(.(((.(((((((((.((.....)).))))))))).))))))))))).)))..))))))))))... ( -41.00) >DroVir_CAF1 8069 114 + 1 CG------AUUUGUUUUUCGUGUUGUUUUCCGUUGAUUAUCCUAGCUCAUCAAAGCUGGCUGUGAUAUGCGUCGGGUAUCCAUAUCACAACCACUUGAUGAGGCUUAGAUAAGCAACAUC ((------(........)))...........((((.(((((..((((((((((.(.(((.(((((((((.(........)))))))))).))))))))))).)))..))))).))))... ( -37.20) >DroGri_CAF1 6663 110 + 1 CA------A----AUUUUCAUGUUGUUCUCCGUUGAUUAUCCUAGCUCAUCAAAGCUGGCUGUGAUAUGCGUCGGGUAUCCAUAUCACAACCACUUGAUGAGGCUUAGAUAAGCAACAUC ..------.----..................((((.(((((..((((((((((.(.(((.(((((((((.(........)))))))))).))))))))))).)))..))))).))))... ( -36.30) >DroWil_CAF1 27716 114 + 1 UUUGUUAGG----A--UUUGUGUUGUUUUCCGUUGAUUAUCCUAGCUCAUCAAAGCUGGCUGUGAUAUGCGUUGGGUAUCCAUAUCACAACCACUUGAUGAGGCUUAGAUAAGCAACAUC .......((----(--............)))((((.(((((..((((((((((.(.(((.(((((((((.((.....)).))))))))).))))))))))).)))..))))).))))... ( -38.40) >DroMoj_CAF1 27478 110 + 1 ----------UUGUUUCUCUUGUUGUUUUCCGUUGAUUAUCCUAGCUCAUCAAAGCUGGCUGUGAUAUGCGUCGGGUAUCCAUAUCACAACCACUUGAUGAGGCUUAGAUAAGCAACAUC ----------.....................((((.(((((..((((((((((.(.(((.(((((((((.(........)))))))))).))))))))))).)))..))))).))))... ( -36.30) >DroAna_CAF1 6279 110 + 1 AU----AAG----A--UUUAUGUUGUUUCCCGUUGAUUAUCCUAGCUCAUCAAAGCUGGCUGUGAUAUGCGUUGGGUAUCCAUAUCACAACCACUUGAUGAGGCUUAGAUAAGCAACAUC ..----...----.--...............((((.(((((..((((((((((.(.(((.(((((((((.((.....)).))))))))).))))))))))).)))..))))).))))... ( -36.40) >consensus CU______A____A__UUCAUGUUGUUUUCCGUUGAUUAUCCUAGCUCAUCAAAGCUGGCUGUGAUAUGCGUCGGGUAUCCAUAUCACAACCACUUGAUGAGGCUUAGAUAAGCAACAUC ...............................((((.(((((..((((((((((.(.(((.(((((((((.(........)))))))))).))))))))))).)))..))))).))))... (-36.30 = -36.30 + 0.00)


| Location | 19,565,392 – 19,565,500 |
|---|---|
| Length | 108 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 88.80 |
| Mean single sequence MFE | -43.10 |
| Consensus MFE | -41.70 |
| Energy contribution | -41.70 |
| Covariance contribution | -0.00 |
| Combinations/Pair | 1.00 |
| Mean z-score | -6.33 |
| Structure conservation index | 0.97 |
| SVM decision value | 2.87 |
| SVM RNA-class probability | 0.997475 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2L_DroMel_CAF1 19565392 108 - 22407834 GAUGUUGAUUAUCUAAGCCUCAUCAAGUGGUUGUGAUAUGGAUACCCAACGCAUAUCACAGCCAGCUUUGAUGAGCUAGGAUAAUCAACGGGAGACAACGUAAA--U----G------AA ..((((((((((((.(((.((((((((((((((((((((((........).)))))))))))))..))))))))))).))))))))))))(....)........--.----.------.. ( -47.80) >DroVir_CAF1 8069 114 - 1 GAUGUUGCUUAUCUAAGCCUCAUCAAGUGGUUGUGAUAUGGAUACCCGACGCAUAUCACAGCCAGCUUUGAUGAGCUAGGAUAAUCAACGGAAAACAACACGAAAAACAAAU------CG ..(((((.((((((.(((.((((((((((((((((((((((........).)))))))))))))..))))))))))).)))))).)))))......................------.. ( -41.70) >DroGri_CAF1 6663 110 - 1 GAUGUUGCUUAUCUAAGCCUCAUCAAGUGGUUGUGAUAUGGAUACCCGACGCAUAUCACAGCCAGCUUUGAUGAGCUAGGAUAAUCAACGGAGAACAACAUGAAAAU----U------UG ..(((((.((((((.(((.((((((((((((((((((((((........).)))))))))))))..))))))))))).)))))).))))).................----.------.. ( -41.70) >DroWil_CAF1 27716 114 - 1 GAUGUUGCUUAUCUAAGCCUCAUCAAGUGGUUGUGAUAUGGAUACCCAACGCAUAUCACAGCCAGCUUUGAUGAGCUAGGAUAAUCAACGGAAAACAACACAAA--U----CCUAACAAA ...((((.((((((.(((.((((((((((((((((((((((........).)))))))))))))..))))))))))).)))))).))))(((............--)----))....... ( -42.20) >DroMoj_CAF1 27478 110 - 1 GAUGUUGCUUAUCUAAGCCUCAUCAAGUGGUUGUGAUAUGGAUACCCGACGCAUAUCACAGCCAGCUUUGAUGAGCUAGGAUAAUCAACGGAAAACAACAAGAGAAACAA---------- ..(((((.((((((.(((.((((((((((((((((((((((........).)))))))))))))..))))))))))).)))))).)))))....................---------- ( -41.70) >DroAna_CAF1 6279 110 - 1 GAUGUUGCUUAUCUAAGCCUCAUCAAGUGGUUGUGAUAUGGAUACCCAACGCAUAUCACAGCCAGCUUUGAUGAGCUAGGAUAAUCAACGGGAAACAACAUAAA--U----CUU----AU (((((((.((((((.(((.((((((((((((((((((((((........).)))))))))))))..))))))))))).)))))).)))).(....).......)--)----)..----.. ( -43.50) >consensus GAUGUUGCUUAUCUAAGCCUCAUCAAGUGGUUGUGAUAUGGAUACCCAACGCAUAUCACAGCCAGCUUUGAUGAGCUAGGAUAAUCAACGGAAAACAACAUAAA__U____C______AA ..(((((.((((((.(((.((((((((((((((((((((((........).)))))))))))))..))))))))))).)))))).))))).............................. (-41.70 = -41.70 + -0.00)

Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 12:25:17 2006