
| Sequence ID | 2L_DroMel_CAF1 |
|---|---|
| Location | 18,467,920 – 18,468,069 |
| Length | 149 |
| Max. P | 0.999907 |

| Location | 18,467,920 – 18,468,036 |
|---|---|
| Length | 116 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 90.62 |
| Mean single sequence MFE | -34.77 |
| Consensus MFE | -32.64 |
| Energy contribution | -32.36 |
| Covariance contribution | -0.28 |
| Combinations/Pair | 1.06 |
| Mean z-score | -4.18 |
| Structure conservation index | 0.94 |
| SVM decision value | 4.48 |
| SVM RNA-class probability | 0.999907 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
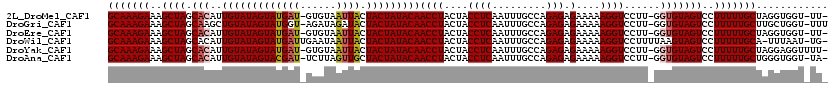
>2L_DroMel_CAF1 18467920 116 + 22407834 -AA-ACCACCUAGCAAAAAGGACUACACC-AAGGACCUUUUUCUCUCUGGCAAAUUGAGGUAGUAGGUUGUAUAGUAGUAAUUACAC-AUCAUACUAUACAAUGUGCUAGCUUUCUUUGC -..-..((...((.(((((((.((.....-.))..)))))))))...))(((((..(((.(((((.(((((((((((..........-....))))))))))).))))).)))..))))) ( -33.74) >DroGri_CAF1 27234 117 + 1 AAA-ACCAGCAAGCAAAAAGGACUACACC-AAGGACCUUUUUCUCUCUGGCAAAUUGAGGUAGUAGGUUGUAUAGUAGUAUCUAUCU-ACCAUACUAUACAGCUUGCUAGCUUUCUUUGC ...-..(((..((.(((((((.((.....-.))..)))))))))..)))(((((..(((.((((((((((((((((((((......)-))..))))))))))))))))).)))..))))) ( -41.70) >DroEre_CAF1 22234 116 + 1 -AA-ACCACCUAGCAAAAAGGACUACACC-AAGGACCUUUUUCUCUCUGGCAAAUUGAGGUAGUAGGUUGUAUAGUAGUAAUUACAC-AUCAUACUAUACAAUGUGCUAGCUUUCUUUGC -..-..((...((.(((((((.((.....-.))..)))))))))...))(((((..(((.(((((.(((((((((((..........-....))))))))))).))))).)))..))))) ( -33.74) >DroWil_CAF1 28686 117 + 1 -CA-AUUAAA-UGCAAAAAGGACUACUUAAAAGGACCUUUUUCUCUCUGGCAAAUUGAGGUAGUAGGUUGUAUAGUAGUAAUUAUUCAAUCAUACUAUACAAUGUGCUAGCUUUCUUUGC -..-......-...(((((((.((........)).))))))).......(((((..(((.(((((.(((((((((((...............))))))))))).))))).)))..))))) ( -32.56) >DroYak_CAF1 22155 117 + 1 -AAAACCUCCUAGCAAAAAGGACUACACC-AAGGACCUUUUUCUCUCUGGCAAAUUGAGGUAGUAGGUUGUAUAGUAGUAAUUACAC-AUCAUACUAUACAAUGUGCUAGCUUUCUUUGC -..........((.(((((((.((.....-.))..))))))))).....(((((..(((.(((((.(((((((((((..........-....))))))))))).))))).)))..))))) ( -33.24) >DroAna_CAF1 18204 116 + 1 -UA-ACCACCCAGCAAAAAGGACUACACC-AAGGACCUUUUUCUCUCUGGCAAAUUGAGGUAGUAGGUUGUAUAGUAGCAACUAAGA-AUCGUACUAUACAAUGUGCUAGCUUUCUUUGC -..-......(((.(((((((.((.....-.))..)))))))....)))(((((..(((.(((((.(((((((((((..........-....))))))))))).))))).)))..))))) ( -33.64) >consensus _AA_ACCACCUAGCAAAAAGGACUACACC_AAGGACCUUUUUCUCUCUGGCAAAUUGAGGUAGUAGGUUGUAUAGUAGUAAUUACAC_AUCAUACUAUACAAUGUGCUAGCUUUCUUUGC ............(.(((((((.((........)).))))))))......(((((..(((.(((((.(((((((((((...............))))))))))).))))).)))..))))) (-32.64 = -32.36 + -0.28)

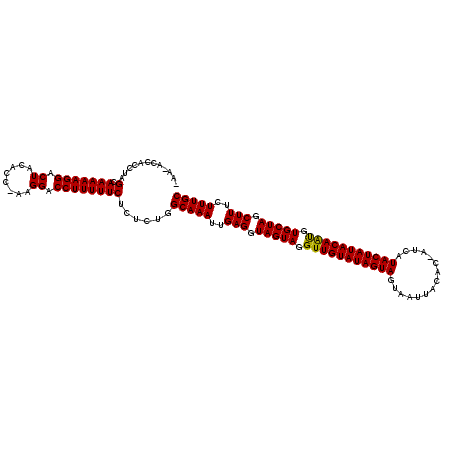
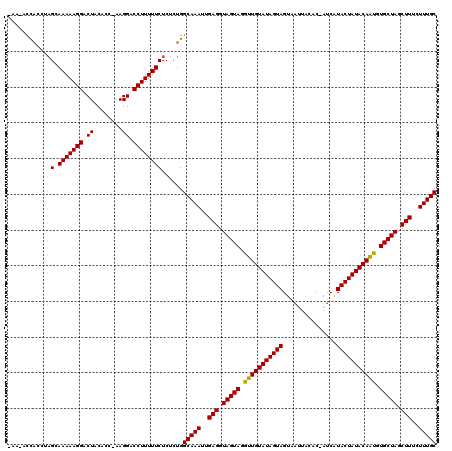
| Location | 18,467,920 – 18,468,036 |
|---|---|
| Length | 116 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 90.62 |
| Mean single sequence MFE | -29.12 |
| Consensus MFE | -24.93 |
| Energy contribution | -25.10 |
| Covariance contribution | 0.17 |
| Combinations/Pair | 1.06 |
| Mean z-score | -1.74 |
| Structure conservation index | 0.86 |
| SVM decision value | 0.44 |
| SVM RNA-class probability | 0.738713 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2L_DroMel_CAF1 18467920 116 - 22407834 GCAAAGAAAGCUAGCACAUUGUAUAGUAUGAU-GUGUAAUUACUACUAUACAACCUACUACCUCAAUUUGCCAGAGAGAAAAAGGUCCUU-GGUGUAGUCCUUUUUGCUAGGUGGU-UU- (((((((..((((.(((..(((((((((((((-.....)))).)))))))))((((....((((.........))).)....))))....-.)))))))..)))))))........-..- ( -28.10) >DroGri_CAF1 27234 117 - 1 GCAAAGAAAGCUAGCAAGCUGUAUAGUAUGGU-AGAUAGAUACUACUAUACAACCUACUACCUCAAUUUGCCAGAGAGAAAAAGGUCCUU-GGUGUAGUCCUUUUUGCUUGCUGGU-UUU ......(((((((((((((......(((((((-((.......))))))))).....(((((.((((...(((...........)))..))-)).))))).......))))))))))-))) ( -36.90) >DroEre_CAF1 22234 116 - 1 GCAAAGAAAGCUAGCACAUUGUAUAGUAUGAU-GUGUAAUUACUACUAUACAACCUACUACCUCAAUUUGCCAGAGAGAAAAAGGUCCUU-GGUGUAGUCCUUUUUGCUAGGUGGU-UU- (((((((..((((.(((..(((((((((((((-.....)))).)))))))))((((....((((.........))).)....))))....-.)))))))..)))))))........-..- ( -28.10) >DroWil_CAF1 28686 117 - 1 GCAAAGAAAGCUAGCACAUUGUAUAGUAUGAUUGAAUAAUUACUACUAUACAACCUACUACCUCAAUUUGCCAGAGAGAAAAAGGUCCUUUUAAGUAGUCCUUUUUGCA-UUUAAU-UG- (((((((..((((......((((((((((((((....))))).)))))))))((((....((((.........))).)....)))).........))))..))))))).-......-..- ( -24.40) >DroYak_CAF1 22155 117 - 1 GCAAAGAAAGCUAGCACAUUGUAUAGUAUGAU-GUGUAAUUACUACUAUACAACCUACUACCUCAAUUUGCCAGAGAGAAAAAGGUCCUU-GGUGUAGUCCUUUUUGCUAGGAGGUUUU- (((((((..((((.(((..(((((((((((((-.....)))).)))))))))((((....((((.........))).)....))))....-.)))))))..)))))))...........- ( -28.10) >DroAna_CAF1 18204 116 - 1 GCAAAGAAAGCUAGCACAUUGUAUAGUACGAU-UCUUAGUUGCUACUAUACAACCUACUACCUCAAUUUGCCAGAGAGAAAAAGGUCCUU-GGUGUAGUCCUUUUUGCUGGGUGGU-UA- (((((((..((((.(((..(((((((((((((-.....)))).)))))))))((((....((((.........))).)....))))....-.)))))))..)))))))........-..- ( -29.10) >consensus GCAAAGAAAGCUAGCACAUUGUAUAGUAUGAU_GUGUAAUUACUACUAUACAACCUACUACCUCAAUUUGCCAGAGAGAAAAAGGUCCUU_GGUGUAGUCCUUUUUGCUAGGUGGU_UU_ (((((((..((((.(((..(((((((((((((......)))).)))))))))((((....((((.........))).)....))))......)))))))..)))))))............ (-24.93 = -25.10 + 0.17)
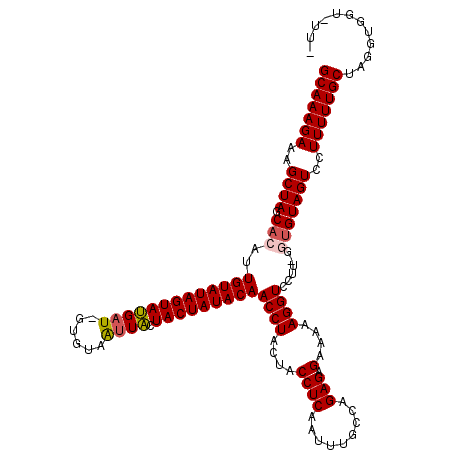
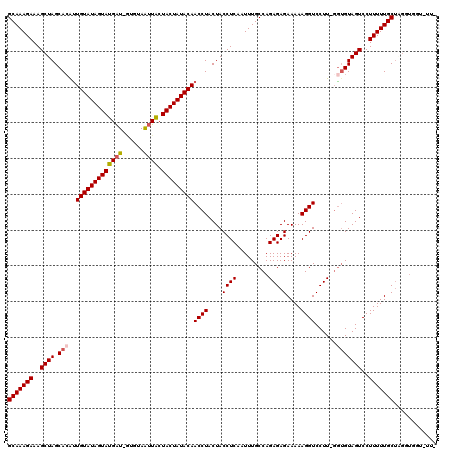
| Location | 18,467,957 – 18,468,069 |
|---|---|
| Length | 112 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 85.70 |
| Mean single sequence MFE | -31.92 |
| Consensus MFE | -30.97 |
| Energy contribution | -30.69 |
| Covariance contribution | -0.28 |
| Combinations/Pair | 1.07 |
| Mean z-score | -3.46 |
| Structure conservation index | 0.97 |
| SVM decision value | 3.42 |
| SVM RNA-class probability | 0.999190 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2L_DroMel_CAF1 18467957 112 + 22407834 UUCUCUCUGGCAAAUUGAGGUAGUAGGUUGUAUAGUAGUAAUUACAC-AUCAUACUAUACAAUGUGCUAGCUUUCUUUGCUUGACUACAAGCCGCA--UUUGAUAAAAGAAUCC-----C ((((.((.((((((..(((.(((((.(((((((((((..........-....))))))))))).))))).)))..)))))).))...((((.....--)))).....))))...-----. ( -31.54) >DroGri_CAF1 27272 108 + 1 UUCUCUCUGGCAAAUUGAGGUAGUAGGUUGUAUAGUAGUAUCUAUCU-ACCAUACUAUACAGCUUGCUAGCUUUCUUUGCUUGACUAUAAGCAGCA--UAGAAC----GAAACC-----C (((..((((((.....(((.((((((((((((((((((((......)-))..))))))))))))))))).)))....((((((....)))))))).--))))..----)))...-----. ( -36.00) >DroSec_CAF1 26968 112 + 1 UUCUCUCUGGCAAAUUGAGGUAGUAGGUUGUAUAGUAGUAAUUACAC-AUCAUACUAUACAAUGUGCUAGCUUUCUUUGCUUGACUACAAGCCGCA--UUUGAUUAAAGAACCC-----C ((((.((.((((((..(((.(((((.(((((((((((..........-....))))))))))).))))).)))..)))))).))...((((.....--)))).....))))...-----. ( -31.44) >DroSim_CAF1 22787 112 + 1 UUCUCUCUGGCAAAUUGAGGUAGUAGGUUGUAUAGUAGUAAUUACAC-AUCAUACUAUACAAUGUGCUAGCUUUCUUUGCUUGACUACAAGCCGCA--UUUGAUUAAAGAACCC-----C ((((.((.((((((..(((.(((((.(((((((((((..........-....))))))))))).))))).)))..)))))).))...((((.....--)))).....))))...-----. ( -31.44) >DroWil_CAF1 28723 108 + 1 UUCUCUCUGGCAAAUUGAGGUAGUAGGUUGUAUAGUAGUAAUUAUUCAAUCAUACUAUACAAUGUGCUAGCUUUCUUUGCUUGACUAUAAGCCACAGAUAUGAUCUAA------------ .....((.((((((..(((.(((((.(((((((((((...............))))))))))).))))).)))..)))))).))........................------------ ( -30.96) >DroAna_CAF1 18241 117 + 1 UUCUCUCUGGCAAAUUGAGGUAGUAGGUUGUAUAGUAGCAACUAAGA-AUCGUACUAUACAAUGUGCUAGCUUUCUUUGCUUGACAAUAAGCCGCA--UUUGAUUUGAAAAUCCCCCCCC .....((.((((((..(((.(((((.(((((((((((..........-....))))))))))).))))).)))..)))))).))............--...................... ( -30.14) >consensus UUCUCUCUGGCAAAUUGAGGUAGUAGGUUGUAUAGUAGUAAUUACAC_AUCAUACUAUACAAUGUGCUAGCUUUCUUUGCUUGACUACAAGCCGCA__UUUGAUUAAAGAACCC_____C .....((.((((((..(((.(((((.(((((((((((...............))))))))))).))))).)))..)))))).)).................................... (-30.97 = -30.69 + -0.28)

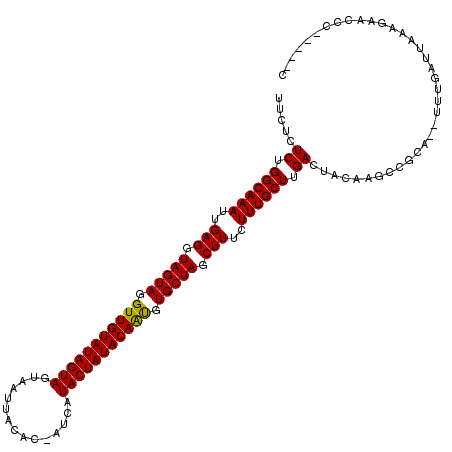
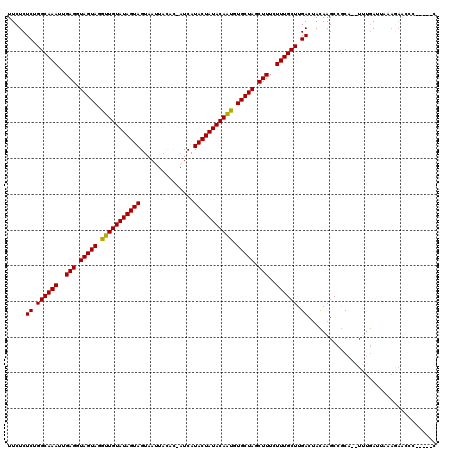
Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 12:14:21 2006