
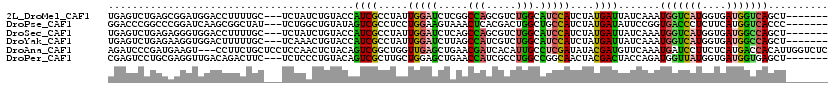
| Sequence ID | 2L_DroMel_CAF1 |
|---|---|
| Location | 1,784,735 – 1,784,845 |
| Length | 110 |
| Max. P | 0.550131 |

| Location | 1,784,735 – 1,784,845 |
|---|---|
| Length | 110 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 64.71 |
| Mean single sequence MFE | -37.07 |
| Consensus MFE | -8.74 |
| Energy contribution | -7.50 |
| Covariance contribution | -1.24 |
| Combinations/Pair | 1.68 |
| Mean z-score | -2.11 |
| Structure conservation index | 0.24 |
| SVM decision value | 0.03 |
| SVM RNA-class probability | 0.550131 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
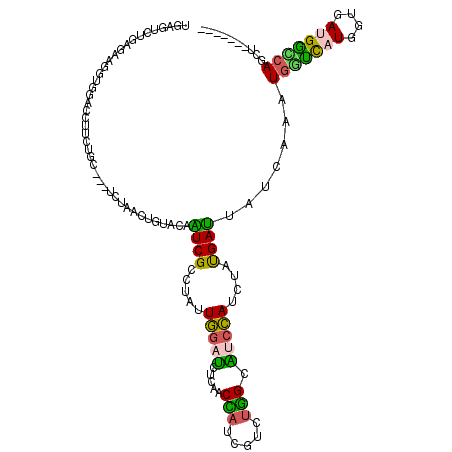
>2L_DroMel_CAF1 1784735 110 + 22407834 UGAGUCUGAGCGGAUGGACCUUUUGC---UCUAUCUGUACCAUCGCCUAUUGGAUCUCGGCCAGCGUCUGGCAUCCAUCUAUGAUUAUCAAAUGGUCAUGGUGAUGGUCAGCU------- ..((.(((((((((((((.(....).---))))))))).((((((((...(((((....(((((...))))))))))...((((((((...))))))))))))))))))))))------- ( -42.80) >DroPse_CAF1 48605 110 + 1 GGACCCGGCCCGGAUCAAGCGGCUAU---UCUGGCUGUAUAGUCGCCUCCUGGAAGUAAACUCACGACUGGCUGCCAUCUAUGAUAUUCCGGUGACCCUCUUCAUGGUCACCC------- (((...(((((((.((..((((((((---.(.....).)))))))).....(..((....))..)))))))..)))(((...)))..)))(((((((........))))))).------- ( -35.00) >DroSec_CAF1 41683 110 + 1 UGAGUCUGAGAGGGUGGACCUUUUGC---UCUAUCUGUACCAUCGCCUAUUGGAUCUCAGCCAGCGUCUGGCAUCCAUCUAUGAUUAUCAAAUGGUCAUGGUGAUGGCCAGCU------- .((((..((((((.....))))))))---))...(((..((((((((...(((((....(((((...))))))))))...((((((((...)))))))))))))))).)))..------- ( -38.80) >DroYak_CAF1 52885 110 + 1 UGAGUCUGAGAAGGUGGACUUUUUGC---UCAAACUGUACCAUCGCCUAUUGGAUCUUAGCCAUCGUCUGGCAUCCAUCUAUGAUUAUCAAAUGGUCAUGGUGAUGGCCAGCU------- (((((..((((((.....))))))))---)))..(((..((((((((...(((((....((((.....)))))))))...((((((((...)))))))))))))))).)))..------- ( -36.30) >DroAna_CAF1 42164 117 + 1 AGAUCCCGAUGAAGU---CCUUCUGCUCCUCCAACUCUACAGUCGGCUGGUUGAGCUGAACGAUCACAUUGCCUCGAUAUACGAUGUUCAAAUGAUCCUUCUCAUGACCACAUUGGUCUC .((..((((((..((---(.....((((..(((.((........)).)))..)))).(((.(((((....((.(((.....))).)).....))))).)))....)))..))))))..)) ( -30.00) >DroPer_CAF1 47569 110 + 1 CGAGUCCUGCGAGGUUGACAGACUUC---UCUCCCUGUACAGUCGCUUGCUGGAGCUGAACCAUCGCCUGGCCGGCAACUACGACUACCAGAUGGUUAUGGUGAUGGUGAGCU------- ....(((.(((((((((((((.....---.....)))).))).).))))).)))(((..(((((((((((((((....)..(........)..))))).))))))))).))).------- ( -39.50) >consensus UGAGUCUGAGAAGGUGGACCUUCUGC___UCUAACUGUACAAUCGCCUAUUGGAUCUCAACCAUCGUCUGGCAUCCAUCUAUGAUUAUCAAAUGGUCAUGGUGAUGGCCAGCU_______ .........................................((((.....(((((.....(((.....))).)))))....)))).......(((((((....))))))).......... ( -8.74 = -7.50 + -1.24)
Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 09:40:16 2006