
| Sequence ID | 2L_DroMel_CAF1 |
|---|---|
| Location | 14,528,267 – 14,528,378 |
| Length | 111 |
| Max. P | 0.987223 |

| Location | 14,528,267 – 14,528,378 |
|---|---|
| Length | 111 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 92.21 |
| Mean single sequence MFE | -37.54 |
| Consensus MFE | -32.44 |
| Energy contribution | -33.44 |
| Covariance contribution | 1.00 |
| Combinations/Pair | 1.00 |
| Mean z-score | -2.65 |
| Structure conservation index | 0.86 |
| SVM decision value | 2.07 |
| SVM RNA-class probability | 0.987223 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
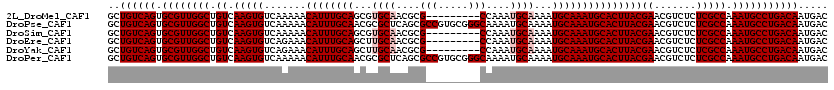
>2L_DroMel_CAF1 14528267 111 + 22407834 GCUGUCAGUGCGUUGGCUGUCAAGUGUCAAAAACAUUUGCAGCGUGCAACGCG---------CCAAAUGCAAAAUGCAAAUGCACUUACGAACGUCUCUCGCCAAAUGCCUGACAAUGAC ..((((((.((((((((.((.(((((.......(((((((((((.....)))(---------(.....))....)))))))))))))))((.......))))).)))))))))))..... ( -36.11) >DroPse_CAF1 65846 120 + 1 GCUGUCAGUGCGUUGGCUGUCAAGUGUCAAAAACAUUUGCAACGCGCUCAGCGCCGUGCGGGCAAAAUGCAAAAUGCAAAUGCACUUACGAACGUCUCUCGCCAAAUGCCUGACAAUGAC ..((((((.((((((((.((.(((((.......((((((((.(((((........))))).((.....))....)))))))))))))))((.......))))).)))))))))))..... ( -40.11) >DroSim_CAF1 45671 111 + 1 GCUGUCAGUGCGUUGGCUGUCAAGUGUCAAAAACAUUUGCAGCGUGCAACGCG---------CCAAAUGCAAAAUGCAAAUGCACUUACGAACGUCUCUCGCCAAAUGCCUGACAAUGAC ..((((((.((((((((.((.(((((.......(((((((((((.....)))(---------(.....))....)))))))))))))))((.......))))).)))))))))))..... ( -36.11) >DroEre_CAF1 55363 111 + 1 GCUGUCAGUGCGUUGGCUGUCAAGUGUCAGAAACAUUUGCAGCUUGCAACGCG---------CCAAAUGCAAAAUGCAAAUGCACUUACGAACGUCUCUCGCCAAAUGCCUGACAAUGAC ..((((((.((((((((.((.(((((.......((((((((..(((((.....---------.....)))))..)))))))))))))))((.......))))).)))))))))))..... ( -36.41) >DroYak_CAF1 50415 111 + 1 GCUGUCAGUGCGUUGGCUGUCAAGUGUCAGAAACAUUUGCAGCUUGCAACGCG---------CCAAAUGCAAAAUGCAAAUGCACUUACGAACGUCUCUCGCCAAAUGCCUGACAAUGAC ..((((((.((((((((.((.(((((.......((((((((..(((((.....---------.....)))))..)))))))))))))))((.......))))).)))))))))))..... ( -36.41) >DroPer_CAF1 69597 120 + 1 GCUGUCAGUGCGUUGGCUGUCAAGUGUCAAAAACAUUUGCAACGCGCUCAGCGCCGUGCGGGCAAAAUGCAAAAUGCAAAUGCACUUACGAACGUCUCUCGCCAAAUGCCUGACAAUGAC ..((((((.((((((((.((.(((((.......((((((((.(((((........))))).((.....))....)))))))))))))))((.......))))).)))))))))))..... ( -40.11) >consensus GCUGUCAGUGCGUUGGCUGUCAAGUGUCAAAAACAUUUGCAGCGUGCAACGCG_________CCAAAUGCAAAAUGCAAAUGCACUUACGAACGUCUCUCGCCAAAUGCCUGACAAUGAC ..((((((.((((((((.((.(((((.......((((((((...((((....(((.....)))....))))...)))))))))))))))((.......))))).)))))))))))..... (-32.44 = -33.44 + 1.00)
| Location | 14,528,267 – 14,528,378 |
|---|---|
| Length | 111 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 92.21 |
| Mean single sequence MFE | -38.83 |
| Consensus MFE | -34.09 |
| Energy contribution | -34.87 |
| Covariance contribution | 0.78 |
| Combinations/Pair | 1.03 |
| Mean z-score | -1.91 |
| Structure conservation index | 0.88 |
| SVM decision value | 1.23 |
| SVM RNA-class probability | 0.933313 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
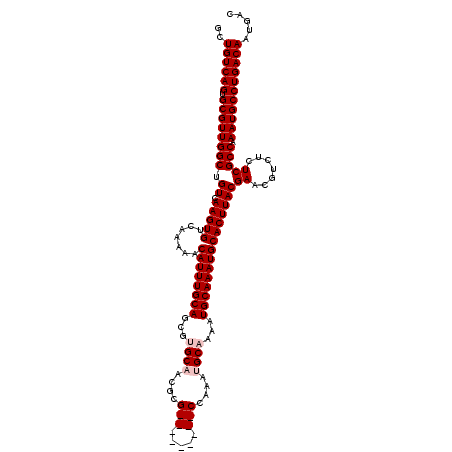
>2L_DroMel_CAF1 14528267 111 - 22407834 GUCAUUGUCAGGCAUUUGGCGAGAGACGUUCGUAAGUGCAUUUGCAUUUUGCAUUUGG---------CGCGUUGCACGCUGCAAAUGUUUUUGACACUUGACAGCCAACGCACUGACAGC ....((((((((((((((.((((.....)))))))))))...(((.....))).....---------.((((((...(((((((.((((...)))).))).)))))))))).))))))). ( -38.20) >DroPse_CAF1 65846 120 - 1 GUCAUUGUCAGGCAUUUGGCGAGAGACGUUCGUAAGUGCAUUUGCAUUUUGCAUUUUGCCCGCACGGCGCUGAGCGCGUUGCAAAUGUUUUUGACACUUGACAGCCAACGCACUGACAGC ....(((((((((..(((((....((.((...((((.(((((((((...(((.(((.((((....)).)).))).))).))))))))).))))..))))....))))).)).))))))). ( -40.10) >DroSim_CAF1 45671 111 - 1 GUCAUUGUCAGGCAUUUGGCGAGAGACGUUCGUAAGUGCAUUUGCAUUUUGCAUUUGG---------CGCGUUGCACGCUGCAAAUGUUUUUGACACUUGACAGCCAACGCACUGACAGC ....((((((((((((((.((((.....)))))))))))...(((.....))).....---------.((((((...(((((((.((((...)))).))).)))))))))).))))))). ( -38.20) >DroEre_CAF1 55363 111 - 1 GUCAUUGUCAGGCAUUUGGCGAGAGACGUUCGUAAGUGCAUUUGCAUUUUGCAUUUGG---------CGCGUUGCAAGCUGCAAAUGUUUCUGACACUUGACAGCCAACGCACUGACAGC ....((((((((((((((.((((.....)))))))))))...(((.....))).....---------.((((((...(((((((.((((...)))).))).)))))))))).))))))). ( -38.20) >DroYak_CAF1 50415 111 - 1 GUCAUUGUCAGGCAUUUGGCGAGAGACGUUCGUAAGUGCAUUUGCAUUUUGCAUUUGG---------CGCGUUGCAAGCUGCAAAUGUUUCUGACACUUGACAGCCAACGCACUGACAGC ....((((((((((((((.((((.....)))))))))))...(((.....))).....---------.((((((...(((((((.((((...)))).))).)))))))))).))))))). ( -38.20) >DroPer_CAF1 69597 120 - 1 GUCAUUGUCAGGCAUUUGGCGAGAGACGUUCGUAAGUGCAUUUGCAUUUUGCAUUUUGCCCGCACGGCGCUGAGCGCGUUGCAAAUGUUUUUGACACUUGACAGCCAACGCACUGACAGC ....(((((((((..(((((....((.((...((((.(((((((((...(((.(((.((((....)).)).))).))).))))))))).))))..))))....))))).)).))))))). ( -40.10) >consensus GUCAUUGUCAGGCAUUUGGCGAGAGACGUUCGUAAGUGCAUUUGCAUUUUGCAUUUGG_________CGCGUUGCACGCUGCAAAUGUUUUUGACACUUGACAGCCAACGCACUGACAGC ....((((((((((((((.((((.....)))))))))))...(((.....)))...............((((((...(((((((.((((...)))).))).)))))))))).))))))). (-34.09 = -34.87 + 0.78)


Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 11:35:57 2006