
| Sequence ID | 2L_DroMel_CAF1 |
|---|---|
| Location | 13,013,719 – 13,013,839 |
| Length | 120 |
| Max. P | 0.683307 |

| Location | 13,013,719 – 13,013,839 |
|---|---|
| Length | 120 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 83.17 |
| Mean single sequence MFE | -40.34 |
| Consensus MFE | -30.25 |
| Energy contribution | -29.34 |
| Covariance contribution | -0.91 |
| Combinations/Pair | 1.43 |
| Mean z-score | -1.86 |
| Structure conservation index | 0.75 |
| SVM decision value | 0.31 |
| SVM RNA-class probability | 0.683307 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
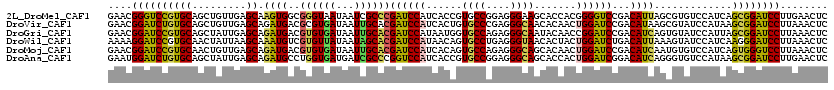
>2L_DroMel_CAF1 13013719 120 + 22407834 GAACGGGUCCGUGCAGCUGUUGAGCAAGUGGCGGGUAAUAAUCGCCCGAUCCAUCACCGUGCCGGAGGGAAGCACCACGGGGUCCGACAUUAGCGUGUCCAUCAGCGGAUCCUUGAACUC ....((((((((((((((((((..(..(((((((((.......))))).(((....(((...)))..)))....))))...)..))))...))).)))......))))))))........ ( -39.90) >DroVir_CAF1 44681 120 + 1 GAACGGAUCUGUGCAGCUGUUGAGCAGAUGACGCGUGAUAAUUGCACGAUCCAUCACUGUGCCCGAGGGCAACACAACUGGAUCCGACAUAAGCGUAUCCAUAAGCGGAUCCUUAAACUC ....((((((((...(((....))).((((.((((((.......)))((((((....((((((....))).)))....))))))........))))))).....))))))))........ ( -39.40) >DroGri_CAF1 46347 120 + 1 GAACGGAUCCGUGCAGCUAUUGAGCAGAUGACGUGUGAUAAUUGCACGAUCCAUAAUGGUGCCAGAGGGCAAUACAACCGGAUCCGACAUCAGUGUAUCCAUUAGCGGAUCCUUAAACUC ....((((((((...(((....))).((((..(((..(...)..)))(((((....((.((((....))))...))...)))))...)))).............))))))))........ ( -38.10) >DroWil_CAF1 60821 120 + 1 AAAAGGAUCCGUGCAACUAUUAAGCAAAUGUCGUGUUAUAAUAGCACGAUCCAUAACAGUGCCUGAGGGUAACACUACUGGAUCUGACAUUAAAGUAUCCAUCAAGGGAUCCUUAAACUC ..((((((((.(((.........)))((((((((((((...))))))((((((......((((....)))).......)))))).))))))...............))))))))...... ( -37.22) >DroMoj_CAF1 42031 120 + 1 GAACGGAUCCGUGCAACUGUUGAGCAGAUGACGUGUGAUAAUUGCACGAUCCAUCACAGUGCCAGAGGGCAGCACAACUGGAUCCGACAUCAAUGUGUCCAUCAGUGGGUCCUUAAACUC ....((((((((((.(((((.((...(((..((((..(...)..)))))))..)))))))(((....))).)))).(((((....(((((....)))))..)))))))))))........ ( -41.40) >DroAna_CAF1 44902 120 + 1 GAAUGGAUCUGUGCAGCUAUUGAGCAGAUGCCUGGUGAUGAUCGCCCGGUCCAUCACCGUGCCGGAGGGCAGCACCACUGGAUCGGACAUCAGGGUGUCCAUAAGCGGAUCCUUGAACUC ....((((((((...(((....))).(((....((((((((((....))).)))))))...((((.((......)).)))))))((((((....))))))....))))))))........ ( -46.00) >consensus GAACGGAUCCGUGCAGCUAUUGAGCAGAUGACGUGUGAUAAUUGCACGAUCCAUCACAGUGCCAGAGGGCAACACAACUGGAUCCGACAUCAGCGUAUCCAUCAGCGGAUCCUUAAACUC ....((((((((((.........)).((((..((((((...))))))((((((......((((....)))).......))))))...)))).............))))))))........ (-30.25 = -29.34 + -0.91)


Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 11:20:35 2006