
| Sequence ID | 2L_DroMel_CAF1 |
|---|---|
| Location | 10,840,358 – 10,840,478 |
| Length | 120 |
| Max. P | 0.651809 |

| Location | 10,840,358 – 10,840,478 |
|---|---|
| Length | 120 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 88.44 |
| Mean single sequence MFE | -50.13 |
| Consensus MFE | -41.44 |
| Energy contribution | -42.47 |
| Covariance contribution | 1.03 |
| Combinations/Pair | 1.16 |
| Mean z-score | -1.92 |
| Structure conservation index | 0.83 |
| SVM decision value | 0.25 |
| SVM RNA-class probability | 0.651809 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2L_DroMel_CAF1 10840358 120 - 22407834 UGGCGGUGCCGUUGAUGAUGACACAGCGCGCUUGCAACAGCGUGCGGCACGAUUCUCACAGCAGGGCUCCAGCUCGGCCAAAAAAUCGGUCGUCGCCAUUGCAAGCUCACCGUUUGGUCU .(((((((.(((((.((....))))))).((((((((..(((.(((((.(((((......((.((((....)))).)).....)))))))))))))..)))))))).)))))))...... ( -48.70) >DroVir_CAF1 97355 120 - 1 GGGCGGUGCCGUUGAUGAUGACACAGCGCGCUUGCAACAGCGUGCGGCACGUUUCUCACAGUCGAGCAGCGGCUCGUCUAAGAAAUCUGUCGUCGCAAUUGCAAGCUCACCGUUUGGUCU ((((((((.(((((.((....))))))).((((((((..(((.((((((.((((((...((.(((((....))))).)).)))))).)))))))))..)))))))).))))))))..... ( -53.80) >DroPse_CAF1 75792 120 - 1 GGGUGGGGCCGUUGAUGAUGACACAGCGCGCUUGCAACAGCGGGCGGCACGUUUCUCGCAGCAGGGCUCCGGCUCGGCUAAGAAAUUUGUCGUCGCCAUUGCAAGUUCGCCUUUUGGUCU .....((((((((......)))...(((.((((((((..((((.(((((.((((((...(((.((((....)))).))).)))))).)))))))))..)))))))).))).....))))) ( -49.90) >DroWil_CAF1 115792 120 - 1 UGGCGGUGCCGUUGACGAUGACUCAGCGCGUUUGCAACAGCGUGCGGCACGAUUCUCUCAGCAGGGCUCUGGUUCGGCUAAGAAAUCGGUCGUUGCGAUUGCAAGCUCACCGUUUGGUCU .(((((((.((((((.......)))))).((((((((..(((.(((((.(((((.(((.(((.((((....)))).))).))))))))))))))))..)))))))).)))))))...... ( -49.30) >DroMoj_CAF1 103822 120 - 1 UGGCGGUGCUGUUGAUGAUGACACAGCGCGCUUGCAACAGCGUGCGGCACGUUUCUCACAGACGAGCGGUGGCUCGGCUAAGAAAUCUGUCGUCGCAAUUGUAAGCUCACCGUUUGGUCU .(((((((((((..........)))))(.((((((((..(((.((((((.((((((...((.(((((....))))).)).)))))).)))))))))..)))))))).)))))))...... ( -49.20) >DroPer_CAF1 75618 120 - 1 GGGUGGGGCCGUUGAUGAUGACACAGCGCGCUUGCAACAGCGGGCGGCACGUUUCUCGCAGCAGGGCUCCGGCUCGGCUAAGAAAUUUGUCGUCGCCAUUGCAAGUUCGCCUUUUGGUCU .....((((((((......)))...(((.((((((((..((((.(((((.((((((...(((.((((....)))).))).)))))).)))))))))..)))))))).))).....))))) ( -49.90) >consensus GGGCGGUGCCGUUGAUGAUGACACAGCGCGCUUGCAACAGCGUGCGGCACGUUUCUCACAGCAGGGCUCCGGCUCGGCUAAGAAAUCUGUCGUCGCCAUUGCAAGCUCACCGUUUGGUCU .(((((((.(((((.((....))))))).((((((((..(((.((((((.((((((...(((.((((....)))).))).)))))).)))))))))..)))))))).)))))))...... (-41.44 = -42.47 + 1.03)

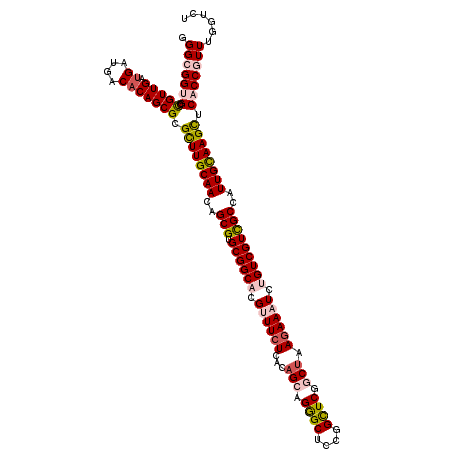
Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 10:59:20 2006