
| Sequence ID | 2L_DroMel_CAF1 |
|---|---|
| Location | 6,452,332 – 6,452,452 |
| Length | 120 |
| Max. P | 0.996972 |

| Location | 6,452,332 – 6,452,452 |
|---|---|
| Length | 120 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | forward |
| Mean pairwise identity | 90.61 |
| Mean single sequence MFE | -41.02 |
| Consensus MFE | -33.53 |
| Energy contribution | -34.67 |
| Covariance contribution | 1.14 |
| Combinations/Pair | 1.05 |
| Mean z-score | -1.96 |
| Structure conservation index | 0.82 |
| SVM decision value | 0.10 |
| SVM RNA-class probability | 0.583615 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
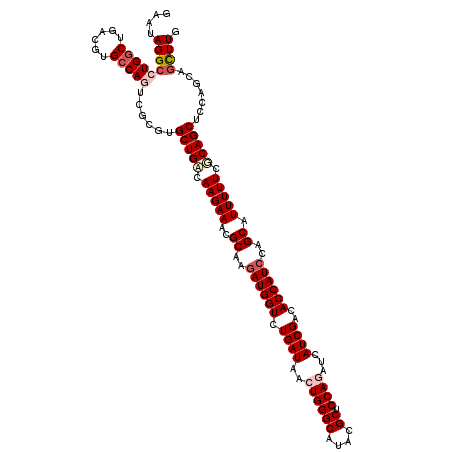
>2L_DroMel_CAF1 6452332 120 + 22407834 GCGUAGGCCUGGCUAACGUGCCAGUCCCUGGCUGCUAAGAAACGCAGGAUGGUCUGAUAACUGGGCACACGCUCCAAGUCAUCGACACCAUCCAGCAUUUUUCGCAGCUCCAGCAGCUUG ((.((((.(((((......)))))..))))(((((.(((((..((.(((((((.((((.(((((((....)).)).))).))))..))))))).)).))))).)))))....))...... ( -47.60) >DroVir_CAF1 36021 120 + 1 GCAUAGGCCUGGCUGACGUGCCAGUCGCGUGCUGACAAGAAACGCAAGAUGGUCUGAUAACUGGGCAUGCGCUCCAGAUCAUCGACACCAUCCAGCAUUUUUCGCAGCUCCAGCAGCUUG ...((((((((((......)))))..((..((((.(.(((((.((..((((((.((((..((((((....)).))))...))))..))))))..)).))))).)))))....)).))))) ( -42.40) >DroGri_CAF1 33076 120 + 1 GAAUAGGCCUGGCUGACGUGCCAAUCGCGUGCUGACAAGAAACGCAAGAUGGUCUGAUAACUGGGCAUACGCUCCAGAUCAUCGACACCAUCGAGCAUUUUUCGCAGCUCCAACAGCUUG ..........((((((((((.....)))))((((.(.(((((.((..((((((.((((..((((((....)).))))...))))..))))))..)).))))).))))).....))))).. ( -39.10) >DroWil_CAF1 28314 120 + 1 GAAAAGGCCUGACUGACAUGCCAAUCUCUGGCUGACAAGAAACGCAAGAUGGUCUGAUAACUGGGCAUACGCUCCAAGUCAUCGACACCAUCAAGCAUUUUUCUCAGCUCCAGCAAUUUG .....(((.((.....)).)))...((..((((((.(((((..((..((((((.((((.(((((((....)).)).))).))))..))))))..)).))))).))))))..))....... ( -33.70) >DroMoj_CAF1 45637 120 + 1 GCAUAGGCCUGGCUAACGUGCCAGUCGCGUGCUGACAAGAAACGCAAGAUGGUCUGAUAACUGGGCAUACGCUCCAGAUCAUCGACACCAUCGAGCAUUUUUCUCAGCUCCAGCAGCUUG ...((((((((((......)))))..((..(((((.(((((..((..((((((.((((..((((((....)).))))...))))..))))))..)).))))).)))))....)).))))) ( -43.60) >DroAna_CAF1 19452 120 + 1 GAAAAGGCCUGGCUGACGUGCCAGUCUCUAGCUGCCAAGAAACGCAGUAUGGUCUGAUAACUGGGCACACGCUCCAGGUCAUCGACACCAUCCAGCAUUUUUCGCAGCUCCAGCAGCUUG ....(((((((((......))))).((..((((((.(((((..((.(.(((((.((((..((((((....)).))))...))))..))))).).)).))))).))))))..))..)))). ( -39.70) >consensus GAAUAGGCCUGGCUGACGUGCCAGUCGCGUGCUGACAAGAAACGCAAGAUGGUCUGAUAACUGGGCAUACGCUCCAGAUCAUCGACACCAUCCAGCAUUUUUCGCAGCUCCAGCAGCUUG ....(((((((((......)))))......(((((.(((((..((..((((((.((((..((((((....)).))))...))))..))))))..)).))))).))))).......)))). (-33.53 = -34.67 + 1.14)

| Location | 6,452,332 – 6,452,452 |
|---|---|
| Length | 120 |
| Sequences | 6 |
| Columns | 120 |
| Reading direction | reverse |
| Mean pairwise identity | 90.61 |
| Mean single sequence MFE | -49.00 |
| Consensus MFE | -43.37 |
| Energy contribution | -43.07 |
| Covariance contribution | -0.30 |
| Combinations/Pair | 1.11 |
| Mean z-score | -2.97 |
| Structure conservation index | 0.89 |
| SVM decision value | 2.78 |
| SVM RNA-class probability | 0.996972 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2L_DroMel_CAF1 6452332 120 - 22407834 CAAGCUGCUGGAGCUGCGAAAAAUGCUGGAUGGUGUCGAUGACUUGGAGCGUGUGCCCAGUUAUCAGACCAUCCUGCGUUUCUUAGCAGCCAGGGACUGGCACGUUAGCCAGGCCUACGC ...((..(((..(((((...((((((.(((((((.(.(((((((.((.((....)))))))))))).))))))).))))))....))))))))((.(((((......))))).))...)) ( -54.00) >DroVir_CAF1 36021 120 - 1 CAAGCUGCUGGAGCUGCGAAAAAUGCUGGAUGGUGUCGAUGAUCUGGAGCGCAUGCCCAGUUAUCAGACCAUCUUGCGUUUCUUGUCAGCACGCGACUGGCACGUCAGCCAGGCCUAUGC ...((....((.(((((((.((((((.(((((((.(.(((((.((((.((....)))))))))))).))))))).)))))).))).))))......(((((......))))).))...)) ( -50.10) >DroGri_CAF1 33076 120 - 1 CAAGCUGUUGGAGCUGCGAAAAAUGCUCGAUGGUGUCGAUGAUCUGGAGCGUAUGCCCAGUUAUCAGACCAUCUUGCGUUUCUUGUCAGCACGCGAUUGGCACGUCAGCCAGGCCUAUUC ...((((((((.(((((((.((((((..((((((.(.(((((.((((.((....)))))))))))).))))))..)))))).))).)))).).))))((((......)))))))...... ( -46.40) >DroWil_CAF1 28314 120 - 1 CAAAUUGCUGGAGCUGAGAAAAAUGCUUGAUGGUGUCGAUGACUUGGAGCGUAUGCCCAGUUAUCAGACCAUCUUGCGUUUCUUGUCAGCCAGAGAUUGGCAUGUCAGUCAGGCCUUUUC ......(((.(.(((((.((((((((..((((((.(.(((((((.((.((....)))))))))))).))))))..)))))).)).))))))...((((((....)))))).)))...... ( -45.90) >DroMoj_CAF1 45637 120 - 1 CAAGCUGCUGGAGCUGAGAAAAAUGCUCGAUGGUGUCGAUGAUCUGGAGCGUAUGCCCAGUUAUCAGACCAUCUUGCGUUUCUUGUCAGCACGCGACUGGCACGUUAGCCAGGCCUAUGC ...((....((.(((((.((((((((..((((((.(.(((((.((((.((....)))))))))))).))))))..)))))).)).)))))......(((((......))))).))...)) ( -48.80) >DroAna_CAF1 19452 120 - 1 CAAGCUGCUGGAGCUGCGAAAAAUGCUGGAUGGUGUCGAUGACCUGGAGCGUGUGCCCAGUUAUCAGACCAUACUGCGUUUCUUGGCAGCUAGAGACUGGCACGUCAGCCAGGCCUUUUC ...((..((..((((((.((((((((...(((((.(.((((((.(((.((....)))))))))))).)))))...)))))).)).))))))..)).(((((......)))))))...... ( -48.80) >consensus CAAGCUGCUGGAGCUGCGAAAAAUGCUGGAUGGUGUCGAUGACCUGGAGCGUAUGCCCAGUUAUCAGACCAUCUUGCGUUUCUUGUCAGCAAGCGACUGGCACGUCAGCCAGGCCUAUGC .........((.(((((.((((((((..((((((.(.(((((.((((.((....)))))))))))).))))))..)))))).)).)))))......(((((......))))).))..... (-43.37 = -43.07 + -0.30)


Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 10:26:33 2006