
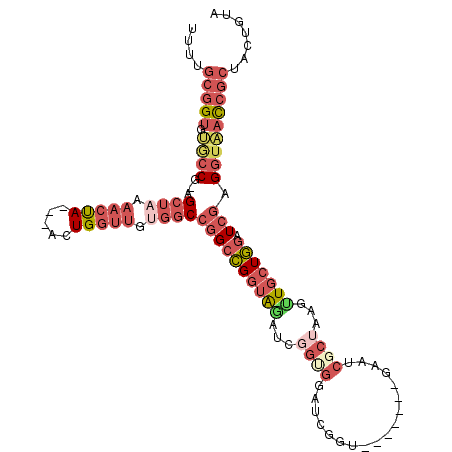
| Sequence ID | 2L_DroMel_CAF1 |
|---|---|
| Location | 3,482,348 – 3,482,477 |
| Length | 129 |
| Max. P | 0.543965 |

| Location | 3,482,348 – 3,482,449 |
|---|---|
| Length | 101 |
| Sequences | 5 |
| Columns | 112 |
| Reading direction | forward |
| Mean pairwise identity | 71.82 |
| Mean single sequence MFE | -36.82 |
| Consensus MFE | -16.90 |
| Energy contribution | -20.59 |
| Covariance contribution | 3.69 |
| Combinations/Pair | 1.28 |
| Mean z-score | -1.66 |
| Structure conservation index | 0.46 |
| SVM decision value | -0.06 |
| SVM RNA-class probability | 0.500000 |
| Prediction | OTHER |
Download alignment: ClustalW | MAF
>2L_DroMel_CAF1 3482348 101 + 22407834 UUUUGCGGUGUACCG-AGCUAAAACUA---ACUGGUUGUGGCCGGCCGGUAAAUCGGUGGAUCGGU-------GAAUCGCUGAGUUGCUGGAUCGAGGUAACCGCUACUGUA ....(((((.((((.-.((((.((((.---...)))).))))((((((((((.(((((((.((...-------)).))))))).))))))).))).)))))))))....... ( -39.40) >DroVir_CAF1 18514 97 + 1 UUU-GCGGCGCAC----GCUUACAGCAGCCACUG--UG---CGAGCUGUCGAGUCUGUGGACCGGACUCCGACCAAGCUCUCAGCU--UAACUCG---AGCUGUGGCCCGUA ..(-((((.....----((.....)).(((((..--.(---.(((((((((((((((.....)))))).))))..))))).)((((--(.....)---)))))))))))))) ( -38.80) >DroSim_CAF1 9567 101 + 1 UUUUGCGGUGUGCCG-AGCUAAAACUA---ACUGGUUGUGGCCGGCCGGUAGAUCGGUGGAUCGGU-------GAAUCGCUAAGUUGCUGGAUCGAGGUAACCGCUACUGUA ....(((((.((((.-.((((.((((.---...)))).))))((((((((((...(((((.((...-------)).)))))...))))))).))).)))))))))....... ( -34.70) >DroEre_CAF1 9855 101 + 1 UUUUGCGGUGUGCCG-AGCUAAAACCA---ACUGGUUGUGGCCGGCCGGUAGAUCGGCGGAUCGGU-------GAAUCGCUAAGCUGCUGGAUCGAGGUAACCGCUACUGUA ....(((((.((((.-.((((.((((.---...)))).))))((((((((((...(((((.((...-------)).)))))...))))))).))).)))))))))....... ( -41.30) >DroYak_CAF1 9620 94 + 1 CUUUGCGGUGAGCCGUAGCUUAAACUA---ACUGGUUGUGGCCGGCCGGUAGAU--------CGGU-------GAAUCGCUAAGUUGCUGGAUCGAGGUAACCGCUACUGUA ....(((((..(((...(((..((((.---...))))..)))((((((((((..--------.(((-------(...))))...))))))).))).))).)))))....... ( -29.90) >consensus UUUUGCGGUGUGCCG_AGCUAAAACUA___ACUGGUUGUGGCCGGCCGGUAGAUCGGUGGAUCGGU_______GAAUCGCUAAGUUGCUGGAUCGAGGUAACCGCUACUGUA ....(((((.((((...((((.(((((.....))))).))))((((((((((...((((..................))))...))))))).))).)))))))))....... (-16.90 = -20.59 + 3.69)

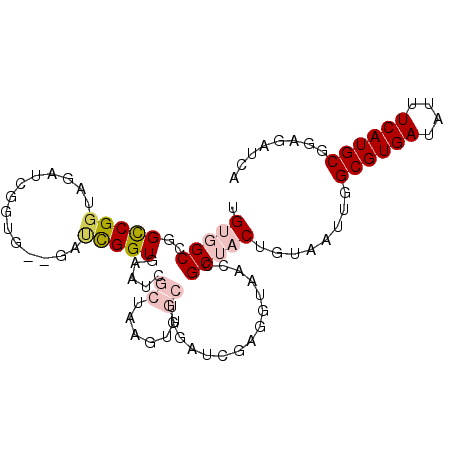
| Location | 3,482,380 – 3,482,477 |
|---|---|
| Length | 97 |
| Sequences | 6 |
| Columns | 99 |
| Reading direction | forward |
| Mean pairwise identity | 73.39 |
| Mean single sequence MFE | -32.07 |
| Consensus MFE | -12.62 |
| Energy contribution | -13.51 |
| Covariance contribution | 0.89 |
| Combinations/Pair | 1.17 |
| Mean z-score | -1.90 |
| Structure conservation index | 0.39 |
| SVM decision value | 0.02 |
| SVM RNA-class probability | 0.543965 |
| Prediction | RNA |
Download alignment: ClustalW | MAF
>2L_DroMel_CAF1 3482380 97 + 22407834 UGUGGCCGGCCGGUAAAUCGGUG--GAUCGGUGAAUCGCUGAGUUGCUGGAUCGAGGUAACCGCUACUGUAAUUGGCGUGAUAUUUCAUGCGGAGAUCA .(((((((((((((((.((((((--(.((...)).))))))).))))))).))).((...))))))).(...((.((((((....)))))).))...). ( -35.00) >DroPse_CAF1 11183 84 + 1 UGCUGCUUGUCGGCUUACUGUUGCUUACUGGUGGAUCGCUG--------G-------AGCUCGCUCCAGUAAUUGGCGUGAUAUUUCAUGCAUCGAUCA ....(((.((.(((........))).)).))).((((((((--------(-------((....))))))).....((((((....))))))...)))). ( -31.00) >DroSim_CAF1 9599 97 + 1 UGUGGCCGGCCGGUAGAUCGGUG--GAUCGGUGAAUCGCUAAGUUGCUGGAUCGAGGUAACCGCUACUGUAAUUGGCGUGAUAUUUCAUGCGGAGAUCA .(((((((((((((((...((((--(.((...)).)))))...))))))).))).((...))))))).(...((.((((((....)))))).))...). ( -30.30) >DroEre_CAF1 9887 97 + 1 UGUGGCCGGCCGGUAGAUCGGCG--GAUCGGUGAAUCGCUAAGCUGCUGGAUCGAGGUAACCGCUACUGUAAUUGGCGUGAUUUUUCAUGCGGAGAUCA .(((((((((((((((...((((--(.((...)).)))))...))))))).))).((...))))))).(...((.((((((....)))))).))...). ( -34.40) >DroYak_CAF1 9653 89 + 1 UGUGGCCGGCCGGUAGAU----------CGGUGAAUCGCUAAGUUGCUGGAUCGAGGUAACCGCUACUGUAAUUGGCGUGAUUUUUCAUGCGGAGAUCA .(((((((((((((((..----------.((((...))))...))))))).))).((...))))))).(...((.((((((....)))))).))...). ( -28.10) >DroPer_CAF1 11259 84 + 1 UGCCGCUUGUCGGCUUACUGUUGCUUACUGGUGGAUCGCUG--------G-------AGCUCGCUCCAGUAAUUGGCGUGAUAUUUCAUGCAUCGAUCA ...((((.((.(((........))).)).))))((((((((--------(-------((....))))))).....((((((....))))))...)))). ( -33.60) >consensus UGUGGCCGGCCGGUAGAUCGGUG__GAUCGGUGAAUCGCUAAGUUGCUGGAUCGAGGUAACCGCUACUGUAAUUGGCGUGAUAUUUCAUGCGGAGAUCA .(((((..(((((..............))))).....((......))...............)))))........((((((....))))))........ (-12.62 = -13.51 + 0.89)

Generated by rnazCluster.pl (part of RNAz 1.0) on Mon Dec 4 09:59:41 2006